Clear Sky Science · it
Identificazione dei geni batterici chiave e dei target terapeutici in pazienti ipertesi con diabete di tipo 2 mediante analisi bioinformatica
Perché il tuo intestino conta per la pressione sanguigna e la glicemia
L’ipertensione e il diabete di tipo 2 spesso compaiono insieme, aumentando il rischio di infarti, ictus e malattie renali. I medici hanno a lungo trattato queste condizioni separatamente, concentrandosi su farmaci che agiscono sul cuore, sui vasi sanguigni o sull’insulina. Questo studio pone una domanda diversa: potrebbero i piccoli microrganismi che vivono nell’intestino — e i geni che portano — contribuire a entrambe le problematiche contemporaneamente, e potrebbero rivelare nuove opzioni terapeutiche?
Il mondo nascosto dentro l’intestino
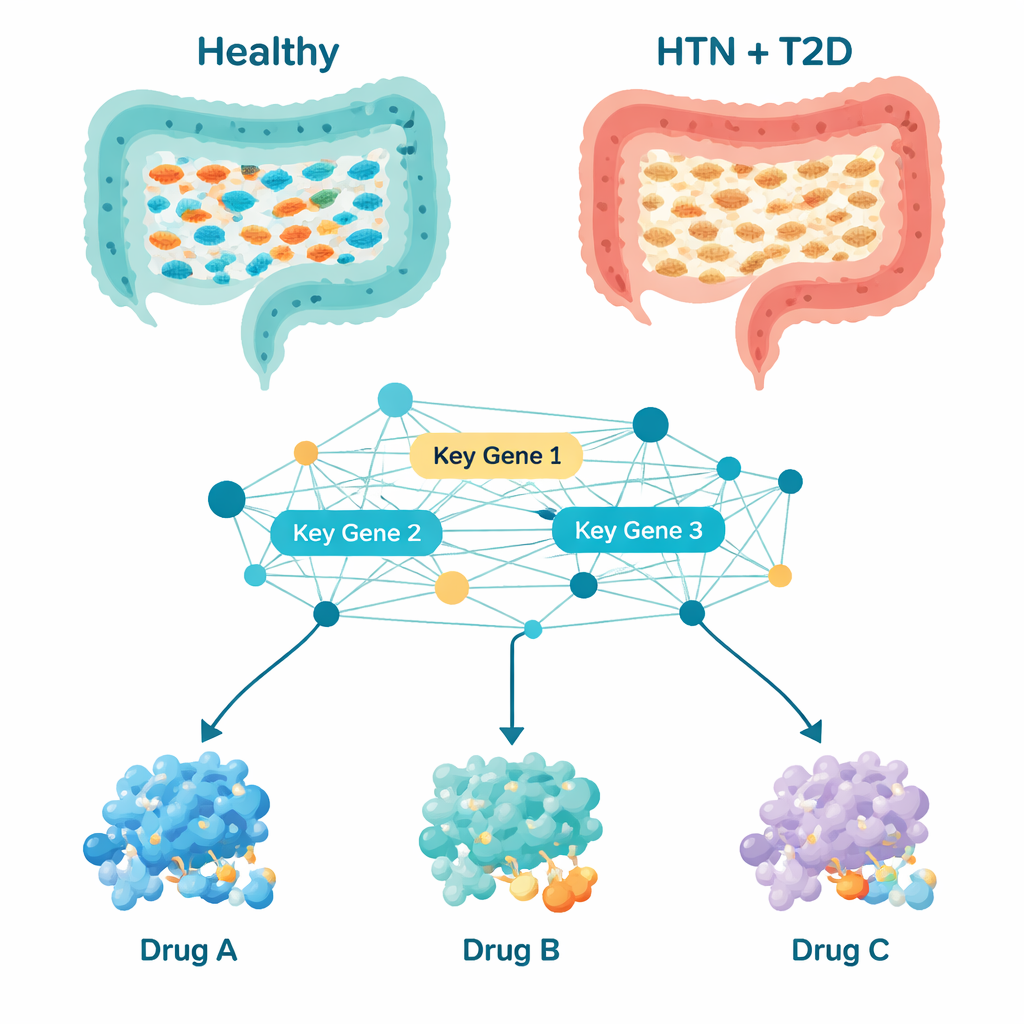
I ricercatori hanno analizzato campioni di feci di 124 adulti, confrontando 29 persone con ipertensione e diabete di tipo 2 con 95 volontari sani. Usando il sequenziamento genetico di marker batterici, hanno costruito un quadro dettagliato dei microrganismi presenti e della diversità di ciascuna comunità intestinale. Le persone con entrambe le condizioni avevano comunità batteriche più ricche e più equamente distribuite che si raggruppavano separatamente rispetto a quelle degli individui sani, il che indica che i loro ecosistemi intestinali erano chiaramente riorganizzati piuttosto che solo lievemente alterati.
Uno spostamento microbico dal benefico al dannoso
Quando il team ha esaminato più da vicino quali tipi di batteri erano più abbondanti, ha osservato un modello distinto. Nelle persone sane erano comuni batteri che aiutano a produrre acidi grassi a catena corta — composti noti per sostenere la salute della barriera intestinale e per contribuire al controllo dell’infiammazione e del metabolismo —, tra cui gruppi come Bacteroides, Prevotella, Roseburia e Akkermansia. Nelle persone con ipertensione e diabete molti di questi microrganismi utili erano impoveriti. Allo stesso tempo, batteri associati in altri studi a infiammazione e squilibri metabolici, come Megasphaera, Lactobacillus, Streptococcus e Veillonella, erano più comuni. Diciannove gruppi batterici risultavano consistentemente diversi tra i pazienti e i controlli sani, suggerendo uno spostamento coordinato verso un ambiente intestinale che potrebbe favorire infiammazione di basso grado e stress metabolico.
Dai microbi ai “manopole” molecolari
Contare solo i microrganismi non basta a spiegare come influenzino l’organismo, così gli scienziati hanno usato strumenti computazionali per inferire cosa probabilmente fanno i batteri intestinali. Hanno previsto quali vie metaboliche — catene di reazioni chimiche — erano più o meno attive nei pazienti. Su oltre mille vie, 195 sono emerse come alterate. Molte riguardavano come i batteri producono proteine, processano energia e gestiscono mattoni come nucleotidi e aminoacidi. Costruendo una rete delle interazioni tra le proteine batteriche corrispondenti, il team ha identificato dieci geni “hub” che occupavano snodi chiave in questa rete. Questi geni, con nomi come gltB, gyrB, fusA e mdh, fungono da manopole di controllo per funzioni batteriche fondamentali quali produzione di energia, duplicazione del DNA, sintesi proteica e metabolismo degli acidi grassi e dei nucleotidi. Poiché queste attività sono strettamente connesse all’infiammazione, alla salute dei vasi e al controllo del glucosio, le variazioni in questi geni microbici possono riverberare all’esterno influenzando pressione sanguigna e glicemia.
Alla ricerca di nuovi usi per farmaci esistenti
Con questa lista di geni batterici di controllo, i ricercatori si sono rivolti allo screening computazionale di farmaci. Hanno raccolto 189 farmaci già studiati per ipertensione, diabete di tipo 2 o problemi metabolici correlati, e hanno usato il docking molecolare — essenzialmente un puzzle 3D — per vedere quali composti potessero legarsi più saldamente alle proteine codificate dai dieci geni chiave. Sono emersi tre candidati: la naringina e la neoesperidina, composti di origine vegetale presenti negli agrumi, e la bromocriptina, un farmaco già approvato per il diabete di tipo 2. Simulazioni dettagliate su scale temporali di 100 miliardesimi di secondo hanno suggerito che i complessi con Neohesperidin e Bromocriptine erano particolarmente stabili, il che significa che questi farmaci potrebbero legarsi e influenzare in modo affidabile le proteine batteriche target nella realtà. Controlli aggiuntivi sulle proprietà drug-like di questi composti e sul loro possibile assorbimento, distribuzione e eliminazione nell’organismo hanno indicato la Bromocriptina come il candidato più praticabile a breve termine, sebbene tutti e tre richiederanno accurati studi di sicurezza e dosaggio.
Cosa significa per le cure future
In termini chiari, questo lavoro mappa una catena in tre passaggi: le persone con ipertensione e diabete di tipo 2 tendono ad avere un microbioma intestinale distinto; quel microbioma porta un set di geni batterici che possono spingere il metabolismo e i vasi sanguigni in direzioni dannose; e alcuni farmaci esistenti sembrano in grado di prendere di mira questi geni batterici. Lo studio non dimostra che modificare questi microbi o i loro geni curerà la malattia, né testa trattamenti sui pazienti. Ma traccia una tabella di marcia per diagnostici e terapie basati sul microbioma, dove un giorno i medici potrebbero modificare i batteri intestinali o usare farmaci mirati per alleviare il carico combinato di ipertensione e diabete.
Citazione: Rahat, M.T.I., Sumi, M.S.A., Nurejannath, M. et al. Identification of bacterial key genes and therapeutic targets in hypertensive patients with type 2 diabetes through bioinformatics analysis. Sci Rep 16, 6431 (2026). https://doi.org/10.1038/s41598-026-36467-5
Parole chiave: microbioma intestinale, ipertensione, diabete di tipo 2, geni batterici, riproposta di farmaci