Clear Sky Science · it
Modellizzazione con reti neurali artificiali e ottimizzazione di un biosensore elettrochimico per il rilevamento di miR-155 plasmatico nel cancro al seno
Perché è importante per i controlli precoci del cancro
I medici e i ricercatori cercano esami del sangue semplici in grado di individuare il cancro molto prima della comparsa dei sintomi. Un segnale promettente nel sangue è un frammento genetico molto piccolo chiamato miR-155, collegato al cancro al seno e a diverse condizioni immunitarie e infiammatorie. Costruire un sensore in grado di misurare in modo affidabile un segnale così debole è complicato e di solito richiede mesi di tentativi in laboratorio. Questo studio mostra come abbinare modelli informatici intelligenti a un biosensore elettrochimico possa rendere quel processo più veloce, economico ed efficace, avvicinando un passo in più i test pratici per la diagnosi precoce.
Trasformare una goccia di sangue in un segnale di allarme
Il lavoro si concentra su un biosensore elettrochimico che legge i livelli di miR-155 nel plasma, la parte liquida del sangue. Il nucleo del dispositivo è un piccolo elettrodo d’oro la cui superficie viene preparata con cura in diverse fasi. Per prima cosa, brevi filamenti di DNA progettati per riconoscere miR-155 vengono legati al metallo. Poi una piccola molecola occupa gli spazi vuoti per impedire l’adesione di sostanze estranee. Quando si aggiunge il campione del paziente, l’eventuale miR-155 si lega ai filamenti di DNA e una molecola colorante chiamata Oracet Blue si inserisce in queste strutture appaiate. Infine, una scansione elettrica misura quanto carica viene trasferita, producendo una corrente la cui ampiezza riflette la quantità di miR-155 presente nel campione. 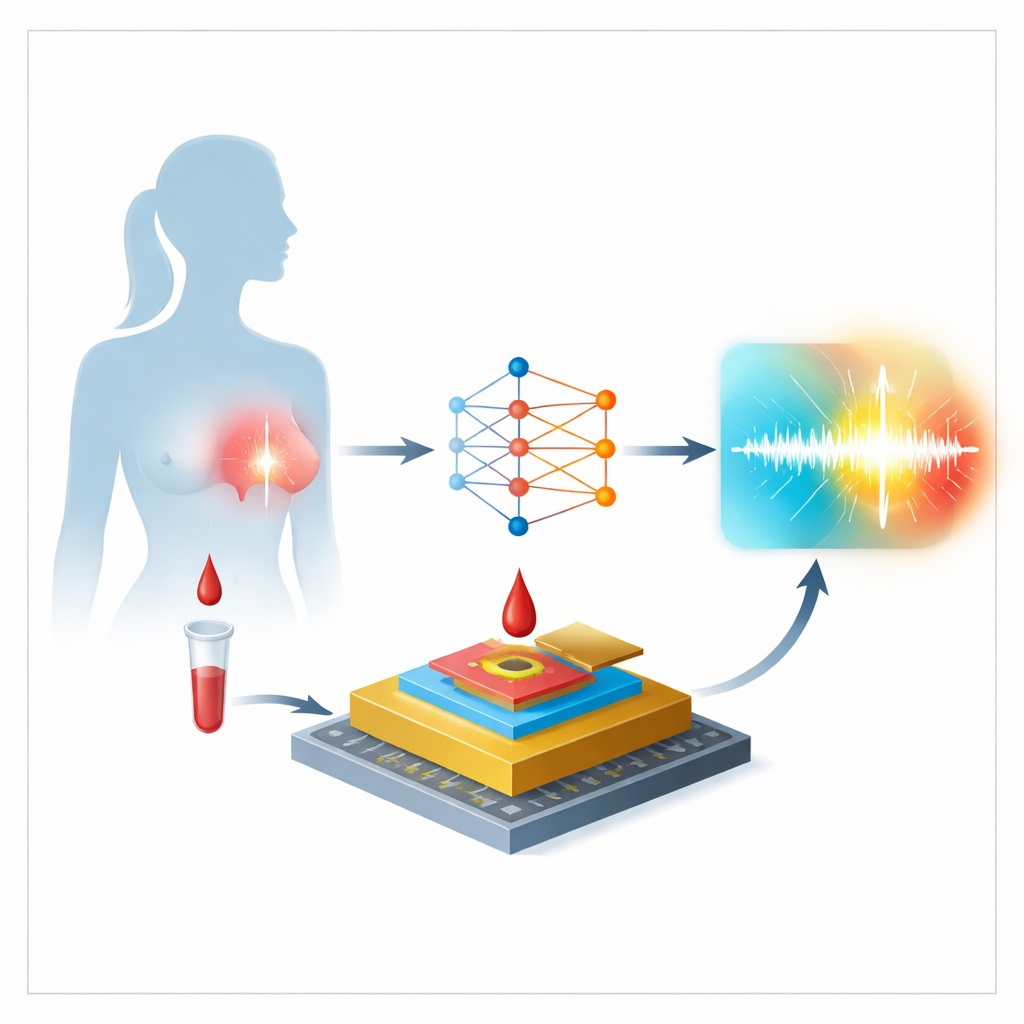
Perché la messa a punto tradizionale è lenta e dispendiosa
Benché l’idea di base del rilevamento sia semplice, le prestazioni del biosensore dipendono fortemente da come viene costruito. Sei passaggi chiave contano: la concentrazione della sonda di DNA, il tempo di attacco della sonda, il tempo di esposizione della molecola bloccante, il tempo concesso al miRNA target per legarsi, e sia la quantità sia il tempo di attesa per l’Oracet Blue. In lavori precedenti i ricercatori modificavano una o due di queste variabili alla volta, eseguivano nuovi esperimenti e procedevano a piccoli passi verso un progetto migliore. Questo approccio consuma materiali costosi, richiede molto tempo dei ricercatori e può non individuare le migliori combinazioni, specialmente quando il comportamento sottostante è altamente non lineare—piccole variazioni nei tempi o nelle concentrazioni possono improvvisamente raddoppiare o dimezzare il segnale.
Lasciare che i computer imparino la ricetta migliore
Per superare questo collo di bottiglia, gli autori si sono rivolti al machine learning, usando due tipi di modellizzazione: reti neurali artificiali (ANN) e un sistema neuro-fuzzy adattivo (ANFIS). Hanno compilato dati da 51 modalità diverse di fabbricazione dello stesso sensore per miR-155, ciascuna definita da una combinazione unica dei sei passaggi chiave, e hanno registrato la corrente elettrica risultante. L’ANN ha imparato a mappare direttamente le scelte di fabbricazione sull’output del sensore usando una rete compatta con un livello nascosto e 13 unità interne. L’approccio ANFIS ha combinato regole fuzzy (come livelli “bassi” o “alti”) con l’addestramento in stile neuronale e ha anche impiegato un espediente statistico per ridurre la sovrapposizione tra gli ingressi. Dopo un addestramento e test accurati, l’ANN si è rivelata più precisa e più facile da gestire, cogliendo meglio le interazioni complesse tra i passaggi rispetto al modello fuzzy, più basato su regole.
Esplorare lo spazio di progetto con l’evoluzione digitale
Una volta che l’ANN è stata in grado di emulare fedelmente il biosensore, il team l’ha collegata a un algoritmo genetico, un metodo di ricerca ispirato all’evoluzione. Questo ottimizzatore digitale è partito da molte ricette casuali per costruire il sensore e le ha ripetutamente “sperate” e mutate, mantenendo quelle che l’ANN prevedeva avrebbero prodotto segnali più forti. In questo ambiente virtuale non era necessario nuovo lavoro di laboratorio: il computer poteva esplorare in silico innumerevoli possibilità. La ricetta vincente è risultata sorprendente. Rispetto alle migliori condizioni effettivamente testate al banco, la combinazione ottimizzata usava complessivamente meno sonda di DNA e meno Oracet Blue, accorciava diversi passaggi di incubazione e tuttavia era prevista raddoppiare più che il valore della corrente di uscita del sensore—da 98 a 223 nanoampere—rendendo il segnale più forte e più facile da distinguere dal rumore di fondo. 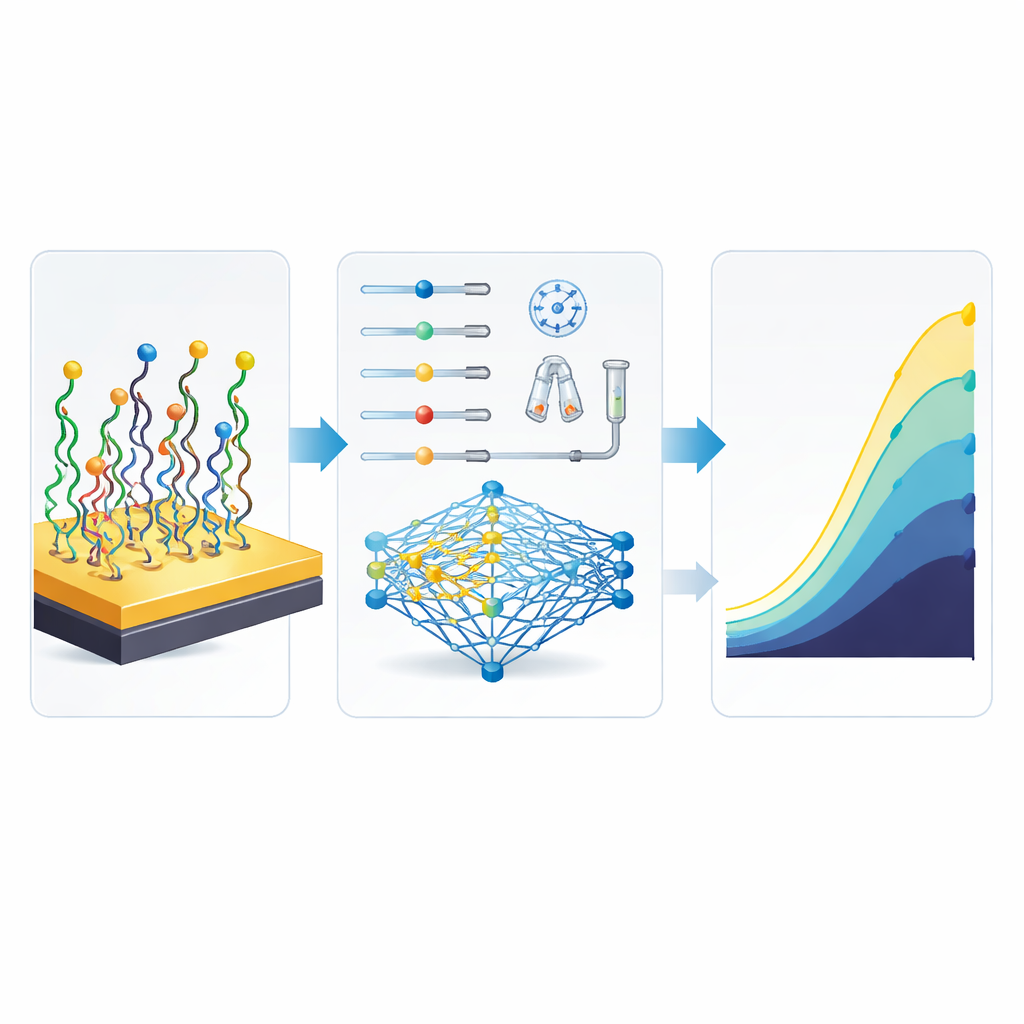
Cosa significa per i futuri test del sangue
Per il lettore non specialista, il messaggio chiave è che gli autori hanno trasformato la messa a punto dei biosensori da lavoro empirico in un processo guidato e basato sui dati. Permettendo a una rete neurale di apprendere come i passaggi di fabbricazione influenzano il segnale elettrico finale e poi lasciando a un algoritmo evolutivo il compito di cercare la migliore ricetta, hanno trovato condizioni che dovrebbero fornire una lettura di miR-155 più luminosa e più affidabile, sprecando meno tempo e materiale. Sebbene le impostazioni ottimizzate richiedano ancora una conferma sperimentale completa e lo studio si concentri su un singolo tipo di marcatore del cancro al seno, la stessa strategia può essere applicata a molti altri biosensori. A lungo termine, questo tipo di progettazione intelligente potrebbe aiutare a rendere di routine test del sangue rapidi ed economici per la diagnosi precoce del cancro e di altre malattie.
Citazione: Imani, A., Hosseinpour, S., Azimzadeh, M. et al. Artificial neural network modeling and optimization of an electrochemical biosensor for plasma miR-155-based breast cancer detection. Sci Rep 16, 7893 (2026). https://doi.org/10.1038/s41598-026-36466-6
Parole chiave: biosensore per il cancro al seno, rilevamento microRNA-155, sensore elettrochimico, reti neurali artificiali, ottimizzazione con algoritmo genetico