Clear Sky Science · it
Identificazione dei geni hub e costruzione di un modello di previsione della sopravvivenza per i pazienti con carcinoma nasofaringeo
Perché questa ricerca sul cancro è importante
Il carcinoma nasofaringeo è un tumore che ha origine dietro il naso e sopra la gola. È relativamente raro a livello mondiale ma comune in alcune aree della Cina meridionale e del Sud-est asiatico, dove rappresenta una minaccia per molte famiglie nonostante i progressi nella radioterapia. I medici possono curare la maggior parte dei pazienti, ma faticano ancora a prevedere chi vivrà molti anni e chi è a rischio maggiore di morire a causa della malattia. Questo studio esamina l’interno delle cellule tumorali per trovare segnali molecolari d’allarme — e poi trasforma questi indizi in uno strumento pratico per stimare le probabilità di sopravvivenza di un paziente dopo la terapia.
Segnali nascosti all’interno delle cellule tumorali
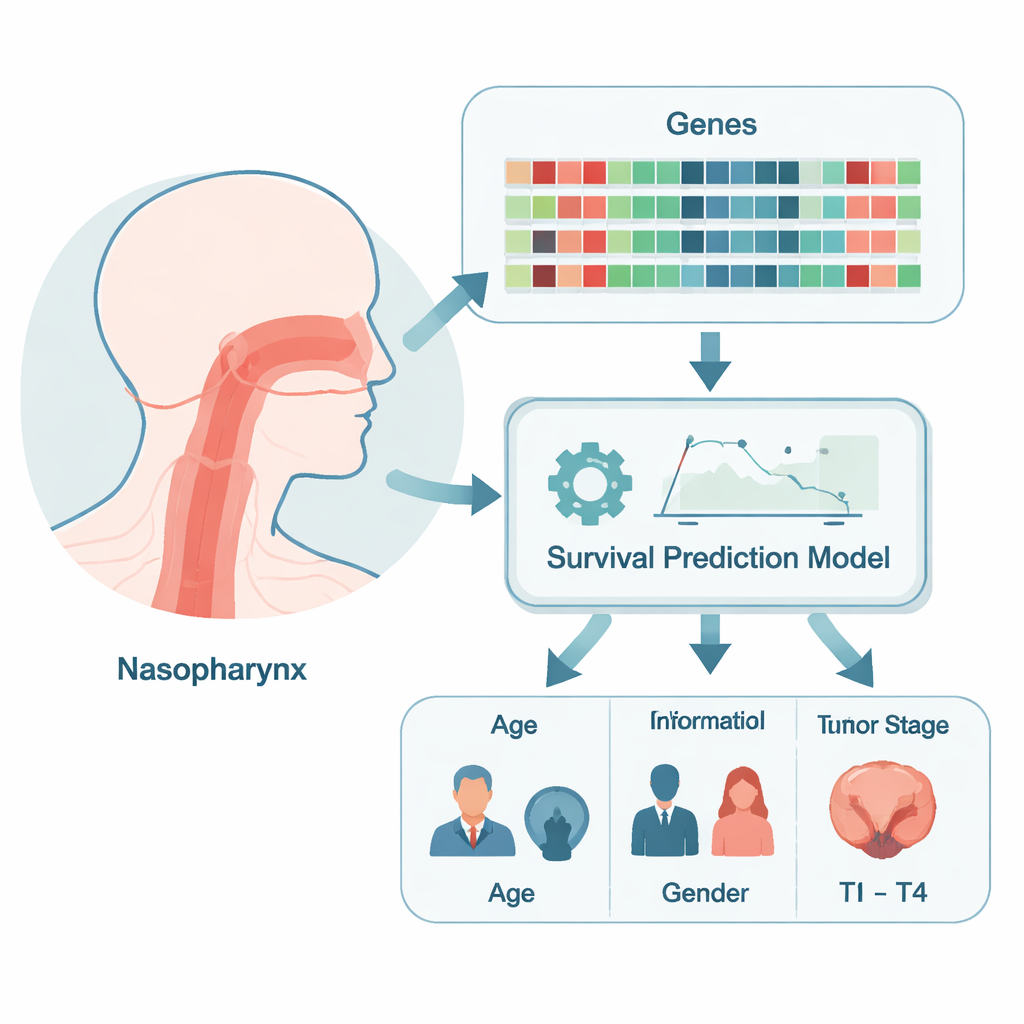
Le cellule tumorali differiscono da quelle sane non solo nell’aspetto, ma anche nei geni che sono attivi o spenti. I ricercatori hanno innanzitutto cercato nei database pubblici i profili di attività genica nei tumori nasofaringei e nei tessuti normali della stessa regione della gola. Hanno combinato due set di dati e corretto le differenze tecniche per poterli confrontare in modo affidabile. Questa analisi ha messo in luce oltre duemila geni la cui attività cambiava marcamente nel cancro, molti dei quali coinvolti nella duplicazione del DNA e nella spinta alla divisione cellulare — la macchina di base che permette alle cellule tumorali di moltiplicarsi in modo incontrollato. Da questo panorama affollato, il gruppo si è concentrato su un piccolo cluster di “geni hub” che sembravano trovarsi al centro di molte reti cellulari importanti.
Sette protagonisti centrali, tre emergenti
Utilizzando strumenti informatici che mappano come le proteine interagiscono tra loro, gli scienziati hanno identificato sette geni hub: AURKA, AURKB, BUB1, BUB1B, CCNA2, CCNB2 e CDK1. Tutti erano molto più attivi nei campioni tumorali rispetto al tessuto normale, e ciascuno è noto per contribuire al controllo di come e quando le cellule si dividono. Per capire quali di questi geni fossero davvero rilevanti per i pazienti, il team ha raccolto biopsie tumorali di 120 persone con carcinoma nasofaringeo trattate in un unico ospedale e le ha seguite per più di sette anni. Quando hanno colorato questi tumori al microscopio, tre geni — AURKA, BUB1 e CDK1 — si sono distinti: brillavano molto di più nei campioni dei pazienti che in seguito sono deceduti rispetto a quelli dei sopravvissuti.
Collegare l’attività genica alla sopravvivenza dei pazienti
Il passo successivo è stato verificare se questi segnali luminosi si traducessero in differenze negli esiti. I ricercatori hanno diviso i pazienti in gruppi con alta o bassa espressione di ciascun gene e hanno tracciato quante persone in ogni gruppo erano ancora vive nel tempo. I pazienti i cui tumori mostravano alti livelli di AURKA, BUB1 o CDK1 sono morti prima e più frequentemente rispetto a quelli con bassi livelli degli stessi geni. Al contrario, gli altri geni hub non separavano in modo chiaro buoni e cattivi esiti. Questo schema suggerisce che AURKA, BUB1 e CDK1 catturano qualcosa di fondamentale sull’aggressività di un tumore dato — quanto velocemente cresce e quanto può essere resistente al trattamento.

Costruire un calcolatore di rischio pratico
I medici già usano caratteristiche cliniche come la dimensione del tumore, il coinvolgimento dei linfonodi e la presenza di metastasi per stadiare il carcinoma nasofaringeo e guidare la terapia. Il team si è chiesto se aggiungere informazioni geniche potesse affinare queste previsioni. Hanno costruito un modello di previsione della sopravvivenza che combina fattori standard — età, sesso e gli stadi tumorali noti come T, N e M — con i livelli di AURKA e BUB1 in ciascun tumore. I test statistici hanno mostrato che questo modello combinato era altamente accurato nel distinguere i pazienti che avrebbero vissuto più a lungo da quelli a rischio più elevato, performando meglio rispetto a un modello basato solo sui dati clinici usuali. Non solo separava bene i gruppi a basso e alto rischio, ma era anche ben calibrato, nel senso che le probabilità di sopravvivenza previste corrispondevano a quanto osservato nei dati di follow-up.
Cosa significa per i pazienti
Questo lavoro suggerisce che tre geni coinvolti nella divisione cellulare, in particolare AURKA e BUB1, potrebbero fungere da spie molecolari nel carcinoma nasofaringeo. Misurarne l’attività nelle biopsie tumorali, insieme alle informazioni cliniche di routine, potrebbe aiutare i medici a stimare la sopravvivenza di un paziente con maggiore precisione e a individuare chi potrebbe beneficiare di un monitoraggio più attento o di trattamenti più intensivi. Lo studio è ancora preliminare — basato su un singolo centro con un numero modesto di pazienti — e non cambia ancora la pratica clinica quotidiana. Ma indica una strada verso un futuro in cui un semplice esame di laboratorio sul tessuto tumorale potrebbe trasformare complessi schemi di attività genica in una previsione di sopravvivenza chiara e personalizzata per le persone colpite da questo difficile tumore.
Citazione: Zhu, J., Feng, Y., Zhu, Z. et al. Identification of hub genes and construction of a survival prediction model for patients with nasopharyngeal carcinoma. Sci Rep 16, 5299 (2026). https://doi.org/10.1038/s41598-026-36395-4
Parole chiave: carcinoma nasofaringeo, biomarcatori del cancro, espressione genica, previsione della sopravvivenza, AURKA BUB1 CDK1