Clear Sky Science · it
ONCOPLEX: un modello ipergrafico ispirato all’oncologia che integra conoscenze biologiche diverse per la predizione dei geni driver del cancro
Perché questa ricerca è importante
Il cancro è guidato da un piccolo numero di potenti alterazioni genetiche nascoste tra migliaia di varianti innocue. Individuare quei geni “driver” veramente pericolosi è essenziale per diagnosi migliori e terapie mirate, ma è come riconoscere pochi capi in una folla vasta e rumorosa. Questo studio presenta ONCOPLEX, un nuovo framework di intelligenza artificiale che osserva i geni non uno per uno, ma nel contesto dei percorsi biologici in cui operano insieme, offrendo un modo più preciso per identificare i geni che realmente alimentano i tumori.
Vedere i geni del cancro nei loro quartieri biologici
La maggior parte dei metodi attuali scansiona i genomi tumorali alla ricerca di mutazioni che compaiono in modo anomalo o che risaltano in semplici reti geniche. Questi approcci sono utili, ma la biologia è raramente così semplice. I geni generalmente agiscono in gruppi all’interno di percorsi che controllano crescita cellulare, riparazione del DNA e molti altri processi. ONCOPLEX abbraccia questa complessità rappresentando i geni come punti e i percorsi come gruppi più ampi e sovrapposti che possono contenere molti geni contemporaneamente. Questo tipo di struttura, nota come ipergrafo, permette al modello di considerare direttamente relazioni multi-geniche invece di spezzarle in molte coppie separate.
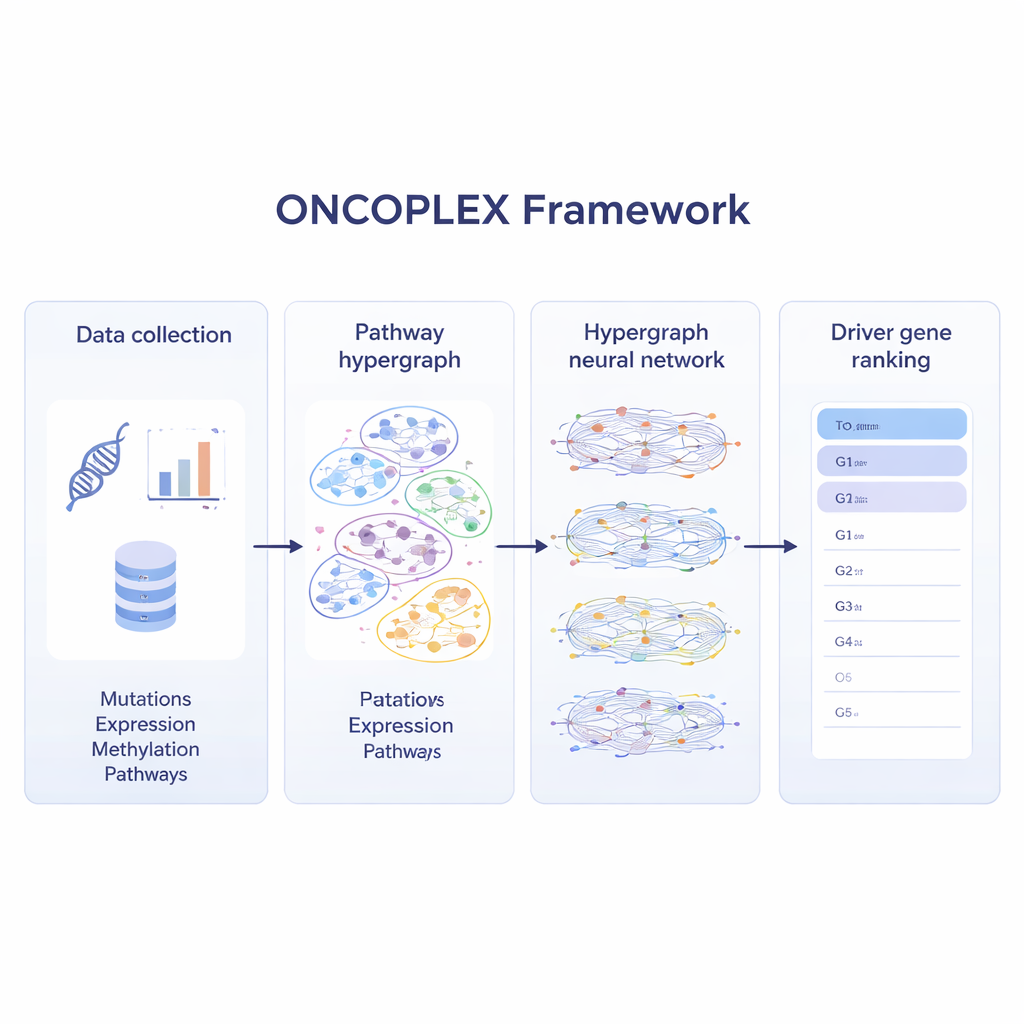
Mischiare molti livelli di dati sul cancro
Per sfruttare al meglio i moderni set di dati sul cancro, ONCOPLEX combina diversi tipi di informazione per ciascun gene. Usa le frequenze di mutazione, i cambiamenti nell’espressione genica, i marcatori chimici sul DNA (metilazione) e un insieme ricco di caratteristiche biologiche come la conservazione evolutiva e le annotazioni funzionali. Queste caratteristiche sono associate a ogni gene nell’ipergrafo. Una rete neurale specializzata poi trasferisce informazioni attraverso i percorsi, permettendo alla rappresentazione di ciascun gene di essere plasmata sia dai propri dati sia dal comportamento dei geni con cui collabora. Il modello viene addestrato usando geni già noti come driver del cancro, imparando al contempo da molti geni non etichettati che potrebbero essere importanti ma non ancora riconosciuti.
Superare gli strumenti esistenti in molti tipi di cancro
I ricercatori hanno testato ONCOPLEX sui dati del The Cancer Genome Atlas, sia aggregando molti tipi di tumore sia esaminando 11 tumori individuali, tra cui seno, polmone, fegato, vescica e testa/collo. Lo hanno confrontato con diversi metodi leader basati su grafi e ipergrafi. In generale, ONCOPLEX è risultato migliore nel distinguere i geni driver noti dai molto più comuni non-driver e nel collocare i probabili driver in cima alle sue classifiche. Il suo vantaggio è risultato particolarmente marcato osservando i geni con i punteggi più alti, dove l’identificazione accurata è più preziosa per esperimenti successivi e traduzione clinica.
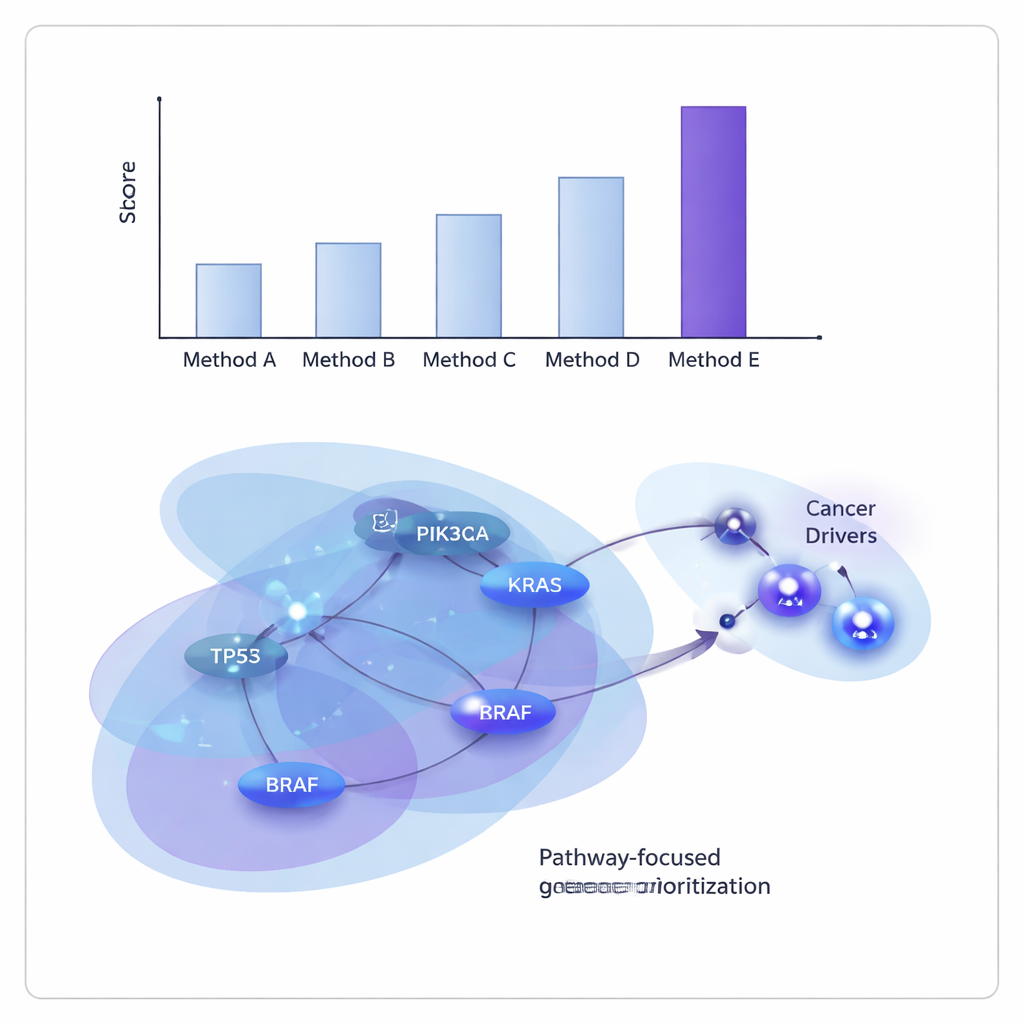
Rivelare colpevoli condivisi e specifici del cancro
Oltre ai numeri di performance, le classifiche geniche di ONCOPLEX hanno recuperato molti geni del cancro noti, come KRAS, BRAF e membri della via di segnalazione PI3K–AKT, confermando che il modello cattura biologia ben consolidata. Ha inoltre evidenziato candidati promettenti non ancora saldamente riconosciuti come driver in alcuni tipi di cancro, inclusi geni come GRB2 e MAPK3 nel tumore al seno e SHC1 nel cancro dello stomaco. Quando il team ha esaminato i geni in cima alla classifica tramite analisi di arricchimento dei percorsi, ha trovato forti firme di vie cancerogene ben note, tra cui la segnalazione ErbB e PI3K–AKT–mTOR, oltre a vie correlate al sistema immunitario, suggerendo che ONCOPLEX individua reti di rilievo clinico.
Punti di forza, limiti e prossimi passi
Dimostrando che caratteristiche biologiche più ricche migliorano costantemente le sue predizioni, ONCOPLEX mostra il valore di fondere molte fonti di dati all’interno di un quadro centrato sui percorsi. Allo stesso tempo, lo studio mette in luce un limite: poiché molti tumori condividono un gran numero di percorsi, il modello a volte favorisce geni «pan-cancro» ad azione ampia rispetto a quelli davvero specifici di un solo tipo tumorale. Gli autori suggeriscono che lavori futuri dovrebbero affinare l’uso delle informazioni sui percorsi in modo che segnali comuni e specifici del cancro possano essere separati più chiaramente.
Cosa significa per pazienti e clinici
Per i non specialisti, la conclusione chiave è che ONCOPLEX offre un modo più biologicamente realistico per cercare i geni che guidano il cancro. Osservando i geni nella compagnia che tengono — all’interno dei percorsi anziché isolatamente — migliora la nostra capacità di individuare sia driver ben noti sia quelli precedentemente trascurati, anche in tumori di cui si sa poco. Questo tipo di strumento può aiutare i ricercatori a dare priorità ai geni da studiare in laboratorio, guidare la ricerca di nuovi bersagli farmacologici e, in ultima istanza, supportare strategie terapeutiche più precise e consapevoli dei percorsi in oncologia.
Citazione: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Parole chiave: geni driver del cancro, reti neurali su ipergrafi, integrazione multi-omica, analisi dei percorsi, oncologia di precisione