Clear Sky Science · it
Analisi a livello di aplotipo del metabarcoding dell’eDNA rivelano la biogeografia e la filogeografia dei pesci d’acqua dolce nella Penisola Coreana
Leggere i fiumi attraverso indizi invisibili
I fiumi e i torrenti possono apparire limpidi a occhio nudo, ma sono pieni di tracce microscopiche di vita. Questo studio mostra come gli scienziati possano leggere quell’“inchiostro” genetico invisibile nell’acqua per scoprire quali pesci vivono dove, come le loro popolazioni sono correlate attraverso la Penisola Coreana e persino se alcuni pesci sono stati spostati dalle persone da una regione all’altra. Il lavoro offre uno sguardo su come i conservazionisti potrebbero presto monitorare la biodiversità e proteggere specie rare senza lanciare nemmeno una rete.
Pescare con il DNA, non con le reti
Invece di catturare pesci, i ricercatori hanno raccolto semplici bottiglie da un litro d’acqua da tre piccoli corsi d’acqua — Seom, Gilan e Oshipcheon — ciascuno situato in una diversa regione biogeografica della Corea del Sud. In questi campioni hanno cercato il DNA ambientale (eDNA): minuscoli frammenti di materiale genetico rilasciati dai pesci tramite pelle, escrementi e muco. Utilizzando una tecnica chiamata metabarcoding, hanno amplificato e sequenziato un breve segmento di DNA di pesci, quindi hanno confrontato milioni di letture con banche dati di riferimento per identificare quali specie — e persino quali varianti genetiche, o aplotipi — erano presenti in ciascun corso d’acqua.
Chi vive dove nei torrenti della Corea?
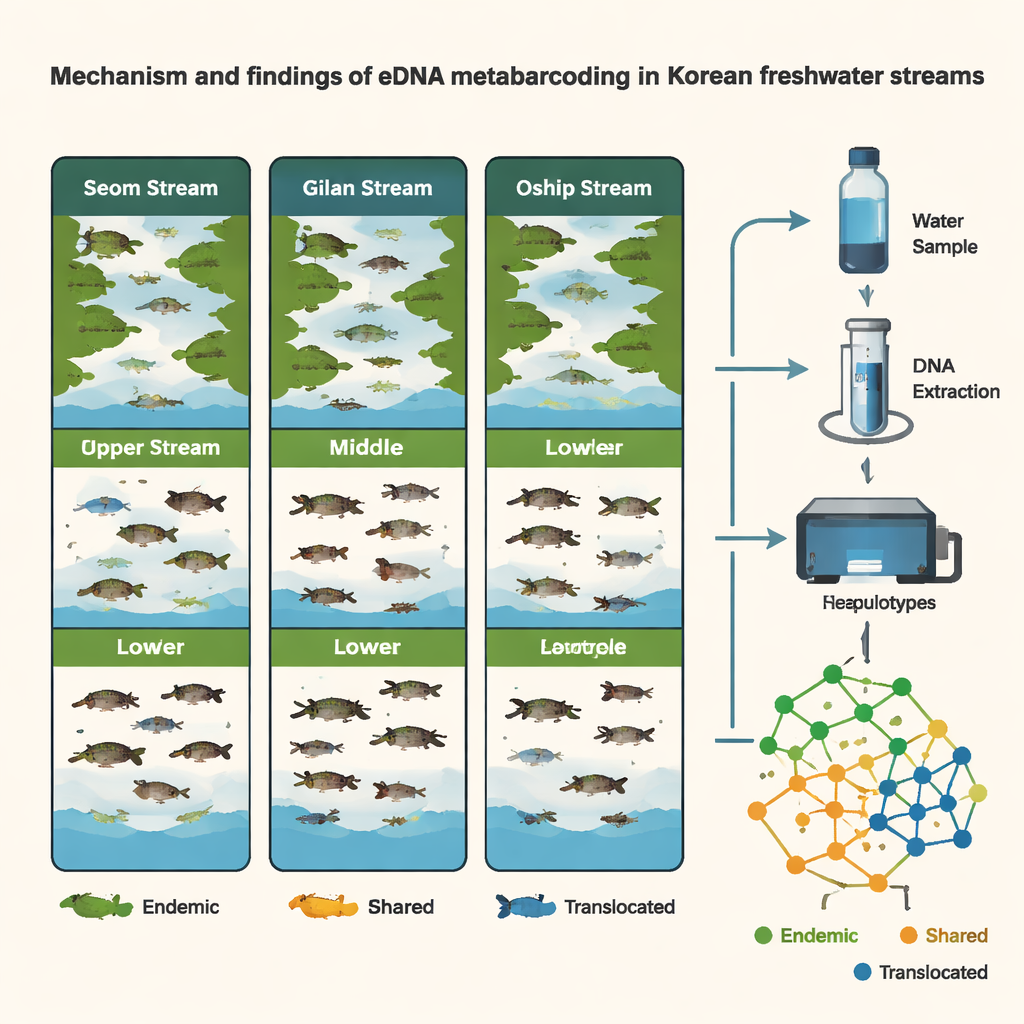
Partendo da soli 54 campioni d’acqua prelevati in nove siti, il team ha rilevato 107 varianti di DNA distinte rappresentanti 76 specie di pesci — circa un terzo di tutti i pesci d’acqua dolce noti in Corea. Il torrente Seom, un fiume a quota più bassa collegato al Mare Giallo, ospitava la comunità ittica più ricca, con 49 specie. Gilan e Oshipcheon, tributari più alti e scoscesi che scorrono verso coste diverse, ne contenevano ciascuno 28. Molti pesci erano condivisi tra i corsi d’acqua, ma quasi 30 specie sono risultate endemiche agli habitat d’acqua dolce coreani, e ogni torrente presentava anche un proprio insieme unico di specie. Nel complesso, i modelli corrispondevano alla conoscenza consolidata secondo cui la vita d’acqua dolce della Corea è divisa in tre regioni principali a causa delle catene montuose e della storia geologica.
Impronte genetiche e spostamenti nascosti
Poiché gli scienziati hanno lavorato a livello di aplotipo — le “sfumature” fini del DNA all’interno di una specie — potevano fare più che elencare le specie; potevano confrontare le popolazioni. Diverse specie native comuni mostrano chiare differenze genetiche tra le regioni, indicando separazione a lungo termine e limitata mescolanza naturale attraverso la penisola. Allo stesso tempo, i dati genetici hanno messo in luce probabili casi di spostamento assistito dall’uomo. Per specie come Pungtungia herzi, Coreoleuciscus splendidus e Nipponocypris koreanus, i modelli di aplotipi nel torrente orientale Oshipcheon corrispondevano strettamente a quelli di fiumi occidentali o meridionali, indicando immissioni o traslocazioni passate. Ricostruendo virtualmente gli “alberi genealogici” di queste varianti di DNA, il gruppo ha potuto inferire le probabili regioni di origine dei pesci spostati — offrendo una sorta di forense genetica per la gestione fluviale.
Stagioni, habitat e bersagli in movimento
Lo studio ha anche monitorato come le comunità ittiche cambiassero nel tempo e nello spazio. Confrontando i campioni raccolti nel tardo inverno (marzo) e in estate (agosto), i ricercatori hanno riscontrato una maggiore ricchezza di specie in estate e chiare variazioni stagionali, in particolare nel torrente Seom. In Oshipcheon, l’eDNA di specie migratorie — come i salmonidi e altri pesci che si spostano tra fiume e mare — appariva e scompariva in modi coerenti con i loro cicli di vita noti. Sorprendentemente, all’interno di ciascun sito riffles, run e pozze non mostravano forti differenze nel DNA dei pesci, probabilmente perché il flusso d’acqua mescola lateralmente l’eDNA attraverso questi piccoli canali. Piuttosto, i contrasti principali emergevano tra diverse sezioni del corso d’acqua (alto, medio, basso) e tra i tre corsi stessi, sottolineando l’importanza della posizione lungo il fiume in cui si prelevano i campioni.
Cosa significa per la protezione della vita d’acqua dolce
In termini semplici, questa ricerca dimostra che una bottiglia d’acqua di fiume può rivelare un’istantanea dettagliata di chi vive nel torrente, come le popolazioni ittiche locali sono correlate su vaste regioni e se le persone hanno alterato quei modelli spostando i pesci. Per la conservazione, ciò significa che i gestori possono monitorare rapidamente specie rare ed endemiche, individuare pesci invasivi e traslocati e seguire i cambiamenti stagionali delle popolazioni migratorie senza lavoro sul campo intensivo o danni agli animali. Pur non potendo ancora sostituire completamente gli studi genetici tradizionali, l’eDNA fornisce uno strumento potente e a basso impatto per sorvegliare la biodiversità d’acqua dolce in un mondo che si riscalda e viene fortemente gestito — e per assicurare che i pesci unici dei fiumi coreani continuino a prosperare nelle loro case naturali.
Citazione: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Parole chiave: DNA ambientale, pesci d’acqua dolce, biodiversità, fiumi coreani, genetica della conservazione