Clear Sky Science · it
IL2Pepscan: Un framework di machine learning per prevedere peptidi induttori di IL-2 e la loro identificazione nei proteomi virali globali
Insegnare al sistema immunitario con minuscoli frammenti proteici
I vaccini moderni e le terapie oncologiche si basano sempre più sul guidare in modo preciso il sistema immunitario invece di trattare la malattia con approcci generalizzati. Questo studio esplora come piccoli frammenti di proteine, detti peptidi, possano essere selezionati per attivare un potente messaggero immunitario, l’interleuchina‑2 (IL‑2). Usando modelli computazionali avanzati, gli autori scandagliano sia dati immunologici noti sia i cataloghi proteici di migliaia di virus per trovare ago nel pagliaio molecolare — peptidi che potrebbero aiutare a progettare vaccini e immunoterapie migliori.
Perché l’IL-2 è importante per salute e malattia
La IL‑2 è una piccola molecola di segnalazione che funge da fattore di crescita per cellule immunitarie chiave conosciute come linfociti T. Quando queste cellule incontrano per la prima volta una minaccia — come un virus o una cellula tumorale — possono rilasciare IL‑2, che incoraggia i linfociti T a moltiplicarsi, specializzarsi e ricordare l’invasore. La IL‑2 contribuisce anche a mantenere le cellule T regolatorie che impediscono al sistema immunitario di attaccare i tessuti del proprio corpo. Per questo ruolo duplice, la IL‑2 è stata impiegata come farmaco per trattare tumori come il melanoma ed è oggetto di studi per malattie autoimmuni. Tuttavia somministrare IL‑2 direttamente può essere gravoso per i pazienti, quindi cresce l’interesse nel progettare peptidi sicuri che inducano la produzione endogena di IL‑2 in modo più controllato e mirato.
Imparare il “sapore” dei peptidi che inducono IL-2
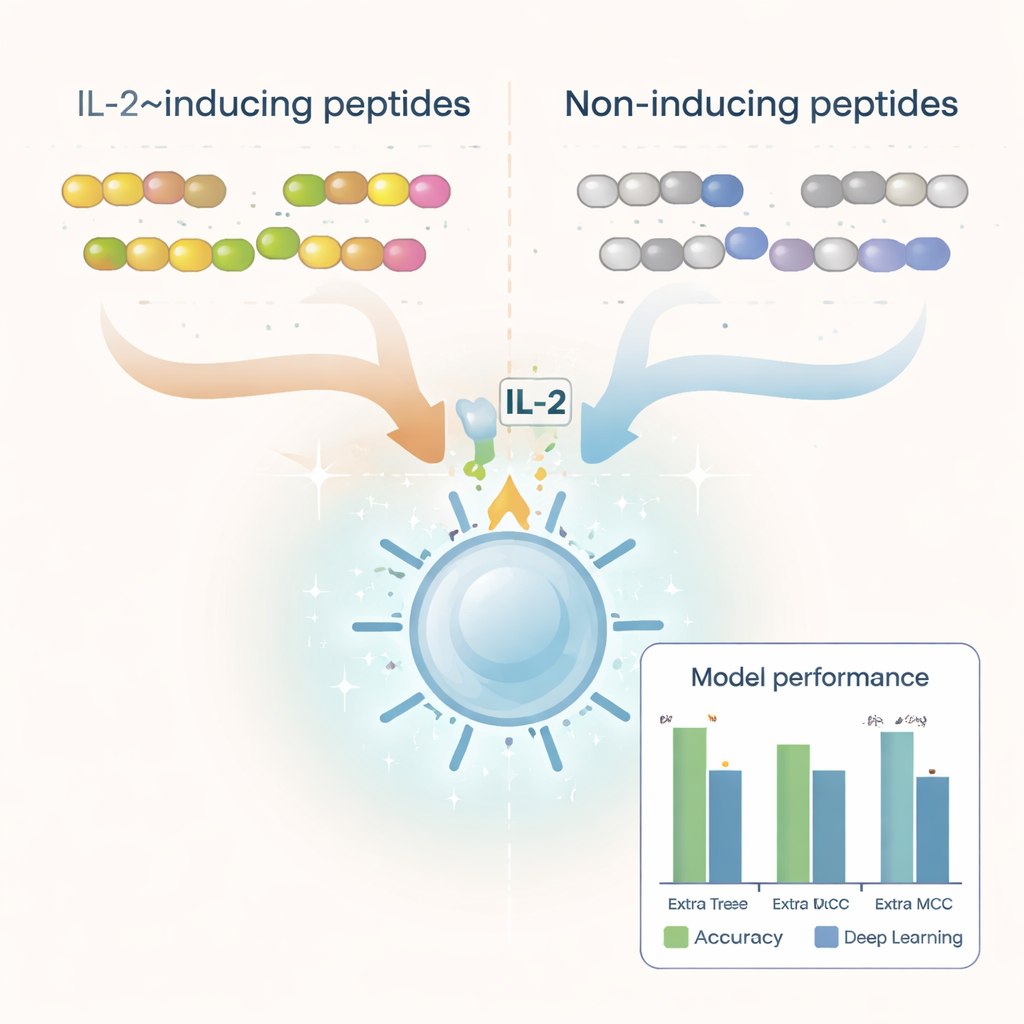
I ricercatori sono partiti da migliaia di sequenze peptidiche già testate sperimentalmente e classificate come induttrici di IL‑2 o non induttrici. Hanno pulito il dataset per rimuovere duplicati, blocchi costitutivi insoliti e peptidi troppo corti o troppo lunghi, ottenendo oltre 6.000 esempi ben caratterizzati. Esaminando i costituenti (amminoacidi) di questi peptidi, hanno rilevato differenze nette tra i due gruppi. I peptidi induttori di IL‑2 tendevano a essere più ricchi di amminoacidi idrofobici, o che respingono l’acqua, come leucina e alanina, mentre i peptidi non induttori presentavano più residui polari e carichi. Alcuni brevi motivi, o pattern, come “LEGS” e “ALEG”, comparivano solo nei peptidi induttori di IL‑2, suggerendo segnature strutturali che potrebbero favorire l’attivazione immunitaria.
Addestrare macchine a riconoscere i pattern che potenziano l’immunità
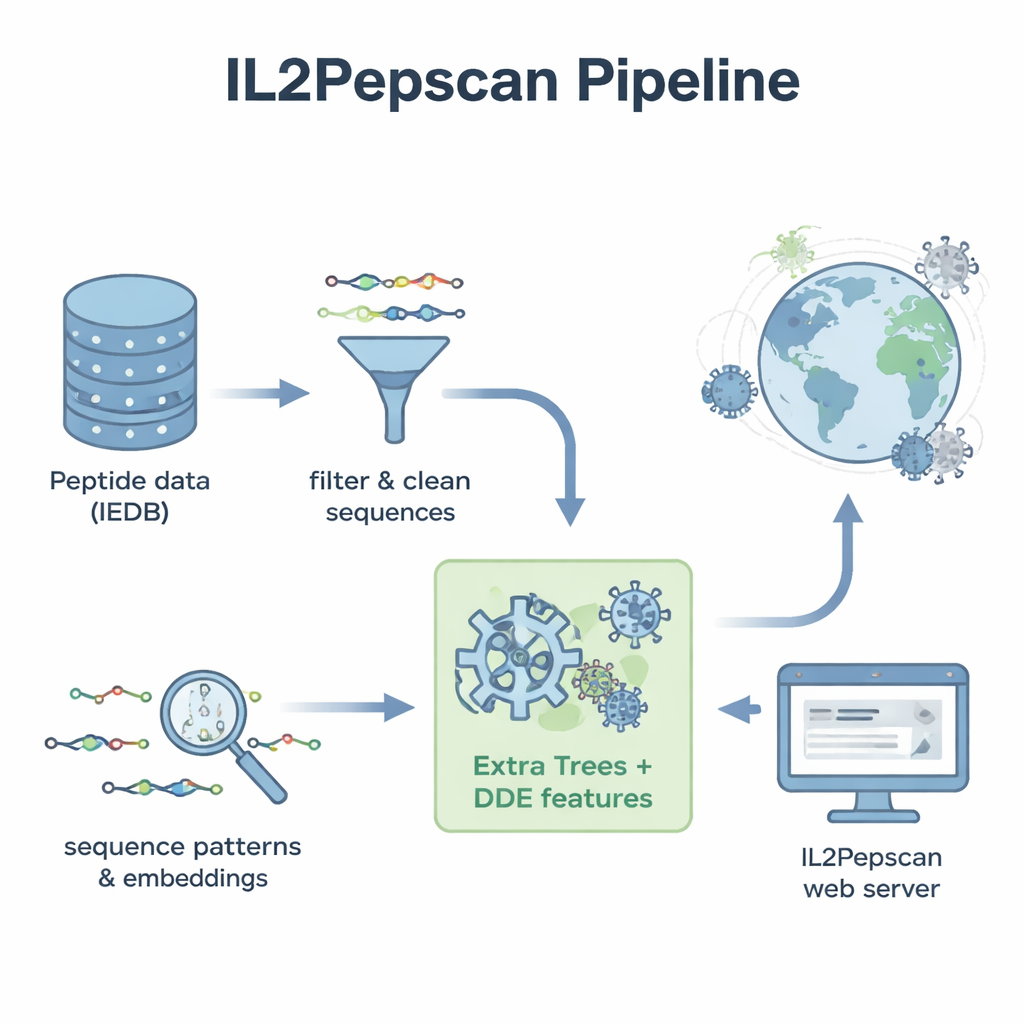
Per trasformare questi pattern in uno strumento predittivo pratico, il team ha convertito ogni peptide in descrittori numerici che catturano la composizione e l’ordine degli amminoacidi. Hanno testato vari metodi di machine learning — tra cui algoritmi diffusi come random forest, support vector machine e boosted trees — insieme ad architetture di deep learning spesso usate per linguaggio e immagini. Hanno inoltre sfruttato un grande “modello linguistico” per proteine chiamato ProtBERT, originariamente addestrato su centinaia di milioni di sequenze proteiche, e lo hanno perfezionato per riconoscere segnali correlati all’IL‑2. Dopo ampi test con cross‑validation e un set di test indipendente, il miglior modello è risultato essere Extra Trees combinato con un insieme di caratteristiche noto come dipeptide deviation from expected mean (DDE). Questo modello ha raggiunto quasi l’80% di accuratezza e un forte punteggio di correlazione, superando diverse soluzioni di deep learning.
Scansionare il mondo virale alla ricerca di inneschi immunitari nascosti
Con il loro miglior modello, gli autori hanno allargato notevolmente la ricerca. Hanno raccolto sequenze proteiche di riferimento da oltre 14.000 virus, suddiviso queste proteine in circa 156 milioni di peptidi sovrapposti e chiesto al modello di prevedere quali potessero indurre IL‑2. Tra i candidati con i punteggi più alti sono emersi peptidi provenienti da famiglie virali ben note, incluse flavivirus come West Nile, Zika, Febbre gialla e virus dell’epatite C, oltre a Influenza e SARS‑CoV‑2. Molti peptidi promettenti derivavano da proteine di envelope o dal nucleocapside — gli stessi tipi di proteine che altri studi hanno mostrato capaci di provocare risposte di IL‑2 negli animali. Il modello ha anche segnalato potenziali peptidi induttori di IL‑2 codificati da batteriofagi, virus che infettano i batteri, suggerendo un panorama ancora più ampio di sequenze rilevanti per l’immunità.
Dall’algoritmo a uno strumento accessibile
Per rendere il loro lavoro utile oltre il laboratorio informatico, gli autori hanno costruito un server web pubblico chiamato IL2Pepscan. I ricercatori possono incollare sequenze peptidiche o proteiche nel sito per stimare il loro potenziale induttivo di IL‑2, progettare nuove varianti introducendo mutazioni, scansionare proteine intere per individuare hotspot o cercare motivi noti correlati a IL‑2. Sebbene lo studio non confermi ancora sperimentalmente ogni peptide predetto, la concordanza con risultati di laboratorio esistenti suggerisce che IL2Pepscan può ridurre in modo affidabile il numero di candidati da testare ulteriormente. Per i non specialisti, la conclusione è che algoritmi ben addestrati possono setacciare enormi dataset biologici per individuare piccoli frammenti proteici che un giorno potrebbero aiutare vaccini e immunoterapie a indurre risposte immunitarie più potenti — e più precise —.
Citazione: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Parole chiave: interleuchina-2, vaccini peptidici, machine learning, proteoma virale, immunoterapia