Clear Sky Science · it
Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning
Perché questo è importante per le aziende agricole e il cibo
La medica è una colonna portante dell’agricoltura moderna: nutre le vacche da latte e contribuisce a costruire suoli sani. Tuttavia, migliorare la medica — piante che resistano meglio all’inverno, limitino i danni e forniscano foraggio di alta qualità — è ostacolato dalla complessità del suo patrimonio genetico. Questo studio introduce un nuovo approccio per passare da lunghe e confuse liste di marcatori del DNA a mappe chiare di causa-effetto che mostrano quali parti del genoma guidano davvero tratti importanti del fusto e quali sono solo associati per caso.
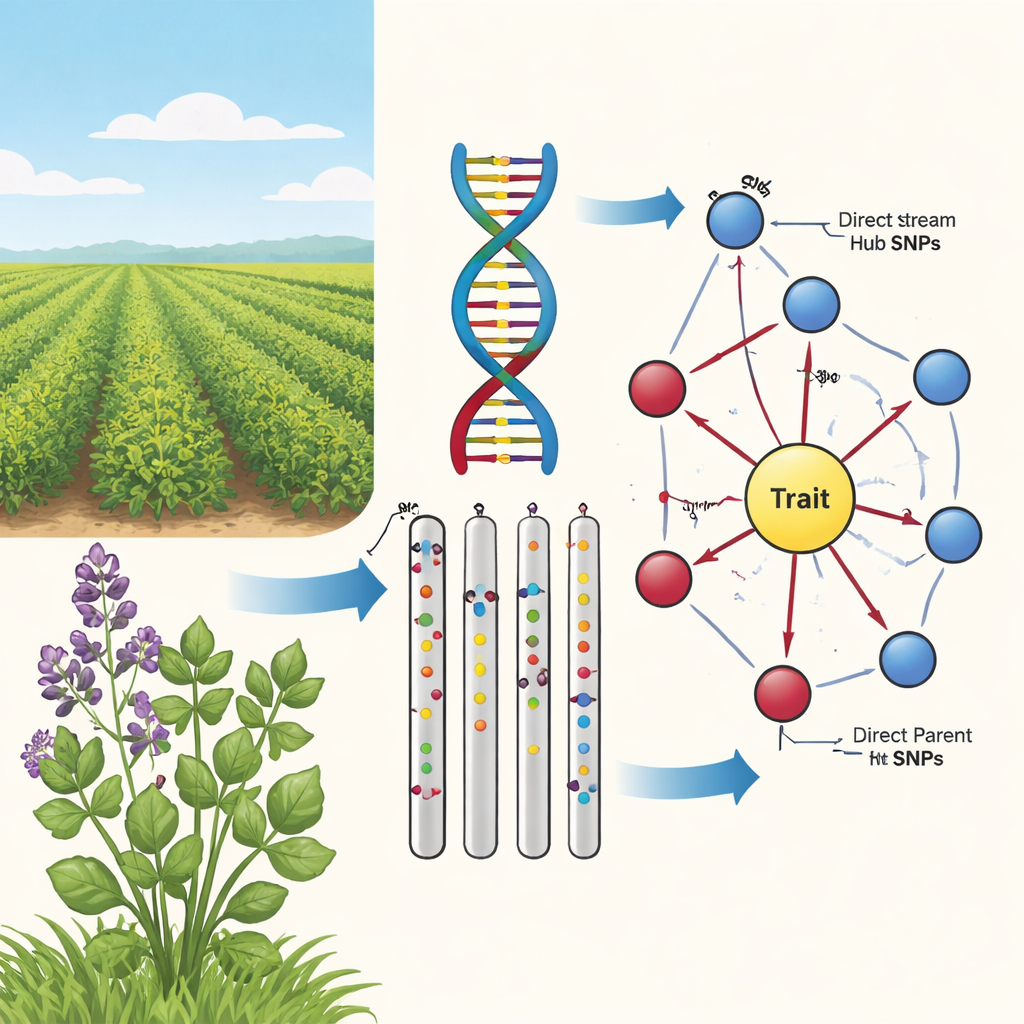
Da legami vaghi a causa-effetto
Gli studi di associazione genome-wide tradizionali scandagliano il genoma alla ricerca di variazioni del DNA, chiamate SNP, che tendono a comparire insieme a un fenotipo, come il colore del fusto o la sopravvivenza invernale. Nella medica, però, la situazione è particolarmente intricata: la specie è tetraploide, ampie porzioni di DNA si muovono insieme e le piante sono geneticamente molto miste. Questo genera una “nebbia di correlazione” in cui molti marcatori sembrano importanti ma solo pochi influenzano realmente il tratto. Gli autori sostengono che i miglioratori abbiano bisogno di più di semplici legami statistici: serve sapere quali marcatori si trovano effettivamente sui percorsi causali dal genotipo ai tratti visibili della pianta.
Come funziona il nuovo quadro metodologico
I ricercatori hanno costruito un framework in due fasi che combina tecniche moderne di machine learning con concetti della teoria dei grafi causali. Per prima cosa hanno usato una tecnica chiamata Double Machine Learning per selezionare circa 2.400 SNP in 500 genotipi di medica. Questo passaggio rimuove l’influenza di fattori nascosti come la struttura familiare e la geografia, usando componenti principali del genoma come proxy. Il risultato è una visione più pulita di quali marcatori mantengono un effetto diretto sui tratti, come il colore del fusto, dopo aver controllato questi fattori di confondimento. In questa vista filtrata sono emersi picchi di segnale forti e stabili soprattutto sui cromosomi 2 e 4, e alcuni marcatori chiave hanno mostrato grandezze d’effetto le cui intervalli di confidenza escludevano chiaramente lo zero, suggerendo un’influenza causale reale.
Trasformare i marcatori in mappe genetiche
Nella seconda fase il team ha impiegato un algoritmo di apprendimento di grafi causali, noto come algoritmo PC, per collegare i marcatori più promettenti in una rete direzionale. In questi diagrammi i nodi rappresentano SNP e il tratto, e le frecce indicano la direzione più probabile dell’influenza. Eliminando i legami che confliggono con la biologia di base (per esempio i tratti non possono modificare il DNA sottostante) e mantenendo solo gli SNP che puntano verso il tratto, gli autori hanno ottenuto mappe compatte e biologicamente sensate. Queste reti a «girasole» rivelano una struttura stratificata: un anello interno di SNP Genitori Diretti che collegano direttamente al tratto e un anello esterno di Hub a monte che influenzano più genitori ma non toccano il tratto direttamente.
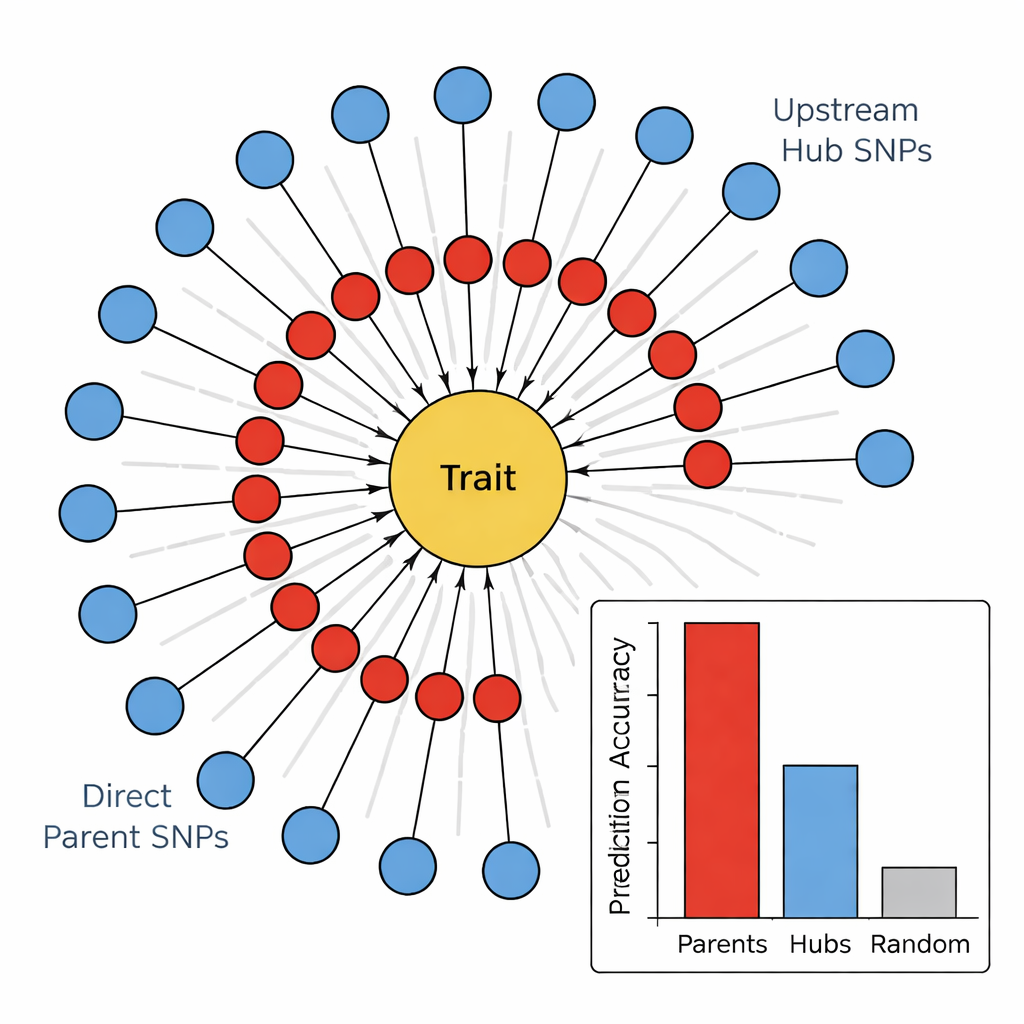
Esecutori versus direttori nel genoma
Per verificare se questa gerarchia avesse senso biologico, gli autori hanno confrontato quanto bene diversi gruppi di marcatori riuscissero a prevedere quattro tratti legati al fusto: colore del fusto, riempimento dello stelo, resistenza del fusto e danno invernale. Per tutti i tratti, gli SNP Genitori Diretti sono risultati costantemente i migliori predittori, spesso spiegando molte volte più variazione rispetto a marcatori casuali o agli Hub a monte. Per contro, gli hub mostravano potere predittivo debole o anche negativo, nonostante la loro alta connettività nella rete. Collegando questi SNP a geni noti è emerso un modello: i Genitori Diretti spesso corrispondono ad enzimi o proteine strutturali che agiscono direttamente sulle pareti cellulari, i pigmenti o i danni da stress, mentre gli Hub tendono a essere fattori di trascrizione e proteine regolatorie che modulano ampiamente molte vie contemporaneamente.
Cosa significa per il futuro del miglioramento della medica
Per allevatori e genetisti, lo studio offre un modo per tagliare i risultati rumorosi delle associazioni e concentrarsi sulle variazioni del DNA che effettivamente incidono su tratti specifici. Gli autori mostrano che combinare uno screening deconfondato con grafi causali può fungere da protezione contro l’overfitting, trasformando lunghe liste di candidati in piccole reti interpretabili e allineate con la biologia conosciuta. In termini pratici, gli SNP Genitori Diretti diventano marcatori ad alta precisione per selezionare piante con fusti migliori o maggiore sopravvivenza invernale, mentre gli Hub a monte indicano interruttori principali che potrebbero rimodellare risposte allo stress più ampie, ma con possibili compromessi. Questa visione strutturale del genoma pone le basi per una selezione genomica più affidabile nelle colture complesse e per integrare in futuro altri livelli di dati, come espressione genica e metabolismo, in modelli coerenti di causa-effetto delle prestazioni delle piante.
Citazione: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Parole chiave: alfalfa genetics, causal graph learning, genomic selection, plant breeding, polyploid crops