Clear Sky Science · it
SwiM-UNet leggero con adattatore multidimensionale per una segmentazione medica efficiente su dispositivo
Scansioni più intelligenti al letto del paziente
Le scansioni cerebrali possono rivelare tumori potenzialmente letali, ma trasformare immagini grezze in contorni nitidi su cui i medici possano intervenire è ancora lento e richiede molta potenza di calcolo. Questo studio presenta SwiM-UNet, un nuovo algoritmo in grado di segmentare i tumori cerebrali da scansioni MRI 3D con precisione di livello avanzato pur funzionando in modo efficiente su dispositivi locali, avvicinando l'analisi precisa delle immagini al letto del paziente o persino a cliniche mobili. 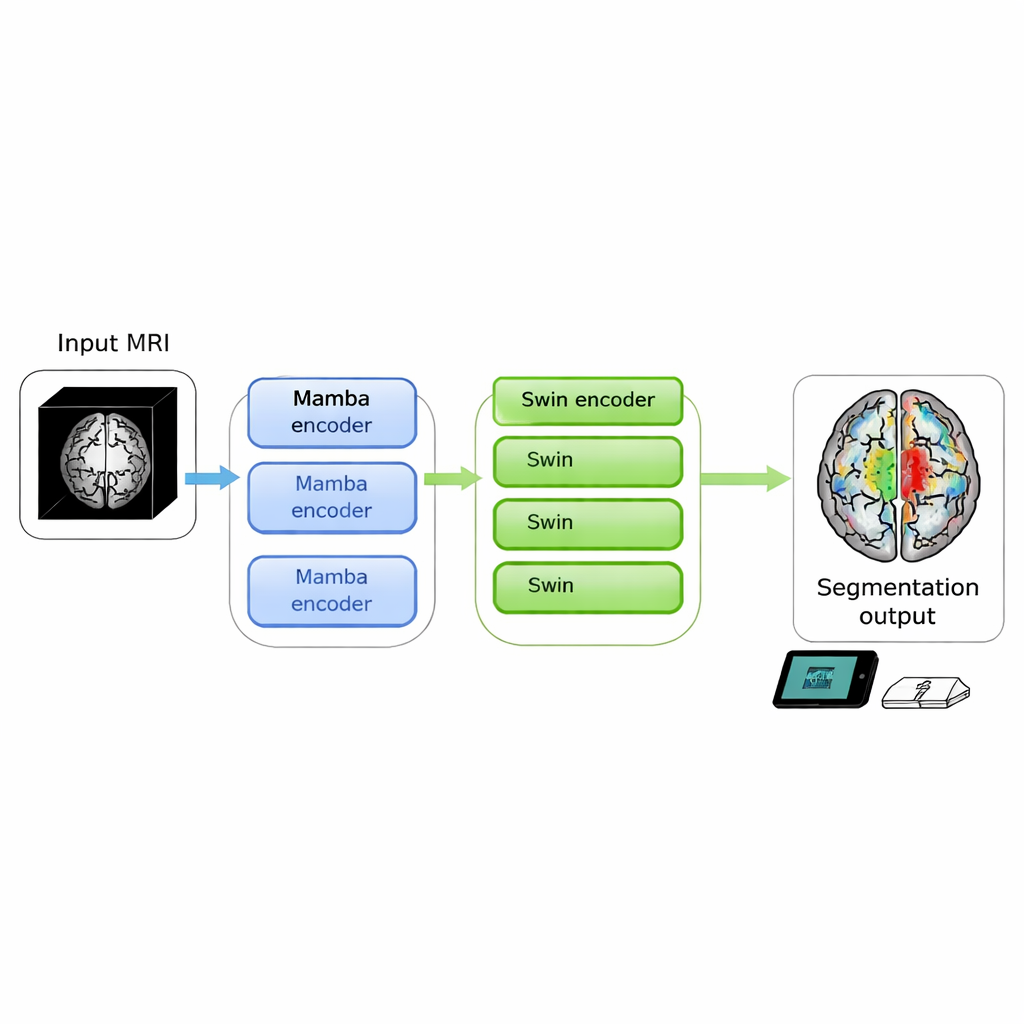
Perché contorni precisi dei tumori sono importanti
La medicina moderna si basa fortemente sull'imaging per pianificare interventi chirurgici, radioterapia e trattamenti farmacologici. Per i tumori cerebrali, i medici non devono solo accertare la presenza di una massa, ma conoscere con precisione dove iniziano e finiscono le sue diverse componenti. Questo compito, chiamato segmentazione, viene solitamente eseguito o raffinato da specialisti immagine per immagine—un processo che richiede tempo, può ritardare le decisioni e varia da un esperto all'altro. Gli strumenti di segmentazione automatica basati sul deep learning hanno migliorato la situazione, ma i più precisi spesso richiedono grandi GPU, rendendoli difficili da impiegare direttamente in clinica, soprattutto su macchine più piccole o portatili.
Due idee potenti che non entrano facilmente su macchine piccole
Le recenti svolte nella visione artificiale provengono principalmente da due famiglie di modelli. I sistemi basati su Transformer, come lo Swin Transformer, sono eccellenti nel cogliere pattern globali su una scansione 3D completa e hanno alimentato i segmentatori di tumore cerebrale più performanti. Tuttavia, la loro operazione centrale, chiamata self-attention, diventa estremamente costosa con l'aumentare della dimensione dell'immagine, limitandone l'uso in tempo reale o su hardware compatto. Una famiglia più recente, nota come Mamba e basata su modelli a spazio di stato, offre una soluzione intelligente: elabora sequenze in tempo praticamente lineare, riducendo il numero di calcoli necessari. Gli esperimenti iniziali in imaging medico hanno mostrato che i modelli in stile Mamba sono rapidi ed efficienti ma di solito restano indietro rispetto ai transformer in termini di qualità della segmentazione, soprattutto per forme tumorali complesse.
Combinare velocità e accuratezza in un unico progetto
Gli autori hanno mirato a fondere i punti di forza di entrambi gli approcci in un singolo modello 3D. Il loro SwiM-UNet conserva la struttura a U familiare, ampiamente usata in imaging medico, con un encoder che comprime l'informazione e un decoder che ricostruisce segmentazioni dettagliate. Nelle prime fasi, quando la scansione è ancora grande e ad alta risoluzione, utilizzano blocchi Mamba efficienti per mantenere i calcoli gestibili. Più in profondità nella rete, dopo che i dati sono stati sottocampionati, passano a blocchi Swin Transformer snelliti che possono ora permettersi di modellare relazioni a lungo raggio senza sovraccaricare l'hardware. Un ponte personalizzato chiamato MS-adapter collega questi due regimi. Esso osserva le caratteristiche separatamente lungo larghezza, altezza e profondità del volume, e anche attraverso i canali, quindi apprende tramite piccole unità di gating quanto ogni vista dovrebbe influenzare la rappresentazione finale. 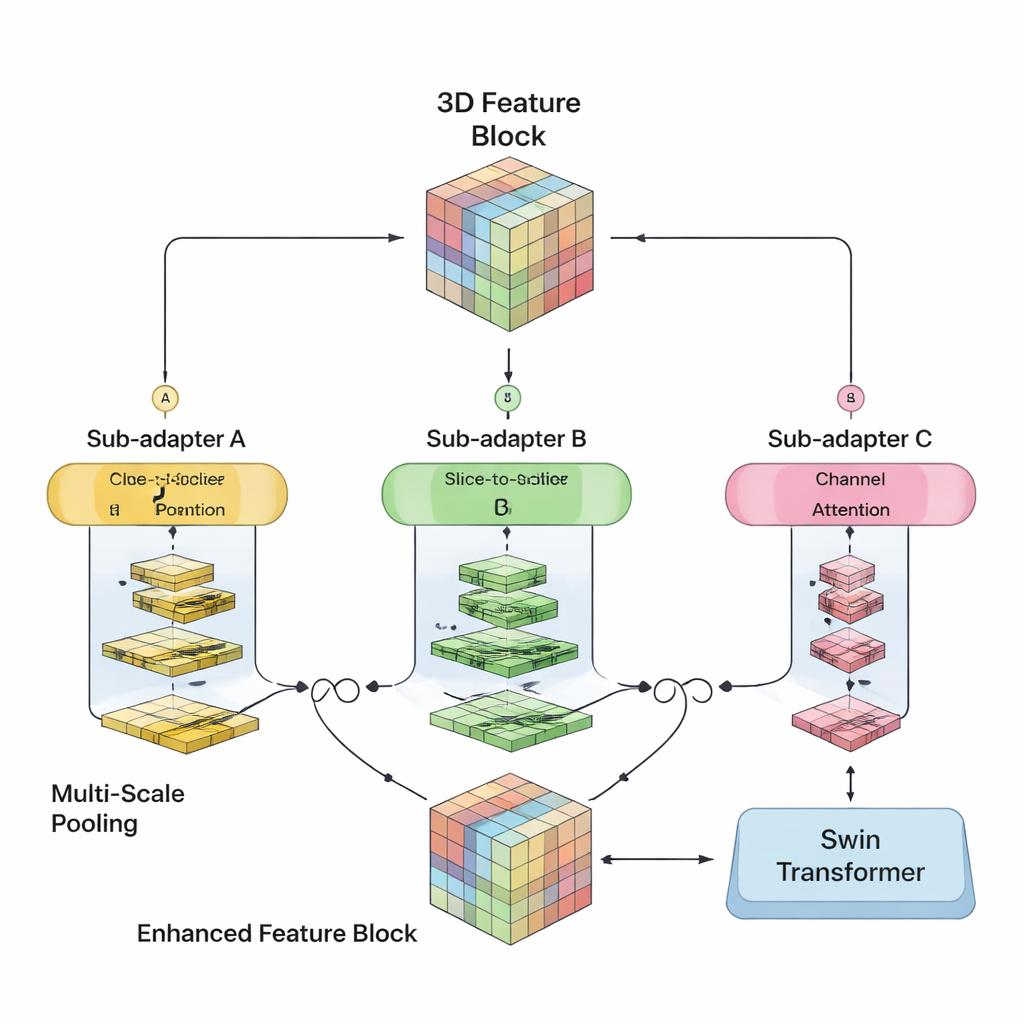
Fare di più con meno calcolo
Oltre a questo layout ibrido, il gruppo riduce i calcoli superflui impiegando layer fully connected a bassa rango e un decoder che riduce deliberatamente il numero di canali da gestire. Hanno testato diverse varianti con mix differenti di layer Mamba e Swin e hanno scoperto che usare Mamba nelle prime tre fasi dell'encoder e Swin solo nello stadio più profondo offriva il miglior bilanciamento tra velocità e accuratezza. Su due grandi dataset pubblici di tumori cerebrali provenienti dalle challenge BraTS 2023 e 2024, SwiM-UNet ha raggiunto maggiore accuratezza e confini più precisi rispetto ai principali modelli basati solo su transformer, solo su Mamba e ai precedenti modelli ibridi, pur usando molte meno operazioni in virgola mobile e riducendo il tempo di inferenza a circa 45 millisecondi per patch di scansione su una moderna scheda grafica.
Pronto per dispositivi reali
Per verificare se questi vantaggi contano al di fuori del laboratorio, gli autori hanno confrontato le esigenze computazionali del modello con le capacità dei tipici sistemi edge clinici—console MRI portatili, computer point-of-care e postazioni in sala operatoria. La loro analisi suggerisce che, a differenza dei modelli transformer più pesanti, SwiM-UNet si inserisce comodamente nei limiti di potenza, memoria e velocità di tali dispositivi, spesso soddisfacendo i requisiti in tempo reale. Ha inoltre mostrato buone prestazioni su un dataset separato di TC addominale, indicando che l'approccio può generalizzare oltre i tumori cerebrali e persino oltre la MRI.
Cosa significa per pazienti e clinici
In termini pratici, SwiM-UNet dimostra che è possibile avvicinarsi all'accuratezza dei modelli di segmentazione più sofisticati mantenendo il calcolo sufficientemente leggero per l'uso su dispositivo. Questo potrebbe abilitare contorni tumorali più rapidi e più coerenti in pronto soccorso, ospedali rurali o unità di imaging mobili senza inviare scansioni sensibili a server remoti. Pur necessitando di ulteriori lavori per adattare il metodo a diversi scanner e condizioni, questo progetto ibrido indica un futuro in cui l'analisi di immagini di alta qualità avviene ovunque si trovi il paziente, non solo nei data center.
Citazione: Noh, Y., Lee, S., Jin, S. et al. Lightweight SwiM-UNet with multi-dimensional adaptor for efficient on-device medical image segmentation. Sci Rep 16, 5807 (2026). https://doi.org/10.1038/s41598-026-35771-4
Parole chiave: segmentazione dei tumori cerebrali, IA per l'imaging medico, reti neurali ibride, inferenzia su dispositivo, analisi 3D MRI