Clear Sky Science · it
Metodi PCA dissociativi strutturati per la decomposizione di segnali neuroimmagini ad alta dimensionalità
Sciogliere i segnali nascosti del cervello
Le moderne scansioni cerebrali possono registrare l’attività da centinaia di migliaia di punti ogni secondo, ma trasformare questo torrente di numeri in reti chiare e significative è estremamente difficile. Processi cerebrali diversi spesso si sovrappongono nello spazio e nel tempo, come più stazioni radio che trasmettono su frequenze vicine. Questo articolo presenta nuovi strumenti matematici che aiutano a separare questi segnali intrecciati in modo più netto, promettendo mappe più nitide della funzione cerebrale sia per la ricerca di base sia per studi clinici.
Perché i metodi abituali non bastano
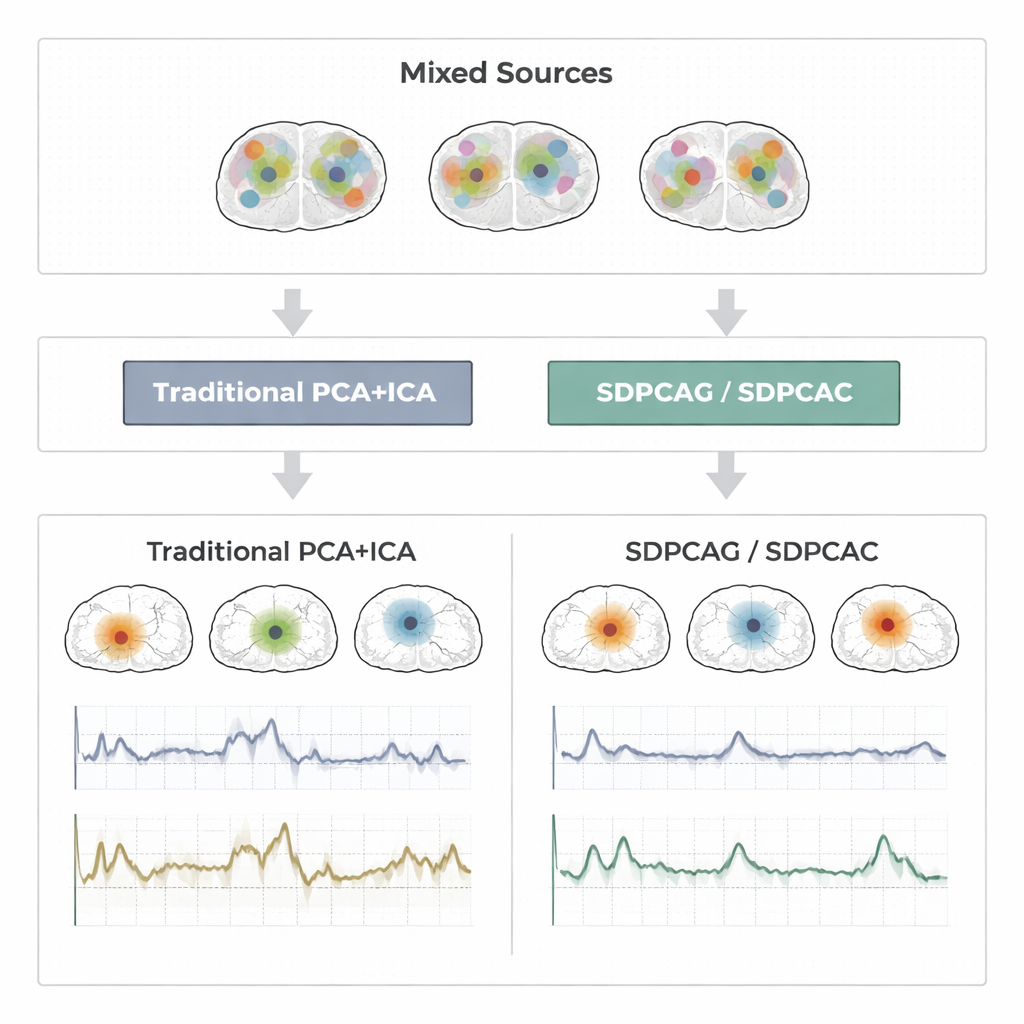
Per decenni i ricercatori si sono affidati a tecniche chiamate analisi delle componenti principali (PCA), PCA sparsa e analisi delle componenti indipendenti (ICA) per comprimere e separare i dati di risonanza funzionale (fMRI). La PCA individua schemi che spiegano la maggior parte della variazione nei dati, ma ogni schema mescola informazioni provenienti da quasi tutte le posizioni cerebrali, rendendo l’interpretazione difficile. La PCA sparsa tenta di risolvere questo problema obbligando ogni componente a usare solo un sottoinsieme di posizioni, e l’ICA va oltre assumendo che i segnali cerebrali sottostanti siano statisticamente indipendenti. In pratica, però, le reti cerebrali reali si sovrappongono e si influenzano a vicenda. Quando ciò accade, le assunzioni di indipendenza e di sparsità si rompono. Il risultato può essere mappe frammentate e corsi temporali rumorosi che non corrispondono più al modo in cui le reti cerebrali effettivamente si comportano.
Un nuovo modo per separare i segnali
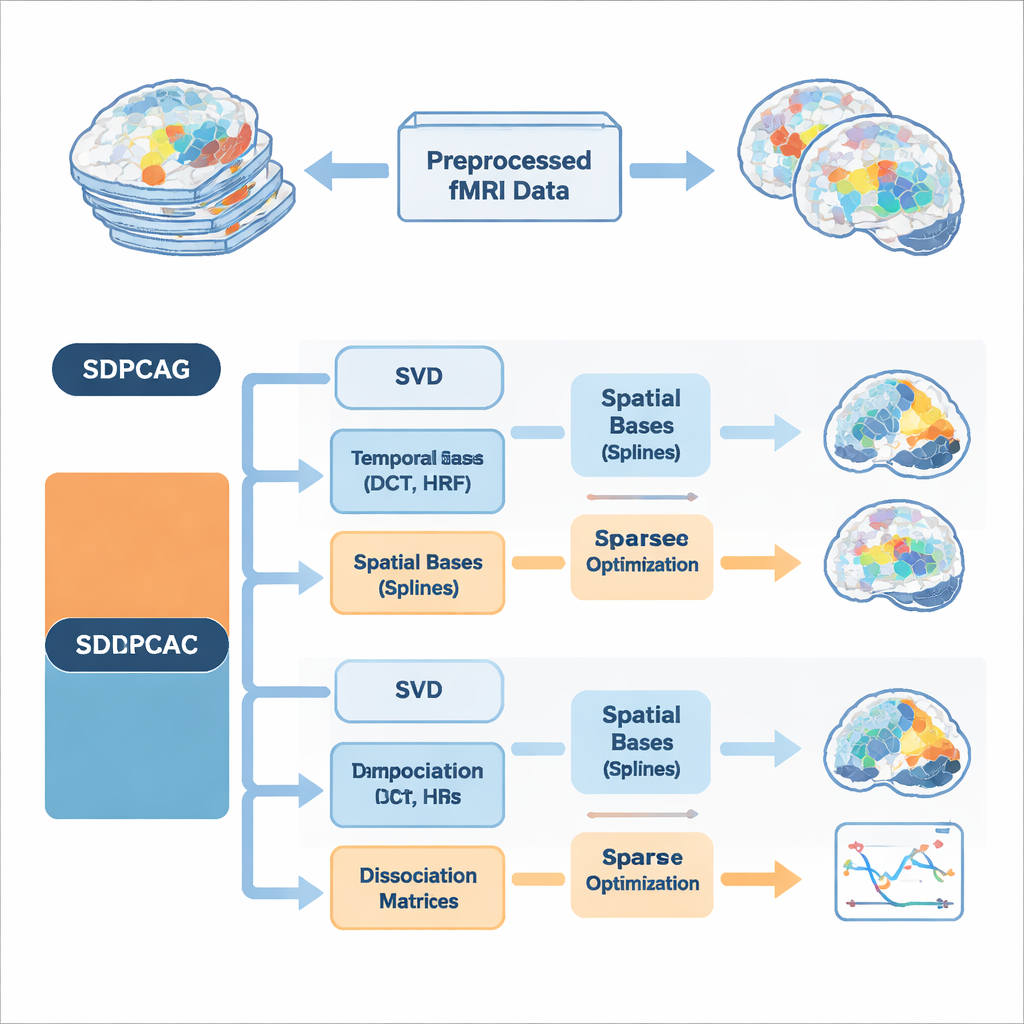
Gli autori propongono un quadro unificato chiamato PCA dissociativa strutturata, implementato in due algoritmi denominati SDPCAG e SDPCAC. Invece di trattare separatamente spazio e tempo, il metodo rimodella l’intero dataset fMRI mediante una singola decomposizione progettata con cura. Parte da una classica scomposizione a basso rango dei dati, poi introduce speciali matrici di “dissociazione” che ripesano e ruotano insieme sia le mappe spaziali sia i corsi temporali. Allo stesso tempo, rappresenta queste componenti usando insiemi di blocchi di costruzione lisci: onde temporali di tipo coseno, modelli della risposta emodinamica del cervello all’attività neurale e curve spaziali lisce chiamate spline. Imparando come combinare questi blocchi mantenendo la sparsità — conservando solo i pezzi più importanti — il metodo può districare reti sovrapposte senza imporre un’indipendenza irrealistica.
Integrare la conoscenza cerebrale fin dall’inizio
Un’innovazione chiave è che gli algoritmi incorporano la conoscenza a priori sui segnali cerebrali direttamente nella decomposizione, invece di ripulire i risultati a posteriori. Sul versante temporale, utilizzano funzioni discreto-coseno per favorire corsi temporali lisci e includono modelli standard della risposta emodinamica, il ritardo del segnale di ossigenazione del sangue misurato dalla fMRI. Sul versante spaziale, basi spline favoriscono pattern di attivazione contigui e coerenti invece di punti sparsi. Vincoli aggiuntivi limitano quante funzioni di base temporali e spaziali ogni componente può usare, riducendo l’overfitting al rumore e rispecchiando l’idea che le reti cerebrali reali siano relativamente compatte sia nello spazio sia nel tempo. Vengono presentate due strategie di ottimizzazione complementari: SDPCAG aggiorna intere matrici a blocchi, mentre SDPCAC affina una componente alla volta usando gli errori residui, scambiando un costo leggermente maggiore per aggiustamenti più flessibili.
Mettere il metodo alla prova
Per valutare l’efficacia di queste idee, gli autori eseguono test estesi su tre tipi di dati: segnali fMRI sintetici progettati con terreno noto; un esperimento motorio a disegno a blocchi del Human Connectome Project; e uno studio event-related di battito delle dita condotto da un laboratorio indipendente. In questi contesti confrontano SDPCAG e SDPCAC con le principali alternative che combinano decomposizione di matrici penalizzata, PCA sparsa, ICA e apprendimento di dizionari. Misurano quanto i corsi temporali recuperati corrispondono ai pattern noti delle attività, quanto le mappe spaziali si allineano con reti a riposo consolidate e quanto accuratamente le sorgenti vengono ricostruite a diversi livelli di rumore. I nuovi metodi producono in modo consistente mappe cerebrali più pulite e più localizzate e serie temporali meno rumorose, mantenendo prestazioni solide anche quando i dati sono fortemente corrotti. Uno degli algoritmi, SDPCAG, migliora l’accuratezza nel recupero delle sorgenti di circa il 22% rispetto a un forte metodo concorrente, oltre a essere più veloce del suo fratello più dettagliato SDPCAC.
Cosa significa per la ricerca sul cervello
In termini semplici, questo lavoro offre un modo migliore per “separare” i segnali all’interno dei dati fMRI. Modellando congiuntamente spazio e tempo, usando priori realistici sul comportamento dell’attività cerebrale e del flusso sanguigno e imponendo una sparsità intelligente, SDPCAG e SDPCAC producono reti cerebrali sia più nitide nelle immagini sia più fedeli ai rispettivi corsi temporali. Ciò può portare a una rilevazione più affidabile delle attivazioni legate a compiti e a una mappatura più precisa delle reti a riposo, supportando a sua volta studi su condizioni come l’Alzheimer, i disturbi psichiatrici e altre malattie cerebrali. Pur essendoci ancora margine per accelerare ed estendere l’approccio — per esempio a studi su più soggetti o all’imaging multimodale — rappresenta un passo significativo verso la trasformazione dei dati di scansioni ad alta dimensionalità in immagini attendibili e interpretabili del cervello umano in funzione.
Citazione: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Parole chiave: decomposizione del segnale fMRI, PCA sparsa, mappatura delle reti cerebrali, separazione cieca delle sorgenti, connettività a riposo