Clear Sky Science · it
Caratterizzazione genetica e analisi genetica basata sul sequenziamento dell’intero genoma dell’influenza B nella provincia di Shandong durante il periodo 2015–2024
Perché i virus influenzali locali contano per te
L’influenza stagionale viene spesso sottovalutata come malattia lieve, ma infetta silenziosamente centinaia di milioni di persone ogni anno e può essere letale, soprattutto per bambini e anziani. Questo studio traccia come un ramo della famiglia influenzale — l’influenza B — è cambiato in quasi un decennio nella provincia di Shandong, una regione costiera densamente popolata della Cina. Leggendo il codice genetico dei virus locali, i ricercatori mostrano quanto gli attuali vaccini corrispondano a ciò che circola realmente, quali fasce d’età sono maggiormente colpite e dove possono emergere segnali di resistenza ai farmaci.
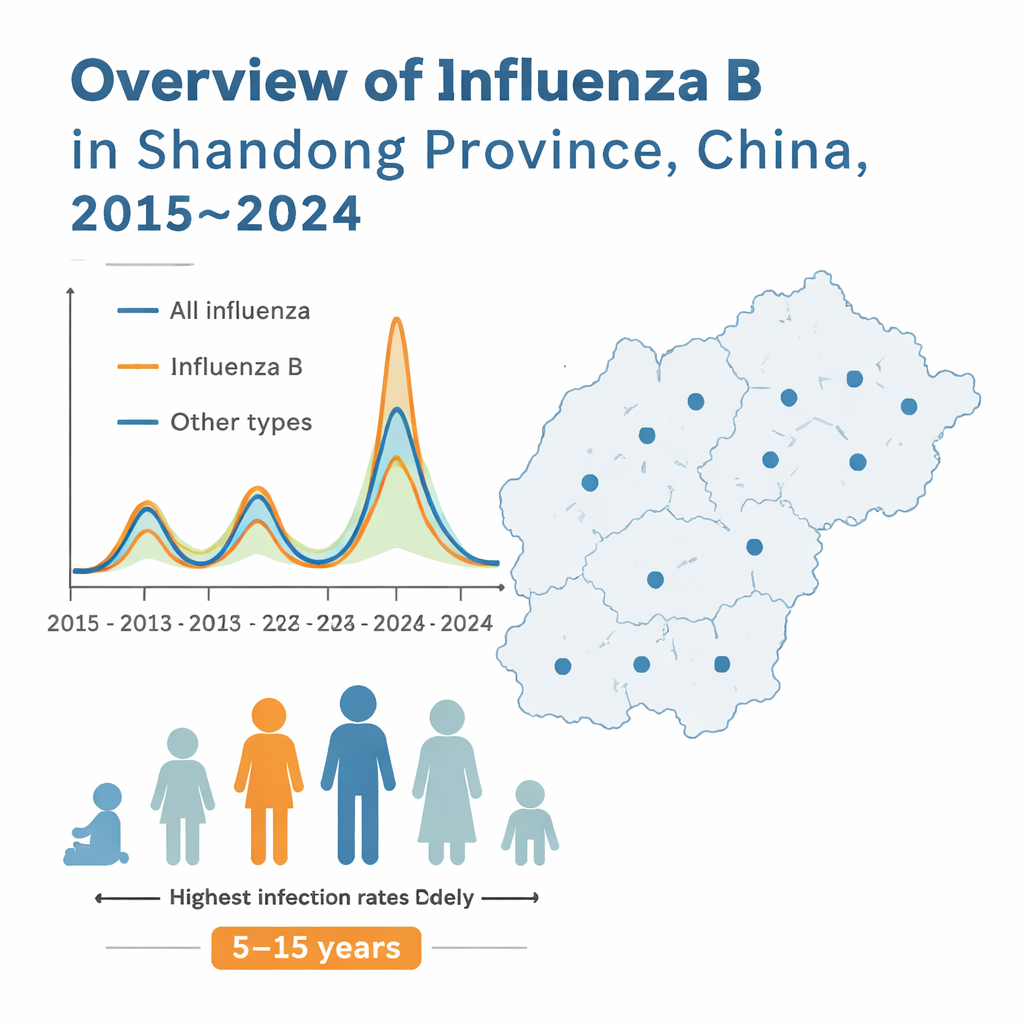
Osservare le ondate influenzali che attraversano una provincia
Tra il 2015 e l’inizio del 2024, gli ospedali di Shandong hanno raccolto tamponi faringei e nasali da quasi mezzo milione di persone con “sintomi simil-influenzali” (febbre più tosse o mal di gola). Circa una persona su otto risultò effettivamente infettata da un virus influenzale e approssimativamente un terzo di queste infezioni era causato dall’influenza B. L’attività influenzale raggiungeva solitamente il picco nei mesi freddi, ma il pattern fu interrotto durante il picco della pandemia di COVID-19, quando l’uso di mascherine e altre precauzioni ridusse le rilevazioni dell’influenza quasi a zero. Quando l’influenza tornava a farsi vedere, i bambini in età scolare tra i 5 e i 15 anni risultavano i più probabili positivi, mentre gli adulti oltre i 60 anni mostravano i tassi di rilevazione più bassi, evidenziando il ruolo dei bambini come principali motori della trasmissione comunitaria.
Due rami dell’influenza B e dominanza variabile
L’influenza B si presenta in due rami stabili nel tempo, denominati B/Victoria e B/Yamagata. Entrambi circolavano a Shandong all’inizio dello studio, ma il ramo Yamagata scomparve gradualmente dopo il 2018, rispecchiando tendenze osservate a livello globale. Da allora, quasi tutte le rilevazioni di influenza B nella provincia appartenevano al ramo Victoria. Il team ha selezionato 109 virus rappresentativi — 76 Victoria e 33 Yamagata — e ha letto la sequenza completa di tutti e otto i segmenti dei loro genomi a RNA. Queste sequenze sono state poi confrontate con i ceppi vaccinali raccomandati dall’Organizzazione Mondiale della Sanità per ogni anno, così come con virus di riferimento provenienti da tutto il mondo, per valutare quanto i virus locali seguissero l’evoluzione globale.
Piccoli cambiamenti genetici con grandi conseguenze
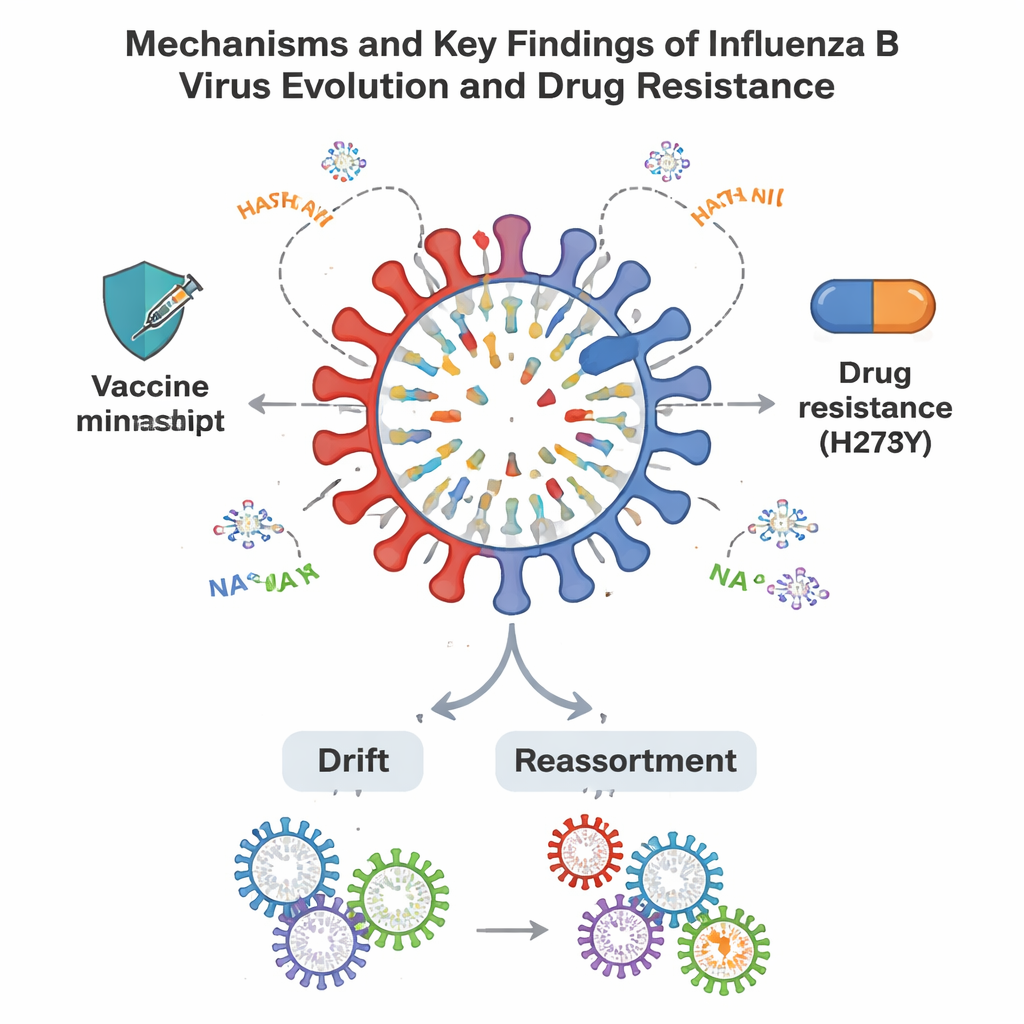
La maggior parte dei virus influenzali B di Shandong è rimasta strettamente correlata ai ceppi vaccinali, ma anno dopo anno hanno accumulato una serie di piccole mutazioni, specialmente in due proteine superficiali chiamate emoagglutinina (HA) e neuraminidasi (NA). Queste proteine si trovano sulla superficie del virus e sono i principali bersagli del nostro sistema immunitario e degli attuali antivirali. Lo studio ha riscontrato cambiamenti ripetuti in punti chiave (“hot spot”) di HA riconosciuti normalmente dagli anticorpi. In diversi periodi, gruppi di virus presentavano quattro o più variazioni in questi siti, sufficienti a essere considerati potenziali varianti da “deriva antigenica” in grado di ridurre la protezione vaccinale. Una mutazione nella posizione 197 di HA, che interessa sia un bersaglio immunitario sia la regione di legame al recettore, divenne particolarmente comune e rimosse anche un sito di glicosilazione — un legame di zucchero — che può modificare il modo in cui la proteina è riconosciuta dal sistema immunitario.
Miscele, ricombinazioni e resistenza ai farmaci
Oltre alla mutazione graduale, lo studio ha individuato segnali di rimescolamento genetico tra linee virali. Un virus B/Victoria presentava un gene interno proveniente dal ramo B/Yamagata, prova chiara di reassortimento — un processo in cui due virus co-infettano una cellula e si scambiano segmenti del genoma, potenzialmente creando nuovi varianti. I ricercatori hanno inoltre cercato mutazioni associate alla resistenza ai farmaci. Tra 109 virus, ne hanno trovato uno con una variazione chiamata H273Y nella proteina NA, nota per ridurre la sensibilità agli inibitori della neuraminidasi comunemente usati come l’oseltamivir; test di laboratorio hanno confermato una suscettibilità ridotta al farmaco. Altri geni interni mostravano mutazioni che potrebbero influenzare l’efficienza di replicazione del virus o la sua capacità di sfuggire alle prime risposte immunitarie, sebbene queste non indichino ancora una resistenza contro le nuove terapie antivirali orali che colpiscono la macchina della polimerasi.
Cosa significa per vaccini e prevenzione
Nel complesso, i virus di influenza B circolanti a Shandong dal 2015 al 2024 somigliavano ancora ai ceppi scelti per i vaccini stagionali, a sostegno del valore delle vaccinazioni annuali contro l’influenza. Tuttavia, l’accumulo costante di mutazioni in regioni chiave riconosciute dal sistema immunitario, la scomparsa di un’importante linea evolutiva, lo scambio occasionale di geni e la comparsa di un virus resistente ai farmaci indicano che l’influenza B è ben lontana dall’essere statica. Per il pubblico, il messaggio è semplice: la vaccinazione resta la migliore protezione, soprattutto per i bambini in età scolare che guidano gran parte della trasmissione. Per le autorità sanitarie, lo studio sottolinea la necessità di un monitoraggio genetico continuo dei virus influenzali locali, aggiornamenti regolari della composizione vaccinale e test vigili per la resistenza antivirale, in modo che trattamenti e strategie preventive tengano il passo con un nemico in continua evoluzione.
Citazione: Wu, J., He, Y., Sun, L. et al. Genetic characterization and whole-genome sequencing-based genetic analysis of influenza B in Shandong Province during 2015–2024. Sci Rep 16, 5229 (2026). https://doi.org/10.1038/s41598-026-35291-1
Parole chiave: influenza B, sorveglianza genomica, deriva antigenica, resistenza antivirale, efficacia del vaccino