Clear Sky Science · it
Analisi di DrugBank con apprendimento automatico rivela nuovi candidati per l'inibizione di BCL-2
Perché trovare farmaci antitumorali più intelligenti è importante
Le cellule tumorali spesso si rifiutano di morire quando dovrebbero. Molti tumori sopravvivono sovrautilizzando una famiglia di proteine «guardaspalle» chiamate BCL-2 che bloccano il programma di suicidio intrinseco della cellula. Esistono già farmaci che prendono di mira BCL-2, ma possono causare effetti collaterali e non funzionano per tutti i pazienti. Questo studio esplora come l'apprendimento automatico moderno possa setacciare migliaia di farmaci esistenti per trovare nuovi candidati più sicuri che possano disattivare BCL-2 e aiutare le cellule tumorali ad auto‑distruggersi.
Come le cellule scelgono tra vita e morte
I tessuti sani eliminano continuamente le cellule danneggiate o non necessarie tramite un processo controllato di auto‑distruzione noto come apoptosi, o morte cellulare programmata. Un gruppo di proteine chiamato famiglia BCL-2 funge da interruttore centrale per questa decisione. Alcuni membri spingono le cellule verso la sopravvivenza, mentre altri verso la morte. In molti tumori, i membri che favoriscono la sopravvivenza, inclusi BCL-2 e il suo stretto parente BCL-XL, sono prodotti in eccesso. Questa protezione aggiuntiva permette alle cellule tumorali di ignorare i segnali di morte e resistere alla chemioterapia. Per questo motivo, bloccare BCL-2 è diventata una strategia interessante nel trattamento del cancro, ma i farmaci attuali spesso colpiscono anche proteine affini, portando a effetti collaterali come pericolose riduzioni del numero di piastrine.
Insegnare ai computer a riconoscere le molecole promettenti
Invece di cercare nuovi composti da zero, i ricercatori si sono rivolti a banche dati di molecole già studiate o utilizzate come farmaci. Hanno cominciato con una grande risorsa pubblica chiamata ChEMBL, che contiene misurazioni sperimentali di quanto fortemente diversi composti chimici si leghino a BCL-2. Dopo aver pulito accuratamente queste informazioni—rimuovendo duplicati, misurazioni incerte e molecole eccessivamente grandi o insolite—sono rimasti con 601 composti ben caratterizzati. Ogni molecola è stata tradotta in una sorta di impronta digitale digitale che cattura le sue caratteristiche strutturali. Queste impronte sono state usate per addestrare e confrontare sette diversi modelli di apprendimento automatico nel compito di decidere se una nuova molecola è probabile che sia un forte inibitore di BCL-2 o essenzialmente inattiva. 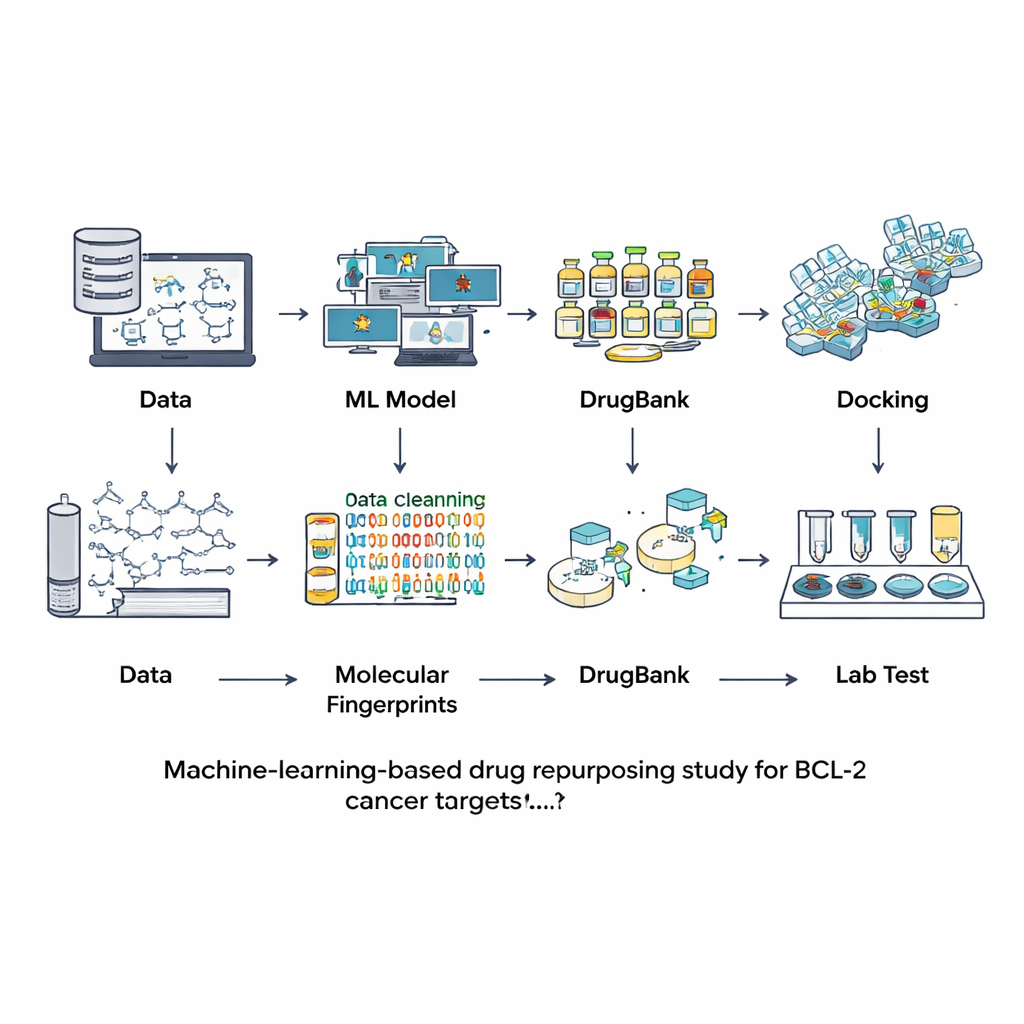
Scegliere il miglior modello e scandagliare una libreria di farmaci
Il team ha valutato i modelli usando un set di test separato che non era stato visto durante l'addestramento, controllando non solo quanto spesso ciascun modello era corretto, ma anche quanto bene distingueva gli attivi dagli inattivi e quanto bilanciate fossero le sue previsioni. Un modello chiamato LightGBM—un metodo moderno di boosting basato su alberi—ha ottenuto le migliori prestazioni nella maggior parte delle misure, inclusa l'accuratezza complessiva e la capacità di assegnare probabilità affidabili. Con questo modello ottimizzato, i ricercatori si sono rivolti a DrugBank, una raccolta curata di oltre 12.000 farmaci approvati, sperimentali e ritirati. Dopo aver calcolato lo stesso tipo di impronte, hanno chiesto a LightGBM quali di queste molecole sembrassero potenziali inibitori di BCL-2. Solo nove composti hanno ottenuto punteggi elevati, all'incirca il decimo di uno per cento dell'intera libreria, mostrando che lo screening virtuale era molto selettivo. Quattro dei nove erano già noti inibitori di BCL-2, rassicurando il team che l'approccio era valido.
Dai colpi informatici alle interazioni molecolari
Tra le restanti molecole con punteggi elevati, i ricercatori si sono concentrati su tre non precedentemente collegati a BCL-2: Dersalazine, Opelconazole e Zongertinib. Per verificare se questi candidati potessero plausibilmente inserirsi nella tasca di legame di BCL-2, hanno usato il docking computazionale, una tecnica che predice come una piccola molecola potrebbe adattarsi sulla superficie della proteina. Le simulazioni hanno suggerito che in particolare Opelconazole e Zongertinib formano reti di contatti favorevoli con gli stessi amminoacidi chiave che legano un farmaco di riferimento ben studiato, ABT-737. Le loro forze di legame predette erano vicine a quelle degli inibitori consolidati, suggerendo che il modello di apprendimento automatico aveva effettivamente individuato molecole capaci di disarmare BCL-2. 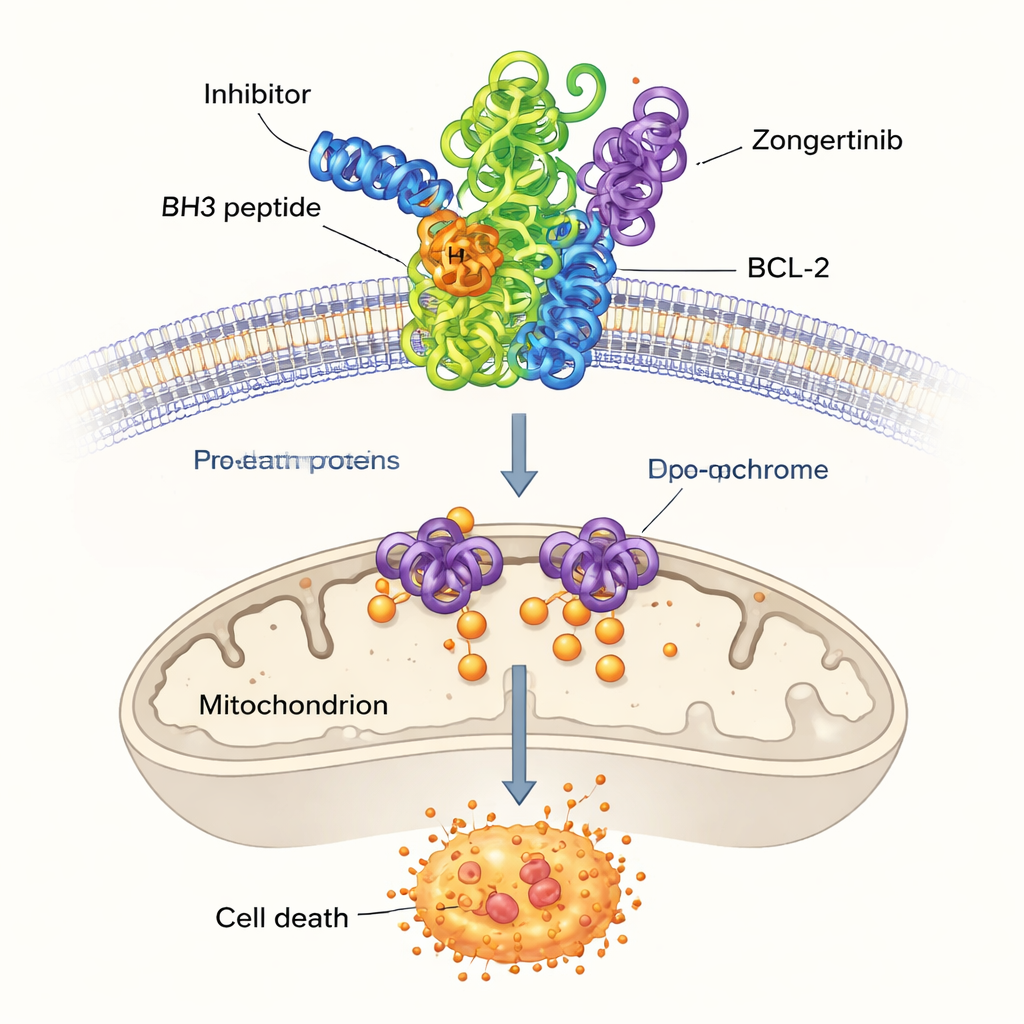
Mettere le previsioni alla prova in laboratorio
I suggerimenti computazionali sono utili solo se resistono alle condizioni del mondo reale. Il team ha quindi testato i tre candidati in un saggio biochimico che misura quanto bene un composto può impedire a BCL-2 di legarsi a uno dei suoi partner naturali. A diverse concentrazioni, Dersalazine ha mostrato scarso effetto. Opelconazole e Zongertinib, invece, hanno ridotto l'attività di BCL-2 a dosi elevate, con Opelconazole che ha quasi annullato il segnale. Sebbene queste concentrazioni siano superiori a quelle ideali per un farmaco pronto per la clinica, dimostrano che i candidati interagiscono realmente con BCL-2 e convalidano l'intera pipeline di scoperta.
Cosa significa per le terapie oncologiche future
Per un non specialista, il messaggio chiave è che i ricercatori sono riusciti ad addestrare un sistema informatico a riconoscere com'è fatto un bloccatore di BCL-2, quindi a usarlo per esplorare una grande libreria di farmaci e composti farmaco‑simili esistenti. L'approccio ha riscoperto farmaci noti per BCL-2 e ha messo in evidenza nuovi candidati, due dei quali hanno mostrato reale attività inibitoria nei test di laboratorio. Sebbene resti molto lavoro da fare—migliorare la potenza, comprendere la sicurezza e testare in cellule e modelli animali—questo studio dimostra come l'apprendimento automatico e una curata gestione dei dati possano accelerare la ricerca di farmaci antitumorali migliori riciclando e rivalutando composti già noti.
Citazione: Park, J., Cho, S., Lee, H. et al. DrugBank mining with machine learning reveals novel candidates for BCL-2 inhibition. Sci Rep 16, 5482 (2026). https://doi.org/10.1038/s41598-026-35117-0
Parole chiave: inibitori di BCL-2, apprendimento automatico, riutilizzo di farmaci, apoptosi, terapia antitumorale