Clear Sky Science · it
Diversità genetica di Pseudomonas aeruginosa isolata da campioni clinici con il marcatore molecolare ISSR in un ospedale universitario di cura terziaria
Perché i germi ospedalieri ci riguardano tutti
Chiunque abbia passato del tempo in ospedale — come paziente o in visita a una persona cara — fa affidamento sugli antibiotici quando servono davvero. Ma alcuni microrganismi stanno diventando così resistenti che anche i farmaci più potenti faticano a fermarli. Questo articolo esamina uno di questi problemi, un batterio chiamato Pseudomonas aeruginosa, e mostra come gli scienziati di un ospedale indiano abbiano mappato la sua varietà genetica nascosta per capire meglio perché sia così difficile da controllare.
Un nemico ostinato negli ospedali moderni
Pseudomonas aeruginosa è un avversario scivoloso. Prosperà in ambienti umidi, dai tubi dei ventilatori alle medicazioni, e colpisce soprattutto persone con difese abbassate per malattia, ustioni o degenze prolungate. Può causare gravi infezioni polmonari, ematiche, urinarie e delle ferite. Ciò che lo rende particolarmente pericoloso è la capacità di resistere a molti antibiotici contemporaneamente, trasformando infezioni di routine in crisi potenzialmente letali e aumentando costi e durata delle cure in tutto il mondo.
Guardare sotto la superficie dell’infezione
Per capire quanto fosse diversa questa popolazione batterica all’interno di un singolo ospedale, i ricercatori hanno raccolto 100 campioni batterici da sangue, urine, espettorato e tamponi di ferite prelevati durante le cure di routine in un grande ospedale universitario dell’India orientale. Si sono concentrati su 18 ceppi resistenti a più farmaci e hanno testato la reazione di ciascuno a un ampio pannello di antibiotici. Preoccupante è che oltre quattro campioni su cinque mostravano resistenza a farmaci chiave come cefoperazone, meropenem e imipenem — farmaci spesso riservati come opzioni di ultima istanza quando altri falliscono. Alcuni antibiotici, inclusi alcuni usati meno frequentemente, funzionavano ancora meglio, suggerendo scelte terapeutiche residue ma in restringimento. 
Leggere i “codici a barre” dei batteri
Contare gli antibiotici a cui i ceppi erano resistenti era solo metà della storia. Il team voleva anche sapere se queste infezioni provenissero da un unico “super ceppo” che si stava diffondendo nell’ospedale o da molte linee indipendenti arrivate e evolutesi separatamente. Per farlo hanno utilizzato un approccio di impronta genetica chiamato ISSR, che mette in evidenza gli intervalli di codice genetico compresi tra brevi sequenze ripetute. Dopo amplificazione con PCR e separazione su gel, questi frammenti formano un modello di bande che funziona come un codice a barre per ogni ceppo. Usando 17 primer informativi, i ricercatori hanno generato 95 bande di DNA distinte e poi confrontato i modelli tra tutti i 18 ceppi con strumenti informatici che raggruppano impronte simili.
Molti cugini lontani, non un unico superbatterio
I confronti genetici hanno rivelato che l’ospedale non stava affrontando un singolo clone fuori controllo. Al contrario, i ceppi sono ricaduti in diversi cluster distinti, con punteggi di somiglianza che andavano da parenti abbastanza vicini a cugini molto distanti. Alcuni isolati che si comportavano in modo simile nei test di sensibilità agli antibiotici si sono rivelati geneticamente diversi, mentre altri geneticamente correlati condividevano elementi di resistenza. Grafici di componenti principali e diagrammi ad albero hanno rafforzato l’idea di molteplici linee coesistenti nella stessa struttura piuttosto che di un ceppo dominante che si diffonde. Questa diversità probabilmente nasce dallo scambio di geni tra batteri, da mutazioni e dall’adattamento sotto continua esposizione agli antibiotici e al sistema immunitario umano. 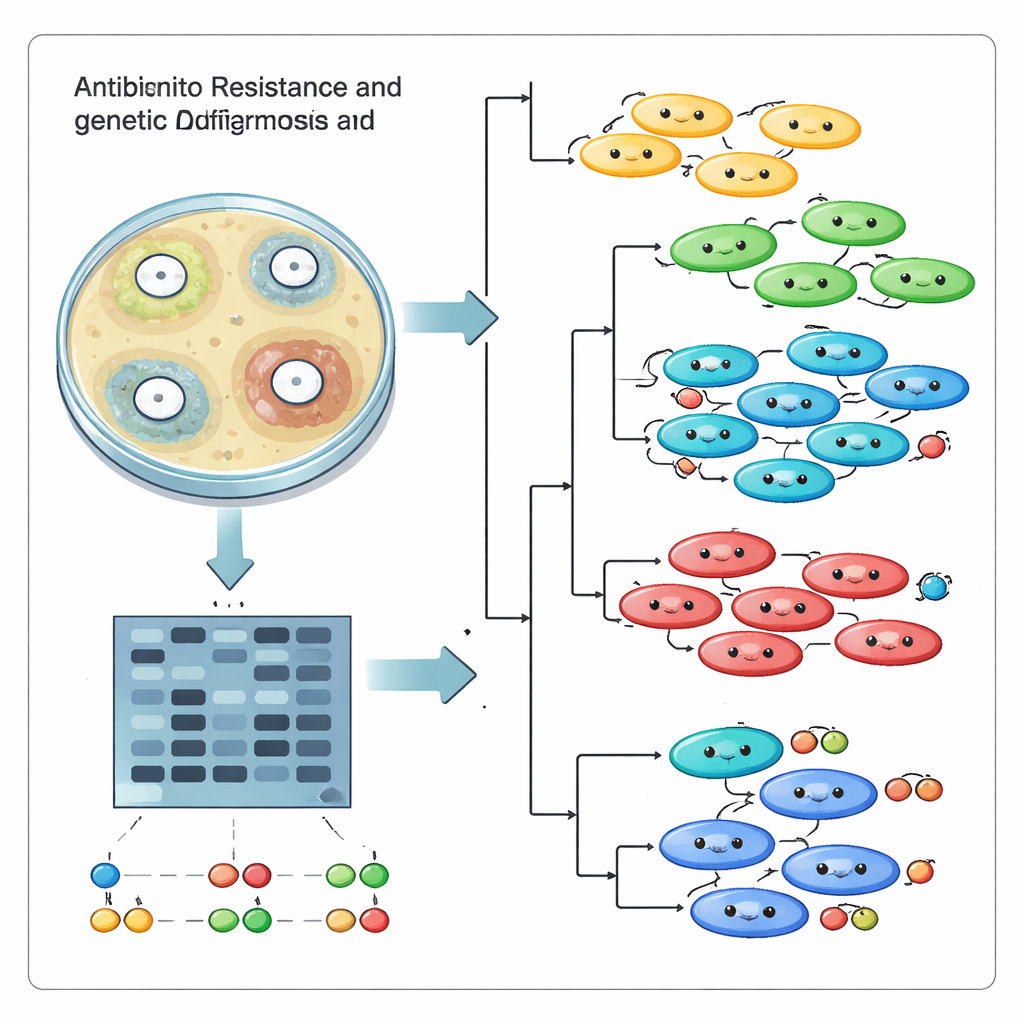
Cosa significa per pazienti e ospedali
Per gli ospedali, questi risultati portano un messaggio chiaro: monitorare solo gli antibiotici a cui si va incontro non è sufficiente. Poiché ceppi geneticamente distinti possono condividere pattern di resistenza simili — e ceppi strettamente correlati possono comportarsi in modo diverso — le équipe sanitarie hanno bisogno sia di test di routine sulla suscettibilità agli antibiotici sia di sorveglianza genetica periodica per osservare come la popolazione batterica cambia nel tempo. L’approccio ISSR usato qui è relativamente semplice e a basso costo, rendendolo interessante per contesti con risorse limitate, sebbene gli autori sottolineino che integrarlo con il sequenziamento dell’intero genoma in studi futuri fornirebbe un quadro più completo.
Un paesaggio nascosto che richiede vigilanza
In termini semplici, questo studio mostra che all’interno di un singolo ospedale Pseudomonas aeruginosa non è un unico nemico ma una folla di individui correlati ma distinti, molti già armati contro più antibiotici. Tracciando questo paesaggio nascosto di diversità, i ricercatori forniscono strumenti e conoscenze che possono aiutare i medici a scegliere terapie più mirate e le squadre di controllo delle infezioni a progettare strategie di contenimento più intelligenti. Un monitoraggio continuo di questi schemi genetici sarà essenziale per restare un passo avanti a questo microrganismo adattabile e per mantenere sicure le cure ospedaliere per i pazienti.
Citazione: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Parole chiave: Pseudomonas aeruginosa, resistenza agli antibiotici, infezioni ospedaliere, diversità genetica, tipizzazione molecolare