Clear Sky Science · it
HMI-LUSC: Un dataset di imaging iperspettrale istologico per il carcinoma squamoso polmonare
Vedere il cancro con nuovi colori
Il cancro polmonare resta una delle malattie più letali al mondo, in parte perché individuare ogni singola cellula cancerosa su un vetrino al microscopio è difficile e richiede tempo. I patologi si affidano di solito a tessuti colorati in rosa e viola osservati al microscopio, un metodo che cattura la struttura ma perde indizi chimici sottili. Questo articolo presenta HMI-LUSC, la prima collezione di immagini microscopiche di carcinoma squamoso polmonare messa a disposizione pubblicamente e acquisita non solo in tre colori, ma in dozzine di bande cromatiche strette, offrendo a computer e clinici una visione molto più ricca di ciò che rende le cellule tumorali diverse dai tessuti sani circostanti.
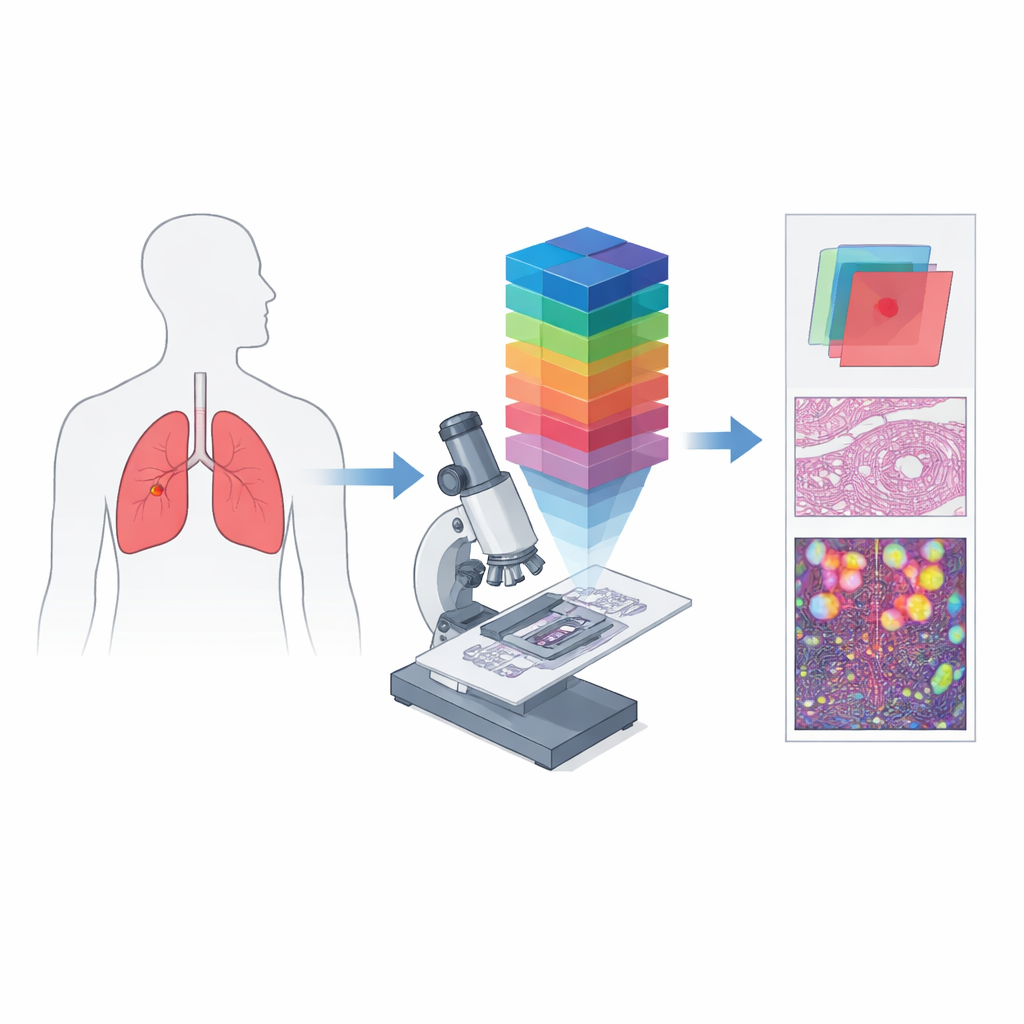
Dalle semplici fotografie a impronte spettrali
La patologia digitale convenzionale funziona in modo simile alla fotocamera di uno smartphone: registra canali rosso, verde e blu per approssimare ciò che l’occhio vede. L’imaging iperspettrale fa diversi passi avanti dividendo la luce in molte lunghezze d’onda ravvicinate, producendo un “cubo di dati” tridimensionale in cui ogni piccolo punto di tessuto ha il proprio spettro di colore dettagliato. Quando questa idea viene combinata con un microscopio, si ottiene l’imaging microscopico iperspettrale, in grado di catturare sia la struttura fine sia informazioni spettrali ricche a livello delle singole cellule. Questi dati possono rivelare differenze nel modo in cui i tessuti assorbono e riflettono la luce, invisibili nelle immagini standard, creando «firme» spettrali uniche per le regioni cancerose e non cancerose.
Costruire una nuova libreria per lo studio del cancro polmonare
Gli autori hanno creato HMI-LUSC per colmare una lacuna evidente: prima di questo lavoro non esisteva un dataset iperspettrale pubblico per i vetrini di cancro polmonare, il che rendeva difficile testare e confrontare metodi diagnostici basati su computer. Hanno raccolto tessuto da dieci pazienti sottoposti a intervento per tumore polmonare, preparato vetrini standard colorati con ematossilina-eosina e li hanno scansionati ad alta risoluzione. Patologi esperti hanno marcato le aree tumorali e normali, e aree rappresentative sono state riesaminate con un microscopio iperspettrale costruito su misura. Ogni immagine risultante copre una piccola porzione di tessuto ma si estende su 61 lunghezze d’onda tra 450 e 750 nanometri, con una risoluzione di 3088 per 2064 pixel. Per ogni regione, il dataset include il cubo spettrale grezzo, una resa RGB convenzionale e le maschere che delineano dove è presente tessuto tumorale.
Trasformare contorni grossolani in mappe a livello cellulare
Se le marcature a livello di vetrino sono utili, l’addestramento degli algoritmi moderni richiede spesso informazioni a livello delle singole cellule. Tracciare manualmente ogni cellula è impraticabile, così il team ha progettato un flusso di lavoro semi-automatico. Prima hanno raggruppato i pixel in cluster basati sulla loro similitudine spettrale usando un metodo standard di visione artificiale. Poi i patologi hanno ispezionato questi cluster sovrapposti all’immagine del tessuto e li hanno assegnati a quattro categorie: cellule tumorali, cellule non tumorali, tessuto non cellulare come stroma o sangue, e sfondo vuoto. Un secondo patologo ha revisionato e aggiustato questi risultati, risolvendo i disaccordi per consenso. Il risultato è un insieme di maschere dettagliate a livello di pixel che catturano sottili miscele di tipi cellulari e zone di confine ambigue, fornendo materiale didattico molto più ricco per i sistemi di apprendimento automatico.
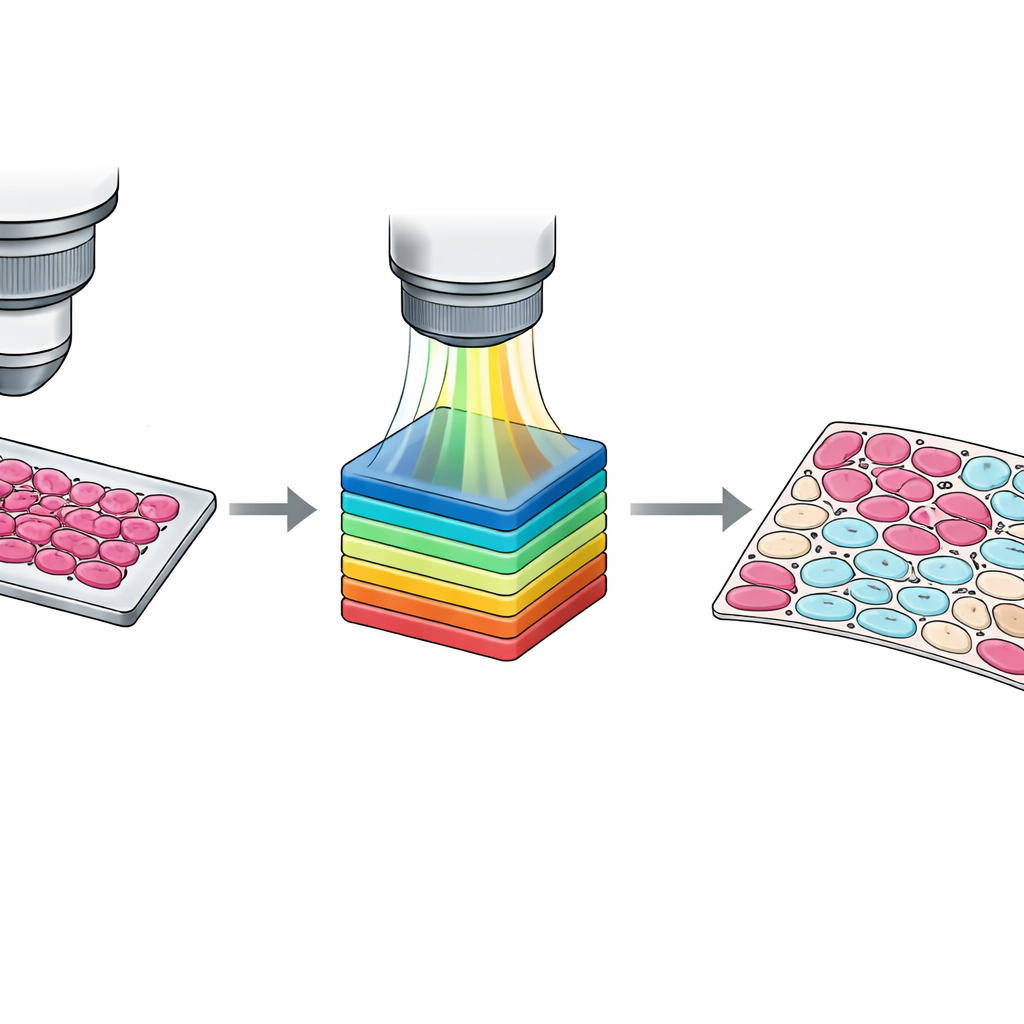
Garantire dati nitidi e affidabili
Per rendere il dataset affidabile, gli autori hanno testato a fondo il loro sistema di imaging. Hanno verificato che il microscopio possa risolvere pattern fini fino a circa un micron — abbastanza piccolo da distinguere singole cellule — e che il rumore di immagine sia basso sulla maggior parte delle lunghezze d’onda. Hanno inoltre confrontato lo spettro misurato di una sorgente luminosa standard con curve di riferimento e con una camera iperspettrale commerciale, riscontrando un eccellente accordo. Infine, hanno dimostrato come i dati possano essere usati eseguendo modelli di base, da metodi classici di machine learning a semplici reti di deep learning, per segmentare le regioni tumorali. Anche senza ampia ottimizzazione, questi modelli hanno raggiunto una buona accuratezza, dimostrando che il dataset è adatto come benchmark per metodi futuri.
Cosa significa per il futuro della cura del cancro polmonare
HMI-LUSC non sostituisce ampie collezioni di vetrini standard, né è ancora uno strumento clinico a sé stante. Offre invece ai ricercatori una finestra accuratamente curata su come le cellule tumorali polmonari differiscono dal tessuto vicino attraverso molte lunghezze d’onda della luce. Rendendo questi dati, etichette e codice disponibili pubblicamente, gli autori forniscono un terreno comune per sviluppare e confrontare algoritmi che sfruttano informazioni spettrali, da semplici classificatori a reti neurali avanzate. Nel lungo periodo, questo lavoro potrebbe aiutare i computer ad assistere i patologi nell’individuare i tumori in modo più accurato e rapido, e potrebbe rivelare pattern spettrali legati al tipo di tumore o alla risposta al trattamento che le immagini ordinarie non possono mostrare.
Citazione: Yan, Z., Huang, H., Guo, Y. et al. HMI-LUSC: A Histological Hyperspectral Imaging Dataset for Lung Squamous Cell Carcinoma. Sci Data 13, 415 (2026). https://doi.org/10.1038/s41597-026-06766-7
Parole chiave: imaging iperspettrale, cancro ai polmoni, patologia digitale, segmentazione del tumore, dataset di imaging medico