Clear Sky Science · it
Un ampio set di immagini di sangue periferico per l'analisi ematologica automatizzata
Perché contano le immagini delle cellule del sangue
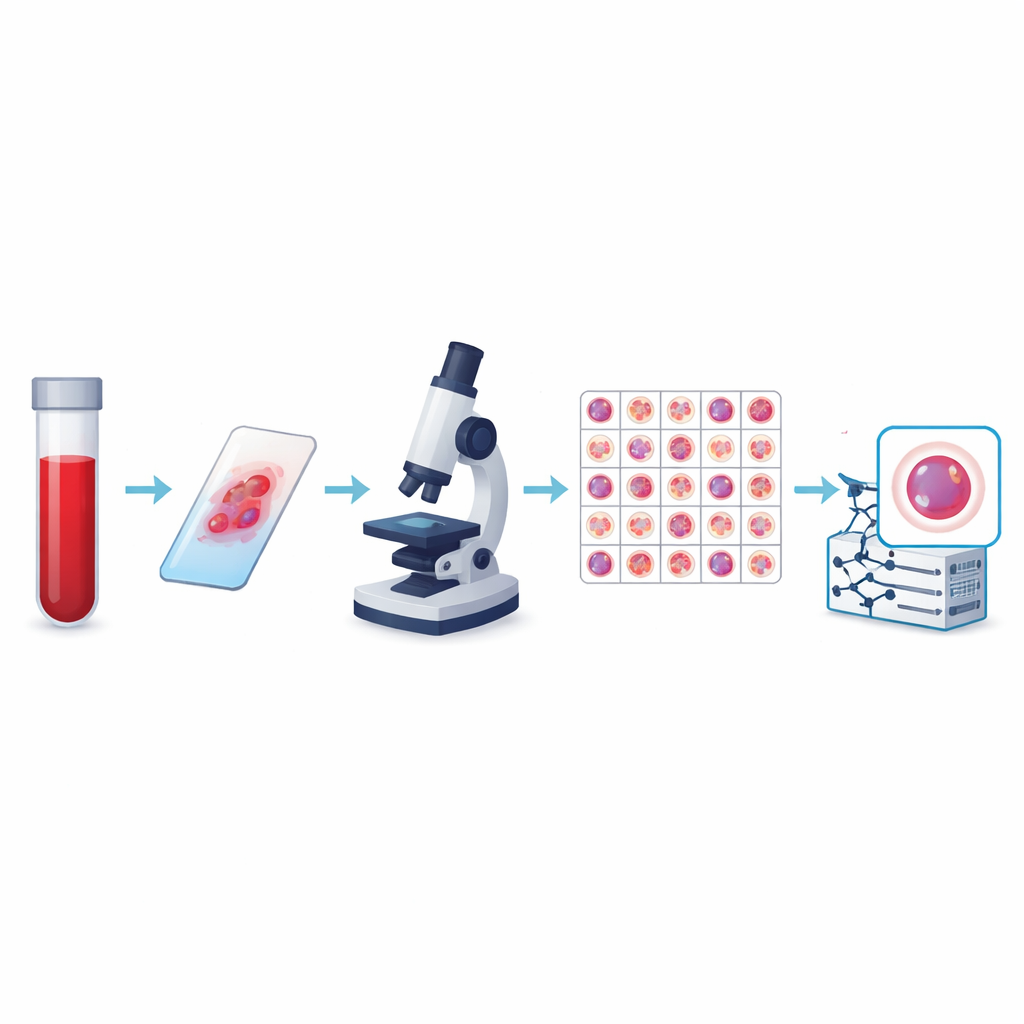
Ogni comune esame del sangue nasconde un mondo microscopico di cellule che può rivelare infezioni, anemia o persino tumori del sangue molto prima che i sintomi diventino evidenti. I medici tradizionalmente inspezzionano queste cellule a occhio al microscopio, un lavoro accurato ma che richiede tempo. Questo studio presenta una raccolta molto ampia e attentamente annotata di immagini di cellule del sangue pensata per insegnare ai computer a riconoscerle automaticamente. L'obiettivo è rendere i futuri esami del sangue più rapidi, coerenti e più accessibili, fornendo all'intelligenza artificiale l'esperienza visiva necessaria per aiutare i medici a interpretare gli strisci ematici con precisione.
Dalle semplici conte ai sistemi di imaging intelligenti
I globuli bianchi sono difensori chiave del nostro sistema immunitario, e la loro composizione e apparenza forniscono indizi cruciali sullo stato di salute. Un aumento di alcuni tipi cellulari può segnalare infezione o allergia, mentre la comparsa improvvisa di cellule immature dette “blasti” può avvertire della leucemia. I laboratori già impiegano macchine automatiche per il conteggio, ma i cambiamenti sottili nella forma spesso richiedono ancora l'occhio dell'esperto. I revisori umani possono non essere d'accordo, e l'esame delle vetrini uno per uno richiede tempo. Con la medicina che si orienta sempre più verso l'imaging digitale e l'intelligenza artificiale, cresce la necessità di grandi collezioni di immagini affidabili che possano addestrare i computer a individuare questi schemi cellulari con la stessa affidabilità di un ematologo esperto.
Costruire una grande libreria di cellule del sangue
Gli autori hanno creato quella che è attualmente la più grande collezione pubblica di immagini di cellule del sangue periferico, chiamata dataset KU-Optofil PBC. Contiene 31.489 immagini ad alta risoluzione di singole cellule suddivise in 13 gruppi, includendo difensori comuni come linfociti e neutrofili segmentati, oltre a tipi più rari ma clinicamente critici come blasti, mielociti e linfociti reattivi. Tutte le immagini provengono da strisci di sangue colorati preparati in condizioni standardizzate in un unico ospedale utilizzando lo stesso sistema di imaging. Questa coerenza significa che i computer che apprendono dai dati vedono una rappresentazione stabile e ben controllata di ciascun tipo cellulare anziché un mosaico di immagini incompatibili.
Occhi esperti e cura nella selezione
Per rendere il dataset affidabile, ogni immagine è stata etichettata indipendentemente da due tecnici di laboratorio esperti, con un terzo esperto che ha risolto eventuali disaccordi. Controlli statistici hanno mostrato un accordo molto elevato tra i revisori per ogni tipo cellulare principale, incluso un accordo perfetto per alcuni. Il team ha anche applicato regole severe per decidere quali immagini conservare, scartando cellule sfocate, sovrapposte o mal colorate. Le immagini finali hanno tutte la stessa dimensione e formato colore, e sono organizzate in cartelle di training, validation e test in modo che altri ricercatori possano confrontare gli algoritmi in modo equo. File aggiuntivi collegano ogni immagine a un paziente anonimo, permettendo studi che valutino se un modello si generalizza veramente da una persona all'altra.
Mettendo alla prova i modelli di IA
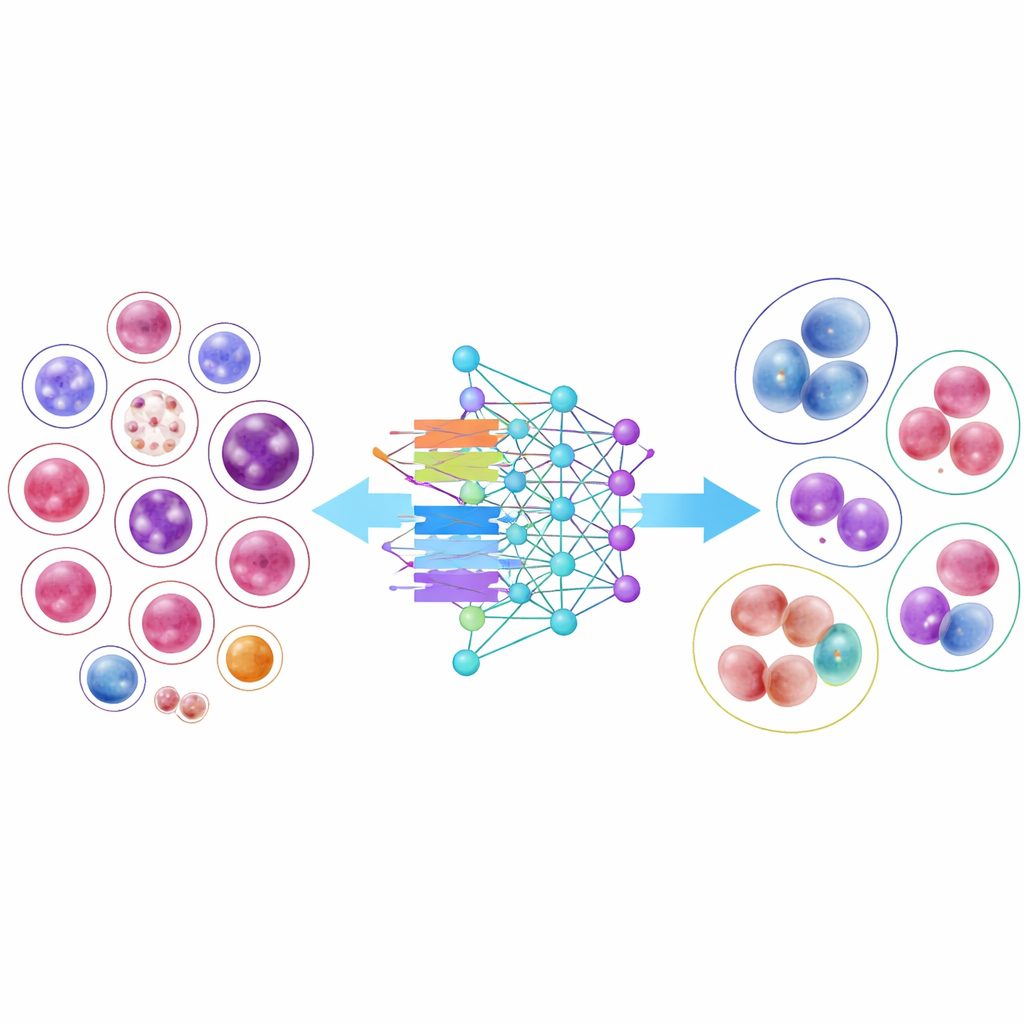
Per dimostrare l'utilità di questa libreria, i ricercatori hanno addestrato 14 modelli moderni di riconoscimento delle immagini, dalle reti neurali convoluzionali classiche a progettazioni più recenti basate su transformer. Diversi modelli compatti ed efficienti hanno ottenuto risultati sorprendentemente buoni, e un'architettura in particolare, DenseNet-121, ha classificato correttamente le cellule in più del 95 percento dei casi in media. Tuttavia, i risultati hanno anche evidenziato una difficoltà concreta: i tipi cellulari comuni con migliaia di esempi venivano riconosciuti quasi perfettamente, mentre le cellule molto rare, con solo poche decine di immagini, restavano molto più difficili da classificare. Anche quando i ricercatori hanno adattato l'addestramento per "prestare più attenzione" a queste classi scarse, l'accuratezza complessiva è diminuita e i guadagni per i tipi rari sono stati modesti, sottolineando la sfida di apprendere da esempi limitati.
Cosa significa per i futuri esami del sangue
Per i non specialisti, il messaggio principale è che questo lavoro fornisce l'esperienza visiva grezza di cui i sistemi informatici hanno bisogno per diventare partner affidabili nella lettura degli strisci ematici. Assemblando una libreria ampia, diversificata e accuratamente controllata di immagini di cellule del sangue e dimostrando che molti modelli di IA diversi possono apprendere da essa, gli autori gettano le basi per strumenti che potrebbero accelerare la diagnosi, ridurre l'errore umano ed estendere l'analisi di livello esperto a cliniche con meno specialisti. Allo stesso tempo, i risultati misti sui tipi cellulari rari ci ricordano che anche i grandi dataset hanno punti ciechi, e che migliorare la cura dei pazienti con malattie insolite o in stadio precoce richiederà di espandere e affinare ulteriormente queste raccolte di immagini.
Citazione: Yarıkan, A.E., Örer, C., Akyıldız, V. et al. A Large-Scale Peripheral Blood Cell Dataset for Automated Hematological Analysis. Sci Data 13, 417 (2026). https://doi.org/10.1038/s41597-026-06761-y
Parole chiave: immagini di cellule del sangue, IA medica, ematologia, deep learning, dataset medici