Clear Sky Science · it
Sequenziamento del genoma, assemblaggio de novo e annotazione del bambù di rilevanza commerciale, Bambusa tulda Roxb
Un’erba a crescita rapida con grande potenziale
Il bambù può sembrare una semplice pianta da giardino, ma in realtà è una potente risorsa naturale per l’edilizia, la carta e persino potenziali biocarburanti futuri. Una specie ampiamente impiegata, Bambusa tulda o bambù del Bengala, cresce rapidamente, accumula grandi quantità di materiale legnoso e fiorisce solo di rado. Fino ad oggi, gli scienziati non disponevano di un “manuale di istruzioni” completo per questa specie. Questo articolo descrive come i ricercatori hanno decodificato e organizzato l’intera sequenza del DNA di B. tulda, creando una risorsa fondamentale che aiuterà a migliorare il bambù per l’industria, la conservazione e le tecnologie a basso impatto climatico.
Perché decodificare il DNA di un bambù?
Bambusa tulda è comune nel subcontinente indiano e in parti del Sud-est asiatico, dove i suoi culmi (fusti) robusti sono usati nelle costruzioni rurali, nei mobili e negli oggetti artigianali. Sta inoltre suscitando interesse come fonte di polpa per carta ed energia rinnovabile. Tuttavia B. tulda si comporta in modo sorprendente: può crescere molto in fretta, accumulare molto materiale legnoso resistente e poi attendere circa 50 anni prima di fiorire, talvolta con tutte le piante di un’area che fioriscono simultaneamente. Senza una sequenza genomica completa, gli scienziati potevano solo ipotizzare quali geni controllino questi tratti. Leggendo e assemblando il suo DNA, gli autori hanno voluto costruire una mappa di riferimento che i futuri ricercatori potranno usare per studiare crescita, fioritura, resistenza alle malattie e altro ancora.
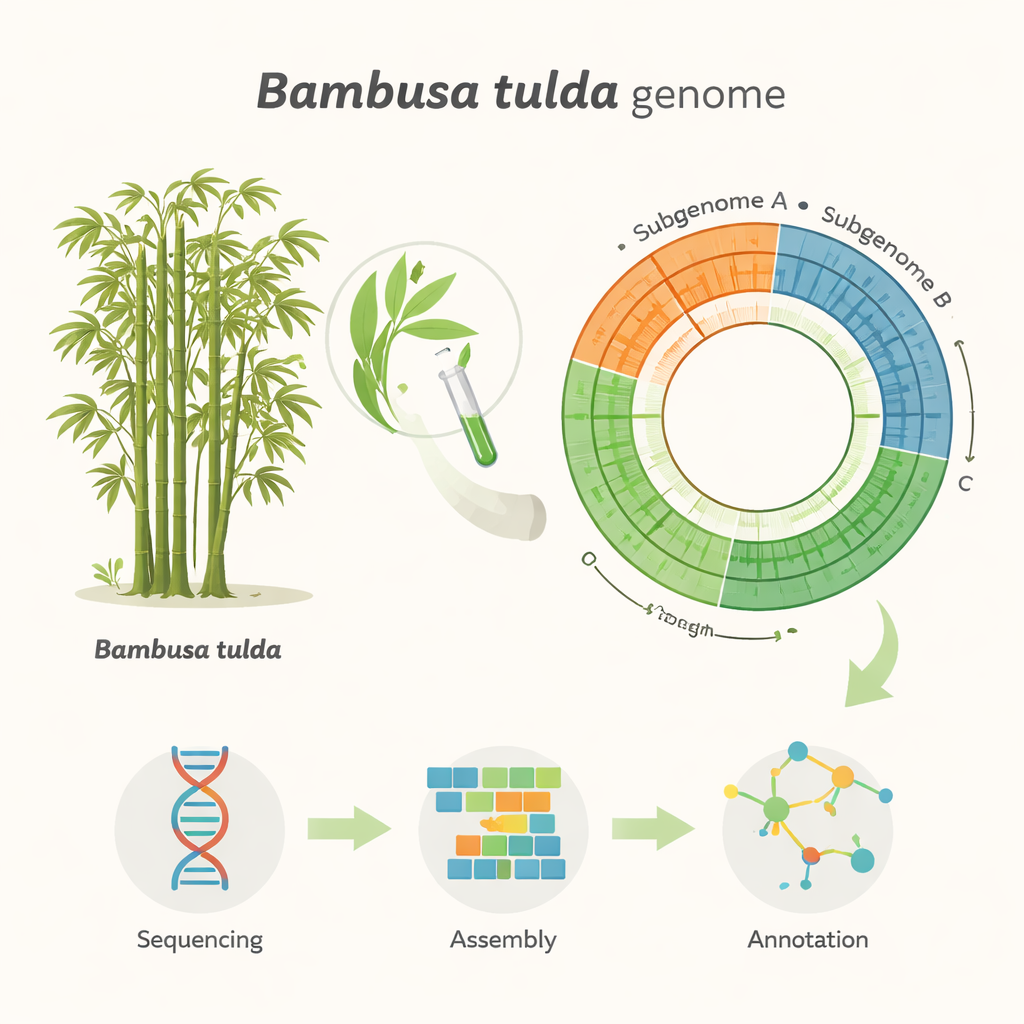
Misurare e leggere un genoma gigante
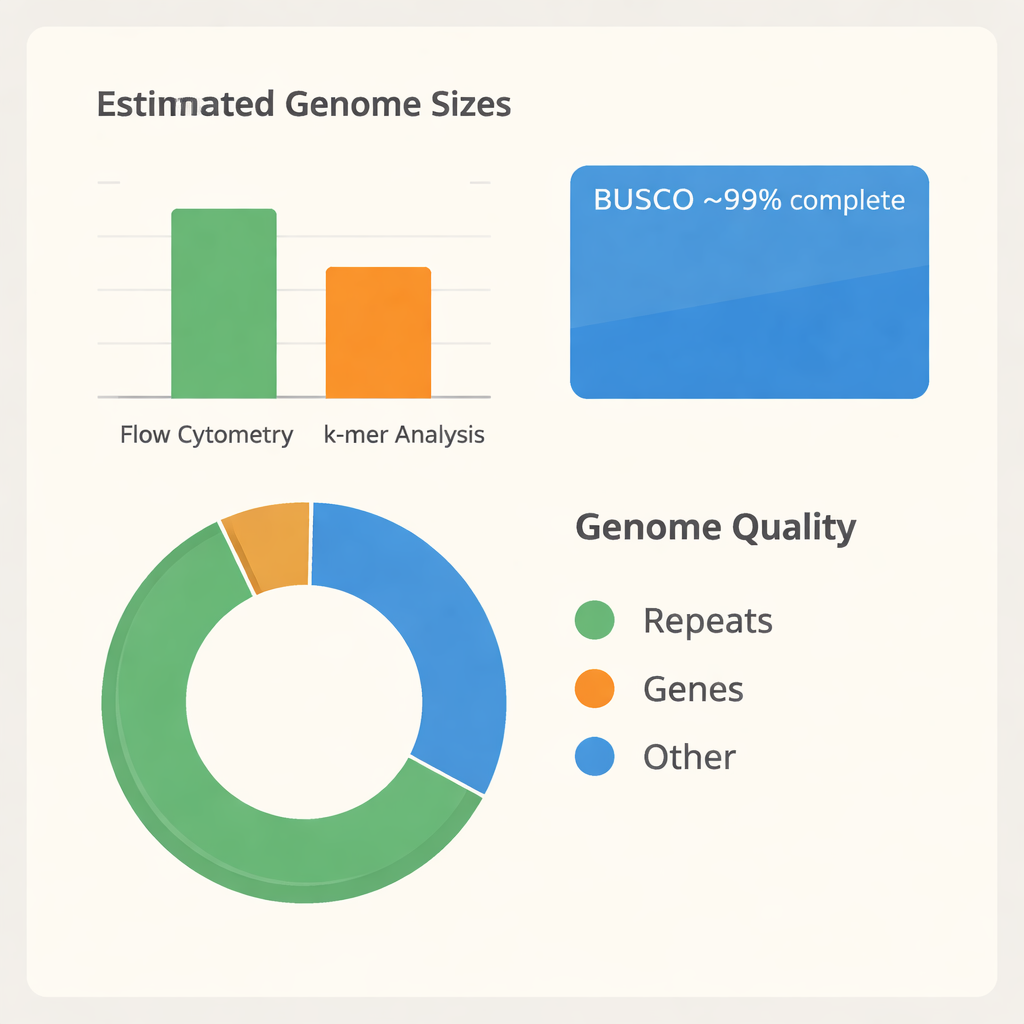
Il gruppo doveva innanzitutto capire quanto fosse grande il genoma di B. tulda. Utilizzando una tecnica chiamata citometria a flusso, hanno confrontato il contenuto di DNA delle cellule fogliari di B. tulda con quello di pomodoro e mais, due piante con dimensioni genomiche già note. Questo ha suggerito una dimensione del genoma diploide di circa 3 miliardi di “lettere” del DNA. Hanno poi impiegato un secondo approccio indipendente basato sul modo in cui frammenti corti di DNA si sovrappongono (analisi dei k-mer), che ha stimato una dimensione leggermente inferiore, di circa 2,34 miliardi di lettere, e ha rivelato che gran parte del genoma è ripetitiva e probabilmente duplicata. Con queste misure, hanno estratto DNA molto lungo e di alta qualità da foglie giovani e lo hanno sequenziato usando la tecnologia avanzata PacBio HiFi, generando oltre 116 miliardi di basi di dati grezzi — sufficienti a leggere il genoma dozzine di volte.
Ricomporre il progetto del bambù
Trasformare milioni di letture di DNA in un genoma ordinato è come assemblare un enorme puzzle senza l’immagine sulla scatola. I ricercatori hanno usato software specializzati per costruire sia un’assemblaggio primario combinato sia due aplotipi separati, che riflettono le due copie parentali del genoma. Dopo aver rimosso pezzi duplicati e derivanti da organelli, sono giunti a un assemblaggio “aploide” snello di 43 grandi segmenti, che coprono circa 1,37 miliardi di basi. Questi segmenti ricadono in tre subgenomi, etichettati A, B e C, coerenti con l’origine complessa e poliploide di B. tulda. Un test di qualità ampiamente usato chiamato BUSCO ha mostrato che circa il 99% dei geni vegetali attesi è presente e intatto, indicando che l’assemblaggio è sia completo sia affidabile per studi successivi.
Geni, ripetizioni e indizi evolutivi
Una volta assemblato il genoma, il passo successivo è stato identificare le sue parti funzionali. Combinando tre linee di evidenza — predizioni dalla sequenza di DNA stessa, somiglianze con geni di altri bambù e dati di RNA di geni attivamente espressi — il team ha annotato 56.890 geni codificanti proteine, che occupano circa un quinto del genoma. Hanno anche catalogato un grande numero di RNA non codificanti, inclusi oltre mille geni per RNA transfer e RNA ribosomali che supportano la produzione proteica. In modo sorprendente, circa due terzi del genoma è costituito da elementi ripetitivi, in particolare segmenti di DNA mobili che si copiano e si spostano. Queste ripetizioni aiutano a spiegare perché le stime precedenti della dimensione differivano e indicano una storia evolutiva dinamica. Il confronto delle famiglie proteiche tra altre dodici specie di bambù, insieme a mais e banana come parenti, colloca B. tulda saldamente tra i bambù legnosi paleotropici con uno sfondo esa-ploidico, confermando che il suo genoma è costruito da più copie ancestrali.
Una nuova base per la ricerca futura sul bambù
Per i non specialisti, il risultato chiave è che B. tulda dispone ora di un genoma di riferimento di alta qualità — un progetto indicizzato e ricercabile del suo DNA. Questa risorsa permetterà agli scienziati di individuare i geni che controllano la crescita rapida, la lignificazione e la fioritura ritardata, e di confrontarli con quelli di altre graminacee. Sosterrà inoltre gli sforzi per selezionare o ingegnerizzare varietà di bambù più adatte all’edilizia, alla produzione di carta o all’energia, preservando al contempo le popolazioni naturali. In breve, tracciando il paesaggio genetico di questo bambù di rilevanza commerciale, lo studio pone le basi per un uso più intelligente di una delle piante più versatili al mondo.
Citazione: Kundu, S., Rupp, O., Dey, S. et al. Genome sequencing, de novo assembly and annotation of the commercially important bamboo, Bambusa tulda Roxb. Sci Data 13, 175 (2026). https://doi.org/10.1038/s41597-026-06679-5
Parole chiave: genoma del bambù, Bambusa tulda, genetica delle piante, erbacee legnose, biomateriali rinnovabili