Clear Sky Science · it
Grande dataset di immagini istologiche con metadati per il microambiente del cancro colorettale
Perché mappare il quartiere nascosto del cancro è importante
Quando i medici osservano un tumore del colon al microscopio, non vedono solo cellule tumorali; vedono un quartiere animato di tessuto adiposo, cellule immunitarie, tessuto connettivo e altro ancora. Questa miscela di tipi cellulari, chiamata microambiente tumorale, influisce fortemente su come un paziente risponde alle terapie e sulla sua prognosi. Tuttavia, i computer che potrebbero aiutare i medici a interpretare queste scene complesse sono stati ostacolati da un problema semplice: non disponevano di immagini ben annotate in numero sufficiente per apprendere. Questo studio presenta una delle raccolte di immagini di tessuto colorettale più grandi e accuratamente annotate mai assemblate, pensata appositamente per addestrare e testare i moderni sistemi di intelligenza artificiale.
Costruire una grande libreria di immagini di tumori del colon
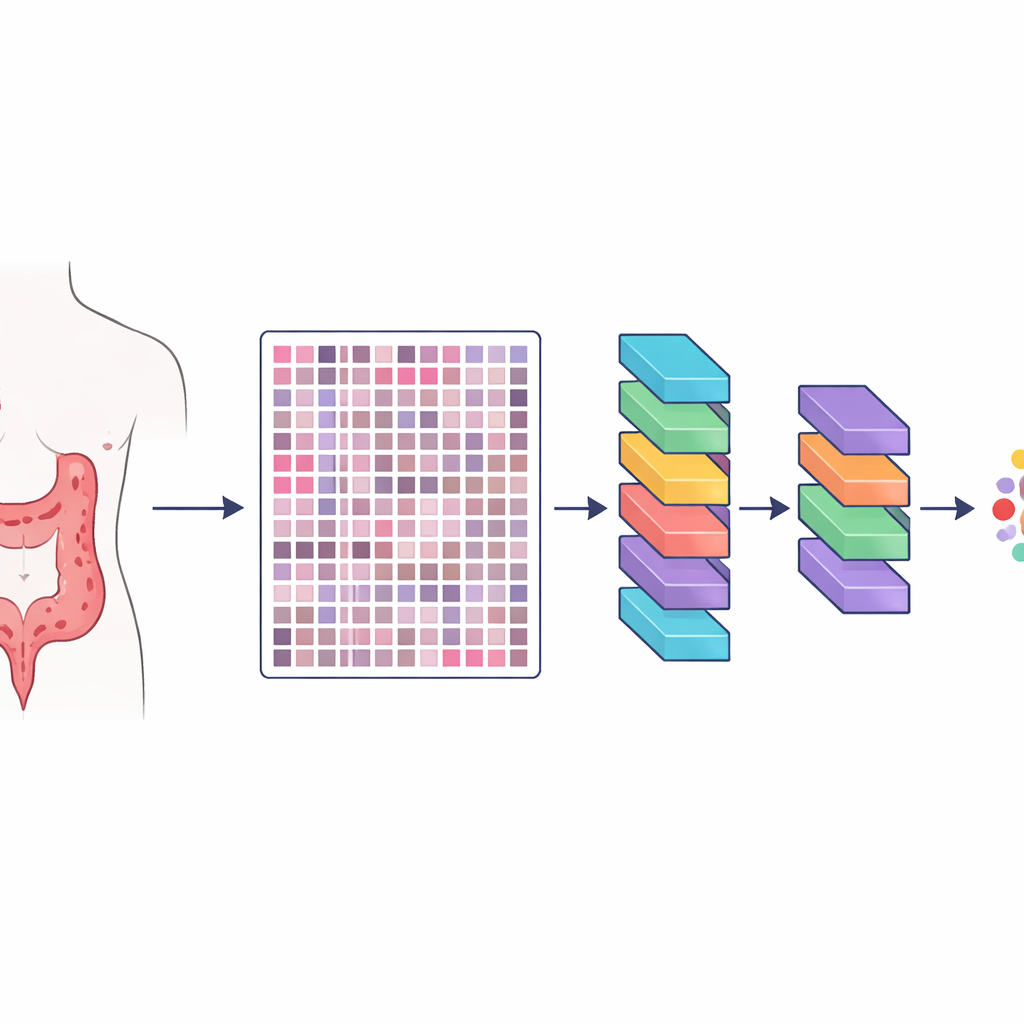
I ricercatori hanno creato una risorsa chiamata HMU-CRC-Hist550K, ricavata dai campioni di tessuto di 500 pazienti trattati per cancro colorettale in un grande ospedale oncologico in Cina. Il tumore di ciascun paziente è stato fissato, colorato con il metodo standard usato nei laboratori di patologia e digitalizzato in una vetrata ad alta risoluzione. Da queste vetrate il team ha ritagliato automaticamente piccole tessere quadrate di immagine, ciascuna approssimativamente delle dimensioni di ciò che un patologo potrebbe vedere attraverso il microscopio in un dato momento. In totale sono state prodotte circa 550.000 tessere di questo tipo, offrendo ai modelli di intelligenza artificiale un insieme enorme e vario di esempi per apprendere l’aspetto dei diversi tessuti.
Annotazione umana accurata del paesaggio tumorale
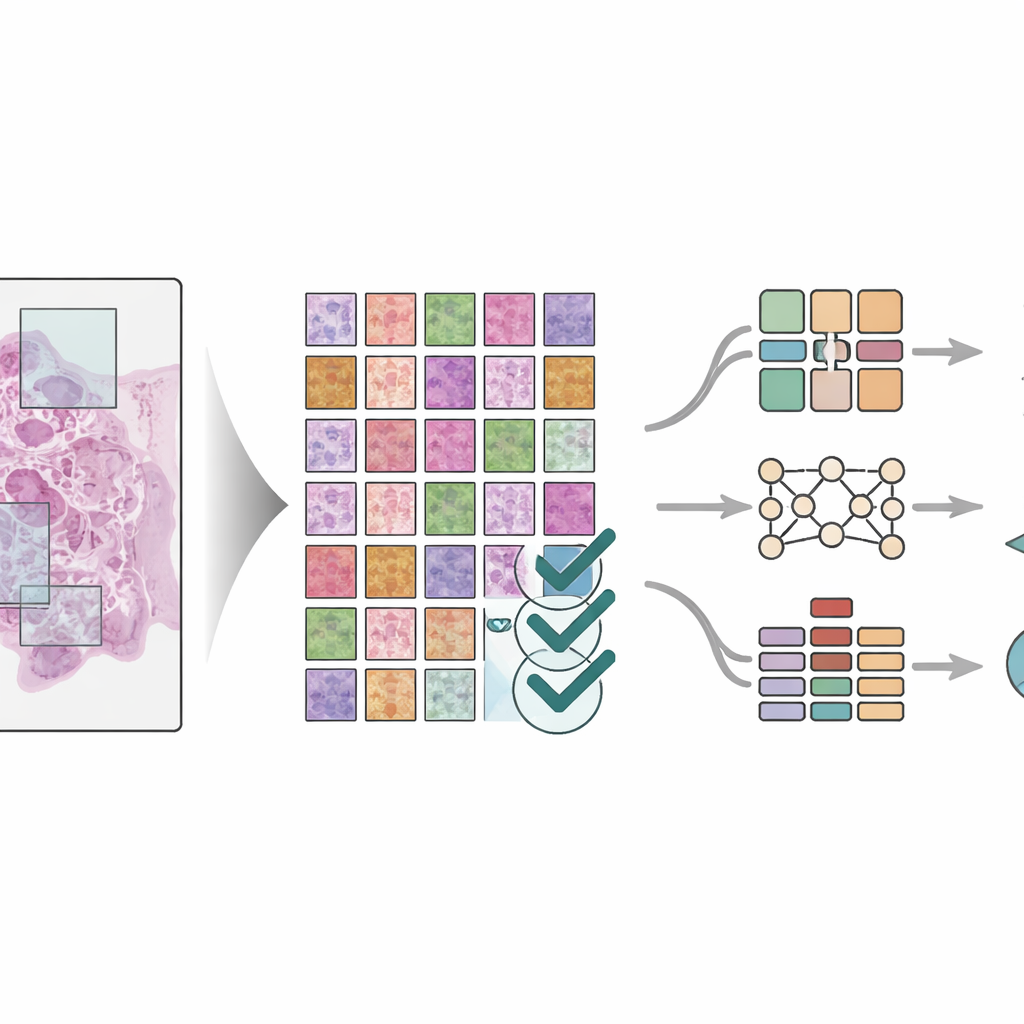
Creare una grande libreria di immagini non basta; le immagini devono anche essere etichettate con precisione. Tre patologi esperti hanno lavorato insieme con un processo in tre fasi per marcare otto componenti chiave dell’ambiente attorno al tumore: tessuto adiposo, detriti cellulari, cellule immunitarie chiamate linfociti, muco, muscolo liscio, mucosa colorettale normale, tessuto connettivo di supporto attorno al tumore e le cellule tumorali stesse. Due patologi hanno prima disegnato regioni sulle grandi vetrate in modo indipendente, quindi hanno controllato il lavoro l’uno dell’altro. Uno specialista senior ha poi effettuato una revisione finale, risolvendo i disaccordi ed escludendo le aree poco chiare. Questo controllo incrociato ha ridotto notevolmente i bias personali e prodotto etichette altamente coerenti a livello di dettaglio fine, così che ogni tessera è associata a un tipo di tessuto specifico all’interno del quartiere tumorale.
Collegare le viste microscopiche alle storie dei pazienti
Ciò che rende particolarmente potente questo dataset è che le immagini sono abbinate a informazioni cliniche ricche per ciascun paziente. Per ogni caso il team ha raccolto dati di base come età e sesso, così come lo stadio del tumore, la sua localizzazione lungo colon e retto, il grado di anormalità delle cellule tumorali, l’eventuale invasione di nervi o linfonodi e la sopravvivenza dopo il trattamento. Sono stati registrati anche i risultati di esami di laboratorio comuni che riflettono il profilo genetico e proteico del tumore. Tutti gli identificatori personali sono stati rimossi in modo che i pazienti non possano essere riconosciuti. Combinando i pattern tissutali con queste caratteristiche cliniche, i ricercatori possono esplorare come determinate configurazioni del microambiente si colleghino a esiti reali, per esempio quali pazienti ottengono risultati migliori o peggiori.
Mettere alla prova l’IA sul nuovo dataset
Per dimostrare l’utilità del dataset, gli scienziati hanno addestrato tre diversi modelli di deep learning—sistemi moderni di riconoscimento dei pattern che eccellono nei compiti di elaborazione delle immagini—per identificare gli otto tipi di tessuto nelle tessere. Hanno usato regole rigorose per separare i pazienti fra i gruppi di addestramento e di test in modo che i modelli venissero valutati su pazienti mai visti prima. I modelli, che includevano sia reti classiche per immagini sia un più recente design “vision transformer”, hanno raggiunto elevatissime accuratezze, con punteggi di performance prossimi alla perfezione su diversi set di test. Il team ha anche confrontato i risultati con altri metodi avanzati di segmentazione delle immagini e ha riscontrato prestazioni altrettanto solide. Sono stati impiegati strumenti visivi per evidenziare le parti di tessuto su cui i modelli si sono basati, confermando che si concentravano su regioni di interesse medico piuttosto che su pattern casuali.
Cosa significa per la futura cura del cancro
Per i non specialisti, il messaggio chiave è che questo lavoro non introduce una nuova cura, ma rappresenta una solida base per diagnosi e prognosi più intelligenti. Condividendo una grande libreria di immagini ben organizzata e liberamente accessibile, collegata a cartelle cliniche dettagliate, gli autori permettono ai ricercatori di tutto il mondo di costruire e confrontare strumenti di intelligenza artificiale su una base comune e affidabile. Tali strumenti potrebbero in futuro aiutare i patologi a mappare il quartiere tumorale più rapidamente e in modo più coerente, prevedere quali pazienti sono a maggior rischio e suggerire strategie terapeutiche più personalizzate. Sebbene i dati attuali coprano solo istanti temporali singoli piuttosto che variazioni nel corso di mesi o anni, questa risorsa rappresenta un passo importante verso l’uso della patologia digitale e dell’IA per comprendere meglio e, in ultima analisi, trattare più efficacemente il cancro colorettale.
Citazione: Wang, H., Li, H., Xue, J. et al. Large-Scale Histological Image Dataset with Metadata for Colorectal Cancer Microenvironment. Sci Data 13, 431 (2026). https://doi.org/10.1038/s41597-026-06675-9
Parole chiave: cancro colorettale, microambiente tumorale, patologia digitale, deep learning, dataset di immagini mediche