Clear Sky Science · it
Un’assemblaggio del genoma a livello cromosomico di Homatula variegata dal bacino del Fiume Yangtze
Un piccolo pesce di torrente con una grande storia genetica
Nei torrenti pietrosi e impetuosi che alimentano l’alto corso del Fiume Yangtze vive un piccolo cobite a strisce chiamato Homatula variegata. È apprezzato sia come alimento sia per gli acquari domestici, eppure finora si sapeva poco o nulla sul suo progetto genetico. Questo studio fornisce la prima mappa quasi completa del genoma della specie, cromosoma per cromosoma, aprendo la strada a strategie di conservazione più intelligenti, a un allevamento più efficiente e a una comprensione più profonda di come la vita si adatti alle acque fredde e rapide di montagna.
Perché mappare il DNA di un pesce dall’aspetto modesto?
Sebbene questo cobite raggiunga solo circa 14 centimetri, svolge un ruolo sproporzionato negli ecosistemi fluviali locali e nell’acquacoltura regionale. Vive bene nei torrenti di media quota con fondi ghiaiosi e correnti costanti, nutrendosi di insetti, detriti organici e pesciolini. Poiché è gustoso e colorato, cresce l’interesse ad allevarlo come specie ornamentale e alimentare autoctona. Tuttavia allevare e proteggere una specie è molto più difficile senza un riferimento genetico preciso. Un genoma completo agisce come una lista dettagliata dei componenti e uno schema dei collegamenti, rivelando i geni che determinano crescita, colore, resistenza alle malattie e capacità di affrontare acque rapide e fredde. Fino ad ora, nessun cobite di questo ramo della famiglia aveva un riferimento di qualità così elevata, lasciando un’importante lacuna nella genetica dei pesci d’acqua dolce.
Costruire una mappa del DNA cromosoma per cromosoma
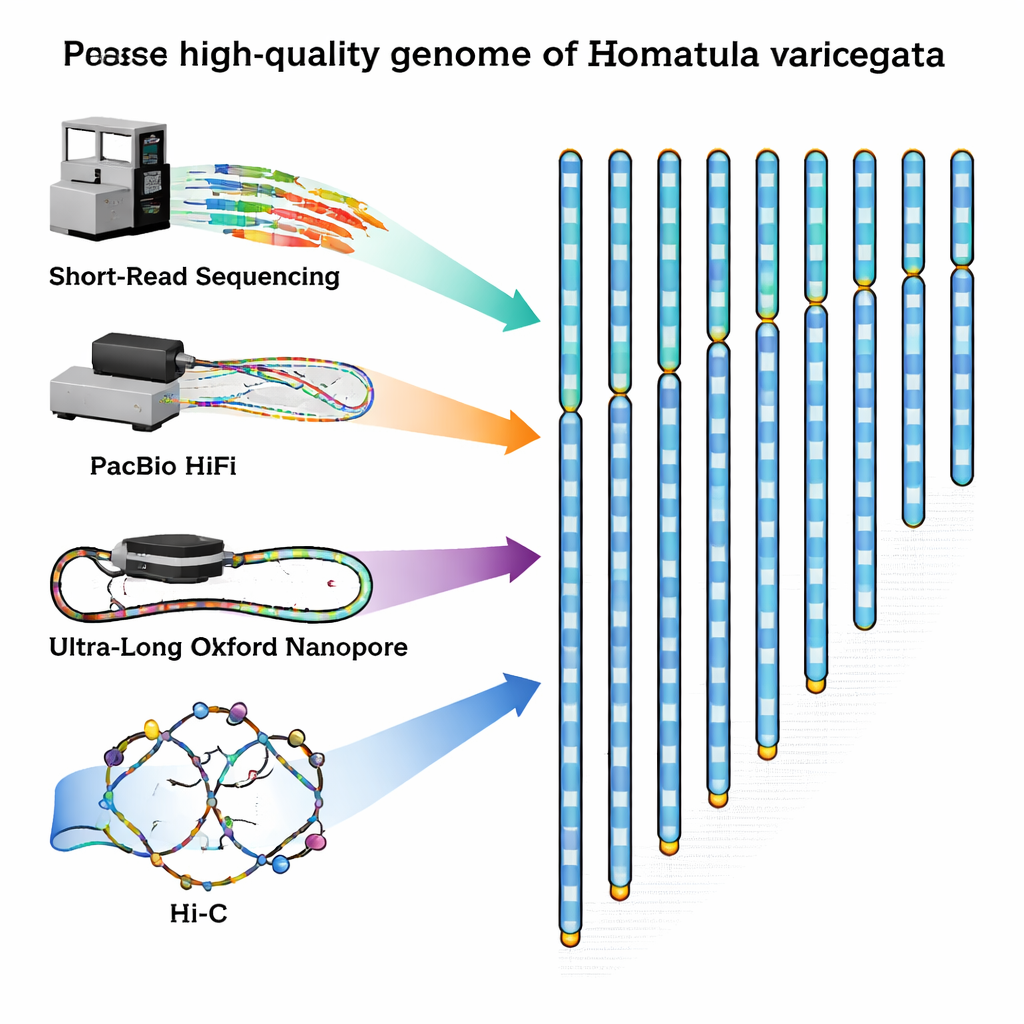
Per colmare questa lacuna, i ricercatori hanno catturato un maschio adulto sano nel Fiume Qingyi, un affluente dello Yangtze, ed hanno estratto con cura DNA e RNA dal suo sangue. Hanno quindi combinato diverse tecnologie di sequenziamento all’avanguardia, ognuna con punti di forza differenti. Macchine a letture corte di Illumina hanno prodotto un’enorme quantità di brevi sequenze DNA molto accurate. La tecnologia PacBio HiFi ha fornito frammenti più lunghi con ottima accuratezza, mentre i dispositivi Oxford Nanopore hanno generato filamenti ultra‑lunghi in grado di attraversare regioni ripetitive difficili da decodificare. Infine, un metodo chiamato Hi‑C ha catturato come i filamenti di DNA si ripiegano e interagiscono all’interno del nucleo cellulare, fornendo una mappa di contatto 3D che aiuta a collegare i frammenti ricostruendo i cromosomi nell’ordine corretto.
Cosa rivela il nuovo genoma
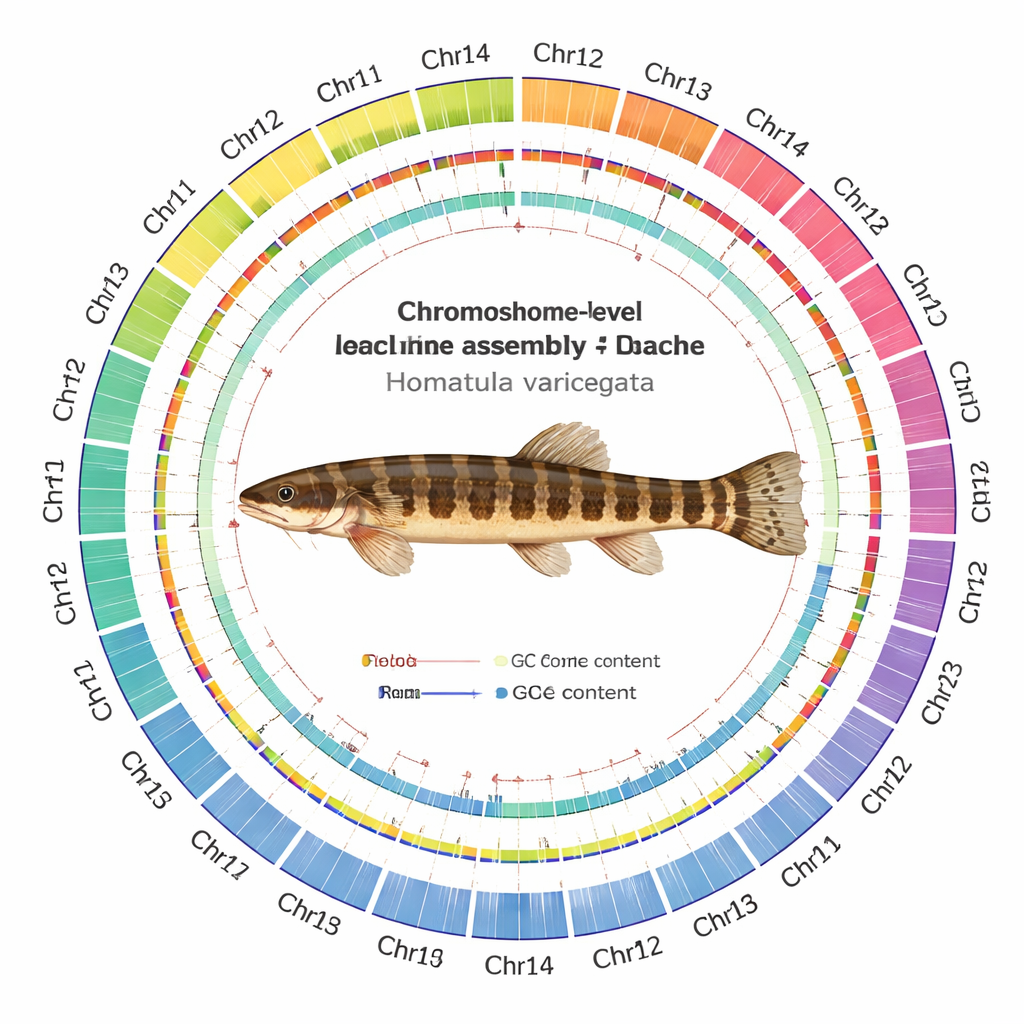
Intrecciando questi dati con software moderni di assemblaggio e controlli di qualità accurati, il team ha prodotto un genoma di 641 milioni di basi di DNA, ordinato in 24 cromosomi. Sorprendentemente, ogni cromosoma è stato assemblato come un unico frammento continuo: 22 non presentano alcuna lacuna e solo due mostrano gap minimi. Sono stati identificati 24 probabili centromeri — la “cintura” centrale di ciascun cromosoma — e rilevata la maggior parte dei capi telomerici protettivi alle estremità cromosomiche. Gli scienziati hanno catalogato 24.479 geni codificanti proteine e sono riusciti ad attribuire probabili funzioni a circa il 93% di essi confrontandoli con grandi database internazionali. Hanno anche mappato il paesaggio del DNA ripetuto, scoprendo che oltre un quarto del genoma è costituito da elementi genetici mobili, in particolare trasposoni a DNA, che possono spostarsi nel genoma e talvolta guidare l’evoluzione.
Testare la qualità sotto il cofano
I numeri a livello elevato hanno senso solo se la mappa sottostante è affidabile. Il team ha quindi sottoposto l’assemblaggio a una serie di test. Le letture provenienti da tutte le piattaforme di sequenziamento si sono riallineate al nuovo genoma a tassi molto alti, con copertura uniforme sulla maggior parte dei cromosomi. Strumenti indipendenti che contano brevi pattern di DNA hanno suggerito che quasi tutto il contenuto sequenziale atteso è presente, e i test standard di completezza genica hanno mostrato che la stragrande maggioranza dei geni universali dei pesci è intatta. Le mappe di contatto Hi‑C hanno formato pattern puliti e squadrati lungo ciascun cromosoma, con pochi segnali vaganti tra di essi, indicando che i segmenti sono correttamente uniti e non mischiati.
Dalla mappa del DNA all’impatto nel mondo reale
Per un non specialista, questo lavoro può sembrare un trionfo tecnico fine a se stesso, ma le sue implicazioni sono pratiche e ampie. Disporre di un genoma quasi end‑to‑end per Homatula variegata fornisce agli scienziati un riferimento con cui confrontare popolazioni selvatiche, monitorare la diversità genetica e individuare segni di endogamia o adattamento locale. Gli allevatori possono cercare marcatori genetici associati a tratti desiderabili come crescita rapida, robustezza o colorazione vivace, accelerando la selezione mantenendo il carattere naturale della specie. Gli ecologi possono esplorare come questo cobite si sia evoluto per vivere nei torrenti montani freschi e veloci, lezioni che possono aiutare anche nella gestione di specie affini. In breve, questo genoma a livello cromosomico trasforma un modesto pesce di fiume in un potente modello per comprendere — e proteggere — la ricca vita degli ecosistemi d’acqua dolce asiatici.
Citazione: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Parole chiave: genoma di pesce, assemblaggio cromosomico, biodiversità d’acqua dolce, genetica dell’acquacoltura, loach del Fiume Yangtze