Clear Sky Science · it
Una risorsa curata di genomi chemolitotrofi autotrofi e geni marker per la predizione delle vie di fissazione del CO₂
Microbi che aiutano a riequilibrare il bilancio del carbonio della Terra
Nascosti nei suoli, negli oceani e negli ambienti estremi, alcuni microbi possono costruire la propria biomassa usando l’anidride carbonica (CO₂) come principale fonte di carbonio. Questi microscopici chimici sono fondamentali per mantenere in equilibrio il ciclo del carbonio terrestre e potrebbero ispirare nuovi metodi per catturare il CO₂ industriale. Tuttavia, fino ad ora i ricercatori non avevano un modo semplice e affidabile per esaminare il DNA di un microbo e determinare quale strategia di fissazione del CO₂ impiega. Questo studio presenta un catalogo di geni curato e un nuovo strumento informatico, AutoFixMark, progettato per colmare questa lacuna.
Molte vie per trasformare l’aria in biomassa
Non tutti gli organismi che fissano il CO₂ lo fanno allo stesso modo. I microbi hanno evoluto almeno sette vie naturali che convertono il CO₂ in materia organica. Alcune, come il ciclo di Calvin–Benson–Bassham, comune nelle piante e in molti batteri, sono ben note; altre, come la via della glicina riduttiva scoperta solo nel 2020, sono ancora poco mappate. Queste vie sono distribuite in molti rami dell’albero della vita e spesso riutilizzano enzimi simili, il che rende sorprendentemente difficile distinguerle soltanto dalla sequenza del genoma. Il software esistente può predire capacità metaboliche generali, ma non è stato ottimizzato né testato a fondo per identificare con precisione le specifiche vie di fissazione del CO₂.
Costruire una mappa di riferimento pulita dei microbi fissatori di CO₂
I ricercatori hanno cominciato assemblando due collezioni di genomi accuratamente verificate. Innanzitutto hanno selezionato 15 microbi ben studiati le cui vie di fissazione del CO₂ sono state caratterizzate in dettaglio. Questi organismi di riferimento, che coprono diversi gruppi batterici e archeali, sono serviti da modelli per definire gli enzimi chiave veramente distintivi di ciascuna via. Successivamente hanno creato un set di benchmark di 347 genomi chemolitotrofi autotrofi—microbi che ricavano energia da composti inorganici e costruiscono biomassa dal CO₂. Ciascun genoma di questo set più ampio è stato associato, manualmente dalla letteratura, a specifiche vie di fissazione del CO₂, fornendo un solido insieme di verità per testare le predizioni.
Geni marker e regole semplici invece di scatole nere
Usando i 15 genomi di riferimento, il team ha identificato “geni marker” per ciascuna delle sette vie di fissazione del CO₂ e li ha mappati a identificatori KEGG Orthology (KO) standardizzati. Invece di affidarsi a metodi opachi di machine learning, hanno codificato regole trasparenti su come questi marker si combinano. Alcune reazioni possono essere catalizzate da uno qualsiasi di diversi enzimi alternativi, gestiti da una regola “one_of”. Altre dipendono da complessi multisubunitari e devono avere “all_of” un insieme definito di KO. Per la via della glicina riduttiva, dove non tutti i componenti sono completamente compresi, lo strumento usa regole “at_least” che richiedono la presenza di un numero minimo di subunità. Queste regole logiche sono salvate in un file JSON leggibile dalle macchine che costituisce la base di conoscenza centrale di AutoFixMark.
Uno strumento leggero che supera software consolidati
AutoFixMark è un piccolo programma basato su regole scritto in Python. Prende in input una lista di ID KO per i geni presenti nel genoma di un microbo, tipicamente prodotta da uno strumento separato chiamato KofamScan, e verifica quali regole marker sono soddisfatte per ciascuna delle sette vie. Gli autori hanno confrontato AutoFixMark con due strumenti di annotazione metabolica ampiamente usati, METABOLIC e gapseq, usando il loro set di benchmark di 347 genomi. Tutti e tre gli strumenti hanno dato buone prestazioni su vie classiche come il ciclo di Calvin, il ciclo tricarbossilico riduttivo e la via di Wood–Ljungdahl. Tuttavia, AutoFixMark ha chiaramente superato gli altri per vie più recenti o meno comuni come il ciclo 3-idrossipropionato/4-idrossibutirrato, il ciclo dicarbossilato/4-idrossibutirrato e la via della glicina riduttiva, alcune delle quali non sono nemmeno coperte dal software concorrente.
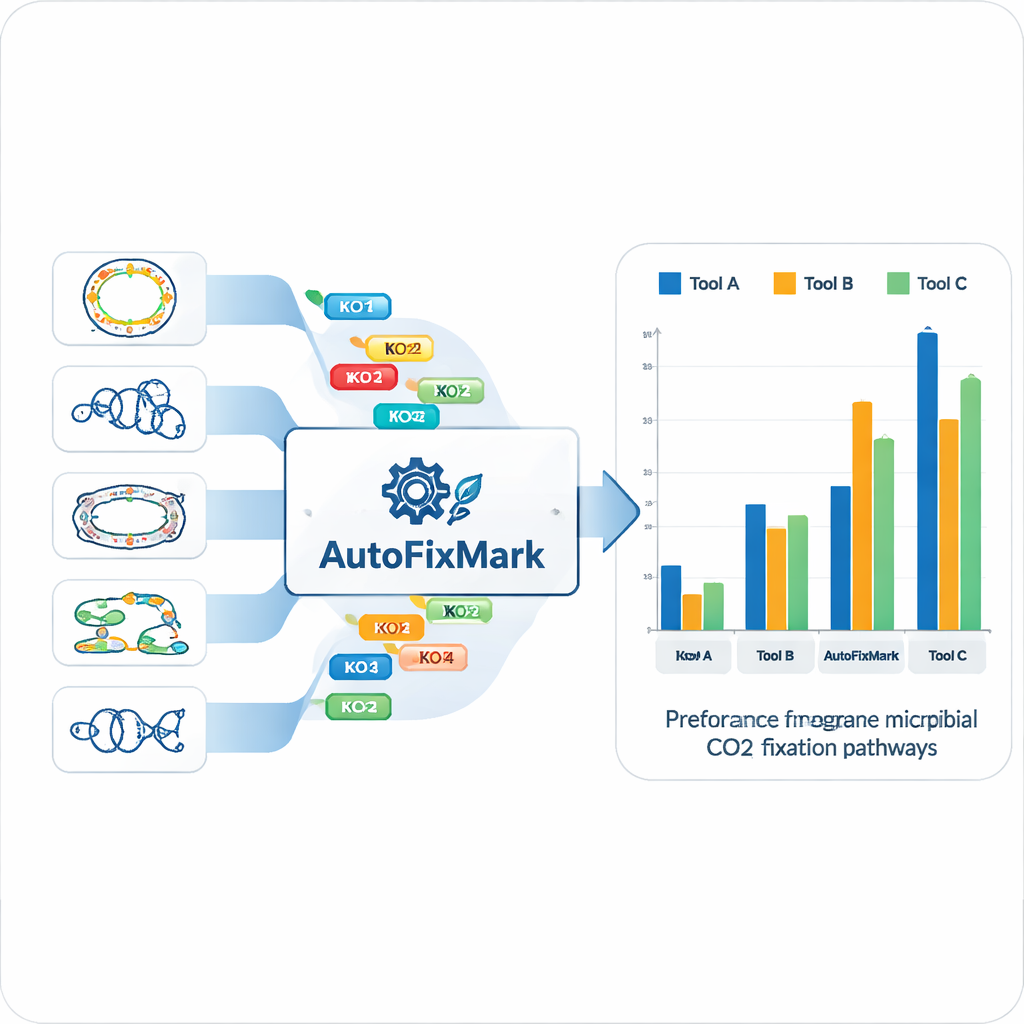
Cosa significano questi risultati per gli studi sul clima e l’ecologia
I set di geni curati, il programma AutoFixMark e l’intera collezione di genomi di benchmark sono disponibili pubblicamente. Ciò significa che i ricercatori possono ora esaminare sia microbi isolati sia genomi assemblati da metagenomi per vedere quali strategie di fissazione del CO₂ sono geneticamente alla loro portata. È importante sottolineare che gli autori precisano che AutoFixMark predice il potenziale genetico, non se una via sia attiva nelle condizioni reali. Molte di queste rotte biochimiche possono funzionare in direzione inversa, a seconda dell’equilibrio energetico della cellula. Anche così, disporre di un metodo robusto e trasparente per identificare i microbi fissatori di CO₂ aiuterà gli scienziati a mappare dove e come la vita rimuove carbonio dall’atmosfera, a guidare esperimenti su vie emergenti e a supportare la progettazione di future biotecnologie basate sul CO₂.
Citazione: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Parole chiave: fissazione microbica del carbonio, metabolismo autotrofo, annotazione del genoma, cattura del CO2, metagenomica