Clear Sky Science · it
Prima assemblaggio e annotazione del genoma a livello cromosomico di una razza d’acqua dolce in pericolo (Fontitrygon garouaensis) dall’Africa
Un raro abitante di fiume sotto i riflettori genomici
Nei torbidi fiumi dell’Africa occidentale vive una razza insolita che ha fatto ciò che quasi tutti i suoi parenti squali e razze non hanno fatto: si è stabilita permanentemente in acqua dolce. Questa razza d’acqua dolce liscia, Fontitrygon garouaensis, è inoltre a rischio e poco studiata. Lo studio dietro questo articolo fornisce la prima mappa completa del suo DNA a livello cromosomico, offrendo uno strumento potente per capire come una linea evolutiva marina così antica si sia adattata alla vita nei fiumi e come potremmo meglio proteggerla.
Perché questa razza è importante
Squali e razze appartengono a uno dei rami più antichi dell’albero genealogico dei vertebrati, separatisi dagli antenati dei pesci ossei centinaia di milioni di anni fa. Eppure, nonostante la loro importanza evolutiva, i loro genomi restano poco esplorati, soprattutto per le specie che vivono nelle acque africane. Fontitrygon garouaensis è particolarmente singolare: è l’unica razza nota completamente adattata ai sistemi d’acqua dolce africani e mostra caratteri corporei distintivi come una fila di spine dorsali ridotta o assente. Poiché il passaggio dal mare salato ai fiumi d’acqua dolce è raro e fisiologicamente impegnativo per squali e razze, questa specie offre un esperimento naturale su come gli animali rimodellano la propria biologia per affrontare nuovi ambienti.
Costruire una mappa genetica di riferimento
Per svelare il progetto genetico della razza, i ricercatori hanno raccolto una singola femmina adulta nel fiume Niger in Nigeria ed estratto DNA e RNA di alta qualità da più tessuti. Hanno poi usato una strategia “ibrida” che combina tre approcci di sequenziamento all’avanguardia. Il sequenziamento Illumina a letture corte fornisce un enorme numero di piccoli frammenti di DNA, il sequenziamento PacBio HiFi a letture lunghe genera tratti molto più lunghi e continui, e il sequenziamento Hi-C cattura come il DNA si piega e interagisce all’interno del nucleo cellulare. Tessendo insieme questi dataset con software specializzati, il team ha assemblato un genoma di circa 4,19 miliardi di basi, organizzato in 41 pezzi a livello cromosomico—comparabile per dimensione ad alcuni dei genomi di squalo più grandi conosciuti.
Cosa rivela il genoma
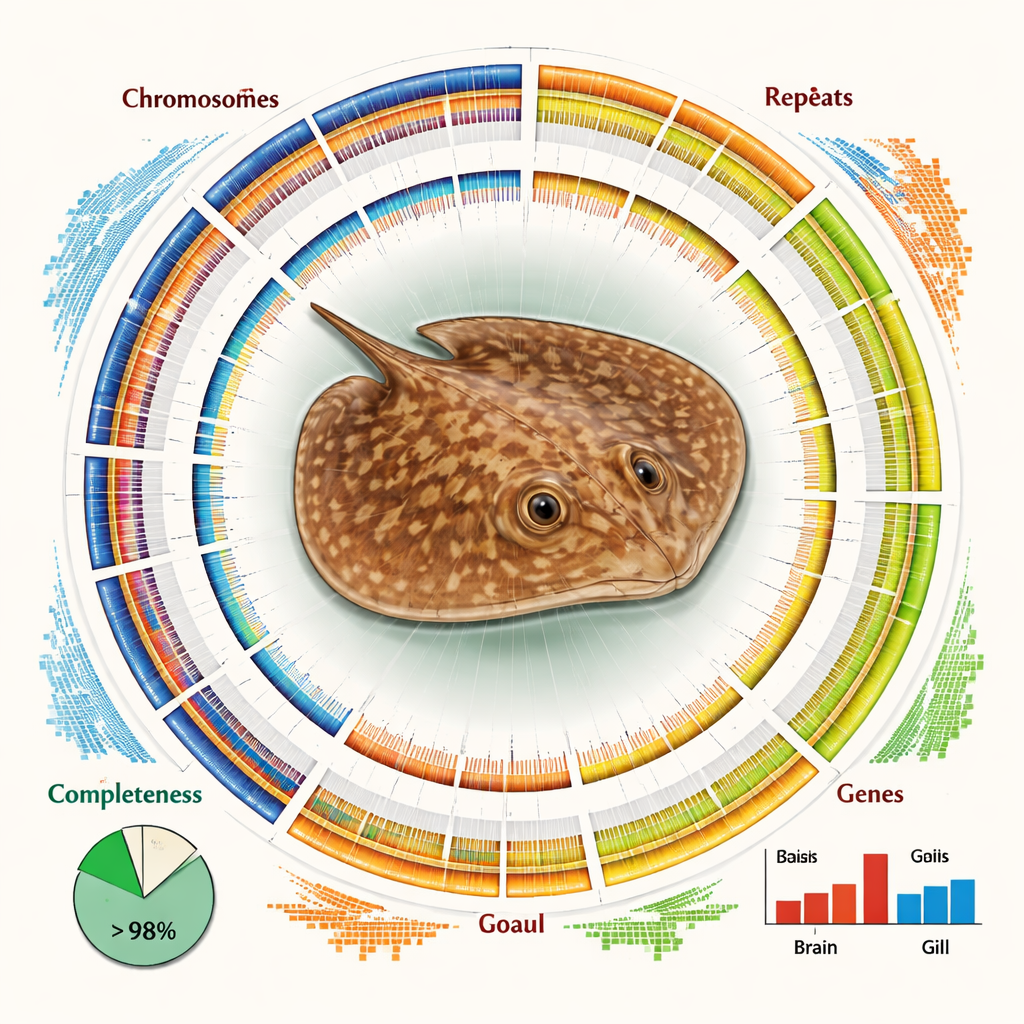
L’assemblaggio finale è sia di grande dimensione sia sorprendentemente completo. Controlli di qualità indipendenti mostrano che oltre il 93 percento dei geni vertebrati core attesi è presente e intatto, e più dell’84 percento della sequenza totale di DNA è assegnata con sicurezza a cromosomi specifici. Il genoma è dominato da DNA ripetitivo—tratti di sequenza che ricorrono molte volte—costituendo circa due terzi della sua lunghezza. Molte di queste ripetizioni appartengono a elementi genetici mobili come LINE e LTR, che si sono copiati e inseriti nel genoma nel corso dell’evoluzione. Nonostante questa complessità, i ricercatori hanno identificato quasi 30.000 geni codificanti proteine e sono riusciti ad assegnare probabili funzioni a oltre il 98 percento di essi usando banche dati internazionali di proteine e vie biologiche.
Indizi sulla vita in acqua dolce e sull’evoluzione
Disporre di una mappa a livello cromosomico ha permesso al team di fare più che elencare geni. Confrontando i cromosomi della razza con quelli di squali e razze affini, hanno scoperto una storia di rimaneggiamenti strutturali—rotture, fusioni e riarrangiamenti di interi segmenti cromosomici—che distinguono questa linea evolutiva. Questi cambiamenti potrebbero aver contribuito a plasmare i tratti unici della specie e la sua nicchia ecologica. Gli autori hanno inoltre esaminato l’attività genica in due tessuti chiave: le branchie, che mediano la respirazione e l’equilibrio salino con l’acqua circostante, e il cervello. Hanno rilevato chiare differenze nei geni espressi, con i geni branchiali arricchiti per vie coinvolte nell’uso dell’energia e nel metabolismo dei grassi, suggerendo gli adattamenti biochimici necessari per sopravvivere in acqua dolce.
Una nuova base per la conservazione
In sostanza, questo lavoro trasforma una razza di fiume oscura e minacciata in uno dei pesci cartilaginei meglio caratterizzati a livello di DNA. Per i non specialisti, ciò significa che gli scienziati dispongono ora di un manuale di riferimento dettagliato per la specie, dai cromosomi fino ai singoli geni. Questo riferimento può guidare studi futuri su come la specie affronta la variazione della qualità dell’acqua, su come sono strutturate le popolazioni lungo i fiumi e su come è imparentata con altre razze. Non meno importante, fornisce una base genomica per la pianificazione della conservazione, offrendo nuovi modi per monitorare la diversità genetica, identificare popolazioni distinte da proteggere e capire come questo raro specialista d’acqua dolce potrebbe rispondere alle pressioni ambientali in corso.
Citazione: Nneji, L.M., Oladipo, S.O., Oyebanji, O.O. et al. First Chromosome-level Genome Assembly and Annotation of an Endangered Freshwater Stingray (Fontitrygon garouaensis) from Africa. Sci Data 13, 302 (2026). https://doi.org/10.1038/s41597-026-06646-0
Parole chiave: razza d’acqua dolce, assemblaggio del genoma, evoluzione degli elasmobranchi, genomica della conservazione, biodiversità fluviale africana