Clear Sky Science · it
Assemblaggio del genoma a livello cromosomico di Sparganium angustifolium Michx. (Typhaceae)
Una pianta tranquilla del lago con una grande storia genomica
Sparganium angustifolium è una pianta d’acqua dall’aspetto modesto che potresti oltrepassare in canoa senza pensarci troppo, eppure plasma silenziosamente la vita in molti laghi e stagni del nord. Offre rifugio ai pesciolini, nutre gli anatidi e ricopre la superficie dell’acqua con foglie galleggianti. In questo studio, gli scienziati svelano una dettagliata mappa genetica di questa pianta, aprendo una nuova finestra su come le piante si adattano alla vita acquatica e fornendo un prezioso riferimento sia per la conservazione sia per la biologia di base. 
Perché questo abitante sommerso è importante
Sparganium angustifolium è comune nelle regioni temperate dell’emisfero settentrionale. Diversamente dalle piante cannetali che stanno per lo più sopra la superficie dell’acqua, questa specie cresce in acque più profonde, con foglie lunghe e sottili per lo più sommerse o galleggianti. Le sue fitte praterie formano foreste subacquee che offrono nascondigli agli animali acquatici, mentre i suoi frutti e le foglie nutrono anatre e altri uccelli selvatici. Poiché si colloca vicino alla base di un ramo importante dell’albero filogenetico delle graminacee e affini (l’ordine Poales, che include anche colture come riso e mais), offre un punto di confronto chiave per capire come le piante hanno compiuto il salto dalla terraferma agli ambienti acquatici.
Costruire una mappa genetica ad alta risoluzione
Per decifrare il genoma della pianta, i ricercatori hanno raccolto un campione da un fiume della Mongolia interna, in Cina, e hanno impiegato diverse tecniche avanzate di sequenziamento del DNA. Hanno combinato letture di DNA lunghe e altamente accurate, sequenziamento a letture corte e un metodo chiamato Hi-C, che cattura come diverse regioni del DNA si trovano vicine tra loro nello spazio tridimensionale all’interno della cellula. Intrecciando questi dati, hanno assemblato il DNA della pianta in 15 cromosomi, coprendo quasi l’intero genoma — circa 487 milioni di “lettere” del codice genetico. Le misure della qualità dell’assemblaggio hanno mostrato che ampi tratti di DNA sono stati uniti senza interruzioni e che oltre il 96% dei geni fondamentali attesi nelle piante era presente, indicando un genoma di riferimento molto completo e affidabile.
DNA ripetitivo e migliaia di geni
Una volta assemblato il genoma, il team ha identificato le sue caratteristiche principali. Hanno trovato 23.767 geni codificanti proteine — segmenti di DNA che possono essere tradotti in proteine che costruiscono e fanno funzionare le cellule della pianta. Per comprendere le possibili funzioni di questi geni, li hanno confrontati con diversi database scientifici principali e sono riusciti ad attribuire probabili funzioni a oltre il 96% di essi. I ricercatori hanno inoltre scoperto che la maggior parte del genoma — poco più del 70% — è costituita da DNA ripetitivo, in gran parte sotto forma di elementi genetici mobili noti come retrotrasposoni. Questi tratti non codificano direttamente per proteine, ma modellano fortemente la dimensione e la struttura del genoma e possono influenzare il comportamento dei geni vicini. 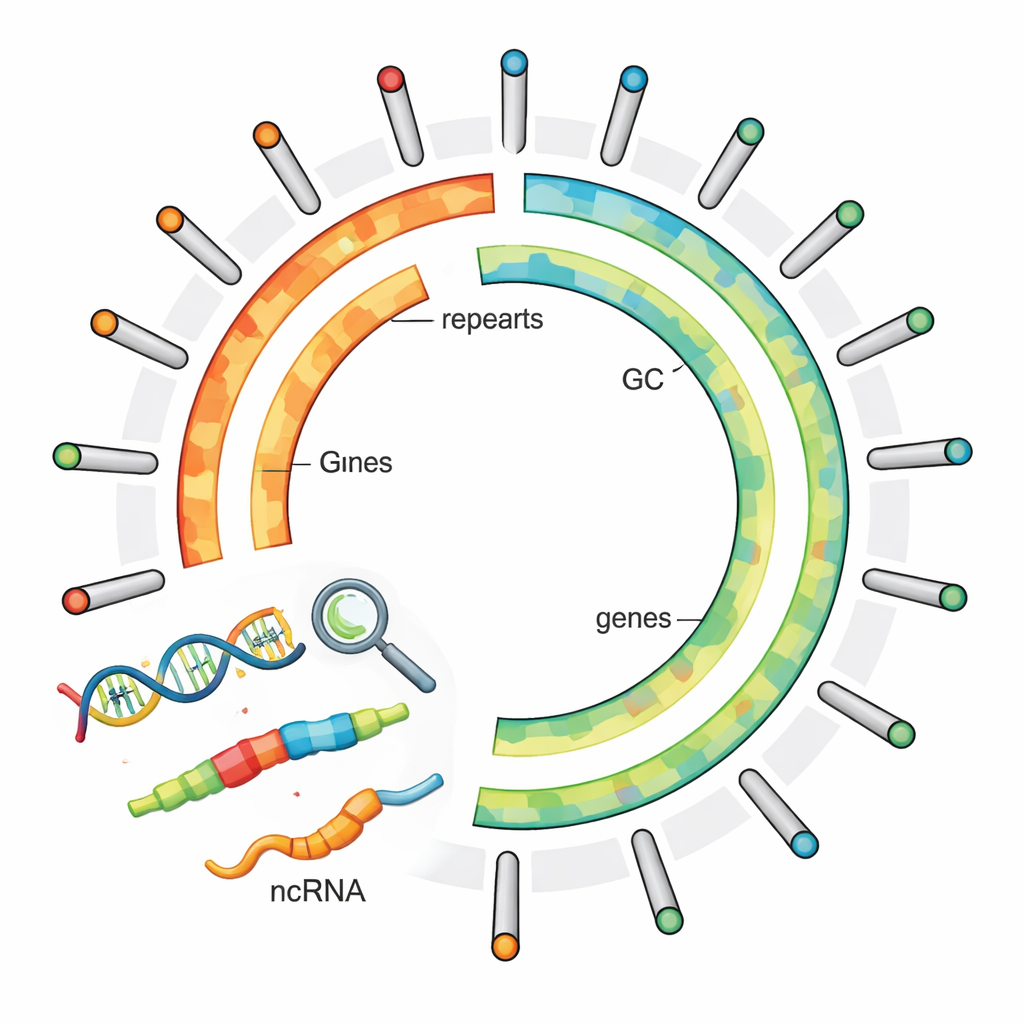
Il kit nascosto di RNA della pianta
Oltre ai geni che producono proteine, il genoma ospita molti RNA non codificanti, molecole che aiutano a controllare e perfezionare l’attività genica. I ricercatori hanno identificato più di 3.300 di questi elementi, inclusi migliaia di RNA ribosomiali che formano il nucleo delle macchine proteiche della cellula, centinaia di RNA di trasporto che consegnano i mattoni per le nuove proteine, e piccoli RNA che possono guidare quali geni vengono attivati o disattivati. Questo ricco kit di RNA suggerisce che Sparganium angustifolium dispone di molteplici livelli di regolazione per rispondere ai cambiamenti di luce, ossigeno, temperatura e movimento dell’acqua nel suo habitat acquatico.
Da una pianta a un quadro evolutivo più ampio
Rendendo questo genoma a livello cromosomico disponibile pubblicamente in banche dati internazionali, gli autori forniscono una nuova potente risorsa per gli scienziati che studiano come le piante si adattano alla vita in acqua. Confrontare questo genoma con quelli di specie affini che vivono in riva all’acqua o sulla terraferma può rivelare quali geni e caratteristiche del DNA sono condivisi e quali sono unici degli stili di vita pienamente acquatici. Per i non specialisti, la conclusione è semplice: decodificando il copione genetico di una pianta di lago apparentemente ordinaria, i ricercatori hanno creato una base per comprendere come le piante si modificano per prosperare sott’acqua, conoscenza che potrebbe infine informare la conservazione delle zone umide e persino l’allevamento di colture più resilienti.
Citazione: Shi, X., Xue, J. & Xu, X. Chromosome-level genome assembly of narrow-leaf bur-reed (Sparganium angustifolium Michx., Typhaceae). Sci Data 13, 284 (2026). https://doi.org/10.1038/s41597-026-06640-6
Parole chiave: piante acquatiche, assemblaggio del genoma, ecologia delle zone umide, evoluzione delle piante, Sparganium