Clear Sky Science · it
Assemblaggio genomico senza gap da telomero a telomero di Opsariichthys evolans (Cypriniformes: Cyprinidae)
Un pesce di torrente con una storia genomica
I torrenti di montagna in rapido scorrimento nel sud-est della Cina e a Taiwan ospitano un piccolo e colorato pesce chiamato Opsariichthys evolans. Sebbene poco noto al di fuori della regione, questa specie è un elemento chiave degli ecosistemi e un’opera d’arte naturale, con strisce vivaci e colori nuziali sgargianti. Per più di un secolo gli scienziati hanno discusso su come classificarla e su quale fosse la sua posizione nell’albero filogenetico dei pesci d’acqua dolce. Questo studio fornisce un pezzo fondamentale del puzzle: il primo genoma completo e senza gap di O. evolans, letto da un estremo del cromosoma all’altro.
Perché questo pesce è importante
O. evolans vive in corsi d’acqua limpidi e veloci, dove contribuisce a mantenere l’equilibrio delle reti trofiche e funge da indicatore sensibile della qualità dell’acqua. I maschi sviluppano durante la stagione riproduttiva strisce laterali vivide e tubercoli granulosi sulla testa e intorno agli occhi, oltre a un muso scuro, tendente al nerastro-porpora. Questi tratti vistosi, insieme alla preferenza della specie per acque a rapido scorrimento, la rendono ideale per studiare come gli animali si adattano ai loro ambienti. Allo stesso tempo, cambiamenti di origine umana — inquinamento, frammentazione dell’habitat e specie invasive — stanno riducendo le sue popolazioni, rendendo importante comprendere la sua biologia per la conservazione.
Una lunga confusione sul nome
Per decenni i biologi hanno faticato a decidere se O. evolans appartenesse al genere Opsariichthys o a Zacco. I tassonomisti iniziali descrissero la specie come Zacco evolans, basando la decisione in gran parte su caratteristiche esterne come la forma delle pinne e le striature del corpo. Studi successivi, più dettagliati, mostrarono che lo schema a strisce e i tubercoli nuziali differiscono da quelli del somigliante Zacco platypus. Analisi del DNA mitocondriale suggerirono che O. evolans si colloca meglio all’interno di Opsariichthys, ma alcuni dati da geni nucleari lasciavano intravedere un legame più stretto con Zacco. Senza un genoma completo, il quadro evolutivo è rimasto sfocato e il dibattito sulla sua corretta collocazione nell’albero dei pesci è continuato.

Leggere ogni lettera del genoma
Per risolvere queste questioni, i ricercatori hanno catturato un maschio selvatico in un fiume della provincia di Anhui, in Cina, e hanno conservato con cura nove diversi tessuti. Hanno quindi combinato diverse tecnologie di sequenziamento del DNA all’avanguardia, ognuna con i propri punti di forza, per leggere il codice genetico dell’animale. Frammenti brevi e altamente accurati hanno aiutato a correggere la sequenza, mentre letture lunghe e ultralunghe provenienti dalle piattaforme PacBio e Oxford Nanopore hanno attraversato regioni difficili e cucito insieme i cromosomi da un estremo all’altro. La tecnologia Hi-C, che cattura il modo in cui il DNA si ripiega all’interno della cellula, è stata usata per organizzare i pezzi in cromosomi completi. Il risultato finale è un genoma da telomero a telomero, senza gap, di circa 0,89 miliardi di coppie di basi, ordinatamente organizzato in 39 cromosomi con un unico pezzo continuo di DNA per ciascuno.
Cosa rivela il genoma
Il genoma completato ha superato rigorosi controlli di qualità, catturando oltre il 99% dei geni conservati attesi e allineandosi strettamente con sequenze note di pesci correlati. Quasi la metà del genoma è costituita da sequenze ripetute, molte delle quali sono “geni saltatori” capaci di spostarsi e rimodellare il genoma nel corso dell’evoluzione. Il team ha identificato quasi 30.000 geni codificanti proteine e migliaia di RNA non codificanti, la maggior parte dei quali è stata associata a funzioni note usando i principali database biologici. Confrontando questo nuovo genoma con quelli di due parenti stretti — Opsariichthys bidens e Zacco platypus — gli scienziati hanno rilevato che la struttura cromosomica complessiva è molto simile, confermando stretti legami evolutivi. All’interno di questo quadro, hanno identificato geni e vie metaboliche candidati probabilmente coinvolti nella colorazione a strisce del corpo e nelle adattazioni alla vita in correnti rapide, fornendo indizi su come si siano evoluti l’aspetto distintivo e lo stile di vita della specie.
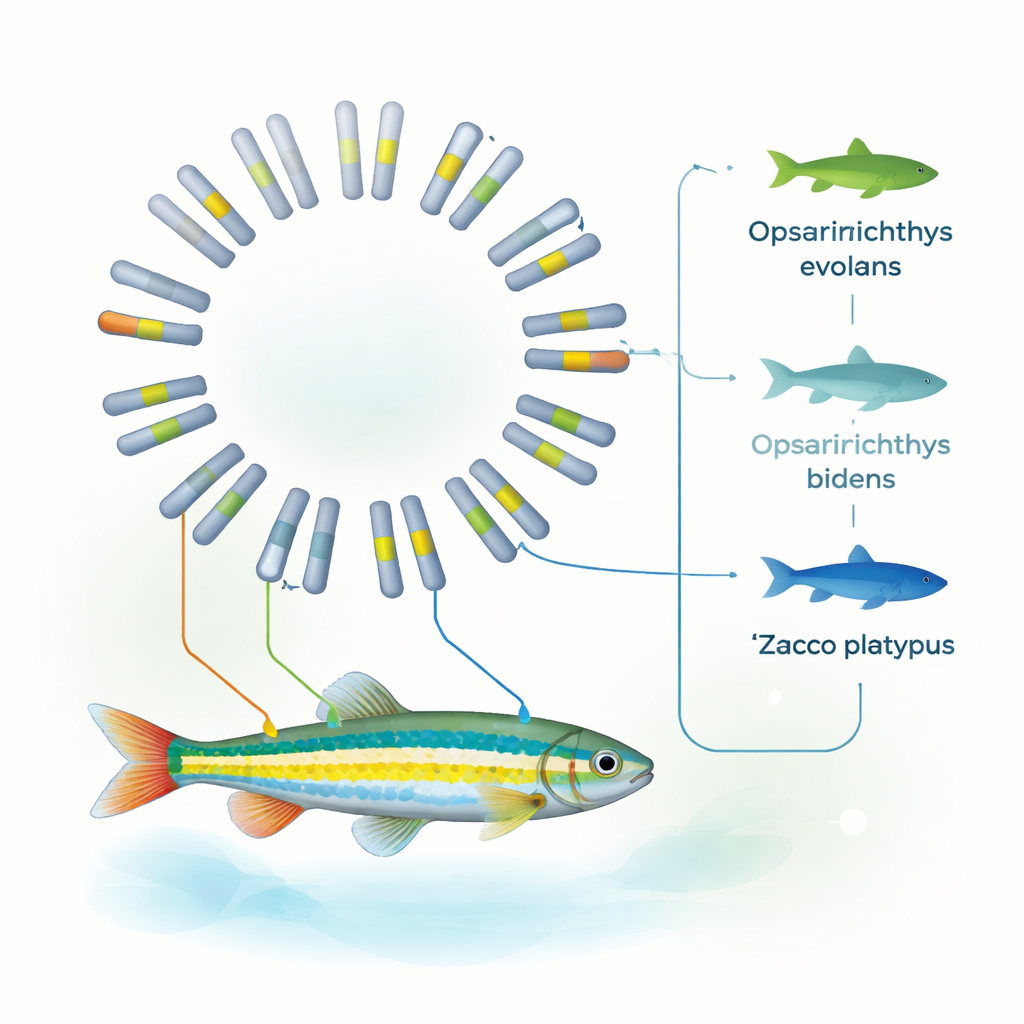
Chiarire la sua posizione nell’albero dei pesci
Usando famiglie geniche condivise tra dieci diverse specie di pesci, il team ha ricostruito un albero evolutivo dettagliato. La loro analisi indica che O. evolans si è separato da Z. platypus approssimativamente 8–19 milioni di anni fa e che la sua struttura genomica è particolarmente vicina a quella di O. bidens. Insieme alle precedenti evidenze mitocondriali, questi schemi supportano l’inclusione di O. evolans nel genere Opsariichthys, e non in Zacco. In altre parole, il genoma completo conferma quanto avevano suggerito le attente osservazioni delle strisce, del colore del muso e delle strutture nuziali: l’apparenza può ingannare, ma quando morfologia e genoma completo concordano, le linee tassonomiche diventano molto più nette.
Perché un genoma completo cambia le regole
Per i non specialisti, il risultato qui è come passare da una mappa sfocata e strappata a un atlante nitido e ad alta risoluzione di una specie. Con un genoma completo e senza gap, gli scienziati possono ora tracciare l’origine dei colori sgargianti di O. evolans, la sua forma snella adattata alla vita in acque veloci e le sue relazioni con altri ciprinidi dell’Asia orientale con una precisione senza precedenti. Questa risorsa aiuterà a raffinare la classificazione dei pesci, guiderà gli sforzi di conservazione per gli ecosistemi di torrente vulnerabili e approfondirà la nostra comprensione di come piccole differenze nel DNA possano generare la ricca diversità osservata nei pesci d’acqua dolce.
Citazione: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Parole chiave: assemblaggio del genoma, pesce d'acqua dolce, da telomero a telomero, evoluzione dei pesci, genomica comparativa