Clear Sky Science · it
Metabarcoding e dati metagenomici lungo gradienti ambientali acquatici sulle coste di Francia e Cile
Vita nascosta in mari mutevoli
Lungo le coste del mondo, dalle tranquille lagune ai drammatici fiordi, la vita microscopica si adatta costantemente alle condizioni che cambiano. Questi minuscoli organismi guidano i cicli del carbonio e dei nutrienti che sostengono la pesca, la qualità dell’acqua e persino il clima. Tuttavia molte acque costiere, in particolare ambienti complessi come lagune e fiordi, sono state esplorate poco a livello genetico. Questo studio ha l’obiettivo di colmare questa lacuna creando un ricco dataset aperto sui microbi costieri di Francia e Cile, offrendo una nuova finestra su come la vita marina risponde a un ambiente in continuo mutamento.
Le coste come laboratori naturali
Le acque costiere raramente sono stabili. Piogge intense, apporti fluviali, evaporazione e maree possono far variare rapidamente temperatura e salinità su brevi distanze e tempi. I nutrienti che alimentano le microalghe possono aumentare o diminuire bruscamente, e le attività umane aggiungono ulteriori perturbazioni. Questa variabilità crea un mosaico di habitat che seleziona comunità microbiche diverse e favorisce nuove adattazioni. Per catturare questa complessità, i ricercatori hanno campionato 26 località lungo le coste francesi e cilene, tra cui lagune, estuari, fiordi, porti, spiagge, acque prossimali e un sito offshore. Alcuni siti francesi sono stati visitati mensilmente per un anno per seguire le stagioni, mentre i siti cileni sono stati campionati nell’autunno meridionale, fornendo un ampio istantaneo di mondi costieri a confronto. 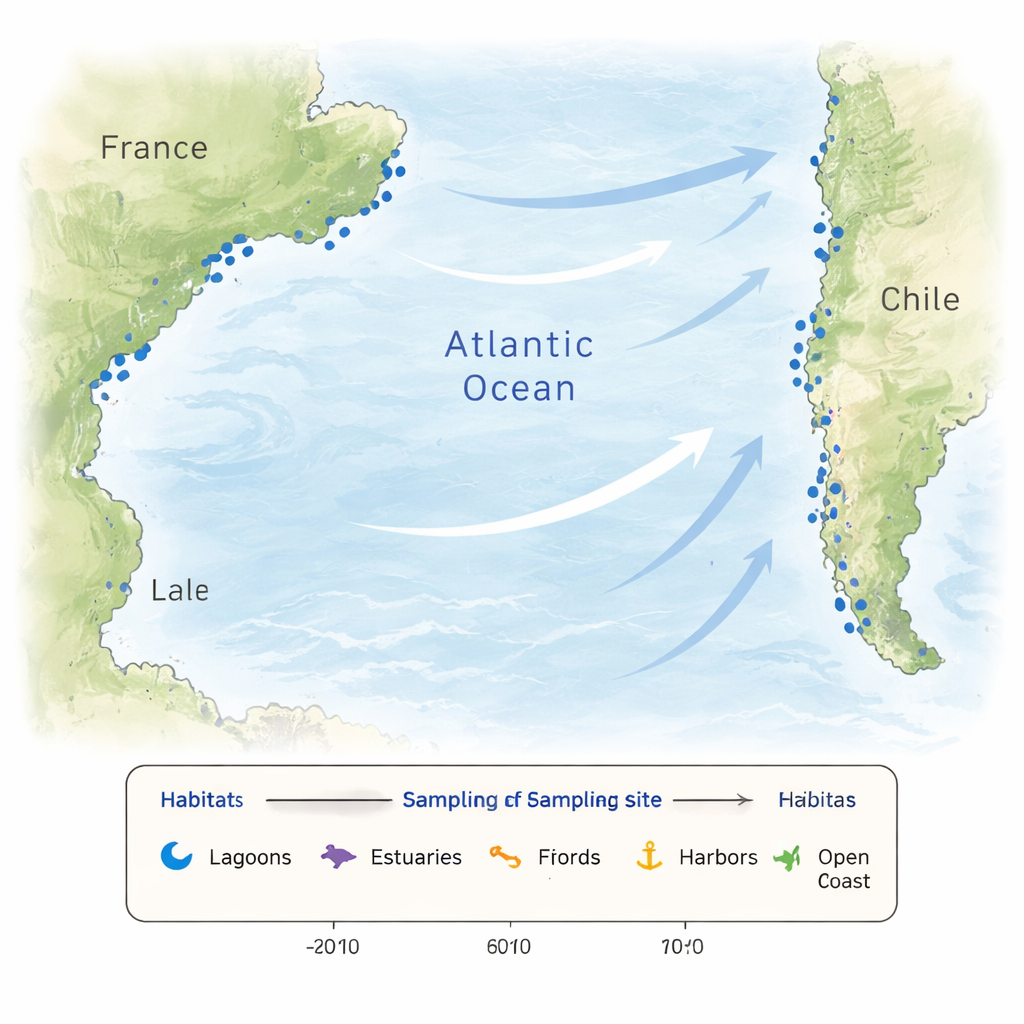
Da secchi d’acqua alle impronte del DNA
In ogni sito il team ha raccolto grandi volumi di acqua di mare, per lo più dalla superficie illuminata dal sole ma anche da strati più profondi in alcuni fiordi e nelle acque offshore selezionate. Sono state misurate condizioni ambientali di base come temperatura, salinità e nutrienti, insieme a indicatori di attività biologica quali clorofilla (un indicatore per le alghe), materia organica disciolta, produzione batterica e respirazione. In laboratorio i microbi sono stati concentrati su filtri fini e il loro DNA è stato estratto. Un insieme di test si è concentrato su un marcatore standard (16S rRNA), che funziona come un codice a barre per identificare batteri e archei. Questo approccio di metabarcoding ha rivelato oltre 53.000 varianti di DNA distinte e ha mostrato che alcuni campioni condividevano appena tre varianti, sottolineando quanto possano differire le comunità vicine.
Ricostruire genomi da una zuppa genetica
La seconda linea di analisi ha seguito una via più ambiziosa: il shotgun metagenomico, in cui tutto il DNA presente in un campione viene sequenziato simultaneamente. Utilizzando metodi avanzati di assemblaggio e binning, il team ha ricostruito 1.372 genomi provvisori, noti come metagenome-assembled genomes (MAG). Molti di questi genomi non hanno trovato corrispondenze con specie note, e solo circa il 4% si allineava a specie microbiche formalmente descritte. In alcuni gruppi, come certi batteri e archei adattati a condizioni insolite, più della metà delle proteine previste non aveva una funzione nota. I ricercatori hanno inoltre costruito un vasto catalogo genico di oltre 23 milioni di geni non ridondanti, scoprendo che approssimativamente il 31% non aveva corrispondenze nei principali database di riferimento. Ciò indica un profondo serbatoio di biologia non caratterizzata presente nelle acque costiere.
Habitat estremi, strumenti innovativi
Alcuni siti, in particolare lagune ipersaline in Francia, si sono distinti come punti caldi di novità genetica. In quei luoghi la salinità è passata da quasi quella normale dell’acqua di mare a più del doppio in pochi mesi. Queste condizioni stressanti possono favorire i cosiddetti microrganismi estremotolleranti dotati di enzimi funzionanti anche in presenza di alte concentrazioni saline o temperature elevate. Tali enzimi sono sempre più ricercati per impieghi industriali nei detersivi, nei biocarburanti, nella bonifica dell’inquinamento e nella trasformazione alimentare. Collegando misure ambientali dettagliate con dati su geni e genomi, questo dataset aiuta a individuare dove sia più probabile trovare organismi insoliti e strumenti biochimici innovativi. 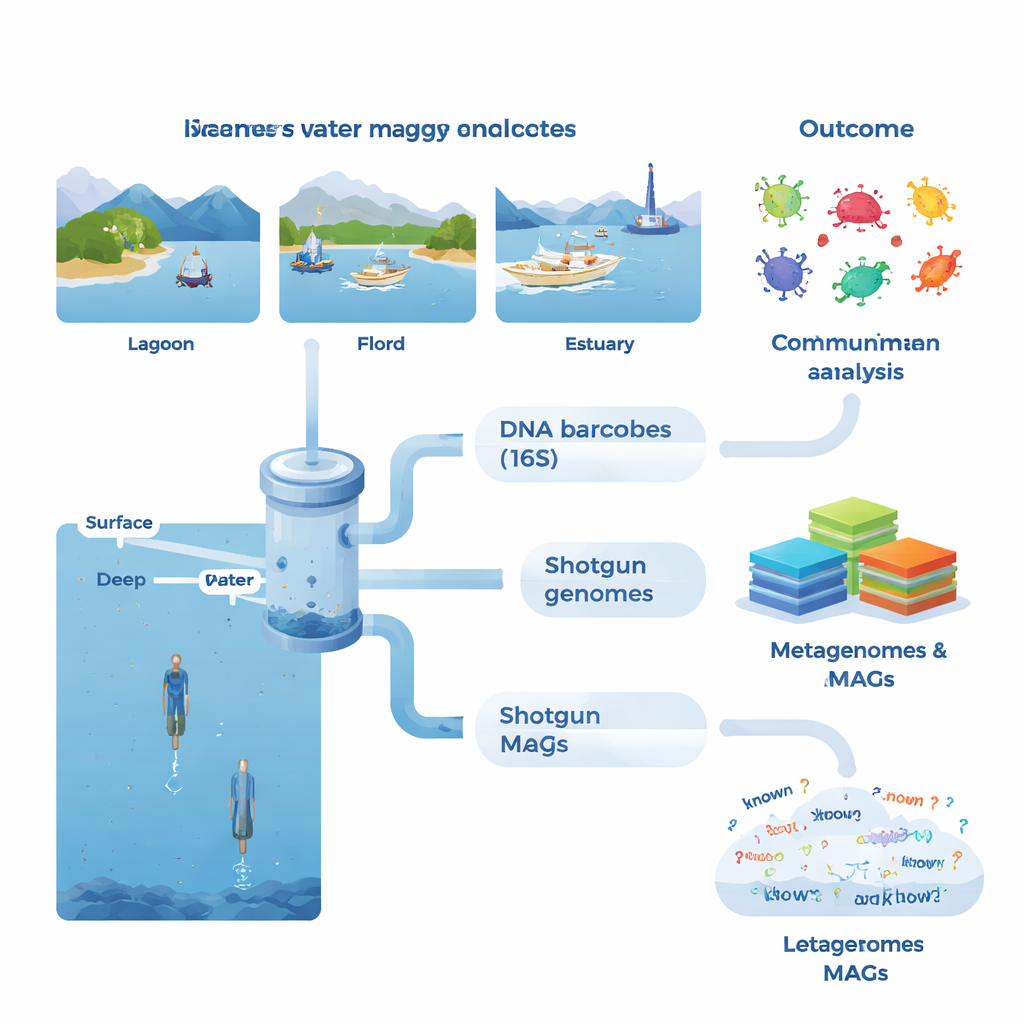
Una risorsa pubblica per il futuro degli oceani
Piuttosto che presentare una singola scoperta, questo lavoro fornisce una risorsa aperta e accuratamente validata che altri scienziati possono esplorare. Tutte le sequenze di DNA, le ricostruzioni di genomi, i cataloghi genici e le misure ambientali sono archiviate pubblicamente, insieme al codice informatico usato per elaborarli. Per i non specialisti, il messaggio principale è che i microbi costieri sono sia diversificati sia pieni di sorprese, soprattutto in ambienti trascurati come lagune e fiordi. Man mano che i ricercatori sfrutteranno questi dati, saranno meglio attrezzati per capire come la vita microscopica lungo le nostre coste risponda al riscaldamento, all’inquinamento e alle perturbazioni — e per valorizzare nuovi geni che potrebbero avvantaggiare la biotecnologia e la gestione ambientale.
Citazione: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Parole chiave: microbiomi costieri, metagenomica, lagune e fiordi, biodiversità marina, DNA ambientale