Clear Sky Science · it
Sequenze di immagini fogliari ad alta risoluzione con allineamento geometrico per la fenotipizzazione dinamica delle malattie fogliari
Osservare la malattia delle piante che si sviluppa in tempo reale
Agricoltori e giardinieri di solito notano le malattie delle piante solo dopo che sono apparse macchie brune e striature gialle. Ma cosa succederebbe se potessimo osservare quei sintomi emergere, ora dopo ora, e capire esattamente come il meteo, le varietà vegetali e i diversi patogeni modellano un focolaio? Questo articolo presenta un dataset pubblico che fa proprio questo per il grano, una delle colture alimentari più importanti al mondo. Seguendo singole foglie con una fotocamera per giorni e settimane, gli autori aprono una nuova finestra su come le malattie fogliari iniziano, si diffondono e interagiscono.
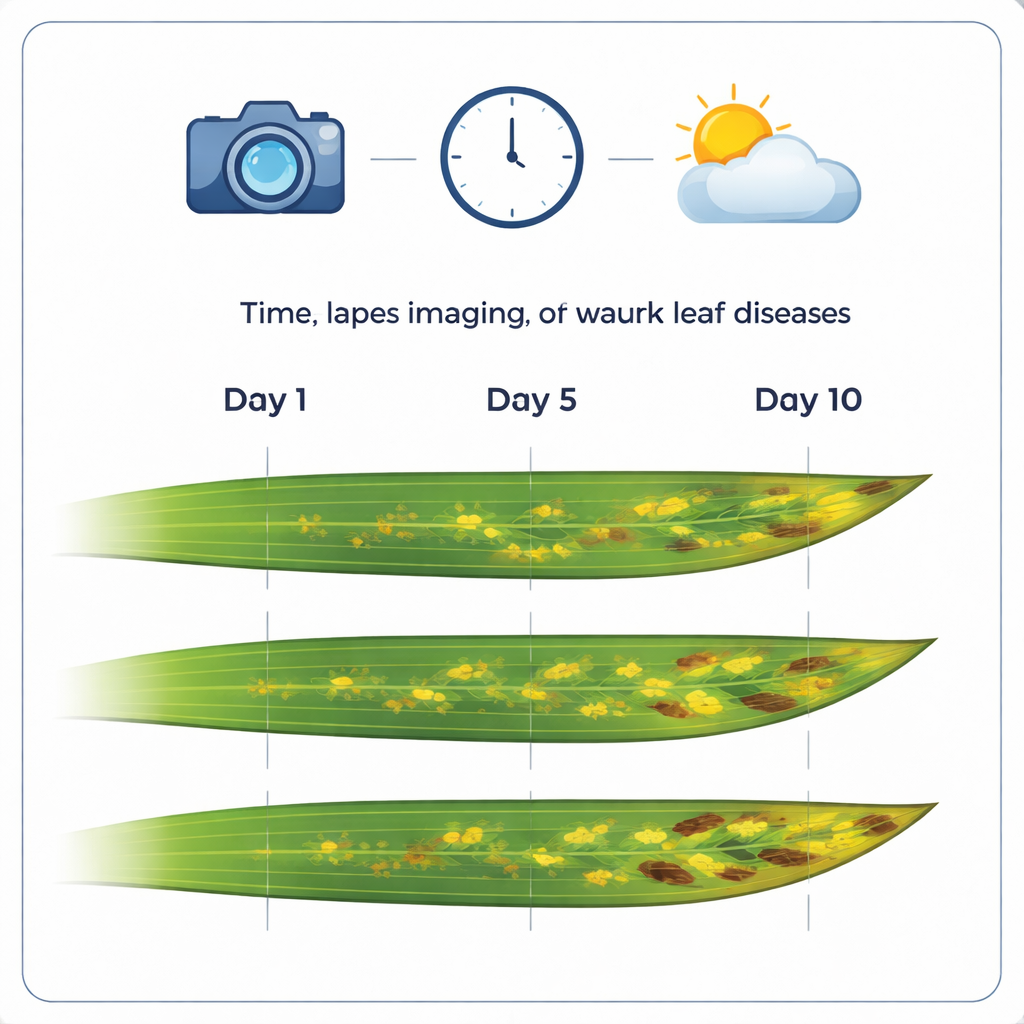
Una nuova libreria fotografica di foglie malate
Il nucleo del lavoro è una raccolta accuratamente assemblata di 12.520 immagini a colori ad alta risoluzione di foglie di grano. Queste immagini sono raggruppate in 1.032 sequenze time-lapse, ciascuna delle quali segue la stessa foglia per circa due settimane con foto quasi quotidiane. Molte delle foglie mostrano malattie importanti del grano come la ruggine bruna, la ruggine gialla e la Septoria tritici blotch. Mantenendo una risoluzione delle immagini molto fine (circa tre centesimi di millimetro per pixel), il dataset cattura dettagli piccoli come singole lesioni, pustole di ruggine e minuscoli corpi fruttiferi dove i funghi producono spore.
Mantenere ogni foglia nello stesso posto
Uno dei maggiori ostacoli tecnici nello studio di serie temporali di questo tipo è che le foglie si muovono e cambiano forma. Per risolvere il problema, i ricercatori hanno appiattito delicatamente ogni foglia contro una lastra trasparente e aggiunto piccoli segni di inchiostro bianco come punti di riferimento. Il software di visione artificiale ha poi usato questi segni per allineare tutte le immagini di una sequenza in modo che la stessa porzione di tessuto appaia nella stessa posizione giorno dopo giorno. L'errore di allineamento mediano è di soli 0,16 millimetri—sufficiente per tracciare la maggior parte delle lesioni mentre si espandono. Insieme alle immagini, il team fornisce le trasformazioni matematiche usate per l'allineamento, così altri possono testare metodi alternativi o migliorare quelli esistenti.
Dalle immagini a una malattia misurabile
Dopo l'allineamento, gli autori hanno applicato modelli di deep learning per individuare e delineare i sintomi su ciascuna foglia. La pipeline di elaborazione rileva punti chiave, segmenta le aree malate e collega la stessa lesione su più giorni in base a quanto si sovrappongono le regioni delineate. Ciò rende possibile misurare la velocità di crescita delle singole macchie, quando compariscono nuove pustole e quanti corpi fruttiferi si sviluppano. Il dataset include anche registrazioni meteorologiche, informazioni sui trattamenti con fungicidi e inoculazioni, e dettagli su 15 cultivar di grano con forme delle foglie e livelli di resistenza contrastanti. Questi elementi aggiuntivi permettono agli scienziati di esplorare come lo sviluppo della malattia dipenda dalla genetica delle piante, dalle scelte di gestione e dalle condizioni del campo in evoluzione.
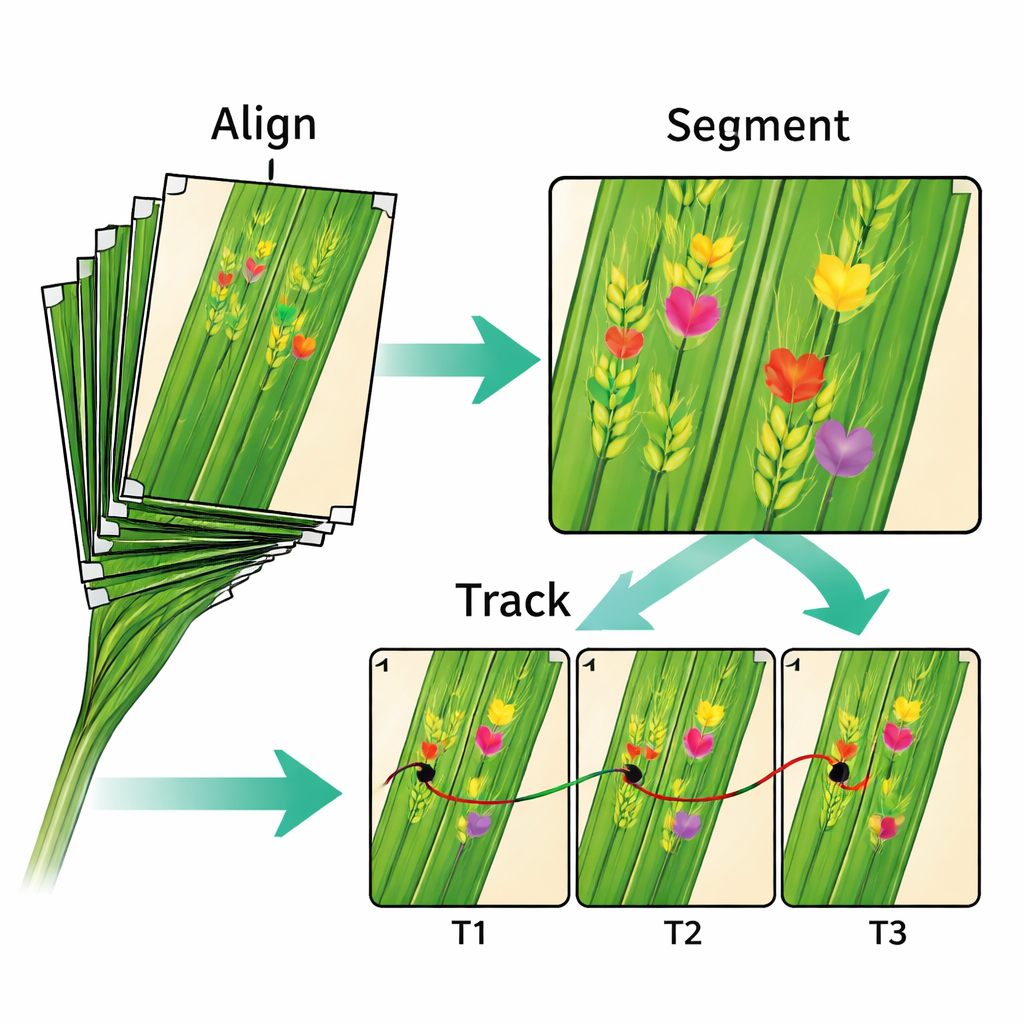
Testare strumenti di imaging più intelligenti
Oltre alla salute delle piante in sé, il dataset è un terreno di prova per informatici e ingegneri. Gli autori mostrano come il loro approccio attuale a passaggi—prima allineare, poi segmentare, poi tracciare—funzioni ragionevolmente bene ma perda ancora contesto e richieda controlli di qualità manuali. Sostengono che la vera opportunità risieda in sistemi più integrati, “end-to-end”, che apprendano contemporaneamente l'allineamento, il rilevamento dei sintomi e il tracciamento, ispirandosi a progressi analoghi nell'imaging medico. Poiché i dati includono sia immagini grezze sia output processati come maschere e coordinate dei marker, i ricercatori possono valutare nuovi algoritmi e confrontarli direttamente con la pipeline esistente.
Cosa significa per i raccolti futuri
Per i non specialisti, il messaggio pratico è che stiamo imparando a monitorare le malattie delle piante con la stessa precisione e continuità utilizzata in medicina moderna. Trasformando le foglie in storie time-lapse invece che in singoli istantanee, questo dataset aiuta gli scienziati a individuare quali tipi di resistenza contano davvero sul campo e sotto quali condizioni meteorologiche i focolai accelerano o rallentano. Sebbene i dati attuali provengano da una singola località e si concentrino sul grano, i metodi e gli strumenti possono essere adattati ad altre colture e stress. A lungo termine, tale tracciamento dettagliato potrebbe orientare i miglioratori verso resistenze più durature alle malattie e supportare sistemi di allerta precoce che proteggano le rese prima che il danno diventi visibile a occhio nudo.
Citazione: Anderegg, J., McDonald, B.A. High-Resolution Leaf Image Sequences with Geometric Alignment for Dynamic Phenotyping of Foliar Diseases. Sci Data 13, 247 (2026). https://doi.org/10.1038/s41597-026-06567-y
Parole chiave: malattie delle foglie del grano, time lapse, fenotipizzazione delle piante, patologia vegetale digitale, resistenza alle malattie delle colture