Clear Sky Science · it
Cereblon induce la degradazione come neosubstrato di G3BP2 tramite mimica della superficie molecolare
Trasformare la pulizia cellulare in un sistema di targeting intelligente
I farmaci moderni puntano sempre più spesso a risolvere le malattie non solo bloccando proteine problematiche, ma eliminandole del tutto. Questo studio esplora un modo ingegnoso per riconfigurare una delle macchine di “pulizia” della cellula in modo che, associata a una piccola molecola, possa riconoscere e distruggere una proteina collegata al cancro e ad altri disturbi. Il lavoro rivela un trucco inaspettato: la macchina di pulizia rimodella una parte della sua superficie per imitare uno dei partner naturali della proteina, consentendole di agganciarsi e inviare la proteina al “cestino” cellulare.
Il netturbino della cellula con flessibilità nascosta
Le nostre cellule marcano costantemente le proteine logore o indesiderate per la distruzione, usando un sistema costruito attorno alle E3 ligasi—complessi proteici ampi che decidono cosa eliminare. Uno di questi complessi si basa su un componente chiamato cereblon, che funziona come un sensore che riconosce caratteristiche specifiche ("degroni") su altre proteine. Alcuni farmaci già approvati sfruttano cereblon agendo come “colla molecolare”: si legano a cereblon e creano una nuova superficie di aggancio che attrae proteine legate alla malattia, le quali vengono quindi marcate e degradate. Fino ad ora, la maggior parte dei bersagli noti utilizzava un particolare schema strutturale, il che faceva sembrare limitato l’insieme di proteine rimovibili in questo modo.
Scoprire un nuovo bersaglio oltre le regole vecchie
Nello studio recente, gli autori hanno testato una raccolta di colla molecolare focalizzate su cereblon in cellule umane e hanno identificato un composto chiamato MRT-5702. Questa piccola molecola ha provocato la rapida scomparsa di una proteina denominata G3BP2, che aiuta a gestire l’RNA e fa parte dei grumi di stress—aggregati associati a cancro, problemi cardiaci e malattie neurodegenerative. Importante, G3BP2 non presenta il consueto motivo degron riconosciuto da cereblon. Esperimenti cellulari di follow-up, incluse letture sensibili basate sulla luce per valutare la prossimità tra proteine, hanno confermato che MRT-5702 avvicina cereblon e G3BP2 in un complesso ternario che porta alla degradazione di G3BP2, risparmiando la sua proteina strettamente correlata G3BP1 a meno che non venga scambiato il suo dominio chiave.
L’imitazione come strategia di legame
Approfondendo, i ricercatori si sono chiesti come G3BP2 potesse legarsi a cereblon senza il motivo di riconoscimento standard. Invece di cercare somiglianze tra G3BP2 e bersagli cereblon conosciuti, hanno capovolto la domanda: cereblon potrebbe assomigliare a uno dei partner abituali di G3BP2? Le proteine G3BP interagiscono comunemente con altre molecole tramite un punto caldo su una regione chiamata dominio NTF2-like, che normalmente riconosce brevi motivi di sequenza. Utilizzando modelli strutturali del partner naturale di G3BP2, USP10, il gruppo ha scansionato computazionalmente la superficie di cereblon e ha individuato una zona su una regione meno studiata, il dominio LON, che imita da vicino forma e chimica del motivo di legame di USP10. Mutare solo alcuni amminoacidi chiave su questa patch, o nel punto caldo di G3BP2, ha indebolito il complesso ternario, suggerendo che cereblon si stia effettivamente spacciando per USP10 per agganciarsi a G3BP2.
Catturare la nuova interfaccia in dettaglio atomico
Per visualizzare questa interazione insolita, il team ha usato crio–microscopia elettronica ad alta risoluzione per risolvere la struttura di un complesso contenente cereblon, un altro componente core della ligasi, MRT-5702 e il dominio NTF2-like di G3BP2. Le immagini hanno rivelato che un anello flessibile nel dominio LON di cereblon si piega e si rimodella per formare quasi metà della superficie di contatto con G3BP2. La forma attiva enantiomerica di MRT-5702 si trova nella consueta tasca di legame dei farmaci di cereblon ma, insieme all’anello, contribuisce a creare un ampio piano di atterraggio che accoglie una metà del dimero di G3BP2. È sorprendente che questa disposizione utilizzi scarsamente il sito canonico di cereblon che gestisce i precedenti bersagli da colla, mostrando che cereblon può impegnare regioni molto diverse della sua superficie a seconda della colla e della proteina coinvolta. Allo stesso tempo, l’altra metà del dimero di G3BP2 rimane libera per legare altri partner, offrendo una via plausibile per la degradazione “collaterale” di proteine che capitano di essere adese.
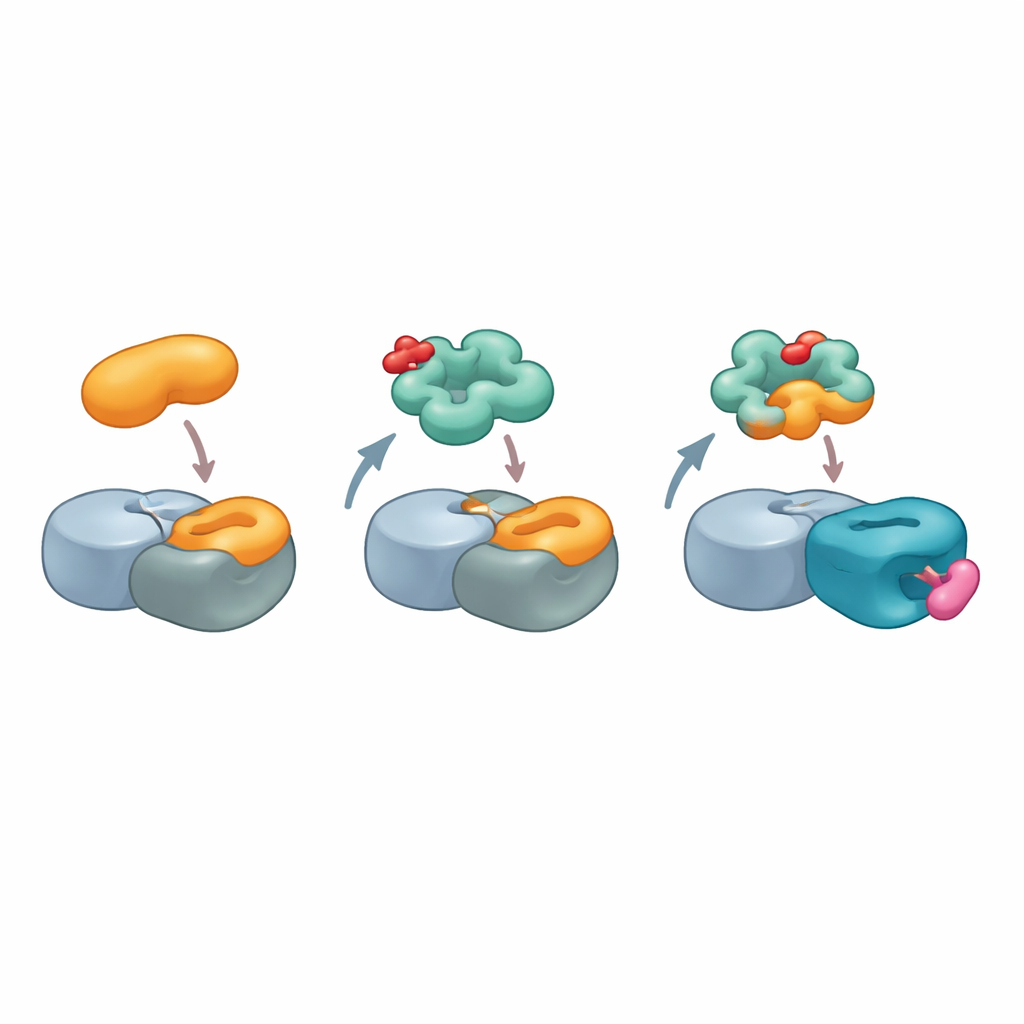
Impronte di colla per il design di farmaci futuri
Nel complesso, i risultati dipingono cereblon come un intermediario molto più versatile di quanto si pensasse. Piuttosto che pretendere che i bersagli portino un unico tipo di degron, cereblon può, quando è armato con la colla molecolare giusta, plasmare una superficie composita che imita contatti proteina–proteina naturali presenti altrove nella cellula. Gli autori propongono che tali superfici combinate di proteina e colla, che chiamano "glueprints", possano essere mappate e progettate per imitare punti caldi di interazione esistenti su molte proteine legate a malattie. Per il lettore non specialistico, il messaggio chiave è che gli sviluppatori di farmaci potrebbero non dover scoprire nuovi siti di legame sulle proteine problematiche; invece, possono insegnare alla stessa macchina di riciclo della cellula a riconoscere quelle proteine copiando con ingegno le forme dei loro partner abituali, ampliando notevolmente il ventaglio di bersagli che possono essere rimossi in modo sicuro e selettivo.
Citazione: Annunziato, S., Quan, C., Donckele, E.J. et al. Cereblon induces G3BP2 neosubstrate degradation using molecular surface mimicry. Nat Struct Mol Biol 33, 479–487 (2026). https://doi.org/10.1038/s41594-025-01738-8
Parole chiave: degradatori a colla molecolare, cereblon, degradazione mirata delle proteine, G3BP2, interazioni proteina–proteina