Clear Sky Science · it
Un modello fondamentale generalizzabile per l’analisi della risonanza magnetica del cervello umano
Insegnare ai computer a leggere le scansioni cerebrali
La risonanza magnetica (MRI) consente ai medici di osservare il cervello vivo senza interventi chirurgici, ma interpretare queste immagini dipende ancora in larga misura da esperti umani e da grandi set di dati etichettati. Questo studio presenta BrainIAC, una sorta di “motore cerebrale a uso generale” che apprende da decine di migliaia di scansioni cerebrali non etichettate e può quindi essere rapidamente adattato a molte questioni cliniche — dalla stima dell’età cerebrale alla delineazione dei tumori — spesso con solo una manciata di esempi. Per i pazienti, una tecnologia di questo tipo potrebbe alla lunga significare diagnosi più rapide, pianificazione terapeutica migliore e accesso a strumenti di imaging avanzato anche in ospedali con competenze specialistiche limitate.
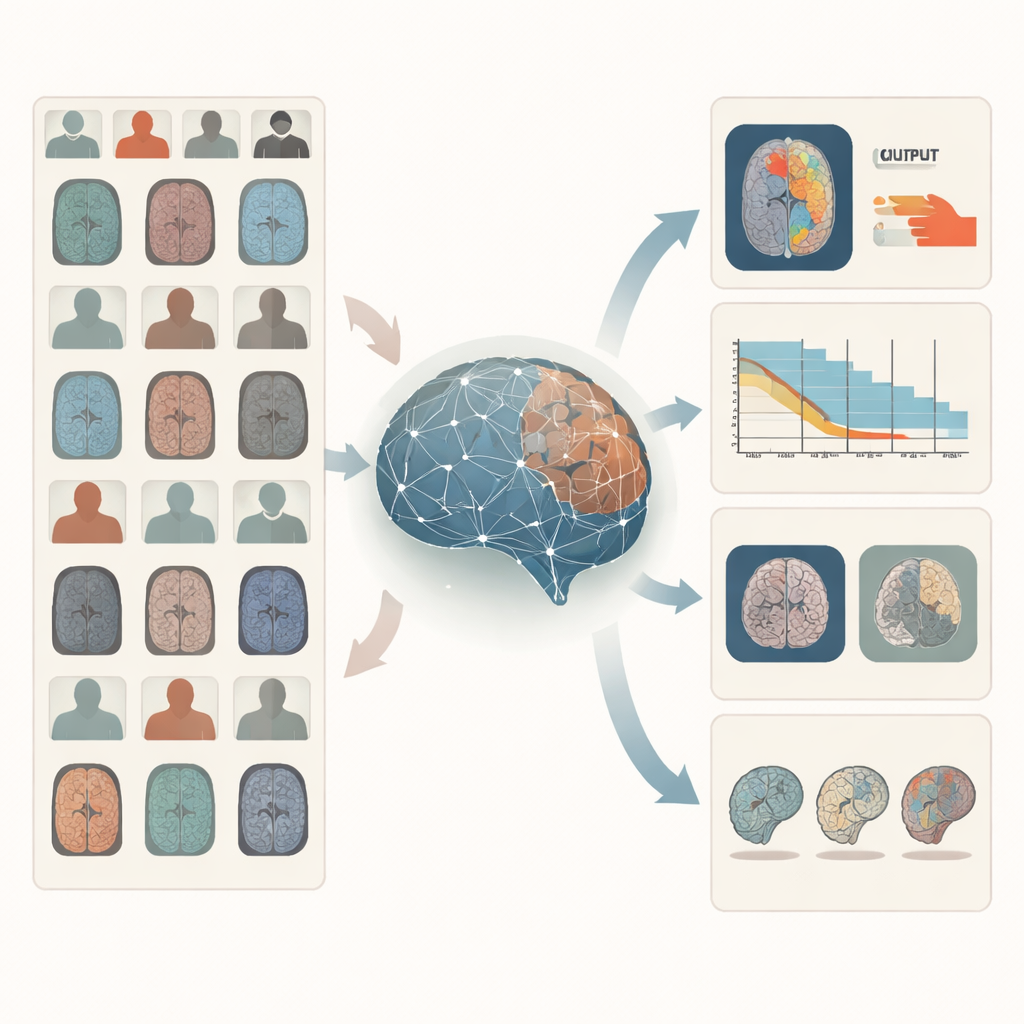
Perché le scansioni cerebrali sono difficili per i computer
La MRI cerebrale è ricca di informazioni ma complessa. Una singola persona può essere scansionata con diverse impostazioni, ciascuna evidenziando tessuti o caratteristiche patologiche differenti. Gli ospedali usano una varietà di scanner e protocolli, quindi le immagini possono apparire molto diverse da un luogo all’altro. Inoltre, le etichette esperte dettagliate — per esempio tracciare con precisione i confini di un tumore o seguire la sopravvivenza a lungo termine — sono costose e rare. I sistemi di intelligenza artificiale tradizionali sono solitamente addestrati per un compito ristretto su un dataset curato e tendono a incontrare difficoltà quando vengono applicati in nuovi ospedali, per malattie rare o per domande per le quali non sono stati progettati specificamente.
Un singolo modello centrale per molte attività cerebrali
BrainIAC prende una strada diversa: invece di apprendere un compito alla volta, impara innanzitutto il “linguaggio” generale della struttura cerebrale e della malattia da 32.015 scansioni MRI provenienti da 34 dataset e dieci condizioni neurologiche, per un totale di quasi 49.000 scansioni nel pool completo. Il modello è addestrato in modo self-supervised, il che significa che non richiede etichette umane. Esamina molte piccole patch tridimensionali tagliate dalle scansioni dell’intero cervello e impara a distinguere quando due versioni diverse e aumentate provengono dalla stessa posizione oppure da cervelli diversi. Avvicinando le patch corrispondenti e allontanando quelle non correlate nel suo spazio interno, BrainIAC costruisce una rappresentazione flessibile di come appaiono comunemente cervelli sani e malati attraverso età, scanner e ospedali.
Mettere in funzione il motore cerebrale
Una volta appresa questa rappresentazione centrale, i ricercatori testano BrainIAC su sette compiti concreti che rispecchiano problemi clinici reali. Questi includono ordinare le scansioni per tipo di sequenza MRI, stimare l’età apparente del cervello, prevedere se un tumore cerebrale porta una mutazione genetica chiave, prevedere la sopravvivenza per pazienti con tumori aggressivi, distinguere problemi di memoria precoci dall’invecchiamento normale, stimare da quanto tempo si è verificato un ictus e delineare i tumori sulle immagini. Per ogni compito confrontano tre strategie: addestrare un modello da zero solo su quel compito, partire da modelli di imaging medico precedenti costruiti per altri scopi, oppure affinare (fine-tuning) le caratteristiche cerebrali già apprese da BrainIAC. In generale, BrainIAC eguaglia o supera le alternative, soprattutto quando sono disponibili solo dati etichettati limitati.
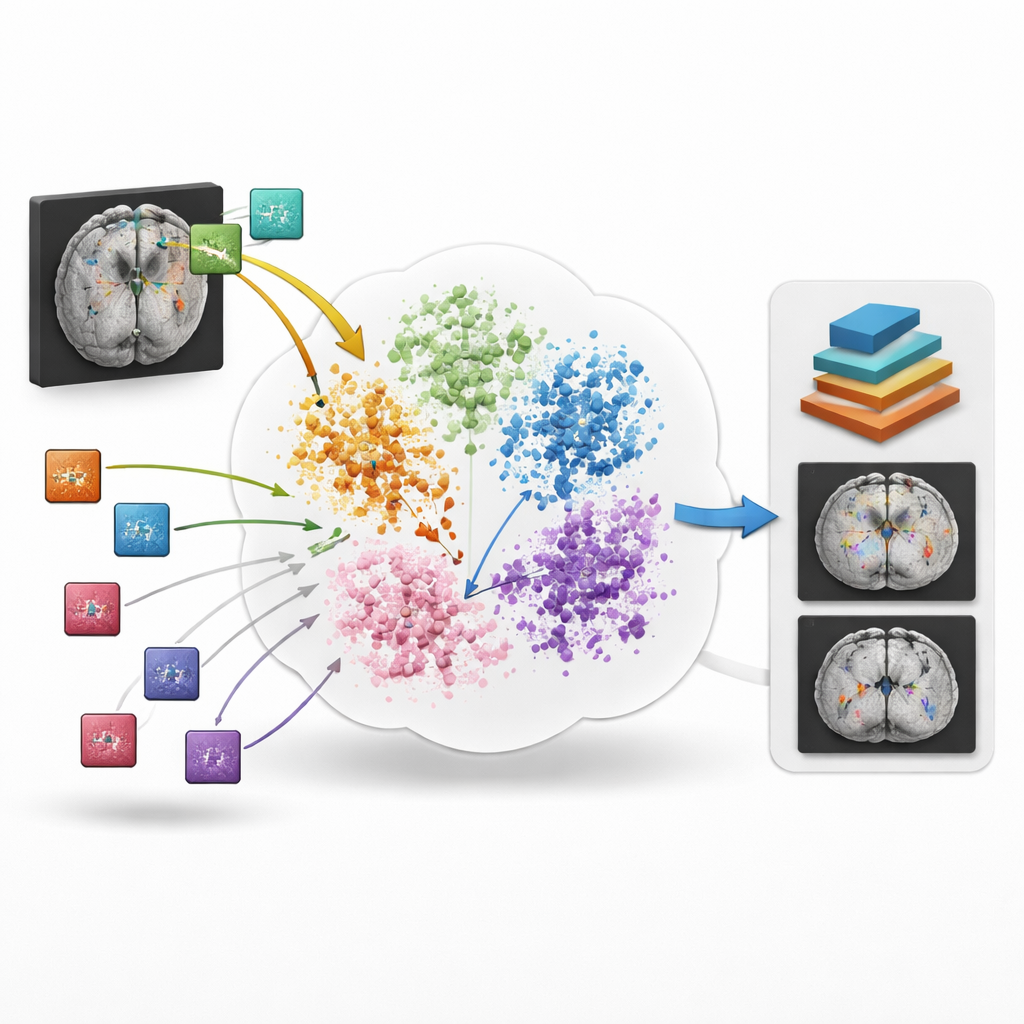
Funzionare bene quando i dati scarseggiano
Una prova fondamentale è come il sistema si comporta quando i dati etichettati sono estremamente scarsi, come spesso accade con malattie rare o studi di imaging costosi. Il team esplora scenari in cui si usa solo il 10% delle scansioni di addestramento abituali e situazioni ancora più difficili di “few-shot” con soltanto uno o cinque esempi etichettati per classe. In queste condizioni ristrette, BrainIAC fornisce costantemente previsioni più accurate rispetto a modelli addestrati da zero o ad altri modelli fondamentali disponibili. Per esempio, distingue meglio tipi sottili di sequenze MRI, predice con maggiore precisione la genetica dei tumori e la sopravvivenza, e disegna contorni tumorali più puliti usando molte meno immagini annotate. Il modello si dimostra inoltre più stabile quando vengono aggiunti artificialmente artefatti comuni della MRI, come variazioni di contrasto o distorsioni legate allo scanner, suggerendo che ha imparato caratteristiche robuste piuttosto che scorciatoie fragili.
Cosa potrebbe significare per pazienti e clinici
Per capire se BrainIAC si concentra su regioni clinicamente rilevanti, gli autori generano «mappe di attenzione» visive che mostrano dove il modello guarda quando prende decisioni. Queste mappe evidenziano strutture come l’ippocampo per i problemi di memoria precoci, regioni della sostanza bianca per la stima dell’età e il nucleo del tumore per le previsioni genetiche e di sopravvivenza — aree che si allineano con l’intuizione degli esperti umani. Poiché BrainIAC può essere integrato in diverse pipeline di analisi e può essere adattato con un minimo addestramento aggiuntivo, offre una spina dorsale flessibile per futuri strumenti di imaging, incluse potenziali combinazioni con cartelle cliniche o dati genetici.
Un passo verso un imaging cerebrale più intelligente e accessibile
Nel complesso, lo studio mostra che un singolo modello fondamentale addestrato con cura può servire come punto di partenza solido per molte diverse attività sulla MRI cerebrale, spesso superando sistemi specializzati che devono essere ricostruiti da zero ogni volta. Per i non specialisti, la conclusione principale è che BrainIAC agisce come un «lettore del cervello» ampiamente istruito che può apprendere rapidamente nuove competenze con solo pochi esempi. Pur non sostituendo modelli su misura o il giudizio medico, pone basi importanti per rendere le previsioni basate sulle immagini più accurate, più robuste e più ampiamente disponibili, anche in situazioni in cui raccogliere grandi dataset etichettati sarebbe altrimenti impossibile.
Citazione: Tak, D., Garomsa, B.A., Zapaishchykova, A. et al. A generalizable foundation model for analysis of human brain MRI. Nat Neurosci 29, 945–956 (2026). https://doi.org/10.1038/s41593-026-02202-6
Parole chiave: risonanza magnetica cerebrale, IA medica, modelli fondamentali, apprendimento self-supervised, neuroimmagine