Clear Sky Science · it
MaAsLin 3: perfezionare ed estendere modelli lineari generalizzati multivariabili per la scoperta di associazioni meta-omiche
Perché i piccoli vicini intestinali contano
I nostri corpi ospitano trilioni di microbi che aiutano a digerire il cibo, addestrano il sistema immunitario e possono persino influenzare il nostro umore. Con il sequenziamento del DNA che ha reso semplice catalogare queste comunità microbiche, è emersa una domanda cruciale: quali microbi specifici sono associati a malattie come le malattie infiammatorie intestinali, o a tratti quotidiani come età e dieta? Rispondere si è dimostrato sorprendentemente difficile. I dati sono rumorosi, pieni di zeri e riportati come percentuali anziché conti veri. Questo articolo presenta MaAsLin 3, un nuovo strumento statistico progettato per estrarre segnali più chiari dai dati di microbioma disordinati, così che i ricercatori possano collegare in modo più affidabile i microbi alla salute umana e all’ambiente.
Cercare schemi in una folla rumorosa
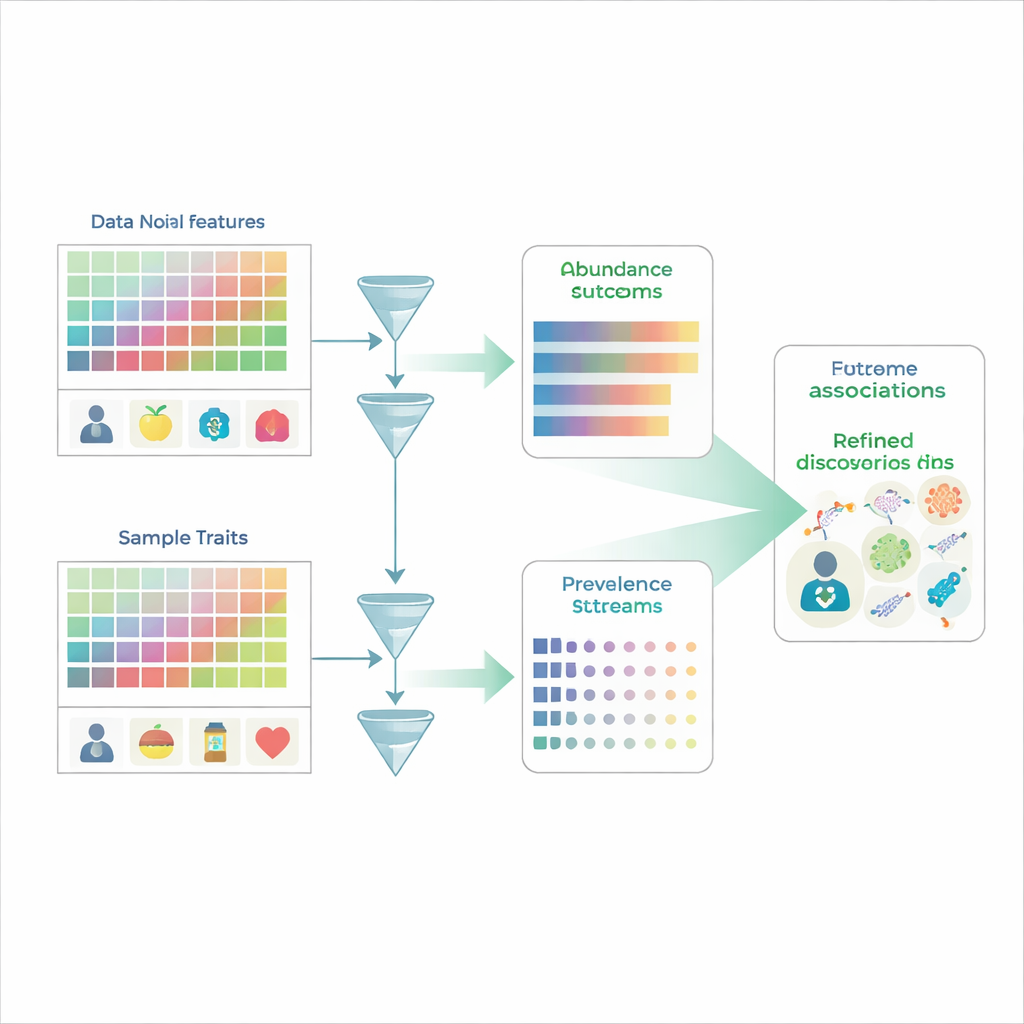
Gli studi tradizionali sul microbioma funzionano un po’ come contare volti in una folla: i ricercatori misurano l’abbondanza relativa di centinaia o migliaia di specie microbiche in molte persone e poi valutano quali specie differiscono, per esempio, tra gruppi malati e sani. Ma i dati del microbioma sono vincolati a percentuali che devono sommare al 100%, quindi se una specie aumenta, almeno un’altra sembra diminuire anche se la sua quantità reale non è cambiata. Inoltre, molte specie semplicemente non vengono rilevate in un campione, producendo molti zeri che possono riflettere sia una reale assenza sia limiti di rilevamento. I metodi di analisi comuni tendono a confondere due domande distinte—se un microbo è presente o no, e quanto è abbondante quando è presente—rendendo facile fraintendere la biologia sottostante.
Separare presenza e quantità
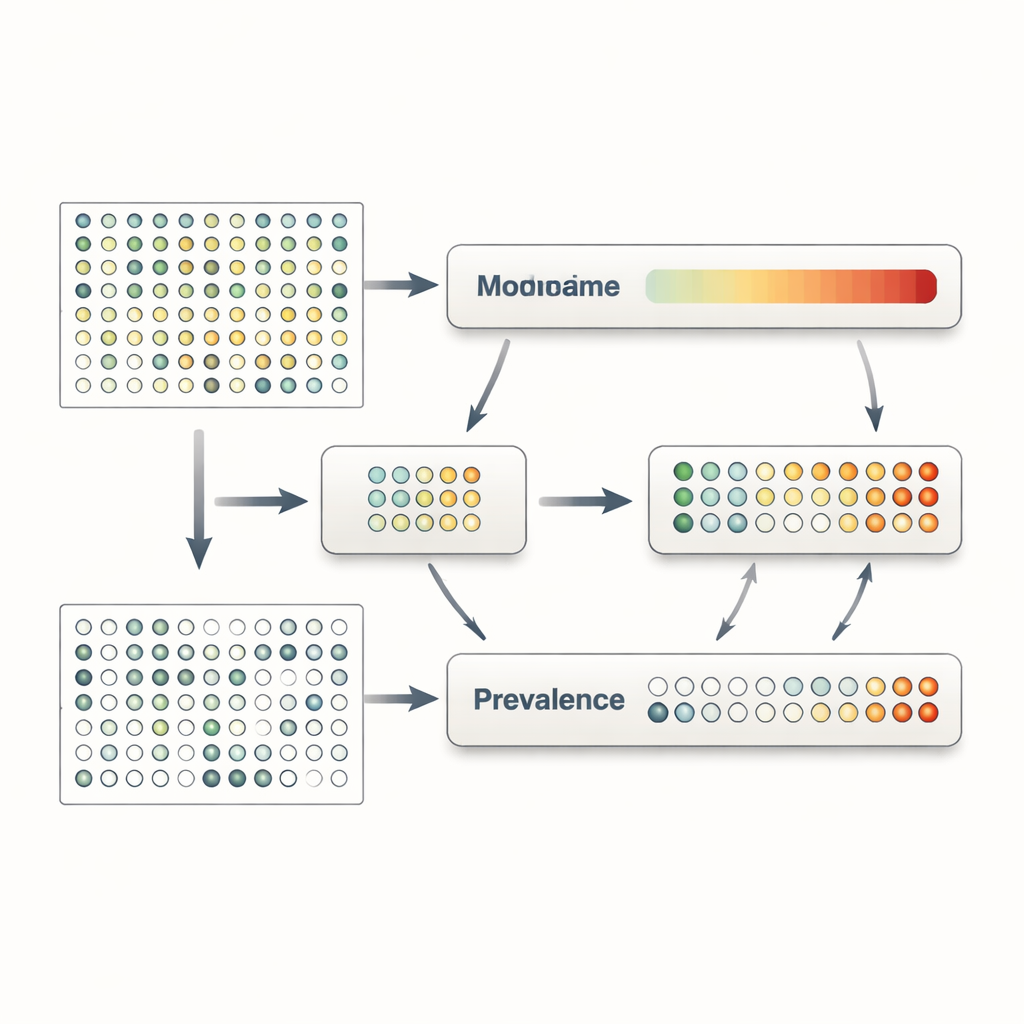
MaAsLin 3 affronta questi problemi trattando esplicitamente presenza e quantità come fenomeni separati ma correlati. Per ogni caratteristica microbica—come una specie, un gene o una via metabolica—costruisce due modelli in parallelo. Un modello esamina la prevalenza, chiedendo quanto spesso la caratteristica viene rilevata nei campioni con tratti diversi. L’altro modello si concentra sull’abbondanza, valutando come cambia il livello della caratteristica solo nei campioni in cui è stata rilevata. Suddividendo così i dati, MaAsLin 3 evita la scorciatoia comune di riempire gli zeri con numeri arbitrariamente piccoli, cosa che può distorcere i risultati. Combina quindi i due effetti in un quadro complessivo di come ciascuna caratteristica si relazioni a ogni tratto, pur consentendo ai ricercatori di vedere se un’associazione riguarda principalmente la presenza, la quantità o entrambe le cose.
Avvicinarsi alle quantità reali
Una complicazione aggiuntiva nella scienza del microbioma è che la maggior parte delle misurazioni è relativa: ci dicono quale frazione della comunità totale occupa una specie, non quante cellule ci sono effettivamente. Eppure le domande biologiche spesso dipendono dall’abbondanza assoluta—forse, per esempio, se il numero di cellule di un patogeno supera una soglia che potrebbe innescare la malattia. MaAsLin 3 offre due soluzioni complementari. Quando gli esperimenti includono informazioni aggiuntive, come quantità note di un organismo di riferimento o stime del carico microbico totale, il metodo può trasformare le percentuali relative in stime di conteggi assoluti e modellare direttamente questi ultimi. Quando tali dati non sono disponibili, MaAsLin 3 confronta invece il comportamento di ciascuna caratteristica con il modello tipico attraverso tutte le caratteristiche, che sotto assunzioni realistiche approssima ciò che si vedrebbe su scala assoluta. Ampie simulazioni al computer e test su dataset reali con abbondanze assolute misurate sperimentalmente mostrano che questa strategia recupera con precisione le tendenze sottostanti e supera diversi strumenti ampiamente usati.
Rivelare segnali nascosti nelle malattie intestinali
Per mostrare cosa significano questi progressi nella pratica, gli autori hanno applicato MaAsLin 3 a un’ampia coorte ben studiata di persone con e senza malattie infiammatorie intestinali come il morbo di Crohn e la colite ulcerosa. Lavori precedenti avevano già identificato molti cambiamenti microbici in queste condizioni, ma MaAsLin 3 ha aggiunto diversi livelli di sfumatura. Ha confermato la maggior parte dei legami noti chiarendo che circa tre quarti delle associazioni riguardavano cambiamenti nella probabilità che i microbi siano presenti, piuttosto che nella loro abbondanza quando presenti. In altre parole, l’infiammazione intestinale spesso coincideva con la perdita completa di alcuni microbi utili o con la mancata loro rilevazione, piuttosto che con una semplice diminuzione graduale dei loro livelli. Il metodo ha anche rivelato microbi la cui sola presenza—indipendentemente da quanto fossero abbondanti—era strettamente associata alla perturbazione della comunità intestinale legata alla malattia.
Cosa significa per studi futuri e cure
Per i non specialisti, il messaggio chiave è che il modo in cui analizziamo i dati del microbioma può plasmare in modo decisivo quali microbi riteniamo importanti per la salute. Gestendo meglio gli zeri, separando presenza e quantità e approssimando i conteggi reali, MaAsLin 3 offre una lente più nitida per scoprire marcatori microbici affidabili di malattia, dieta e ambiente. I risultati nelle malattie infiammatorie intestinali suggeriscono che molti cambiamenti di rilevanza clinica riguardano microbi che scompaiono o compaiono di nuovo, non solo quelli che aumentano o diminuiscono lentamente in abbondanza. Questa distinzione è importante per progettare terapie: se la malattia è legata alla perdita netta di specie benefiche, strategie che reintroducono o proteggono quei microbi potrebbero essere più efficaci di approcci che cercano solo di riequilibrare la comunità complessiva. MaAsLin 3 quindi mette a disposizione dei ricercatori un kit di strumenti più preciso e flessibile per trasformare misurazioni complesse del microbioma in intuizioni biologiche applicabili.
Citazione: Nickols, W.A., Kuntz, T., Shen, J. et al. MaAsLin 3: refining and extending generalized multivariable linear models for meta-omic association discovery. Nat Methods 23, 554–564 (2026). https://doi.org/10.1038/s41592-025-02923-9
Parole chiave: microbioma, malattie infiammatorie intestinali, modellizzazione statistica, abbondanza assoluta, prevalenza microbica