Clear Sky Science · it
Lo studio HUNT identifica fattori genetici ospite riproducibilmente associati alla composizione del microbiota intestinale umano
Perché i tuoi geni e i batteri intestinali contano
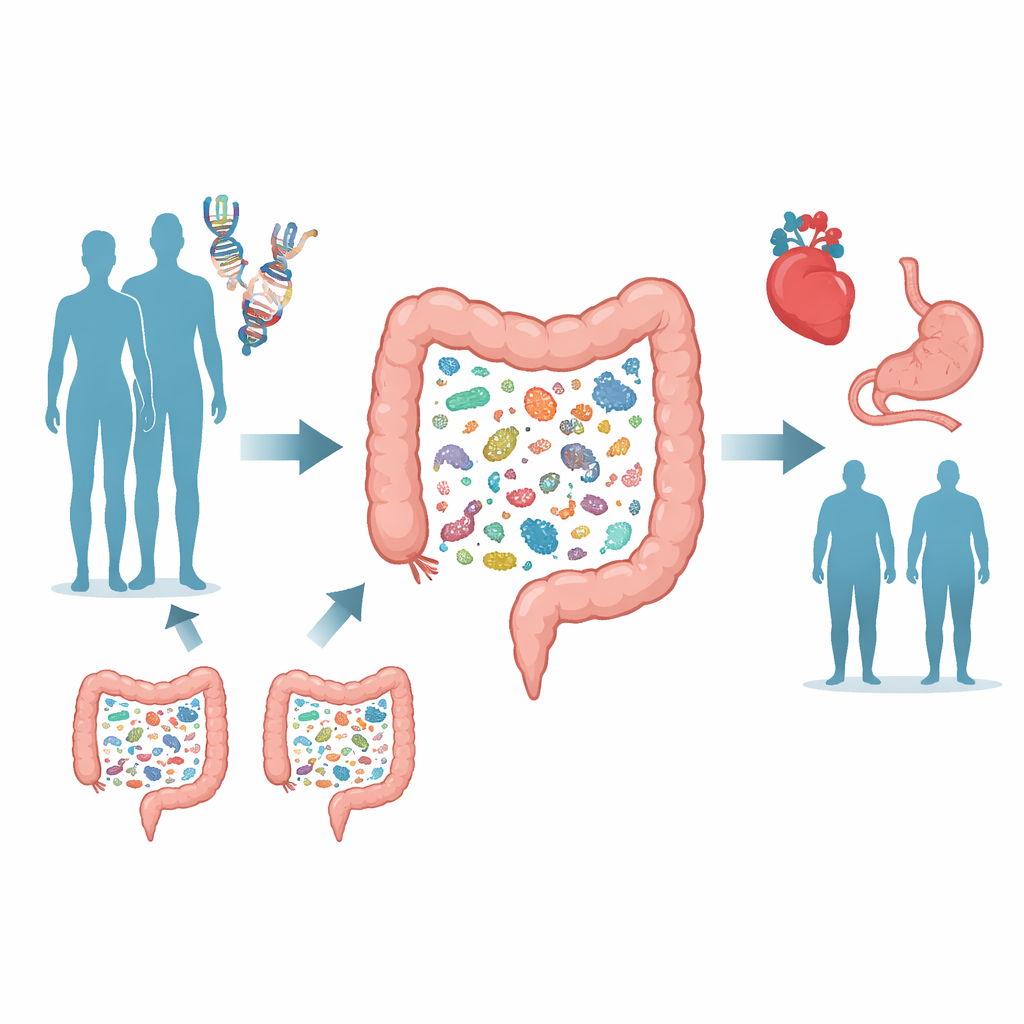
Ognuno di noi ospita trilioni di microbi nell’intestino che aiutano a digerire il cibo, addestrano il sistema immunitario e possono persino influenzare il rischio di malattia. Questo studio pone una domanda apparentemente semplice: quanto di quell’ecosistema interno è scritto nel nostro DNA? Scansionando i genomi di decine di migliaia di persone e confrontandoli con la composizione dettagliata dei loro microbi intestinali, i ricercatori mostrano che specifici geni umani spingono in modo coerente il microbioma in determinate direzioni—e che questi spostamenti si collegano a condizioni come la celiachia, le emorroidi e problemi cardiaci, oltre che al peso corporeo.
Cercare modelli in mezzo alla folla
Per individuare legami gene–microbo, il team ha fatto riferimento allo studio Trøndelag Health in Norvegia, dove oltre 12.000 adulti hanno fornito sia sangue per l’analisi del DNA sia campioni di feci per il profilo microbico. A differenza di molti progetti precedenti che usavano impronte batteriche relativamente grossolane, questo lavoro si è basato su sequenziamento metagenomico profondo, che legge gran parte del DNA di ciascun campione e può distinguere centinaia di specie batteriche distinte e le loro capacità metaboliche. Gli scienziati hanno poi eseguito uno studio di associazione genome-wide, scansionando quasi otto milioni di varianti genetiche umane per vedere quali si allineavano con differenze nell’abbondanza relativa di 546 specie intestinali comuni e con misure della diversità microbica complessiva.
Sei punti caldi genetici che plasmano l’intestino
L’analisi ha rivelato un’impronta genetica sorprendentemente forte. Sono emerse dodici associazioni robuste tra varianti del DNA umano e specie batteriche specifiche, raggruppate in sei regioni del genoma. Due di queste regioni, vicino al gene LCT coinvolto nella digestione del lattosio e al gene del gruppo sanguigno ABO, erano già state implicate in passato, ma quattro—vicino a HLA-DQB1, MUC12, SLC37A2 e FUT2—erano nuove o confermate per la prima volta. Per esempio, le persone con la versione persistente della lattasi del gene LCT tendevano ad avere meno Bifidobacterium adolescentis, una specie che prospera sullo zucchero del latte rimasto nell’intestino quando il lattosio non è completamente scisso. La regione FUT2, che influenza se gli zuccheri dei gruppi sanguigni sono esposti sulla superficie intestinale, è risultata collegata a diverse specie batteriche che sembrano nutrirsi di quelle superfici ricoperte di zuccheri.
Dai microbi al rischio di malattia
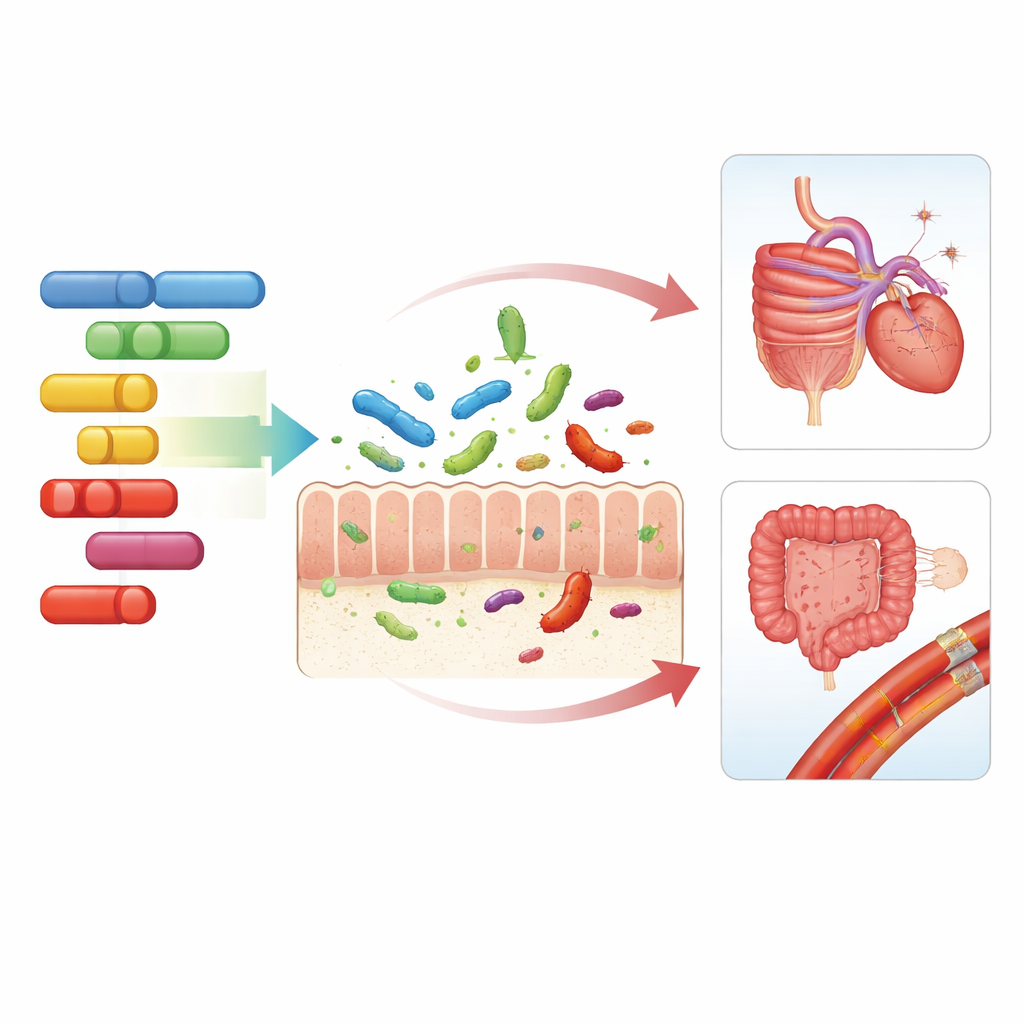
La storia si è fatta più intrigante quando i ricercatori hanno sovrapposto questi risultati genetici a grandi database di malattie umane. Varianti nella regione HLA-DQB1 associate a livelli più alti di una specie di Agathobacter erano anche correlate a un rischio ridotto di condizioni autoimmuni, inclusa la celiachia. Le persone con celiachia nella coorte norvegese tendevano a mostrare livelli particolarmente bassi di questo microbo, suggerendo che la malattia potrebbe, in parte, rimodellare la comunità intestinale. Un’altra regione, vicino al gene MUC12, è risultata collegata sia all’abbondanza di un batterio chiamato Coprobacillus cateniformis sia a un rischio ridotto di malattia emorroidaria. Esperimenti di laboratorio hanno mostrato che MUC12 è prodotto in grande quantità nelle cellule che rivestono il colon, suggerendo che cambiamenti sottili in questa barriera mucosa potrebbero influenzare quali batteri prosperano e come questi, a loro volta, impattano i delicati vasi sanguigni e i tessuti del retto.
Funzioni microbiche, salute cardiaca e peso corporeo
Oltre alle singole specie, il team ha esaminato cosa erano in grado di fare i microbi raggruppando i loro geni in moduli funzionali, come sistemi di trasporto e circuiti regolatori. Le stesse regioni genetiche umane—LCT, ABO e FUT2—influenzavano anche queste funzioni microbiche, suggerendo che il nostro DNA modella non solo chi è presente nell’intestino, ma cosa stanno facendo. Nel sito FUT2, per esempio, varianti associate allo stato di “non-secretore” andavano di pari passo con batteri legati a metaboliti potenzialmente dannosi e con un rischio aumentato di colesterolo alto e ipertensione. Infine, usando una tecnica chiamata randomizzazione mendeliana, che sfrutta varianti genetiche come esperimenti naturali, i ricercatori hanno trovato prove che un indice di massa corporea più elevato altera causalmente il microbioma: le persone geneticamente predisposte a un peso maggiore tendevano ad avere una minore diversità microbica complessiva e cambiamenti coerenti attraverso molte specie.
Cosa significa per la salute quotidiana
Nel complesso, questi risultati delineano un quadro di conversazione a tre vie tra i nostri geni, i nostri microbi intestinali e la nostra salute. Alcuni tratti di DNA umano favoriscono o sfavoriscono in modo sottile specifici abitanti batterici e attività microbiche, che poi intersecano i rischi per malattie digestive, problemi cardiocircolatori e gli effetti dell’eccesso di peso corporeo. Sebbene queste influenze genetiche spieghino solo una parte della enorme variazione nelle comunità intestinali—e non si traducano ancora in test clinici—aiutano a chiarire perché le persone rispondono in modo diverso alla stessa dieta o ambiente e indicano approcci più personalizzati alla nutrizione e alla prevenzione delle malattie che considerino sia il genoma sia il microbioma.
Citazione: Moksnes, M.R., Coward, E., Nethander, M. et al. The HUNT study identifies host genetic factors reproducibly associated with human gut microbiota composition. Nat Genet 58, 530–539 (2026). https://doi.org/10.1038/s41588-026-02502-4
Parole chiave: microbioma intestinale, genetica umana, microbiota e malattia, peso corporeo e microbi, associazione genome-wide