Clear Sky Science · it
Inferenza basata su simulazione della dinamica di migrazione cellulare in ambienti spaziali complessi
Come le cellule immunitarie trovano la strada in tessuti affollati
Le nostre cellule immunitarie spesso devono farsi strada attraverso tessuti densi e simili a labirinti per raggiungere i siti di infezione o i linfonodi. Questo studio pone una domanda apparentemente semplice ma dalle grandi implicazioni: come navigano queste cellule in ambienti così ingombrati e come possiamo inferire in modo affidabile i loro comportamenti da dati microscopici rumorosi? Combinando “labirinti” di laboratorio progettati con precisione, simulazioni al computer avanzate e strumenti moderni di apprendimento automatico, gli autori mostrano un nuovo modo per decodificare le regole che guidano il movimento cellulare in contesti complessi.
Costruire un piccolo labirinto per le cellule immunitarie
Per indagare come l’ambiente plasmi il movimento, i ricercatori si sono concentrati sulle cellule dendritiche—sentinelle immunitarie che devono viaggiare dai tessuti periferici ai linfonodi, guidate da attrattori chimici chiamati chemochine. Hanno costruito un chip microfabbricato: una “foresta di pilastri” piatta di postazioni regolarmente distanziate realizzate in gomma siliconica (PDMS), con strette fessure da 10 micrometri che imitano gli spazi angusti nei tessuti reali. Un lato del chip è stato caricato con decine di migliaia di cellule dendritiche; il lato opposto conteneva una sorgente di chemochina CCL19, che crea un gradiente stabile attraverso i pilastri. Usando microscopia a intervalli temporali, hanno tracciato i nuclei di singole cellule ogni 30 secondi mentre cercavano di muoversi verso la sorgente di chemochina. 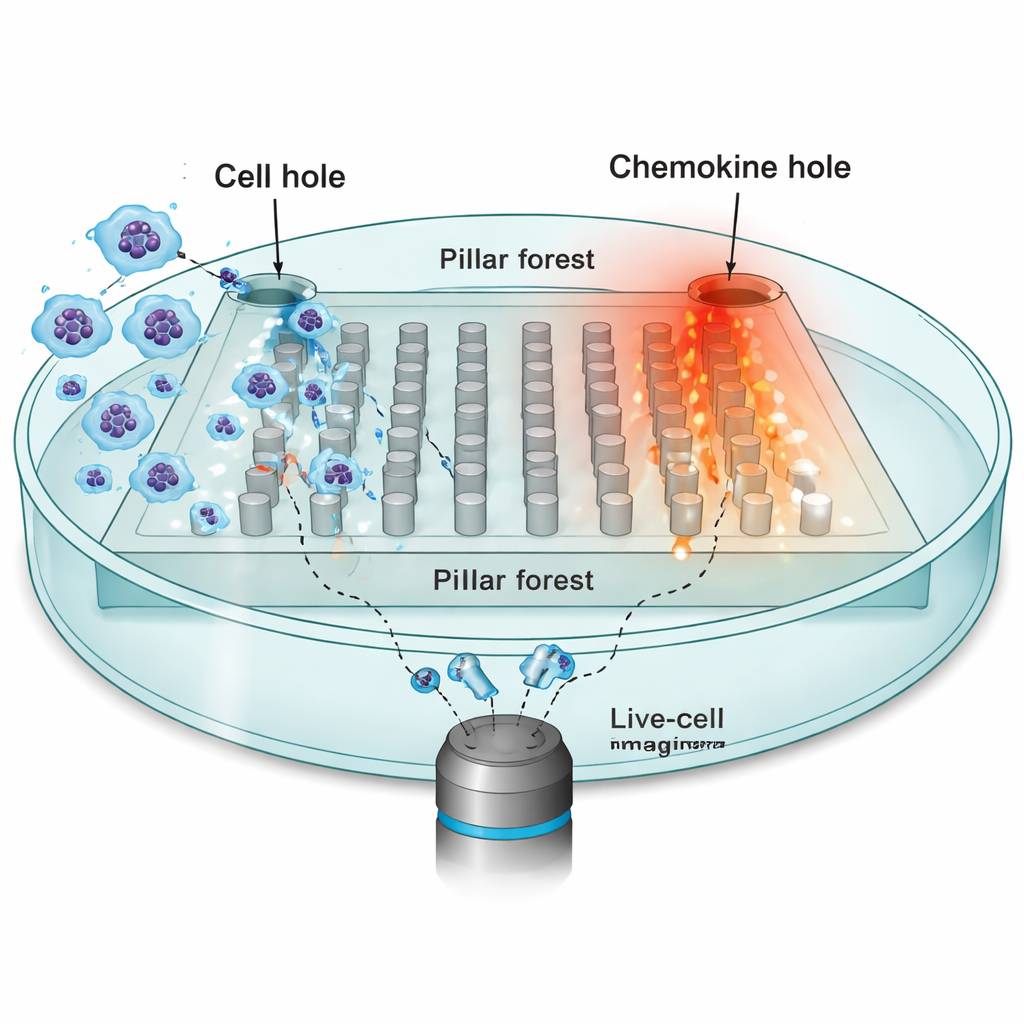
Trasformare la biologia in un esperimento virtuale
Per comprendere questa diversità, il gruppo ha costruito un modello computazionale dettagliato della migrazione cellulare usando un quadro noto come modello di Potts cellulare (Cellular Potts model). Invece di trattare una cellula come un semplice punto, questo approccio rappresenta ogni cellula come una patch estesa su una griglia, permettendole di cambiare forma, schiacciarsi tra i pilastri e rispondere a segnali chimici. Il modello include quattro ingredienti chiave: quanto una cellula è attratta dal gradiente di chemochina (mdir), quanto tende a perseverare nella direzione corrente (mrand), quanto spesso si riorienta (catturato da un tasso λ) e la sua dimensione effettiva (a). Variando questi parametri e eseguendo simulazioni, il modello produce tracce sintetiche che possono essere confrontate direttamente con i percorsi cellulari registrati nella foresta di pilastri.
Perché le misure scelte a mano non bastano
Tradizionalmente, i ricercatori sintetizzano questi dati di movimento con una manciata di statistiche familiari—quanto lontano si sposta una cellula (spostamento), quanto velocemente si muove (velocità) e come cambia la sua direzione nel tempo (angoli di svolta). Gli autori hanno prima utilizzato queste misure fatte a mano all’interno di una tecnica chiamata approssimazione bayesiana per computazione (ABC), che cerca set di parametri che rendano le tracce simulate simili a quelle sperimentali. Hanno scoperto che sebbene questi riassunti catturino le tendenze generali, perdono molta della struttura fine nei dati. Di conseguenza, alcuni parametri del modello, in particolare quelli che governano la persistenza casuale e la tempistica della riorientazione, restavano scarsamente vincolati o addirittura distorti. Inoltre, ABC richiedeva centinaia di migliaia di simulazioni e molte ore di calcolo per raggiungere adattamenti accettabili.
Lasciare che le reti neurali imparino ciò che conta
Per superare questi limiti, lo studio ha fatto ricorso a un filone più recente di metodi chiamati stima della posteriore neurale (NPE). Qui, una rete neurale viene addestrata direttamente su molti coppie di dati simulati e parametri sottostanti. Una parte della rete impara automaticamente il proprio insieme compatto di “caratteristiche riassuntive” dalle collezioni intere di tracce cellulari; un’altra parte impara come queste caratteristiche si ricondurranno ai valori probabili dei parametri. Crucialmente, queste caratteristiche apprese sono ottimizzate esplicitamente per una stima accurata dei parametri, non per l’interpretabilità umana. Gli autori hanno poi riutilizzato i riassunti appresi all’interno di un framework ABC, creando una pipeline ibrida che combina la robustezza di ABC con la flessibilità delle reti neurali. 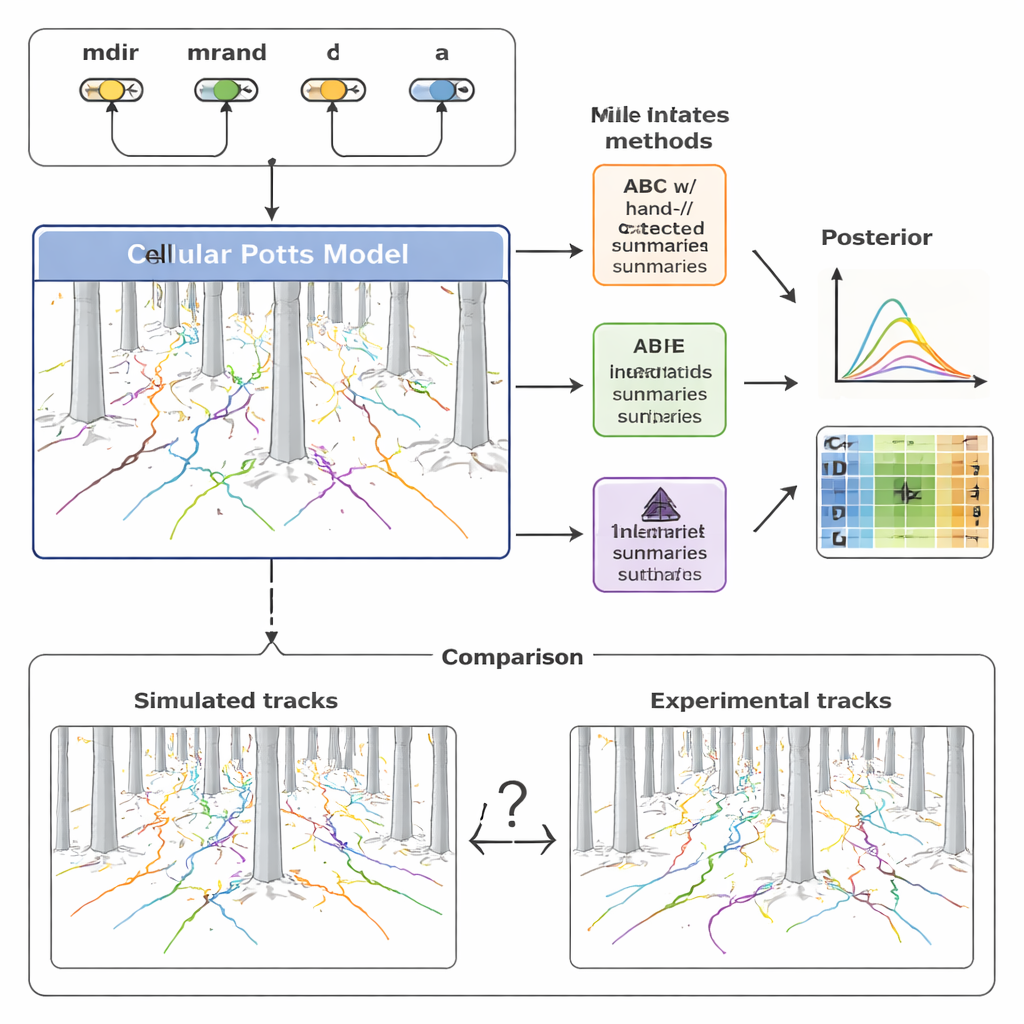
Cosa rivela il nuovo approccio sulla navigazione cellulare
Con questo modello calibrato, i ricercatori hanno esplorato come i segnali di chemochina e gli ostacoli fisici modellano congiuntamente la migrazione. La dimensione cellulare inferita suggeriva che le cellule dendritiche si riducono e si deformano efficacemente per passare attraverso le fessure da 10 micrometri, coerente con la loro flessibilità nota. Le simulazioni indicavano che il moto persistente casuale è un fattore principale nella diffusione delle cellule, anche in assenza di guida chimica, e che la foresta di pilastri può intrappolare le cellule quando forti segnali direzionali e persistenza agiscono insieme. Sorprendentemente, il modello predice che un segnale di chemochina brevemente attivo nelle fasi iniziali può, in alcuni casi, aiutare più cellule a raggiungere l’obiettivo rispetto a un segnale costante, perché un’attrazione prolungata può tenere le cellule a girare all’interno degli ostacoli invece di permettere loro di uscirne.
Perché questo conta per biologia e modellizzazione
Per i non specialisti, il messaggio chiave è duplice. Primo, la migrazione delle cellule immunitarie nei tessuti non consiste solo nel seguire una traccia chimica; emerge da un gioco sottile tra segnali di guida, le tendenze di movimento intrinseche delle cellule e la configurazione fisica dell’ambiente. Secondo, estrarre queste regole dai dati di imaging richiede di permettere al computer di imparare quali pattern nei dati sono più informativi, piuttosto che affidarsi esclusivamente a misure semplici progettate dall’uomo. Integrando esperimenti microingegnerizzati, simulazioni che risolvono la forma e inferenza basata su reti neurali, questo lavoro fornisce un potente modello per studiare come cellule di molti tipi si muovono in ambienti complessi, con potenziali applicazioni che vanno dalla comprensione della sorveglianza immunitaria alla progettazione di terapie oncologiche migliori.
Citazione: Arruda, J., Alamoudi, E., Mueller, R. et al. Simulation-based inference of cell migration dynamics in complex spatial environments. npj Syst Biol Appl 12, 20 (2026). https://doi.org/10.1038/s41540-026-00648-9
Parole chiave: migrazione cellulare, cellule dendritiche, gradienti di chemochine, inferenza basata su simulazione, foreste microfluidiche di pilastri