Clear Sky Science · it
Paesaggio plasmidico di Staphylococcus aureus e l’emergere di un sottoclade CC5 che ospita il plasmide coniugativo pSK41: implicazioni per la sicurezza alimentare e la resistenza antimicrobica
Perché piccoli anelli di DNA sono importanti per il nostro cibo
La maggior parte di noi si preoccupa dei germi alimentari quando sente parlare di carne poco cotta o avanzi andati a male. Ma in alcuni batteri noti si annidano piccoli anelli di DNA chiamati plasmidi che li aiutano a eludere gli antibiotici. Questo studio esamina questi anelli di DNA in Staphylococcus aureus — una causa comune di intossicazione alimentare e di infezioni ospedaliere — e mostra come stiano diventando veicoli potenti per la resistenza ai farmaci, con implicazioni dirette per la sicurezza alimentare e la salute pubblica. 
Uno sguardo mondiale a un germe familiare
I ricercatori hanno riunito una collezione globale di 1.395 campioni di S. aureus completamente sequenziati provenienti da 51 paesi, coprendo 90 anni. La maggior parte proveniva da pazienti umani, con una quota minore da animali. Concentrandosi solo su genomi completi, hanno potuto contare con sicurezza quanti plasmidi ogni ceppo batterico ospitasse e cosa contenessero quei plasmidi. Hanno poi confrontato ceppi con e senza plasmidi, tracciato i cambiamenti nel tempo e collegato i modelli plasmidici alle principali linee genetiche del batterio.
Piccoli anelli di DNA con un grande carico di resistenza
I plasmidi si sono rivelati comuni: circa due terzi dei ceppi li portavano, di solito uno o due per batterio. Pur essendo generalmente di dimensioni piccole o medie, erano densamente popolati da geni che conferiscono resistenza ad antibiotici e disinfettanti. Il gruppo ha identificato 35 diversi geni di resistenza su plasmidi, spesso rivolti a famiglie di farmaci importanti come beta-lattamici e macrolidi. Una volta aggiustato per dimensione, i plasmidi portavano molte più copie di geni di resistenza per unità di DNA rispetto al cromosoma batterico principale, e il numero di geni di resistenza su plasmidi è aumentato nettamente negli ultimi 90 anni.
Una linea ospedaliera ad alto rischio si distingue
Non tutti i ceppi di S. aureus erano uguali nel loro bagaglio plasmidico. Una linea associata agli ospedali, nota come complesso clonale 5 (CC5), presentava il più alto numero medio di plasmidi e una concentrazione di geni chiave per la resistenza. All’interno di CC5, un particolare ramo chiamato CC5.6 era particolarmente preoccupante. Molti ceppi CC5.6 ospitavano un plasmide grande e auto-trasferibile correlato a un tipo chiamato pSK41. Questo plasmide può spostarsi da un batterio all’altro e può anche aiutare a trasportare plasmidi non mobili, combinando efficacemente più tratti di resistenza in un unico pacchetto altamente mobile. 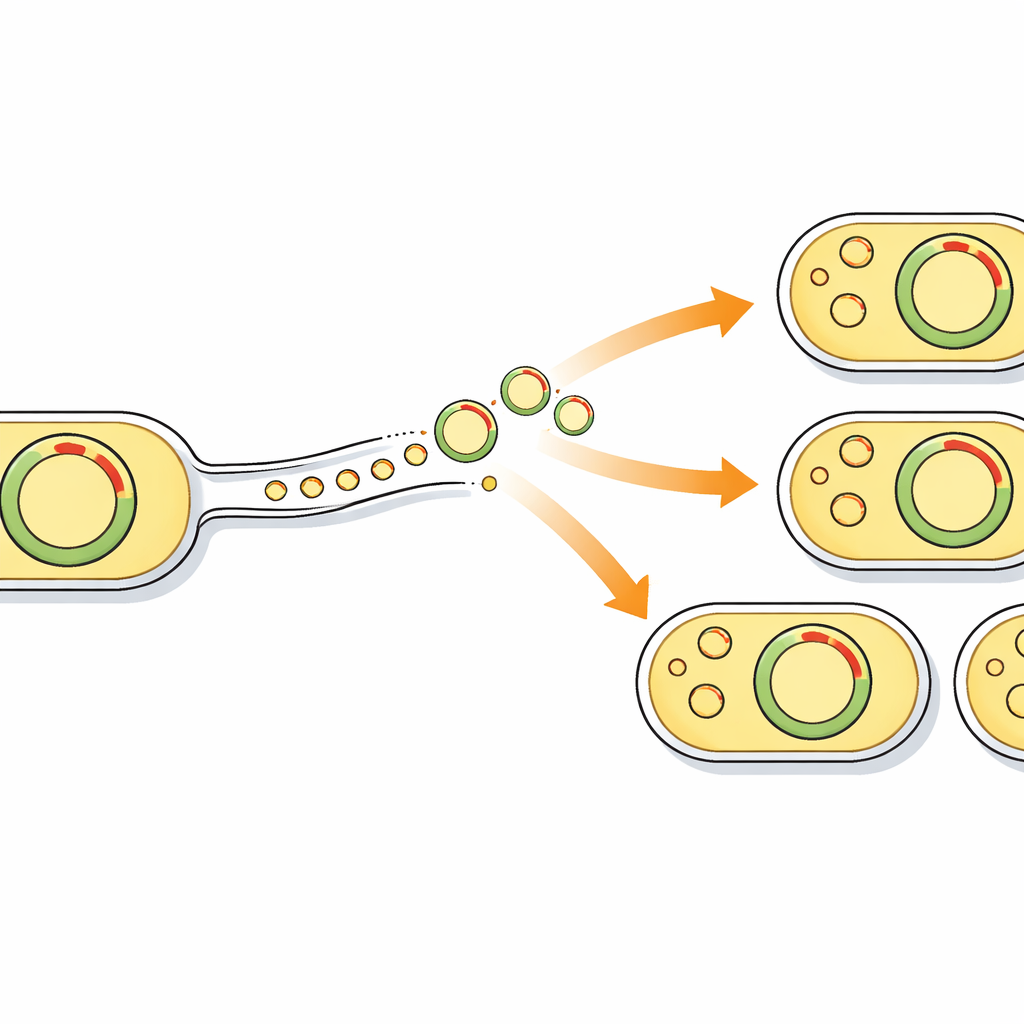
Come è emerso un nuovo sottogruppo resistente
Ricostruendo l’albero genealogico dei batteri CC5, lo studio suggerisce che plasmidi simili a pSK41 non erano presenti nei primi ceppi CC5 ma sono stati acquisiti in eventi successivi e indipendenti. Una acquisizione importante sembra essere avvenuta intorno al 2012 negli Stati Uniti, seguita dall’espansione di un sottogruppo CC5.6 portatore di questi plasmidi. I ceppi di questo sottogruppo generalmente ospitavano un numero maggiore e più vario di geni di resistenza rispetto ai loro parenti, suggerendo che l’evoluzione guidata dai plasmidi li sta aiutando a prosperare in ambienti saturi di antibiotici e disinfettanti, come gli ospedali e, potenzialmente, ambienti intensivi di produzione alimentare.
Cosa significa per cibo e salute
S. aureus può spostarsi tra esseri umani, animali e alimenti, trasformando aziende agricole, macelli e cucine in incroci per ceppi resistenti. La scoperta che una linea ospedaliera comune con un elevato carico plasmidico sta emergendo anche in ambienti legati ad animali e alimenti aumenta il rischio che batteri difficili da trattare possano diffondersi lungo la filiera alimentare. Gli autori concludono che i plasmidi sono attori centrali nell’aumento della resistenza antibiotica di S. aureus e chiedono un monitoraggio più stretto dei ceppi portatori di plasmidi sia in contesti clinici sia nella produzione alimentare, oltre a strategie mirate a bloccare il trasferimento o la persistenza dei plasmidi. Comprendere e colpire questi piccoli anelli di DNA potrebbe essere cruciale per mantenere le infezioni quotidiane trattabili e rendere più sicura la nostra fornitura alimentare.
Citazione: Tian, X., Zhang, Z., Hou, W. et al. Plasmidomic landscape of Staphylococcus aureus and the emergence of a CC5 subclade harboring the conjugative plasmid pSK41: implications for food safety and antimicrobial resistance. npj Sci Food 10, 78 (2026). https://doi.org/10.1038/s41538-026-00733-7
Parole chiave: Staphylococcus aureus, plasmidi, resistenza antimicrobica, sicurezza alimentare, MRSA