Clear Sky Science · it
TONSL sopprime le duplicazioni tandem dipendenti dalla polimerasi theta attraverso la riparazione guidata dalla cromatina
Quando il DNA crea copie extra pericolose
Ogni cellula deve copiare il proprio DNA con sorprendente accuratezza, eppure i nostri genomi sono comunque soggetti a danni che possono riorganizzare i cromosomi. Un cambiamento particolarmente importante è la «duplicazione tandem», in cui un tratto di DNA viene copiato e incollato immediatamente accanto alla sua posizione originale. Queste copie extra possono favorire l’evoluzione fornendo nuovo materiale genico, ma nel cancro spesso guidano una crescita incontrollata. Questo studio rivela come una proteina chiamata TONSL aiuti le cellule a evitare queste duplicazioni rischiose, scoprendo una salvaguardia nascosta che sembra essere condivisa tra animali e piante. 
Copie extra: utili per l’evoluzione, rischiose per la salute
Grandi ripetizioni di DNA disposte una di fianco all’altra, note come duplicazioni tandem, sono tra i cambiamenti strutturali più comuni nei genomi complessi. Possono raddoppiare interi geni, talvolta permettendo l’emergere di nuove funzioni su lunghi tempi evolutivi. Eppure, nei tessuti sani, si trovano pochissime duplicazioni tandem recenti, il che suggerisce che le cellule le prevengono attivamente. In molti tumori, invece, queste duplicazioni sono abbondanti e rimodellano il genoma su larga scala. Il mistero era come le cellule normali riescano normalmente a riparare le rotture del DNA senza creare accidentalmente segmenti copiati così grandi.
Scoprire un guardiano nascosto del genoma
Per cercare protettori naturali contro questi eventi di duplicazione, i ricercatori si sono rivolti al minuscolo verme Caenorhabditis elegans, che può essere allevato e sequenziato in grandi numeri. Rianalizzando una raccolta di circa 2.000 ceppi di vermi mutagenizzati, hanno identificato una manciata con un numero inaspettatamente elevato di duplicazioni tandem. Un filo comune tra questi ceppi era il danneggiamento di un singolo gene, chiamato tnsl-1, che codifica per la proteina TONSL. Quando il gruppo ha deliberatamente disattivato questo gene e propagato i vermi per molte generazioni, i loro genomi hanno accumulato duplicazioni tandem a ritmo costante, circa una per generazione, sparse su tutti i cromosomi. Sorprendentemente, gli animali sono rimasti in gran parte sani, rivelando che un genoma può accumulare silenziosamente molte grandi duplicazioni senza collassare immediatamente.
Cellule rapide fanno duplicazioni piccole, cellule lente ne fanno di grandi
Un’osservazione più attenta ha mostrato che le nuove duplicazioni ricadevano in due principali intervalli di dimensione: un gruppo attorno a decine di migliaia di basi e un altro attorno a qualche centinaio di migliaia. Il team ha ipotizzato che il ritmo della divisione cellulare potesse determinare quanto grande diventasse una duplicazione. Gli embrioni del verme si dividono molto rapidamente, con cicli cellulari di circa 20 minuti, mentre le cellule germinali che danno origine a uova e spermatozoi si dividono molto più lentamente. Usando incroci genetici progettati con cura e il sequenziamento dell’intero genoma della progenie, i ricercatori hanno potuto datare quando sono comparse le duplicazioni. Hanno scoperto che le duplicazioni piccole si formavano durante le rapide divisioni embrionali precoci, mentre quelle grandi avevano origine più tardi nelle germinali a ciclo lento. Questo suggerisce un modello in cui il tempo disponibile per la riparazione e la duplicazione del DNA determina quanto può estendersi un processo di copiatura guidato da una rottura prima che venga bloccato. 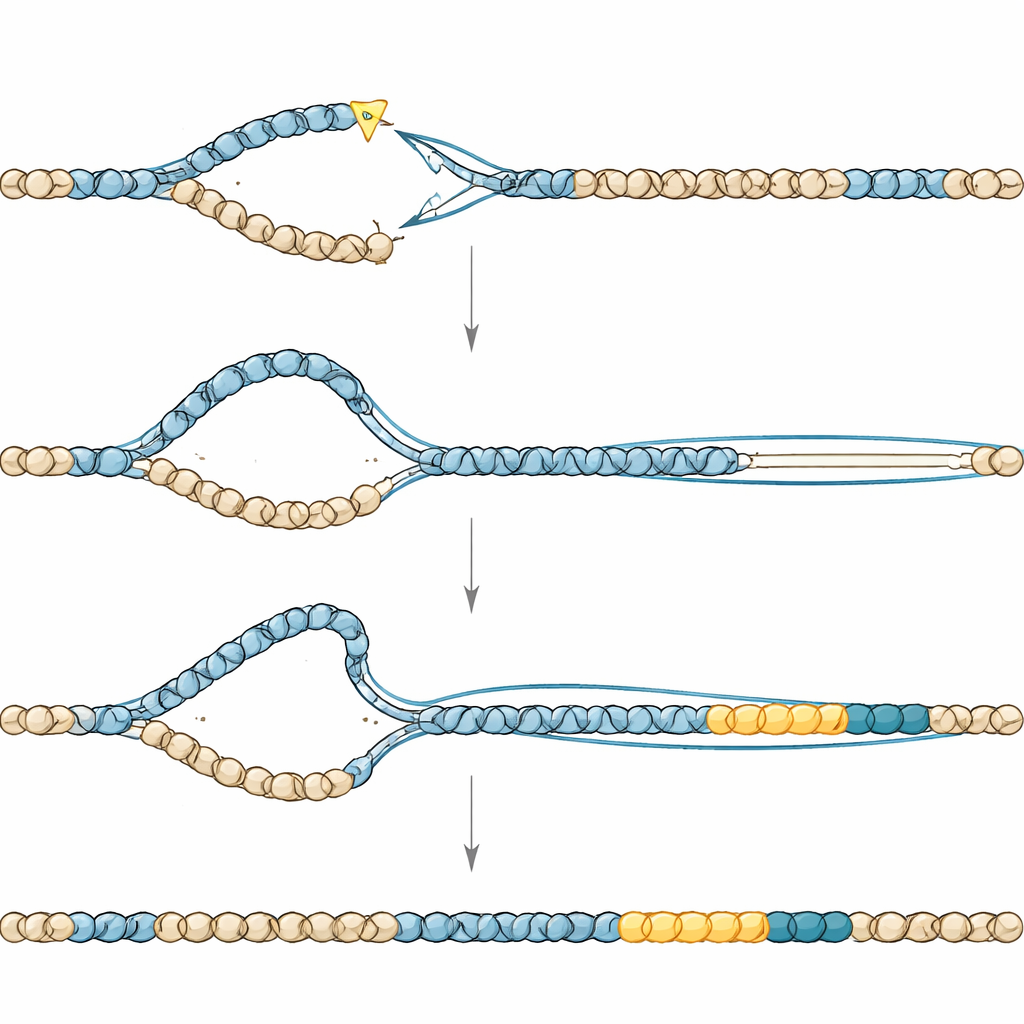
Come la macchina difettosa di riparazione costruisce duplicazioni
Le giunture dove i segmenti duplicati si univano al DNA originale portavano le impronte di una via di riparazione specializzata e soggetta a errori chiamata giunzione mediata dalla polimerasi theta. Quando l’enzima chiave di questa via veniva disabilitato, le duplicazioni praticamente scomparivano, ma i vermi pagavano un prezzo pesante in fertilità, implicando che la stessa via è anche necessaria per salvare i cromosomi spezzati in assenza di TONSL. Altri esperimenti hanno indicato un secondo attore, un processo somigliante alla «replicazione indotta da rottura» (break-induced replication), in cui un estremo di DNA rotto usa un templato intatto per copiare ampi tratti di sequenza. Rimuovere un elicasi che favorisce tale copiatura a lunga distanza riduceva la dimensione delle duplicazioni senza fermarle, rafforzando l’idea che una sintesi del DNA estesa e mal controllata sia alla base di questi eventi.
La cromatina come regista silenzioso della riparazione
Si sa che TONSL si lega a marche chimiche specifiche sulle proteine della corona del DNA appena replicate, suggerendo che aiuti a ricostruire la cromatina — la struttura che avvolge e organizza il DNA — subito dopo la duplicazione. Gli autori hanno introdotto una modifica sottile nella proteina del verme che indebolisce questo legame con la cromatina. I vermi portatori di questa singola sostituzione amminoacidica continuavano a formare duplicazioni, ma in numero e dimensioni inferiori, indicando che la presa di TONSL sulla cromatina fresca limita direttamente la sintesi del DNA sfuggita al controllo nei siti di riparazione. In sua assenza, gli intermedi di riparazione possono estendersi troppo prima di essere infine ricuciti dalla via soggetta a errori, lasciando dietro di sé un blocco duplicato invece di una riparazione pulita.
Una difesa condivisa da vermi a piante
Per verificare se questo ruolo protettivo fosse conservato in altre specie, il team ha esaminato un mutante della pianta modello Arabidopsis thaliana privo della proteina correlata TONSOKU. Dopo pochissime generazioni, queste piante hanno accumulato un numero notevole di grandi duplicazioni tandem, corrispondenti a circa un aumento dell’un per cento della dimensione del genoma per generazione — un cambiamento enorme su scale evolutive. Anche le giunture del DNA portavano le sovrapposizioni corte e le inserzioni caratteristiche associate alla stessa via di riparazione soggetta a errori, suggerendo che vermi e piante usino un sistema profondamente conservato, guidato dalla cromatina, per deviare le rotture legate alla replicazione da esiti favorevoli alla duplicazione.
Cosa significa per il cancro e la stabilità del genoma
In termini chiari, questo lavoro mostra che TONSL e il suo cugino vegetale agiscono come controllori di qualità che si trovano all’incrocio tra copia e riparazione del DNA. Aiutando a ricostruire correttamente la cromatina dopo una rottura, mantengono i processi di riparazione brevi e ordinati, impedendo che lunghi tratti di DNA vengano copiati due volte di seguito. Senza questo controllo, le cellule riparano comunque le rotture, ma lo fanno prolungando e poi riunendo grossolanamente il DNA, lasciando duplicazioni tandem. Poiché schemi di duplicazione simili si osservano in diversi tumori umani, compresi tumori con difetti in fattori associati alla replicazione, comprendere il ruolo di TONSL potrebbe infine aiutare a spiegare perché alcuni tumori acquisiscono genomi così profondamente rimodellati e suggerire nuovi modi per prevedere o influenzare come il loro DNA evolverà durante la terapia.
Citazione: van Schendel, R., Romeijn, R., Kralemann, L.E.M. et al. TONSL suppresses polymerase theta-dependent tandem duplications through chromatin-guided repair. Nat Commun 17, 2875 (2026). https://doi.org/10.1038/s41467-026-70905-2
Parole chiave: stabilità del genoma, duplicazioni tandem, riparazione del DNA, cromatina, TONSL