Clear Sky Science · it
SMART: aggregazione multi-omica spaziale usando reti neurali grafiche e metric learning
Vedere i tessuti come mappe di quartieri
I nostri corpi sono composti da vivaci quartieri cellulari, dove geni, proteine e l’impacchettamento del DNA cooperano in posizioni precise. Nuovi microscopi e strumenti di sequenziamento possono ora leggere molti di questi strati molecolari direttamente all’interno di sottili fette di tessuto, ma trasformare questo flusso di dati spaziali e multilivello in immagini chiare di come gli organi sono organizzati è una sfida computazionale enorme. Questo studio introduce SMART, un metodo computazionale che aiuta i ricercatori a fondere questi segnali complessi in mappe dettagliate di dove vivono diverse comunità cellulari e di come sono disposte.
Perché mappare i quartieri cellulari è difficile
Le moderne tecnologie di “spatial multi-omics” possono misurare contemporaneamente diversi tipi di informazioni molecolari — come RNA, proteine di superficie cellulare e lo stato di apertura del DNA — mantenendo la posizione precisa di ogni misura in una sezione tissutale. Ogni tipo, o “omica”, offre una prospettiva diversa sul comportamento cellulare, ma sono rumorosi, ad alta dimensionalità e non si allineano naturalmente tra loro. Inoltre, cellule dello stesso tipo non sono sempre raggruppate; possono apparire come isole sparse all’interno di un organo. Gli strumenti software esistenti spesso o ignorano la disposizione spaziale, semplificano eccessivamente le relazioni tra le diverse omiche, o faticano a scalare per i dataset molto grandi che i nuovi strumenti possono produrre.
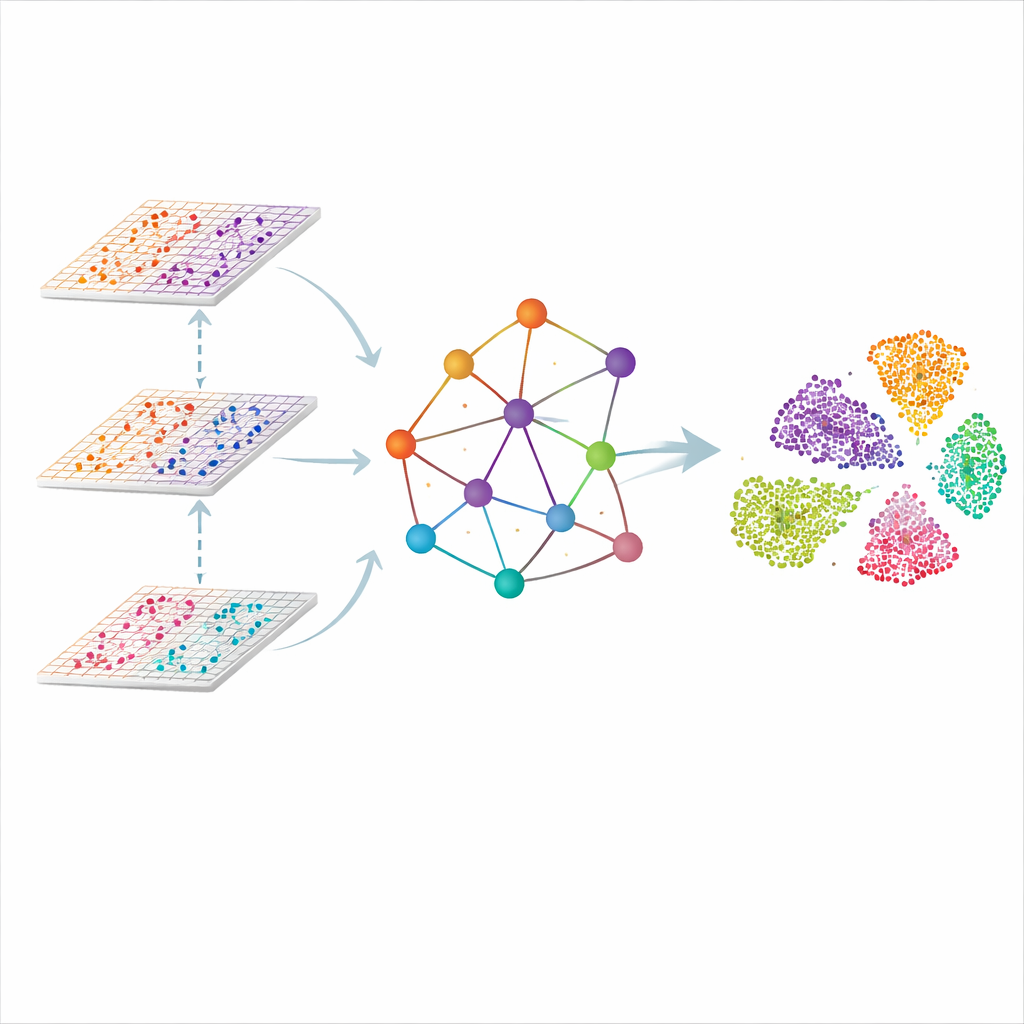
Un grafo del tessuto, non solo una lista di cellule
SMART affronta il problema trattando ogni punto di misura nel tessuto come un nodo di una rete. Punti vicini sono collegati per formare un grafo spaziale, e le letture molecolari di ogni omica vengono in primo luogo compresse in un insieme ridotto di caratteristiche coordinate che catturano pattern complessivi piuttosto che singoli geni. Un tipo di rete neurale progettata per grafi poi trasmette informazioni lungo i collegamenti, permettendo a ogni punto di “ascoltare” i vicini mantenendo traccia di come ciascuna omica contribuisce. Il risultato è una rappresentazione condivisa a bassa dimensionalità in cui regioni simili nel tessuto — come strati distinti del cervello o zone di un linfonodo — si raggruppano naturalmente.
Insegnare al modello cosa dovrebbe essere simile
Seguire semplicemente i vicini fisici non è sufficiente, perché cellule dello stesso tipo possono trovarsi a distanze rilevanti. SMART aggiunge un secondo ingrediente preso dai sistemi di riconoscimento facciale: il metric learning con triplette. Per ogni punto, il metodo trova automaticamente un altro punto con pattern molecolari molto simili (un “positivo”) e uno chiaramente diverso (un “negativo”). Regola quindi la rappresentazione interna in modo che i positivi vengano avvicinati e i negativi allontanati, anche se sono distanti sulla vetrino tissutale. Questa dinamica si svolge insieme a una fase di ricostruzione che costringe SMART a preservare i dettagli chiave di ogni strato omico, bilanciando continuità spaziale e specificità molecolare.
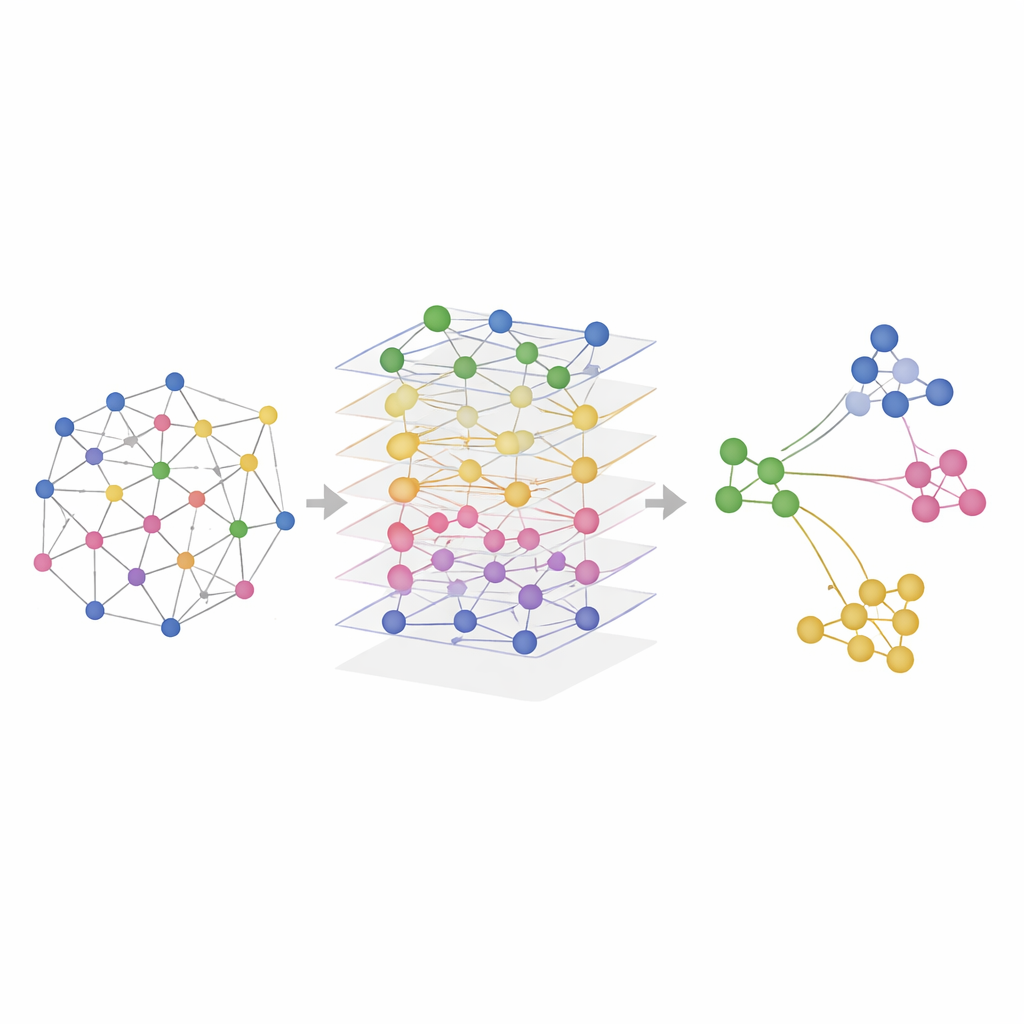
Mettere SMART alla prova su tessuti reali
I ricercatori hanno testato SMART sia su dati simulati sia su esperimenti reali che misuravano combinazioni di RNA, proteine e accessibilità della cromatina in cervelli di topo, milze di topo, linfonodi umani e tonsille. In simulazioni controllate in cui le vere regioni spaziali erano note, SMART ha recuperato con maggiore accuratezza i pattern di verità a terra e ha mantenuto le relazioni presenti in ciascuno strato omico. Nei dataset reali, SMART ha identificato costantemente strutture anatomiche fini — come regioni cerebrali specifiche o zone di cellule immunitarie negli organi linfoidi — in modo più nitido rispetto ai metodi concorrenti, mantenendo al contempo bassi i requisiti computazionali. Una versione correlata, chiamata SMART‑MS, estende le stesse idee su più sezioni tissutali, allineando fette dello stesso organo e correggendo le differenze tecniche tra esperimenti.
Mappe veloci per la prossima ondata di biologia spaziale
In termini pratici, SMART è un motore di mappatura per la prossima generazione di atlas molecolari. Combinando la modellazione in stile rete della disposizione tissutale con un senso incorporato di cosa debba essere “simile”, può trasformare vaste e disordinate collezioni di misure multi-omiche spaziali in mappe coerenti dei quartieri degli organi. Questo permette ai ricercatori di individuare più facilmente dove risiedono particolari tipi cellulari e microambienti, come cambiano durante lo sviluppo o la malattia, e come si integrano le nuove tecnologie sperimentali. Con la crescita in dimensione e complessità dei dati spaziali, strumenti come SMART e SMART‑MS saranno fondamentali per trasformare le misure grezze in intuizioni biologiche.
Citazione: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Parole chiave: multi-omica spaziale, reti neurali grafiche, microambiente tissutale, integrazione dei dati, biologia single-cell