Clear Sky Science · it
Un singolo ammasso di molecole di RNA Polimerasi II è stabilmente associato ai geni attivi
Come le cellule accendono i geni in potenti impulsi
Ogni cellula del tuo corpo deve decidere quali geni usare e quando, spesso attivandoli in brevi e intensi impulsi. Per decenni, gli scienziati hanno ipotizzato che gli enzimi responsabili della lettura del DNA si raggruppino in piccoli “punti caldi” all’interno del nucleo per potenziare questo processo, ma il funzionamento di questi ammassi è rimasto controverso. Questo studio osserva embrioni di moscerino della frutta viventi con microscopi avanzati per mostrare che ogni gene attivo è associato a un singolo ammasso stabile dell’enzima che trascrive il DNA in RNA, e che questi ammassi si comportano più come postazioni di lavoro affollate che come esotiche gocce di materia “separata di fase”.
Piccole macchine che leggono il genoma
L’enzima al centro di questa storia è la RNA Polimerasi II, una macchina molecolare che scorre lungo il DNA e copia i geni in RNA, il primo passo verso la produzione di proteine. Lavori precedenti avevano dipinto quadri contrastanti: alcuni esperimenti suggerivano che le polimerasi si raggruppassero in grandi e duraturi “stabilimenti” al servizio di molti geni contemporaneamente, mentre altri osservavano solo raduni fugaci di poche molecole. Gli autori si sono concentrati su un momento drammatico dello sviluppo precoce del moscerino, chiamato attivazione del genoma zigotico, quando un embrione silenzioso accende improvvisamente migliaia dei propri geni. Questa ondata naturale di attività ha fornito un banco di prova potente per osservare come le molecole di polimerasi si muovono, si raggruppano e interagiscono con i geni in tempo reale.
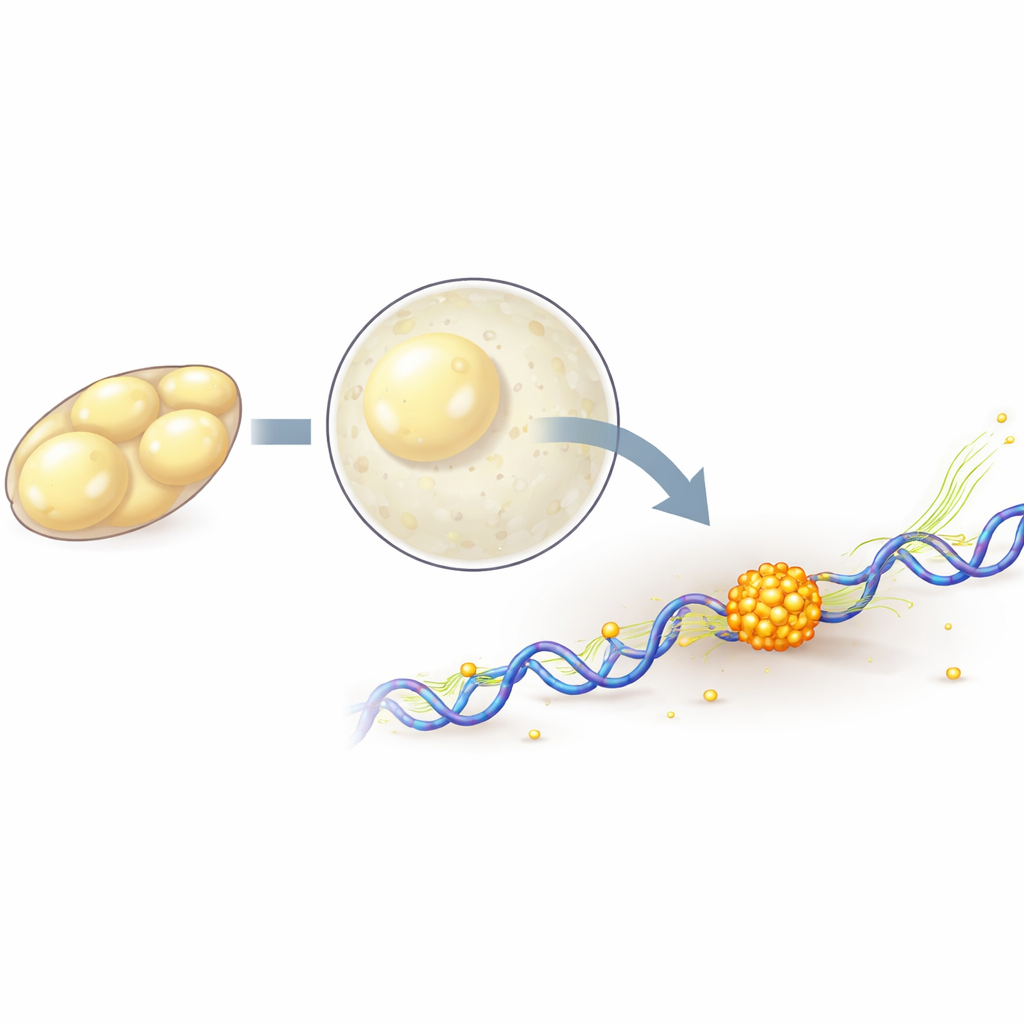
Osservare singole molecole in un embrione vivente
Per seguire le singole molecole di polimerasi, il team ha marcato geneticamente uno dei loro componenti principali con proteine fluorescenti, quindi ha utilizzato microscopia a luce a foglio reticolare e tracciamento a singola molecola per registrarne il movimento in 3D con alta velocità e illuminazione delicata. Hanno scoperto che, quando l’embrione entra nella sua fase principale di attivazione, più molecole di polimerasi diventano saldamente attaccate al DNA, coerente con un maggior numero di geni attivati. Bloccando brevemente con farmaci diversi passaggi della ciclo trascrizionale, hanno potuto separare le molecole che stanno appena iniziando su un gene da quelle che stanno attivamente procedendo lungo di esso. Questa analisi ha mostrato che la formazione degli ammassi dipende dai primissimi passaggi dell’accensione genica, mentre la copiatura attiva lungo il gene tende a indebolire e accorciare gli ammassi.
Ammassi che cambiano carattere durante lo sviluppo
L’imaging di interi nuclei nel tempo ha rivelato dozzine di piccoli ammassi di polimerasi molto prima dell’ondata di attivazione genomica, con numero e spaziatura che cambiano man mano che le divisioni nucleari rallentano. All’inizio dello sviluppo, molti ammassi durano quasi quanto l’intervallo tra due divisioni cellulari, suggerendo che siano dominati da polimerasi in uno stato precoce, “pronto” che spesso non conduce alla produzione di RNA completo. Più tardi, quando la trascrizione aumenta, gli ammassi diventano più dinamici: la loro durata non segue più semplicemente il ciclo cellulare, e la loro composizione interna si sposta verso polimerasi che stanno effettivamente allungando sul gene. Altre misure sul movimento delle molecole dentro e fuori dagli ammassi indicano che, vicino ai geni attivi, le polimerasi sono più confinate e tendono a urtare di nuovo negli stessi siti, a sostegno dell’idea di una zona di lavoro localmente occupata piuttosto che di una goccia liquida disordinata.
Un ammasso, un gene durante un impulso
Per collegare direttamente gli ammassi alla produzione genica, i ricercatori hanno osservato specifici geni reporter che si illuminano dove si sta formando nuovo RNA, tracciando contemporaneamente la polimerasi. Per diversi geni differenti, hanno visto in modo coerente un solo ammasso di polimerasi situato su ciascuna copia genica attiva durante un’esplosione trascrizionale. L’intensità dell’ammasso saliva e scendeva in parallelo con la quantità di RNA nascente e, quando copie sorelle duplicate potevano essere risolte, ciascuna portava il proprio ammasso distinto invece di condividerne uno. Simulazioni al computer, tarate per corrispondere alle condizioni di imaging, hanno mostrato che i geni con forte caricamento di polimerasi formano ammassi visibili, mentre geni più deboli possono comunque reclutare polimerasi ma restare troppo deboli per essere rilevati, spiegando perché solo una minoranza dei geni attivi mostra ammassi chiari al microscopio.
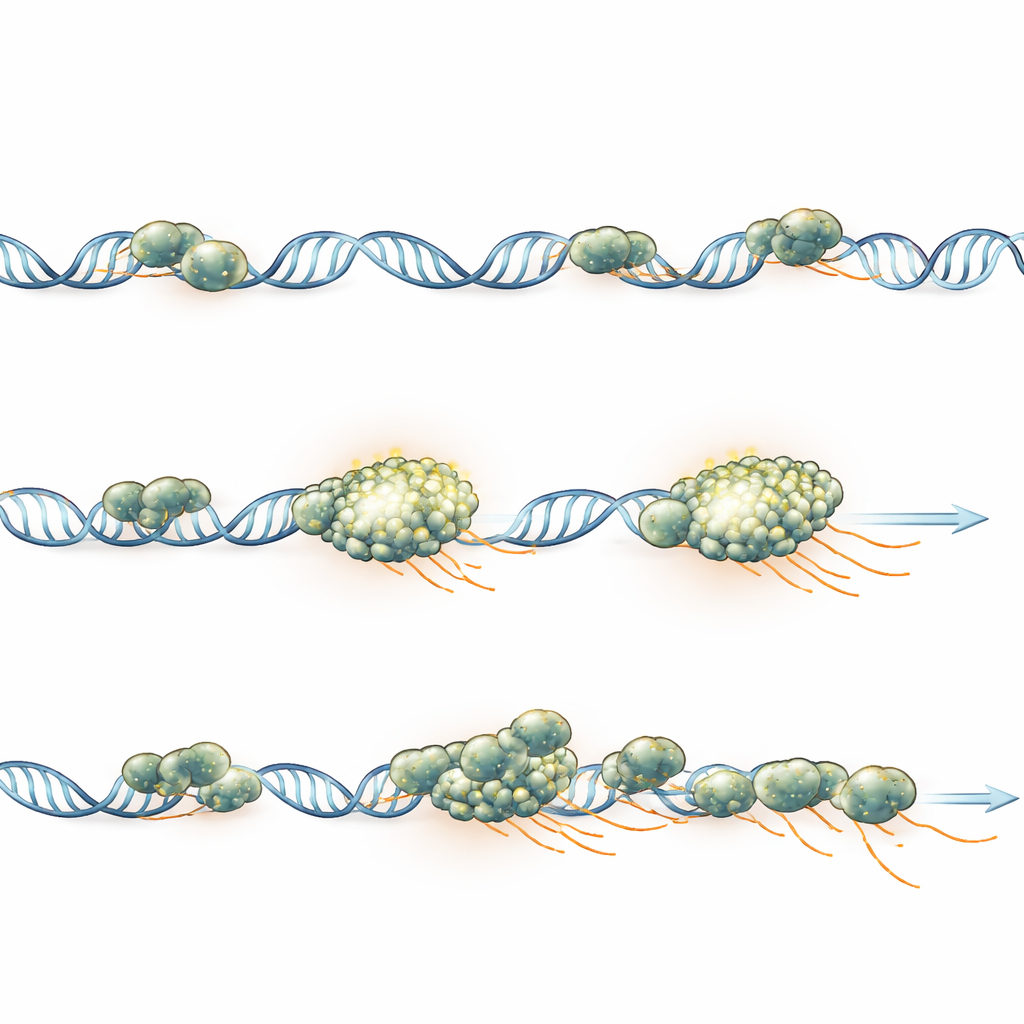
Cosa significa per il controllo genico
Questo lavoro sostiene che, in questi embrioni, gli ammassi di polimerasi riflettono principalmente quante enzimi sono effettivamente impegnati su un singolo gene, non una struttura “fabbrica” separata o una goccia speciale che deve formarsi per permettere la trascrizione. Un ammasso appare quando molte polimerasi vengono caricate in rapida successione, rimane stabilmente associato a quel singolo gene per tutta la durata di un’impennata di attività e si disperde gradualmente man mano che le polimerasi finiscono di copiare e se ne vanno. Per il lettore non specialista, il messaggio centrale è che l’accensione dei geni è organizzata tramite hub focalizzati, gene per gene: ogni gene attivo raduna temporaneamente la propria squadra di macchine di copiatura, e dimensione e durata di quella squadra rispecchiano direttamente quanto fortemente il gene è attivato.
Citazione: Mukherjee, A., Kapoor, M., Shankta, K. et al. A single cluster of RNA Polymerase II molecules is stably associated with active genes. Nat Commun 17, 2580 (2026). https://doi.org/10.1038/s41467-026-70775-8
Parole chiave: aggregazione della RNA polimerasi II, attivazione genomica zigotica, esplosioni trascrizionali, regolazione genica negli embrioni, immagini a singola molecola