Clear Sky Science · it
Profilazione meccanicistica basata sulla solubilità di terapie farmacologiche combinatorie
Perché abbinare i farmaci può fare la differenza
La cura moderna del cancro si basa spesso su combinazioni di farmaci, ma stabilire quali medicine funzionano meglio insieme rimane in gran parte un processo di prova e errore. Questo studio si concentra sulla leucemia mieloide acuta, un tumore ematologico aggressivo che spesso recidiva dopo il trattamento. I ricercatori propongono un nuovo modo per osservare, su scala ampia, come le proteine cellulari rispondono quando due farmaci vengono somministrati insieme. Il loro approccio aiuta a spiegare perché alcune combinazioni sono più efficaci e meno tossiche e offre una mappa per progettare terapie combinate più intelligenti e precise per tumori difficili da trattare.
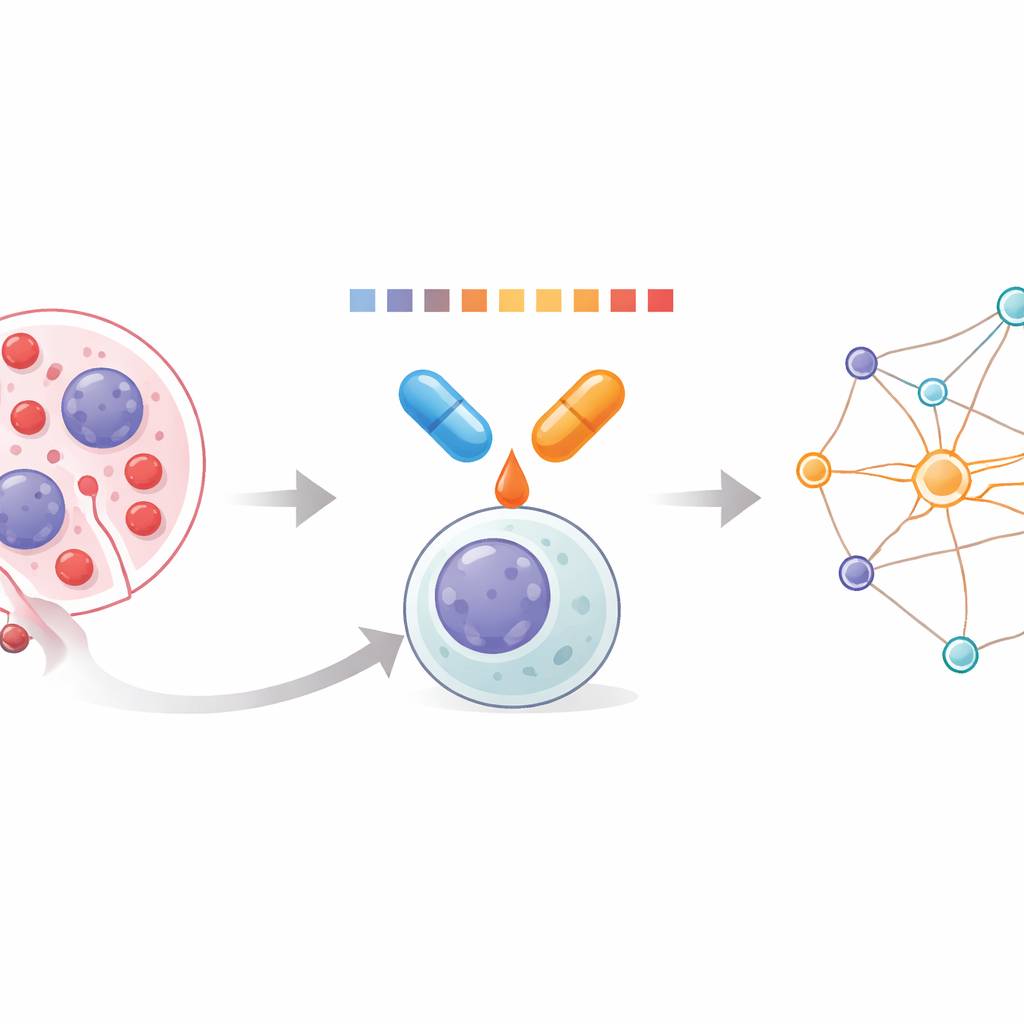
Dentro le cellule leucemiche
La leucemia mieloide acuta (LMA) insorge quando cellule bianche immature del midollo osseo proliferano in modo incontrollato e soppiantano la produzione di cellule sane. Poiché la LMA è guidata da molteplici alterazioni genetiche, i farmaci singoli raramente funzionano a lungo. Le combinazioni possono ottenere risultati migliori, ma i medici hanno avuto strumenti limitati per capire come coppie di farmaci agiscano insieme a livello di migliaia di proteine all’interno della cellula. Il gruppo dietro questo lavoro si è posto l’obiettivo di misurare direttamente quegli effetti combinati, usando un metodo che legge quanto facilmente le proteine si dissolvono o si aggregano quando vengono riscaldate. I cambiamenti nella solubilità rivelano quali proteine vengono stabilizzate o destabilizzate dal trattamento, offrendo una finestra sull’impatto reale dei farmaci.
Un nuovo modo per profilare coppie di farmaci
I ricercatori hanno sviluppato un flusso di lavoro che chiamano Analisi Combinatoria delle Alterazioni di Solubilità/Stabilità del Proteoma Integrale, o CoPISA. Cellule, o estratti proteici cellulari, vengono esposti al farmaco A, al farmaco B, alla combinazione di A e B, o a nessun farmaco. Ogni campione viene quindi riscaldato brevemente attraverso una serie di temperature, e le proteine rimaste disciolte vengono catturate e quantificate mediante spettrometria di massa. Invece di adattare curve complesse proteina per proteina, il metodo utilizza l’area totale sotto il profilo di fusione di ciascuna proteina come misura compatta del suo comportamento. Confrontando queste aree tra i trattamenti si mostra quali proteine diventano più o meno solubili in ogni condizione, rivelando schemi distinti per farmaci singoli rispetto alle combinazioni.
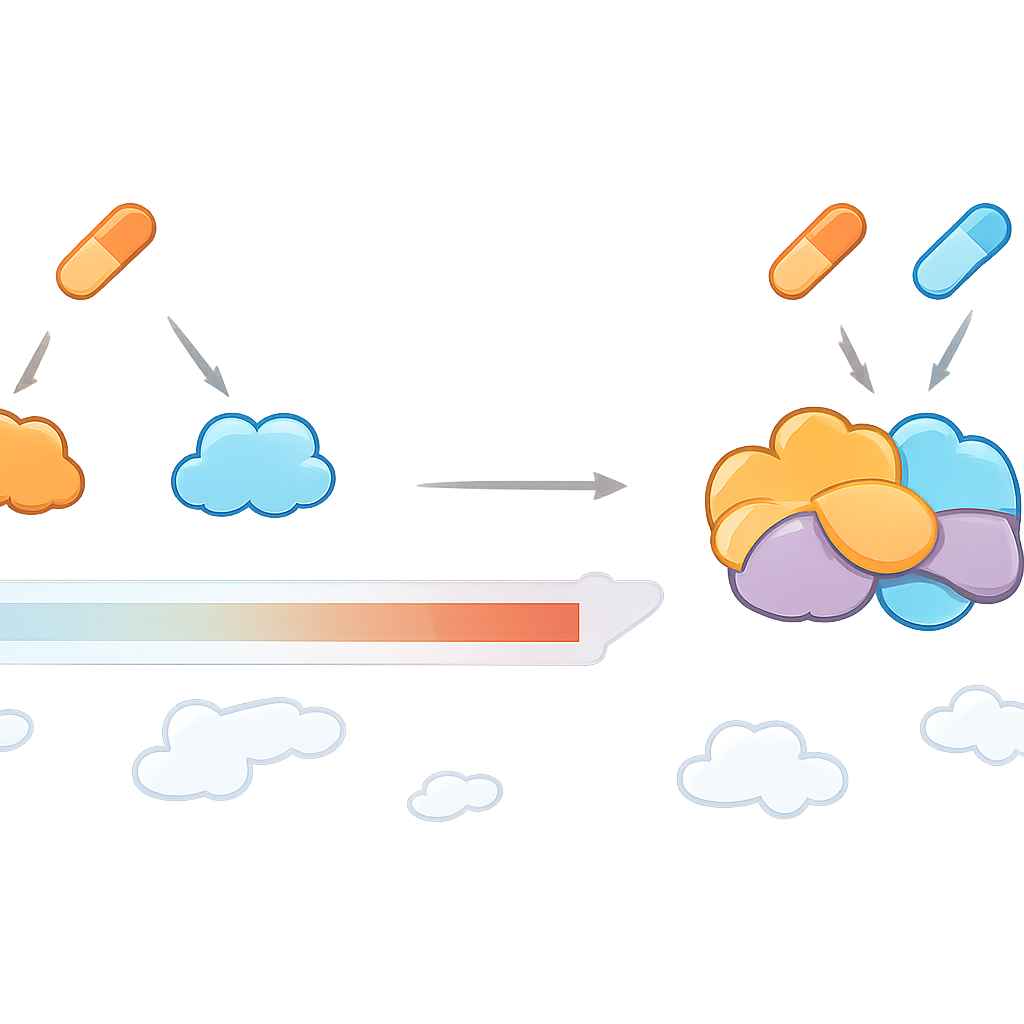
Trovare bersagli che emergono solo con entrambi i farmaci
CoPISA è stato applicato a due coppie di farmaci per LMA scelte con cura: LY3009120 con sapanisertib (denominata LS) e ruxolitinib con ulixertinib (RU). Queste coppie avevano già mostrato forte attività e tossicità relativamente bassa in campioni di pazienti, linee cellulari e modelli di zebrafish. CoPISA ha messo in luce non solo le proteine influenzate da ciascun farmaco singolarmente, ma anche un insieme distinto di proteine la cui solubilità cambiava solo quando erano presenti entrambi i farmaci. Gli autori descrivono questo fenomeno come “targeting congiunzionale”, simile a una porta logica AND: la proteina risponde solo se entrambi gli input (i farmaci) sono attivi. Per LS, questi effetti esclusivi della combinazione convergevano su processi quali l’impacchettamento del DNA, le piccole etichette proteiche chiamate SUMO che controllano la stabilità del genoma e l’adesione delle cellule leucemiche al tessuto circostante. Per RU, i bersagli unici indicavano checkpoint per i danni al DNA indeboliti, produzione energetica mitocondriale compromessa e alterazioni nel processamento dell’RNA.
Mappare i punti deboli del tumore
Sovrapponendo i loro dati di solubilità a grandi mappe di geni e percorsi correlati alla LMA, i ricercatori hanno potuto vedere come ogni trattamento riorganizzasse il wiring interno del cancro. Molti geni noti della LMA—come DNMT3A, NPM1 e TP53—venivano colpiti in modi che apparivano solo sotto terapia combinata, rafforzando l’idea che i farmaci abbinati possano esporre vulnerabilità invisibili agli agenti singoli. Il team ha anche esaminato modifiche chimiche sulle proteine, come acetilazione, metilazione e fosforilazione, che agiscono come interruttori molecolari. Hanno trovato che alcune forme modificate di proteine chiave, inclusi NPM1 e il fattore di riparazione del DNA BLM, venivano bersagliate specificamente dalle combinazioni, suggerendo che alterazioni nella localizzazione e nel segnalamento proteico contribuiscano all’effetto potenziato.
Cosa significa per i trattamenti futuri
Nel complesso, lo studio mostra che le combinazioni di farmaci possono creare un proprio paesaggio unico di bersagli proteici, anziché limitarsi ad aggiungere gli effetti di ciascun farmaco. CoPISA fornisce un modo pratico per mappare quel paesaggio, evidenziando proteine e percorsi che diventano vulnerabili solo quando due medicine agiscono in concerto. Per i pazienti, questo potrebbe tradursi in terapie combinate scelte non solo perché riducono i tumori in coltura, ma perché colpiscono i punti deboli più profondi del cancro limitando la tossicità non necessaria. Sebbene dimostrato qui nella LMA, l’approccio è ampiamente applicabile e può aiutare a guidare la progettazione razionale di trattamenti combinati in molte malattie complesse.
Citazione: Gholizadeh, E., Zangene, E., Vadadokhau, U. et al. Solubility based mechanistic profiling of combinatorial drug therapy. Nat Commun 17, 2744 (2026). https://doi.org/10.1038/s41467-026-70394-3
Parole chiave: leucemia mieloide acuta, combinazioni di farmaci, proteomica, solubilità delle proteine, terapia mirata