Clear Sky Science · it
L’indice di selezione genomica non lineare accelera il miglioramento di colture multi-tratto
Allevamento più intelligente per un mondo più affamato
Con la crescita della popolazione globale e climi sempre meno prevedibili, gli allevatori di piante devono migliorare contemporaneamente più caratteri delle colture — come rendimento, altezza e epoca di fioritura — più rapidamente che mai. Questo articolo presenta un nuovo strumento matematico che aiuta gli allevatori a fare proprio questo utilizzando l’informazione del DNA in modo più realistico, catturando non solo gli effetti individuali dei geni ma anche come interagiscono. L’approccio promette di accelerare la creazione di varietà migliori di mais e frumento senza la necessità di misurare ogni pianta in campo.
Perché combinare molti caratteri è così difficile
Gli allevatori raramente si interessano a un solo carattere. Per esempio, vogliono un rendimento del granello più elevato ma anche piante più corte e robuste che fioriscano al momento giusto. I classici “indici di selezione” trasformano più caratteri in un unico punteggio per classificare le piante. Tradizionalmente, questi indici assumono che ogni carattere contribuisca in modo semplice, lineare, e che gli effetti dei diversi caratteri si sommino. La biologia reale è più complessa: i caratteri si influenzano a vicenda e possono esistere punti ottimali in cui “di più” non è più meglio. Ignorare queste interazioni non lineari può rallentare il progresso genetico e persino indirizzare lo sviluppo varietale nella direzione sbagliata.
Dalle rette semplici a curve flessibili
Strumenti genomici precedenti permettevano agli allevatori di usare marcatori genetici distribuiti sul genoma per prevedere quanto buoni sarebbero stati i discendenti di una pianta, dando origine ai cosiddetti indici di selezione genomica lineari. Questi funzionano bene quando gli effetti genici sono per lo più additivi. Gli autori estendono un’idea più flessibile e più vecchia — l’indice di selezione fenotipico quadratico, che già includeva termini al quadrato e interazioni tra caratteri — nell’era del DNA. Il loro nuovo strumento, chiamato Indice di Selezione Genomica Quadratico (QGSI), usa predizioni del valore genetico genomico e le combina attraverso termini sia lineari sia curvi (quadratici). Questo permette all’indice di catturare schemi complessi come interazioni gene–gene e combinazioni di caratteri ottimali, anche quando le misure di campo non sono disponibili per ogni ciclo.
Mettere alla prova il nuovo indice
Per verificare se questa maggiore complessità ripaga, i ricercatori hanno confrontato il QGSI sia con indici lineari e quadratici basati solo su dati di campo, sia con indici genomici lineari che usano DNA ma restano semplici. Hanno eseguito simulazioni al calcolatore di miglioramento del mais su 10 cicli di selezione e hanno anche analizzato due set di dati reali di mais e cinque di frumento provenienti da programmi di miglioramento internazionali. Sono stati testati due modi di predire il valore genetico dal DNA: un modello additivo standard e un modello a kernel gaussiano più flessibile che può catturare interazioni geniche sottili. In tutti questi scenari, QGSI ha prodotto costantemente risposte di selezione maggiori — cioè un miglioramento complessivo più ampio attraverso i caratteri — rispetto agli indici lineari, e in genere ha superato anche l’indice fenotipico quadratico.
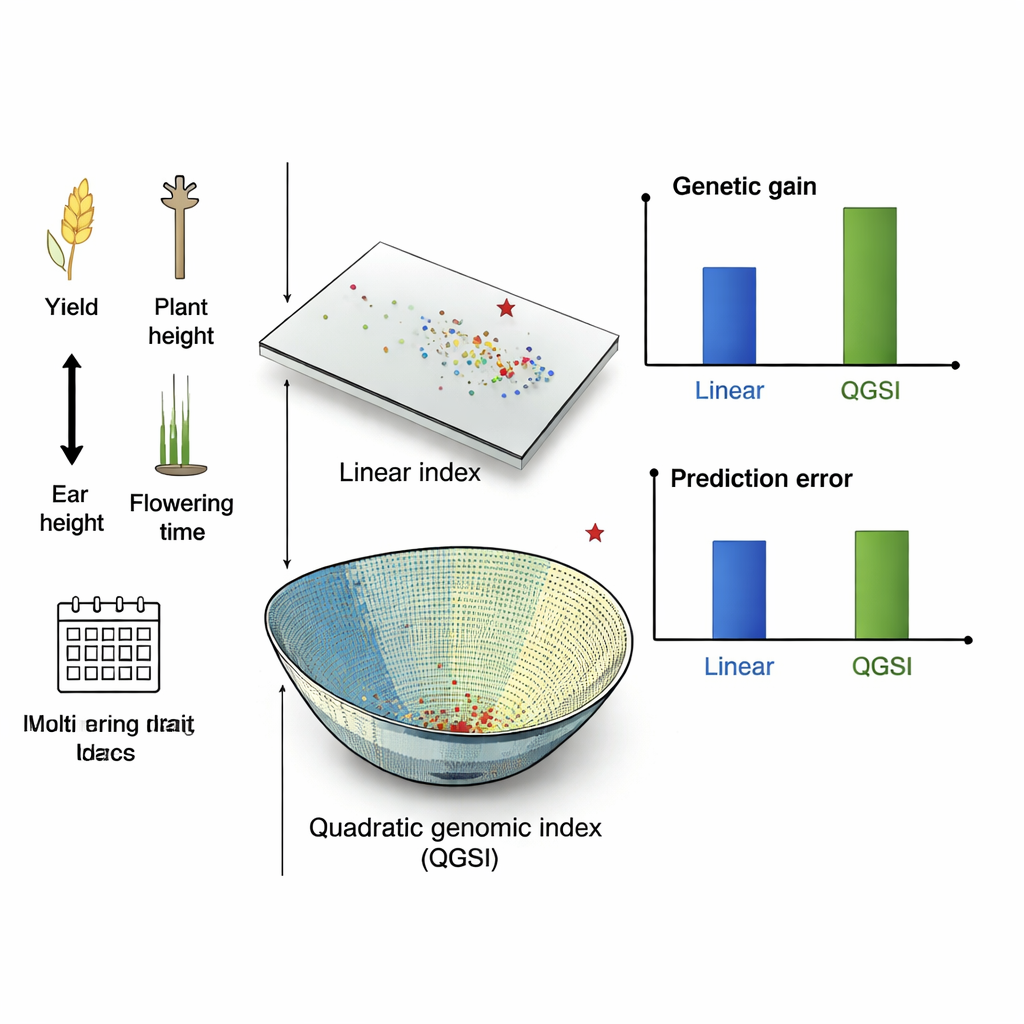
Maggiori guadagni, meno errori, più equilibrio
Nelle simulazioni dei cicli di mais, QGSI ha fornito i guadagni più alti, superando sia gli indici genomici lineari sia gli indici quadratici basati solo su misure di campo. Ha anche mostrato tendenzialmente errori di previsione inferiori, il che significa che i suoi punteggi sono state guide più affidabili per la scelta dei genitori. Nelle popolazioni di mais reali dal Messico e dallo Zimbabwe, QGSI ha raggiunto guadagni superiori dell’80–90% rispetto agli indici genomici lineari quando più caratteri venivano migliorati insieme. Negli esperimenti sul frumento condotti sotto diverse condizioni di irrigazione e piovosità, il quadro è stato simile: gli indici quadratici hanno superato quelli lineari, e la combinazione di QGSI con il modello a kernel gaussiano ha fornito i miglioramenti più forti e più stabili tra gli ambienti, in particolare per il rendimento del granello mantenendo altezza della pianta e epoca di fioritura in livelli accettabili.
Cosa significa per le colture future
Per i non specialisti, il messaggio chiave è che gli allevatori ora dispongono di un sistema di punteggio più realistico che riflette come geni e caratteri interagiscono realmente, invece di costringerli in un modello lineare. Gli autori raccomandano di usare l’indice fenotipico quadratico quando sono disponibili solo dati di campo nelle fasi iniziali, e di passare al QGSI una volta che dati genomici e cicli di selezione rapidi sono attivi. Catturando meglio le relazioni genetiche non lineari, il QGSI può accelerare il miglioramento multi-tratto delle colture e contribuire a fornire nuove varietà di mais e frumento più produttive, più resilienti e meglio adattate ad ambienti difficili.
Citazione: Jesús Cerón-Rojas, J., Montesinos-López, O.A., Montesinos-López, A. et al. Nonlinear genomic selection index accelerates multi-trait crop improvement. Nat Commun 17, 1991 (2026). https://doi.org/10.1038/s41467-026-69890-3
Parole chiave: selezione genomica, miglioramento delle colture, mais, frumento, miglioramento multi-tratto