Clear Sky Science · it
eQTL nel tessuto del colon malato identifica potenziali geni bersaglio associati alla IBD
Perché questa ricerca conta per la salute intestinale
Le malattie infiammatorie intestinali (IBD), come il morbo di Crohn e la colite ulcerosa, colpiscono milioni di persone nel mondo, spesso insorgendo in età adulta e causando problemi digestivi per tutta la vita. Sappiamo da grandi studi genetici che centinaia di posizioni nel nostro DNA influenzano il rischio di sviluppare IBD, ma per la maggior parte di queste regioni non conosciamo ancora quali geni controllino né come modifichino l’intestino. Questo studio affronta quel mistero analizzando direttamente il tessuto del colon di persone con IBD per vedere come le loro varianti genetiche alterano l’attività genica, rivelando potenziali punti deboli nella barriera intestinale e nel sistema immunitario che potrebbero essere presi di mira da terapie future.
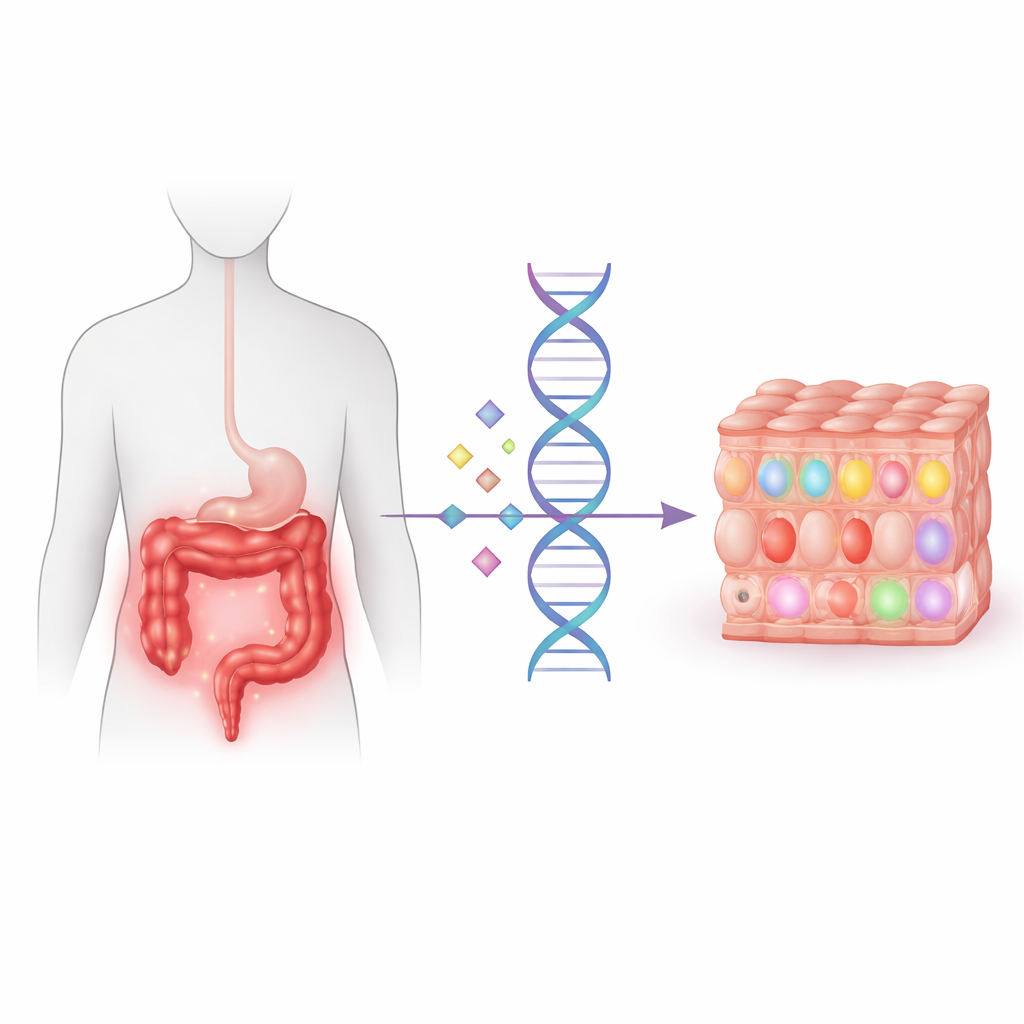
Leggere gli interruttori di controllo genetico nel colon malato
I ricercatori si sono concentrati sugli “interruttori di controllo” nel genoma: punti in cui le varianti del DNA modulano in modo sottile l’attività dei geni vicini. Questi sono chiamati loci quantitativi di espressione (expression quantitative trait loci, eQTL) ed è più facile individuarli quando si misura l’attività genica nel tessuto giusto. Invece di studiare solo donatori sani, il team ha raccolto campioni di colon non infiammato da 252 pazienti con IBD. Hanno misurato quali geni erano attivi in ciascun campione e hanno confrontato questi dati con il DNA di ogni persona, analizzando più di otto milioni di varianti su oltre trentamila geni per trovare varianti che cambiavano in modo consistente l’attività genica nel colon.
Confrontare il tessuto IBD con il colon sano
Per capire cosa c’è di speciale nel tessuto malato, il team ha confrontato i propri risultati con due grandi progetti di riferimento che hanno mappato gli eQTL nel colon di persone senza IBD. La maggior parte dei segnali di controllo genetico era condivisa: circa l’88% degli eQTL rilevati nel colon IBD coincideva con quelli osservati nel colon sano e i loro effetti risultavano fortemente correlati. Ciò suggerisce che il programma regolatorio di base del colon rimane in gran parte intatto anche nei pazienti con IBD. Tuttavia, circa il 5–10% dei segnali nella coorte IBD non corrispondeva ai riferimenti sani, nonostante quegli studi avessero più partecipanti e quindi maggiore potenza statistica. Questi segnali “solo IBD” indicano cambiamenti regolatori che diventano visibili, o più forti, solo nel contesto della malattia.
Collegare il DNA di rischio a geni specifici del colon
Il passo cruciale è stato collegare questi interruttori di controllo alle 320 regioni genomiche precedentemente associate al rischio di IBD negli studi di associazione su base genome-wide. Chiedendosi dove le varianti legate alla malattia e gli eQTL del colon condividessero lo stesso segnale di base, gli autori hanno identificato 194 potenziali geni bersaglio per 108 di queste regioni di rischio, portando la frazione di loci IBD con candidati genici concreti derivati dal tessuto del colon a circa un terzo. Molti geni rientravano in categorie biologicamente coerenti con l’IBD: risposta immunitaria, adesione cellulare, crescita cellulare e vie di segnalazione che regolano come le cellule intestinali rispondono ai microbi. Alcuni geni, come FUT2, ELMO1 e diversi regolatori immunitari nella regione HLA, erano già stati implicati nella difesa intestinale, ma altri sono emersi come candidati nuovi o più solidi quando si è considerato il tessuto malato.
Nuovi indizi dal gruppo sanguigno ABO e da TNFRSF14
Due esempi particolarmente significativi mostrano come lo studio del tessuto IBD riveli connessioni che gli studi su tessuto sano avevano mancato. In una regione di rischio per il morbo di Crohn vicina al gene del gruppo sanguigno ABO, una variante ben nota che determina il tipo sanguigno risultava anche controllare l’attività di ABO specificamente nel colon IBD, ma non nei dataset di colon sano. Le persone portatrici della versione associata al gruppo sanguigno O—già ritenuta in parte protettiva—mostravano un’espressione ridotta di ABO, a sostegno di un modello in cui i zuccheri del gruppo sanguigno sulla superficie del colon influenzano il microbioma e le risposte immunitarie. In un’altra regione associata alla colite ulcerosa, il tessuto IBD ha indicato TNFRSF14, un recettore che aiuta a bilanciare le reazioni immunitarie nella mucosa intestinale. Nei dati del colon sano, segnali vicini ma differenti puntavano invece ad altri geni di rilevanza poco chiara. In studi su animali, la perdita di questo recettore peggiora la colite sperimentale, quindi trovare un legame genetico con la sua espressione nel colon umano rafforza l’ipotesi che sia un attore chiave nella malattia.
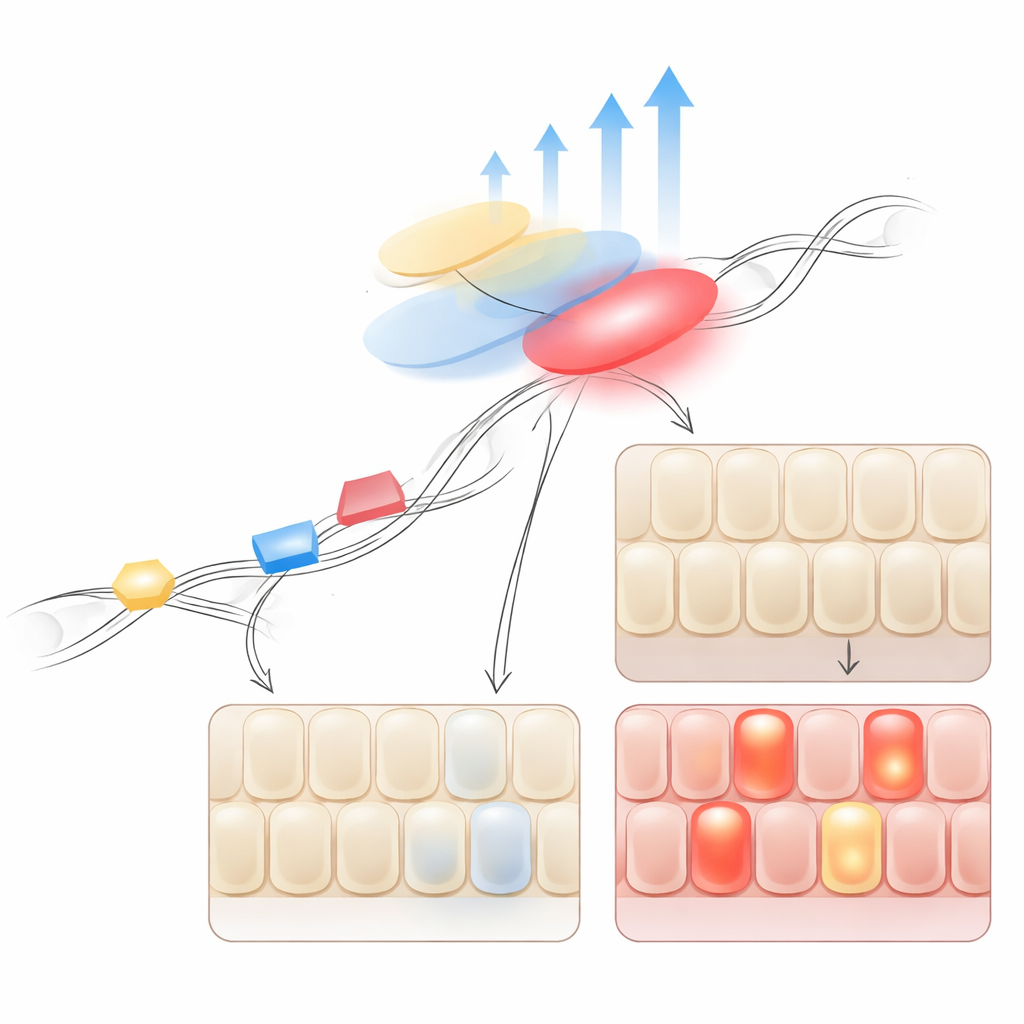
Come la malattia rimodella gli effetti genetici
Analizzando tutte le regioni in cui le varianti di rischio IBD e gli eQTL si sovrapponevano, gli autori hanno osservato che i segnali specifici per IBD non erano solo diversi ma spesso più forti. Nel colon malato, molte di queste varianti si trovavano più lontano dai geni che controllavano, in regioni che probabilmente agiscono come enhancer a lunga distanza. Quando il team ha corretto con attenzione le differenze fra le coorti, ha visto che per un sottoinsieme di geni—soprattutto quelli coinvolti nelle risposte immunitarie e nell’integrità della barriera—la stessa variante aveva un impatto maggiore sull’attività genica nel tessuto IBD rispetto al tessuto sano. Ciò suggerisce che una volta che la malattia ha alterato l’ambiente cellulare, alcuni elementi regolatori diventano più attivi, amplificando l’effetto del rischio genetico esistente.
Cosa significa per i pazienti e per la ricerca futura
Combinando le informazioni sul DNA con l’attività genica direttamente nei coloni dei pazienti con IBD, questo studio fornisce l’elenco più ampio finora di geni candidati che potrebbero mediare il rischio ereditario per l’IBD attraverso il loro comportamento nell’intestino. Mostra che molte varianti di rischio rivelano pienamente il loro impatto solo nel contesto della malattia, dove i circuiti regolatori si spostano e alcuni effetti genetici vengono amplificati. Per i non specialisti, il messaggio chiave è che sapere “dove” nel genoma risiede il rischio non basta; dobbiamo anche sapere “quando” e “in quale stato tissutale” quelle varianti agiscono. Mappe focalizzate sulla malattia come questa aiuteranno i ricercatori a dare priorità a geni come ABO e TNFRSF14 per studi funzionali e sviluppo di farmaci, avvicinandosi a terapie tarate sul cablaggio molecolare specifico di un intestino infiammato.
Citazione: Nishiyama, N.C., Silverstein, S., Darlington, K. et al. eQTL in diseased colon tissue identifies potential target genes associated with IBD. Nat Commun 17, 2736 (2026). https://doi.org/10.1038/s41467-026-69364-6
Parole chiave: malattia infiammatoria intestinale, genetica del colon, regolazione genica, varianti di rischio IBD, eQTL