Clear Sky Science · it
Multicopia eterogenea di varianti blaCTX-M sullo stesso plasmide aumenta l’adattabilità evolutiva in Klebsiella pneumoniae clinica
Perché questo è importante per la medicina moderna
Le infezioni resistenti agli antibiotici rappresentano una minaccia crescente negli ospedali di tutto il mondo, e i medici fanno sempre più spesso affidamento su farmaci di ultima risorsa per salvare i pazienti. Questo studio spiega come un batterio comune degli ospedali, Klebsiella pneumoniae, possa usare un sottile espediente genetico per resistere a potenti combinazioni di antibiotici pensate per sconfiggere la resistenza. Scoprendo questa strategia, la ricerca aiuta a spiegare perché alcune infezioni si ripresentano nonostante trattamenti aggressivi — e offre indizi su come i medici possano restare un passo avanti.
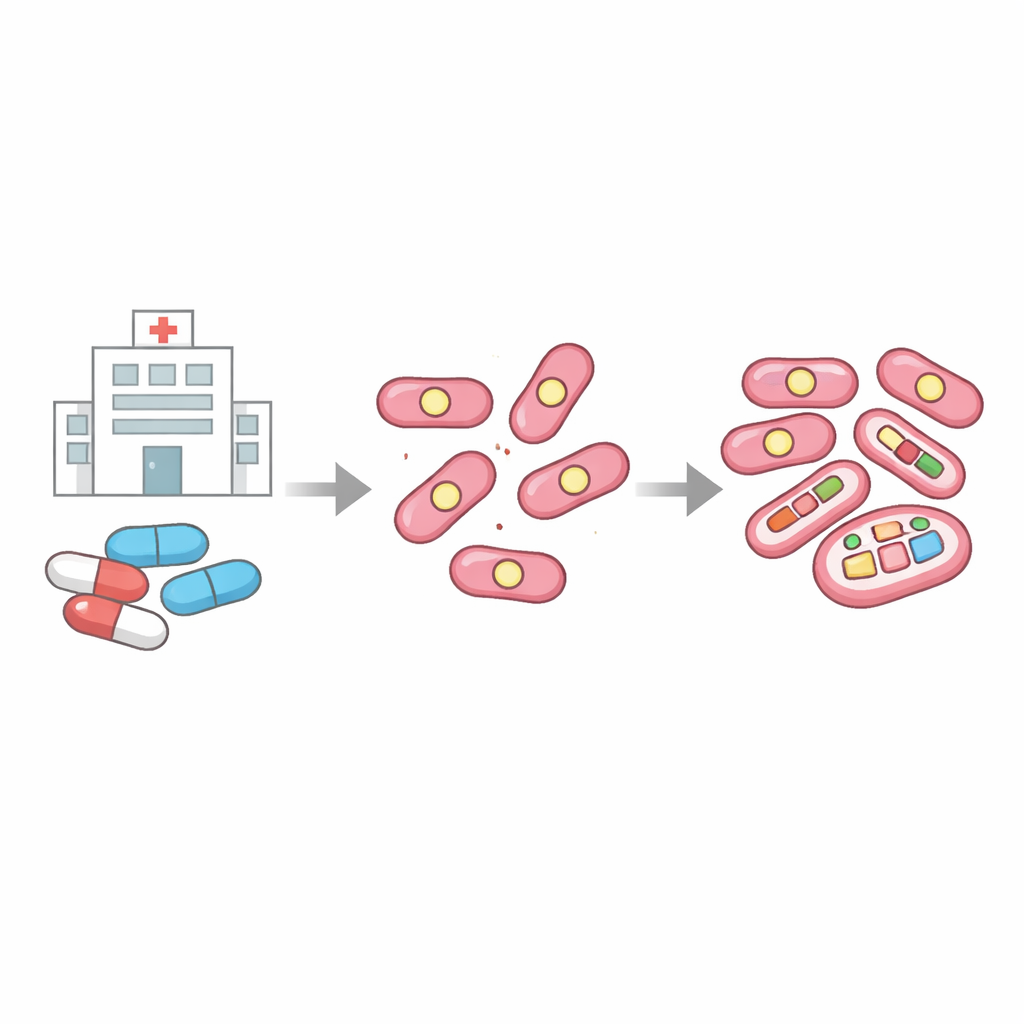
Un germe ospedaliero sotto pressione
La storia inizia in un’unità di terapia intensiva, dove due pazienti sono stati infettati da ceppi quasi identici di K. pneumoniae. Un ceppo è stato facilmente trattato con la moderna coppia di farmaci ceftazidime/avibactam, mentre l’altro risultava fortemente resistente. I confronti genetici hanno mostrato che entrambi i ceppi portavano la stessa ampia famiglia di enzimi di resistenza, chiamati β-lattamasi, su un plasmide condiviso — un piccolo cerchio di DNA mobile all’interno del batterio. Ma nel ceppo resistente uno di questi enzimi era cambiato in modo sottile, e quella variante, denominata CTX-M-249, permetteva al batterio di ignorare la combinazione di farmaci che avrebbe dovuto ucciderlo.
Un piccolo cambiamento con grandi conseguenze
Test biochimici più approfonditi hanno rivelato che CTX-M-249 scambia un tipo di protezione con un altro. La versione comune, CTX-M-65, è eccellente nel degradare alcuni antibiotici come il cefotaxime, ma rimane vulnerabile all’inibitore avibactam. CTX-M-249, alterata in appena due posizioni della proteina, diventa efficace contro ceftazidime più avibactam ma perde gran parte della sua efficacia contro il cefotaxime. Sulla carta, questo somiglia a un classico compromesso evolutivo: acquisire una difesa indebolendone un’altra. Tuttavia il ceppo clinico ha evitato questo svantaggio portando contemporaneamente diverse copie strettamente correlate del gene, così versioni differenti dell’enzima potevano coesistere nella stessa linea batterica.
Molte copie, molte opzioni
Utilizzando sequenziamento del DNA a letture lunghe e metodi di conteggio precisi, i ricercatori hanno scoperto che il plasmide nel ceppo resistente conteneva due siti separati blaCTX-M, e che uno di questi poteva esistere in più versioni lievemente diverse. In assenza di pressione farmacologica, circa metà della popolazione portava la versione CTX-M-65 e quasi metà portava CTX-M-249, con una piccola frazione che presentava forme intermedie. Quando i batteri sono stati esposti a dosi crescenti di ceftazidime/avibactam, sia il numero di copie geniche sia la quota di CTX-M-249 sono aumentati bruscamente. A volte ciò avveniva aumentando il numero di plasmidi per cellula; a livelli di farmaco più elevati, lo stesso plasmide sviluppava ripetizioni a corte tandem del gene di resistenza. In pratica, i batteri usavano la duplicazione del DNA come una manopola che potevano aumentare o diminuire per adattarsi agli antibiotici circostanti.
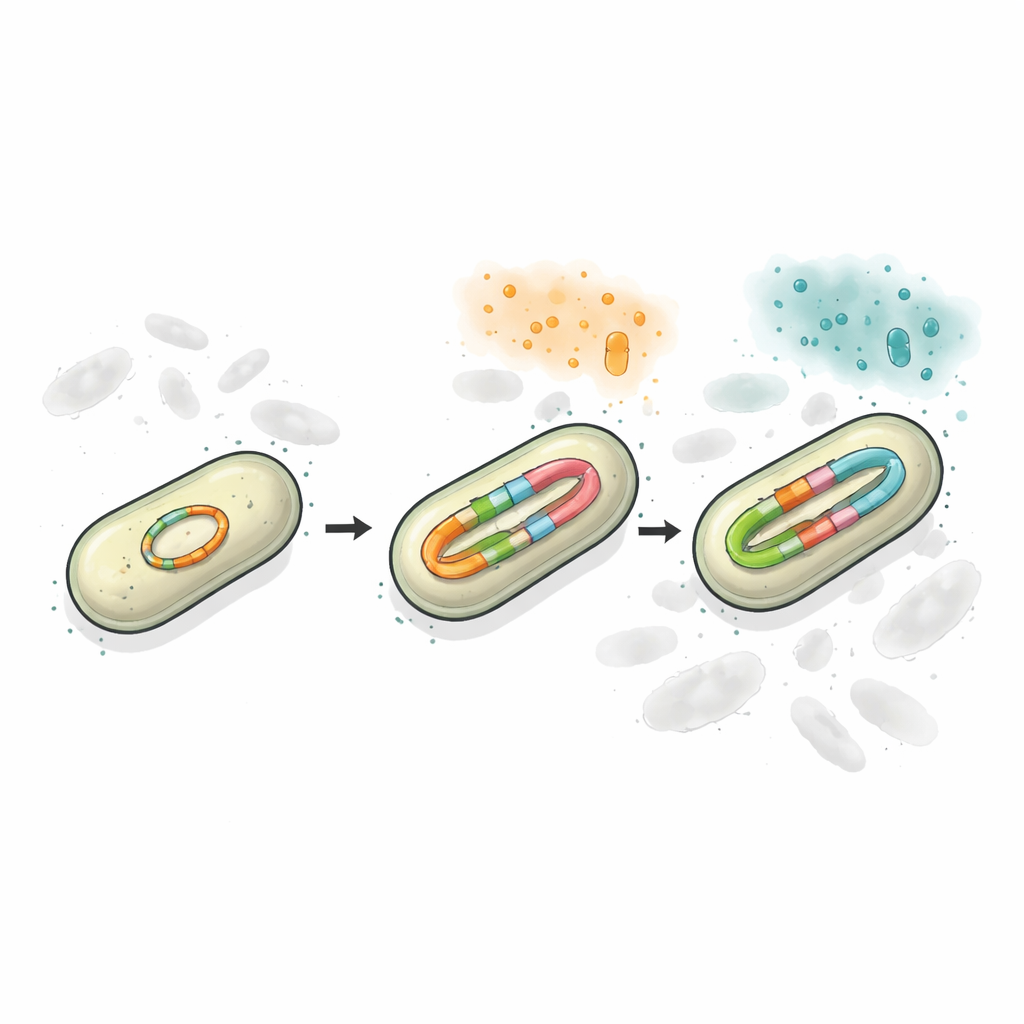
Mantenere la diversità su un unico cerchio di DNA
Per verificare come questa disposizione influenzi la sopravvivenza, il gruppo ha costruito modelli di laboratorio semplificati in cui i batteri portavano o una singola versione di resistenza, o due versioni su plasmidi separati, o entrambe le versioni codificate insieme su un unico plasmide. Quando sono stati sfidati con due diversi cefalosporinici, i sistemi misti hanno superato i ceppi a gene singolo, perché almeno una versione dell’enzima poteva far fronte a ciascun farmaco. Tuttavia, la configurazione in cui entrambe le varianti geniche erano sullo stesso plasmide si è rivelata la più stabile. Quando gli antibiotici venivano applicati per diversi giorni o cambiati da un farmaco all’altro, le cellule con due plasmidi separati spesso ne perdeva uno, sacrificando parte della loro protezione. Al contrario, il plasmide “due-in-uno” veniva ereditato come un pacchetto, preservando entrambe le opzioni di resistenza anche quando ciò imponeva un costo di crescita a breve termine.
Un modello più ampio nei batteri pericolosi
I modelli matematici hanno riprodotto questi esperimenti, mostrando che, oltre certi livelli di antibiotico, i batteri con un singolo plasmide che porta multiple varianti di resistenza finiscono per dominare le popolazioni miste. I ricercatori hanno quindi cercato migliaia di genomi di K. pneumoniae provenienti da ospedali, allevamenti, alimenti e ambiente. Hanno frequentemente trovato copie multiple e leggermente diverse di geni chiave di resistenza — specialmente negli isolati clinici umani che affrontano un forte esposizione a farmaci. Ciò suggerisce che l’inserire “eterogeneità multicopia” nei plasmidi non è una rarità, ma una tattica diffusa che i batteri utilizzano per coprirsi le spalle contro trattamenti variabili.
Cosa significa questo per i pazienti e le terapie
Per un non specialista, il messaggio principale è che alcuni batteri non portano semplicemente un singolo gene di resistenza; portano famiglie di versioni correlate raggruppate sullo stesso elemento di DNA mobile, dotandosi di una cassetta di strumenti flessibile contro farmaci diversi. Questa disposizione permette loro di mantenere la resistenza per lunghi periodi, anche quando i medici cambiano terapia, e aiuta a spiegare perché certe infezioni sono così difficili da eliminare. Allo stesso tempo, lo studio mostra che combinazioni farmacologiche scelte con cura — come l’accoppiamento di ceftazidime/avibactam con cefotaxime — possono sfruttare punti deboli di questo sistema e sopprimere anche ceppi ben armati. Capire come i batteri progettano e utilizzano questi plasmidi multicopia è quindi cruciale per ideare strategie antibiotiche più intelligenti e rallentare la marcia della resistenza.
Citazione: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Parole chiave: resistenza agli antibiotici, Klebsiella pneumoniae, plasmidi, beta-lattamasi, terapia multidrogica