Clear Sky Science · it
TANGO: Analisi e cura delle particelle nella crio–tomografia elettronica
Vedere le cellule in 3D, poi interpretare la folla
La crio–tomografia elettronica permette agli scienziati di congelare le cellule vive in azione e catturarle in tre dimensioni, quasi come mettere in pausa un film a risoluzione atomica. Ma una volta mappati migliaia di minuscoli «puntini» molecolari all’interno di una cellula, emerge un nuovo problema: come capire chi sta accanto a chi, chi forma squadre e dove si nascondono i pattern importanti in questa affollata città molecolare? Questo studio presenta TANGO, un framework software che trasforma mappe 3D grezze di particelle in racconti leggibili su come le molecole sono disposte e collaborano tra loro.
Da punti nel ghiaccio a una mappa dei vicini molecolari
La crio–tomografia elettronica inizia inclinando il campione congelato nel microscopio per registrare molte immagini 2D. Queste vengono combinate in un volume 3D, chiamato tomogramma, dove complessi molecolari individuali appaiono come macchie sfocate. I metodi esistenti già sfruttano questi dati per affilare le forme delle molecole mediando molte copie, ma trascurano in gran parte un tesoro altrettanto ricco: le posizioni e le orientazioni esatte di ogni particella. TANGO è progettato per sfruttare questa informazione trascurata. Tratta tutte le particelle come punti nello spazio, ciascuno con una direzione, e analizza come sono posizionate e orientate l’una rispetto all’altra. In questo modo va oltre la semplice domanda «come è fatta questa molecola?» per chiedersi «come sono organizzate insieme queste molecole nella cellula?» 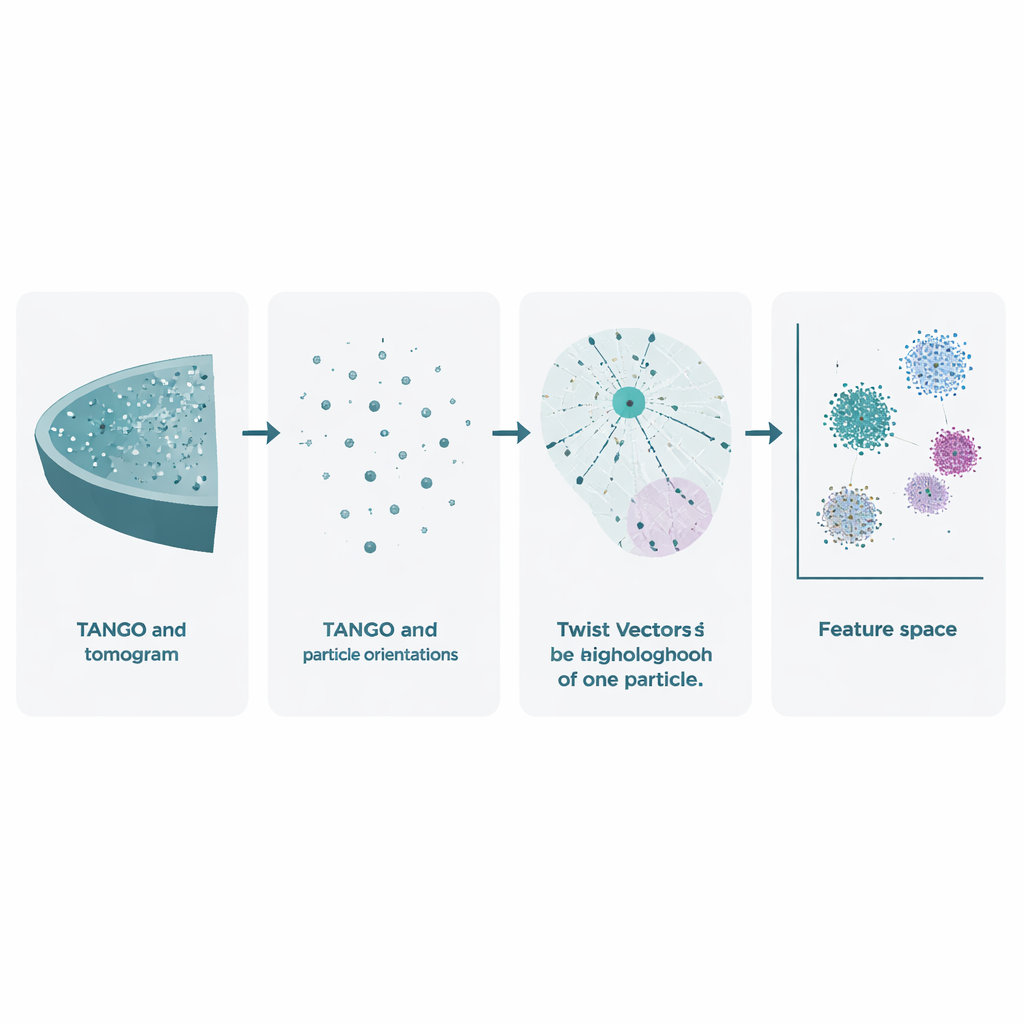
Catturare torsioni e rotazioni con un nuovo descrittore
Al centro di TANGO c’è l’idea dei «vettori di torsione». Per una data particella, il software considera tutti i vicini entro un raggio scelto e registra due cose: dove si trova ciascun vicino nello spazio 3D e come è ruotato rispetto alla particella centrale. Queste relazioni combinate di posizione e angolo vengono codificate in descrizioni numeriche concise note come descrittori di torsione. Poiché TANGO riallinea sempre i dintorni in un sistema di riferimento comune, questi descrittori sono insensibili alla rotazione complessiva del campione nel microscopio. Ciò rende possibile confrontare i vicinati locali attraverso diversi tomogrammi ed esperimenti in modo coerente.
Pulire dati rumorosi e ricostruire assemblaggi molecolari
I dati sperimentali reali sono disordinati: i metodi automatici di rilevamento possono includere molte false particelle e perdere traccia di quali frammenti appartengono a quali strutture più grandi. TANGO affronta questo trasformando la rete di relazioni di torsione in un grafo, dove le particelle sono nodi e i collegamenti di vicinato sono archi. Analizzando come si connettono i nodi, TANGO può raggruppare le particelle nei corretti assemblaggi genitori ed eliminare gli outlier che non si adattano alla geometria attesa. Gli autori mostrano che questo approccio recupera accuratamente l’architettura ad anello dei pori nucleari nella membrana del nucleo, l’organizzazione tubulare dei microtubuli e le conchiglie approssimativamente sferiche delle particelle simili a virus HIV immature. In ciascun caso, TANGO pulisce le liste di particelle e ripristina a quali pezzi appartengono, spesso eguagliando o migliorando una meticolosa curatela manuale.
Individuare difetti sottili e pattern nei reticoli
Molti virus e strutture cellulari formano reticoli ripetitivi, come piastrellature molecolari su superfici curve. TANGO utilizza i suoi descrittori di torsione per misurare quanto siano regolari questi pattern e per rilevare i punti in cui si piegano o si interrompono. Un ingrediente chiave è uno «score angolare» che confronta le orientazioni rispettando le simmetrie intrinseche, come la simmetria a sei delesameri. Applicato ai capsidi maturi di HIV, TANGO individua i pentameri — unità a cinque parti necessarie per chiudere la conchiglia conica — nascosti in ampi campi di esameri. Nei reticoli immaturi di HIV separa regioni ben ordinate da quelle distorte e collega punteggi angolari bassi ad aree irregolari e rotte della conchiglia. Analisi simili su dati di cromatina sintetica e ribosomi rivelano nucleosomi impilati, arrangiamenti elicoidali di DNA–proteina e coppie ricorrenti di ribosomi che somigliano a stati di traduzione descritti in precedenza. 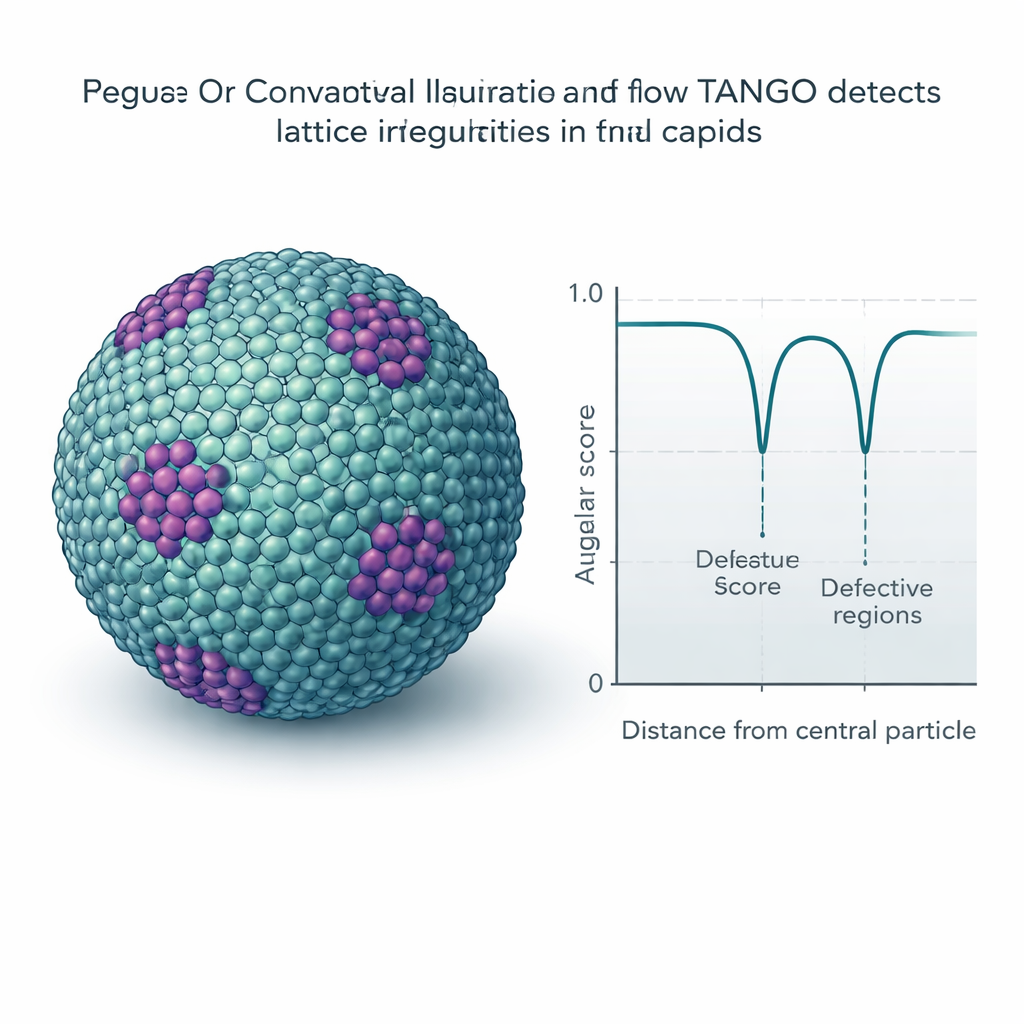
Una cassetta degli attrezzi flessibile per esplorare l’architettura cellulare
TANGO è implementato come software open source in Python e include un’interfaccia grafica in modo che gli utenti possano provare diverse forme di vicinato, filtri e caratteristiche senza programmazione intensa. Poiché è modulare, i ricercatori possono inserire le proprie misure geometriche o descrittori di pattern e usarli immediatamente nello stesso flusso di lavoro. Per i nuovi arrivati, questo abbassa la barriera all’esplorazione dell’organizzazione spaziale; per gli esperti, fornisce un framework che può crescere con nuove idee e dataset.
Perché questo è importante per comprendere le cellule viventi
In termini semplici, questo lavoro offre ai biologi un modo per passare da immagini statiche di singole molecole a mappe dinamiche di come quelle molecole sono disposte e cooperano all’interno delle cellule. Codificando le relazioni «chi sta vicino a chi» e «come sono orientati» in caratteristiche numeriche robuste, TANGO trasforma dati 3D rumorosi di microscopia in pattern che possono essere raggruppati, confrontati e testati statisticamente. Ciò può rivelare assemblaggi nascosti, individuare difetti nelle conchiglie virali e scoprire disposizioni molecolari rare legate a malattie o all’azione di farmaci. Con la diffusione della crio–tomografia elettronica, strumenti come TANGO aiuteranno a trasformare dense nubi di particelle in intuizioni chiare sulla coreografia interna della vita.
Citazione: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Parole chiave: crio–tomografia elettronica, organizzazione spaziale, reticoli molecolari, capsidi virali, ribosomi