Clear Sky Science · it
PRICE: rilevamento diretto e robusto dei microRNA a risoluzione di singolo nucleotide
Perché contano i messaggi genetici minuscoli
All'interno di ogni cellula c'è uno sciame di minuscole molecole di RNA chiamate microRNA che contribuiscono a regolare finemente quali geni vengono attivati o disattivati. Una variazione di una sola “lettera” in queste brevi molecole può spostare l'equilibrio verso la salute o la malattia, compresi i tumori. Medici e ricercatori vorrebbero leggere direttamente queste piccole differenze dal sangue o dal tessuto, ma i metodi attuali sono spesso lenti, costosi e non abbastanza precisi per individuare con affidabilità una singola modifica di lettera. Questo articolo presenta una nuova tecnica di laboratorio, chiamata PRICE, che promette di leggere questi errori microscopici nei microRNA in modo più semplice e accurato, aprendo la strada a una diagnosi più precoce del cancro e a un monitoraggio migliore del comportamento dei tumori.
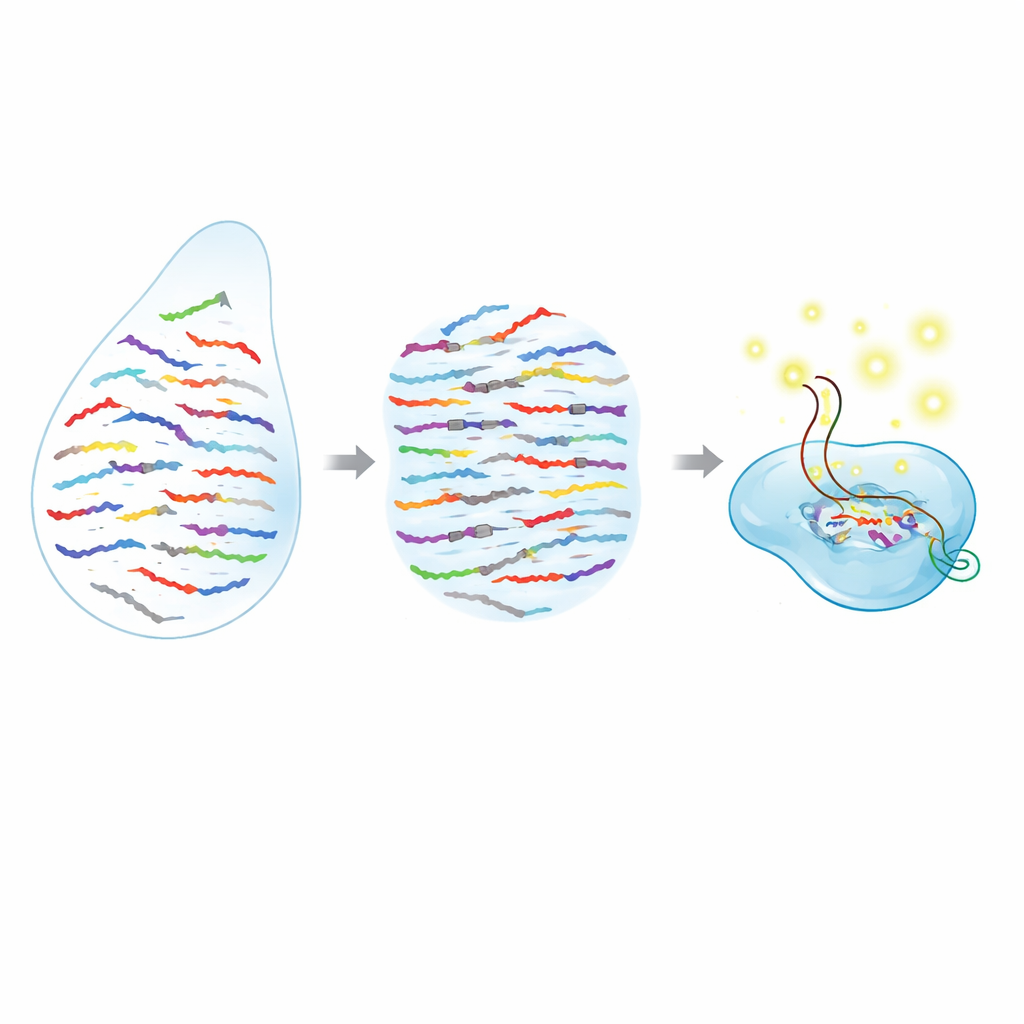
Un nuovo modo per separare molecole simili
I microRNA sono estremamente corti, il che rende difficile distinguerli quando le loro sequenze differiscono di un solo elemento. Molti strumenti attuali, come la PCR e il sequenziamento dell'RNA, contano bene i microRNA nel loro complesso, ma faticano quando due versioni sono quasi identiche oppure richiedono preparazioni complesse del campione e strumenti costosi. Gli autori combinano due idee potenti per superare questo limite: una “forbice” molecolare programmabile della famiglia CRISPR e pezzi sintetici simili al DNA chiamati peptide nucleic acid (PNA). L'enzima CRISPR Cas13a può essere istruito su quale RNA riconoscere e, una volta trovato il bersaglio, inizia a tagliare molecole reporter vicine, producendo un segnale fluorescente brillante. I PNA, nel frattempo, sono brevi filamenti che si legano particolarmente forte alle sequenze RNA corrispondenti ma perdono il loro legame in modo netto se anche una sola lettera è sbagliata.
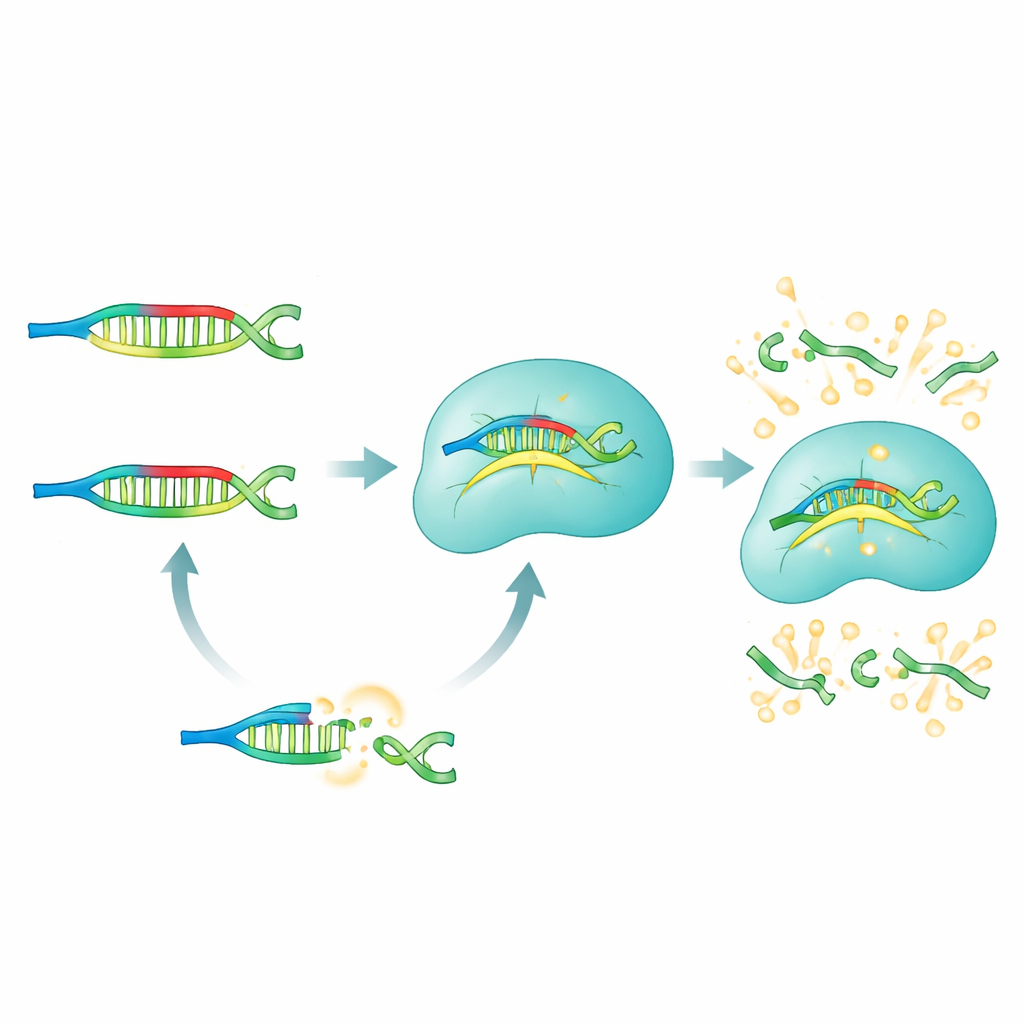
Come funziona il metodo PRICE
Nel sistema PRICE, i PNA agiscono come bloccanti selettivi che silenziano tutto ciò che i ricercatori non vogliono vedere. Per un dato microRNA di interesse, il team progetta un pannello di PNA bloccanti che si accoppiano perfettamente con tutte le versioni “sbagliate” — quelle con cambiamenti di una singola lettera indesiderati — pur essendo intenzionalmente non corrispondenti al bersaglio scelto. Quando un campione biologico (da siero, cellule o tessuto) viene miscelato con questi PNA, i microRNA non bersaglio vengono legati strettamente e mascherati efficacemente. Il vero bersaglio rimane non legato e libero di interagire con il complesso Cas13a, che è stato preprogrammato con un RNA guida che riconosce quel microRNA. Solo questo bersaglio non bloccato può attivare Cas13a nella sua modalità di taglio, che a sua volta scinde le molecole reporter fluorescenti e genera un bagliore forte e facilmente misurabile.
Affinare la precisione di una singola lettera
Gli autori hanno esplorato sistematicamente come progettare i PNA bloccanti in modo che siano abbastanza forti da catturare il microRNA errato, ma abbastanza deboli da ignorare il desiderato che differisce di una sola lettera. Hanno scoperto che due regole di progettazione analoghe alla temperatura sono cruciali: il PNA dovrebbe formare una coppia stabile con il mutante indesiderato a o sopra la temperatura corporea, ma formare una coppia molto più debole con il bersaglio che si disgreghi ben al di sotto di quella temperatura. Usando queste regole, supportate da un modello predittivo semplice, hanno costruito PNA che riducono i segnali falsi provenienti da microRNA mutanti di oltre il 70 percento lasciando quasi intatto il segnale vero. Importante, l'aggiunta dei PNA non ha ridotto la sensibilità complessiva: PRICE è stato comunque in grado di rilevare microRNA a concentrazioni di poche decine di femtomolari, confrontabili con i migliori test basati sull'amplificazione ma senza i passaggi di copia aggiuntivi.
Applicare il test a campioni tumorali
Per dimostrare che PRICE è più di un dispositivo teorico, il team si è concentrato sulla famiglia let‑7 di microRNA, fortemente coinvolta nella biologia del cancro. Hanno dimostrato che PRICE può isolare i microRNA bersaglio da miscele contenenti molti membri di famiglia quasi identici e può persino rilevare varianti rare che costituiscono solo il 5 percento di un campione. I ricercatori si sono poi rivolti a materiale clinico reale: linee cellulari di cancro al fegato, biopsie tissutali e siero di pazienti. Sia nel tessuto tumorale che nel sangue, PRICE ha rilevato coerentemente livelli più bassi di specifici microRNA let‑7 nei pazienti rispetto ai controlli non tumorali, in linea con studi precedenti. In un confronto diretto con la RT‑qPCR standard, PRICE ha mostrato almeno una capacità analoga e spesso migliore di distinguere casi tumorali da non tumorali, specialmente nei campioni di siero a bassa abbondanza dove i risultati della PCR diventavano rumorosi.
Perché questo conta per la diagnostica futura
In sostanza, questo lavoro mostra che è possibile leggere direttamente differenze di una singola lettera in piccoli RNA regolatori in modo pratico e scalabile. Permettendo ai PNA di bloccare sequenze simili indesiderate e affidando la lettura finale a un enzima CRISPR, PRICE offre una cassetta degli attrezzi flessibile per progettare test che possono essere ritargetizzati semplicemente sostituendo il pannello di bloccanti e l'RNA guida. Oltre al cancro al fegato e alla famiglia let‑7, la stessa strategia potrebbe essere estesa a molte altre malattie in cui piccoli cambiamenti di RNA sono importanti, e persino a varianti del DNA se associata a enzimi CRISPR correlati. Gli autori dimostrano inoltre un lettore compatto multicanale che può eseguire saggi PRICE al di fuori dei grandi laboratori centrali, suggerendo futuri test point‑of‑care. Se sviluppato ulteriormente, PRICE potrebbe diventare un modo pratico per monitorare sottili cambiamenti genetici che segnalano il cancro e altre malattie molto prima della comparsa dei sintomi.
Citazione: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Parole chiave: diagnostica dei microRNA, CRISPR Cas13a, peptide nucleic acid, variante a singolo nucleotide, biomarcatori del cancro al fegato