Clear Sky Science · it
Le interazioni proteina-proteina sono una fonte principale di epistasi nelle reti di interazione genetica
Perché questo è importante per capire i geni
Quando medici o test genetici ci dicono che un certo gene “causa” una malattia, suona semplice. In realtà, l’effetto di un singolo gene dipende spesso in modo rilevante da cosa stanno facendo gli altri geni nello stesso momento. Questo articolo indaga perché combinazioni di cambiamenti genetici possono comportarsi in modo imprevedibile e mostra che molte di queste sorprese possono essere ricondotte a come le proteine codificate da quei geni effettivamente si legano tra loro all’interno delle cellule. Capire questo nesso potrebbe affinare la nostra capacità di prevedere il rischio di malattia e di trovare bersagli farmacologici che sfruttino punti deboli nel cancro e in altre patologie.
Due mappe nascoste dentro ogni cellula
I biologi usano due potenti tipi di mappe per comprendere il funzionamento cellulare. Una è la mappa delle interazioni genetiche, che mostra cosa succede a una cellula quando due geni vengono perturbati insieme: talvolta la doppia alterazione è molto peggiore del previsto, talvolta più lieve. Questi effetti non additivi si chiamano epistasi e rendono difficile prevedere i tratti a partire solo dal DNA. La seconda mappa è quella delle interazioni proteina-proteina, che traccia quali proteine toccano fisicamente l’una l’altra per formare complessi e vie. Fino ad ora queste due mappe sono state studiate per lo più separatamente ed era incerto quanto fossero strettamente connesse.
Quanto fortemente si legano le proteine plasma gli effetti gene-gene
Gli autori hanno combinato grandi set di dati da lievito e cellule umane che misuravano sia quanto spesso le proteine si incontrano sia quanto fortemente si legano. Poi hanno sovrapposto a questo paesaggio fisico i dati sulle interazioni genetiche. È emerso un quadro chiaro: le coppie di geni le cui proteine formano complessi forti e ben bilanciati — dove entrambi i partner sono presenti in quantità simili e si legano in rapporti approssimativamente 1-a-1 — tendono a mostrare forti interazioni negative quando entrambi i geni vengono persi. In termini pratici, eliminare uno solo dei due geni danneggia la cellula in certa misura, ma perderli entrambi è particolarmente deleterio, riflettendo il ruolo centrale del complesso proteico condiviso. Per contro, partnership proteiche più deboli o sbilanciate mostravano effetti genetici più miti e variabili.
Trasformare la forza di legame in previsioni a livello di rete
Sapere semplicemente quali proteine si toccano non è sufficiente; la chiave è quanto stretti sono quei contatti. Per catturarlo, i ricercatori hanno usato spettrometria di massa quantitativa per stimare le affinità di legame — quanto facilmente le coppie di proteine si separano — attraverso migliaia di interazioni. Hanno scoperto che, all’aumentare della forza di legame, l’interazione genetica negativa media tra i geni corrispondenti segue una curva sigmoide liscia, molto simile a come un sito di legame si satura all’aumentare della concentrazione. Questo fenomeno era valido sia per il lievito sia per le cellule umane. Utilizzando questa relazione quantitativa, hanno dimostrato che la struttura di una rete di interazioni genetiche può essere in parte ricostruita soltanto dai dati di legame proteico, con gruppi di geni correlati che riemergono dalle misure proteiche.
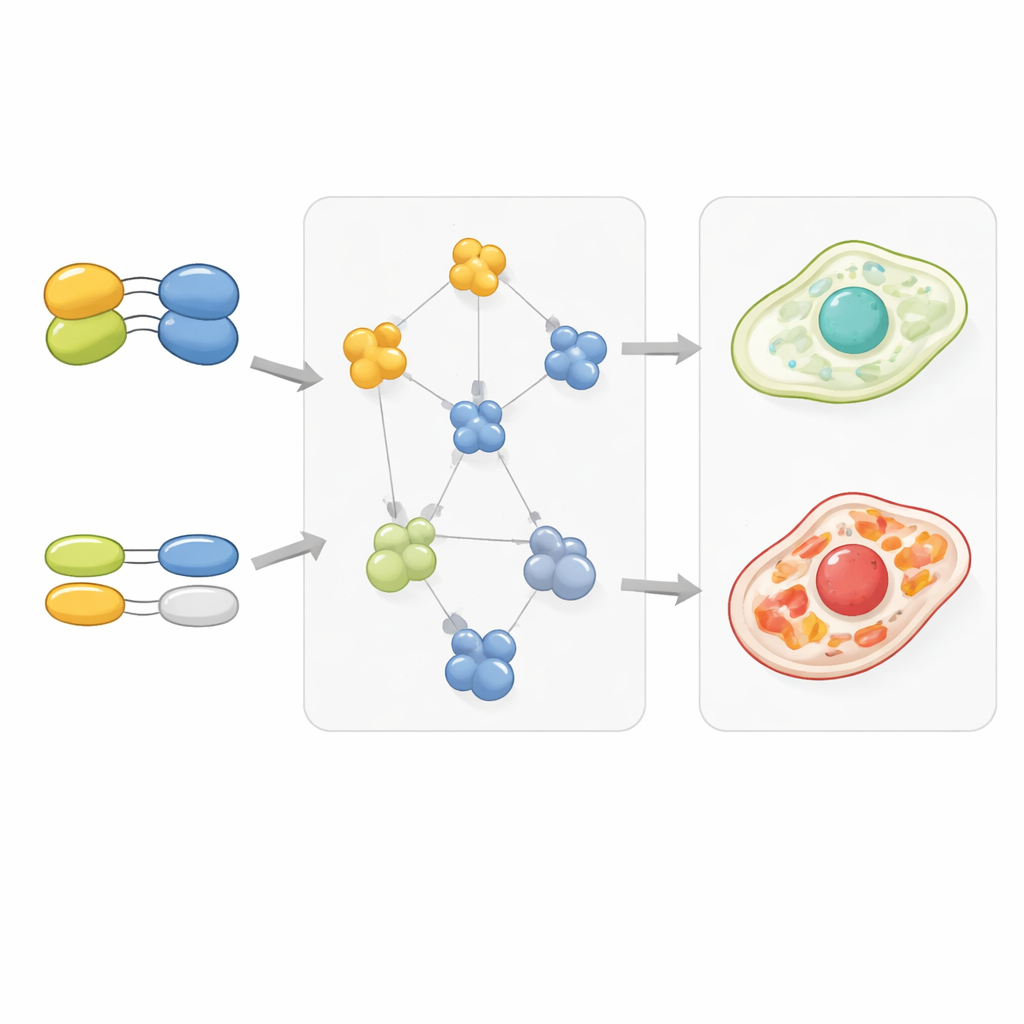
Duplicati genici e schemi di wiring cellulare
Lo studio ha esaminato anche i geni che hanno duplicati, noti come paraloghi, che spesso forniscono una copia di riserva l’uno per l’altro. Le coppie geniche in cui uno o entrambi i partner avevano duplicati tendevano a mostrare interazioni genetiche più deboli con altri geni, suggerendo che la ridondanza attenua l’impatto della perdita di una singola copia. In modo sorprendente, le proteine codificate da geni duplicati tendevano anche a legare i loro partner più debolmente, come se l’evoluzione avesse attenuato l’adesività per mantenere l’equilibrio dei numeri dei complessi nonostante le copie extra. Quando i duplicati divergevano maggiormente in sequenza e funzione, una copia spesso manteneva interazioni forti e focalizzate mentre l’altra perdeva o indeboliva molti dei suoi contatti, un pattern che corrispondeva ai cambiamenti nelle interazioni genetiche di quei geni con il resto della cellula.
Hub condivisi che collegano i sistemi cellulari
Oltre alle singole coppie, gli autori si sono chiesti se le forme su larga scala delle mappe genetiche e proteiche corrispondano. Hanno trovato che gruppi di geni che si raggruppano insieme nei dati di interazione genetica spesso corrispondono strettamente a complessi proteici noti. Altrettanto importante, gli stessi tipi di proteine “connettore” spesso collegano questi complessi in entrambe le mappe, formando schemi ricorrenti modulo-connettore-modulo. Per esempio, fattori di trasporto che muovono carico attraverso il poro nucleare e proteine di segnalazione come Ras appaiono come connettori condivisi, collegando processi cellulari distanti sia nelle reti fisiche sia in quelle genetiche.
Cosa significa per i geni, la malattia e la terapia
Il messaggio centrale per il pubblico non specialistico è che molti effetti misteriosi gene-gene non sono poi così enigmatici: emergono perché le proteine codificate da quei geni dipendono fisicamente l’una dall’altra e l’intensità di quella dipendenza può essere misurata. Collegando l’epistasi genetica alla chimica del legame proteico, questo lavoro ci porta più vicini a prevedere come combinazioni di mutazioni influenzeranno le cellule, anche nelle malattie umane. A lungo termine, mappe integrate di questo tipo potrebbero aiutare a identificare combinazioni di geni che, se bersagliate insieme, debilitano selettivamente le cellule tumorali o rivelano nuovi modi per ripristinare l’equilibrio in reti proteiche alterate.
Citazione: Castellanos-Girouard, X., Serohijos, A.W.R. & Michnick, S.W. Protein-protein interactions are a major source of epistasis in genetic interaction networks. Nat Commun 17, 2398 (2026). https://doi.org/10.1038/s41467-026-69152-2
Parole chiave: interazioni genetiche, reti proteiche, epistasi, complessi proteici, biologia dei sistemi