Clear Sky Science · it
Potenziare il rilevamento dei loop enhancers-promotori tramite metodi di normalizzazione per dati di interazione della cromatina
Vedere i loop nascosti nel nostro DNA
All'interno di ogni cellula, lunghe catene di DNA si piegano e si avvolgono in tre dimensioni, avvicinando tratti distanti del genoma. Alcuni di questi loop collegano fisicamente gli interruttori on–off chiamati enhancer con i geni che regolano, plasmando lo sviluppo cellulare e contribuendo all’insorgenza di malattie come il cancro. Questo articolo presenta un nuovo metodo computazionale, Raichu, che rende molto più facile individuare questi sottili loop regolatori in esperimenti su scala genomica, aprendo una finestra più nitida sul legame tra il ripiegamento del DNA e l’attività genica.
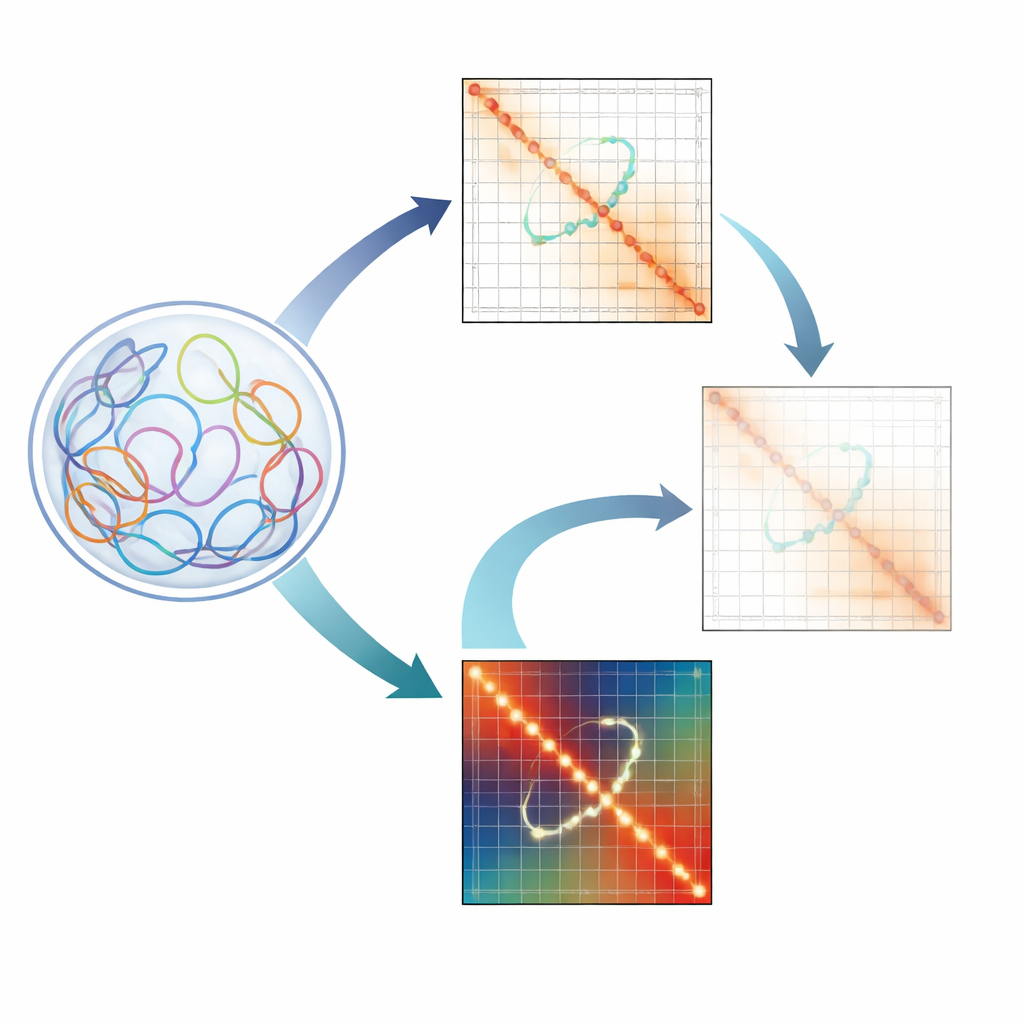
Perché i piccoli loop del DNA sono importanti
I nostri genomi non sono disposti come semplici stringhe di lettere. Si comprimono invece in una struttura 3D complessa all’interno del nucleo. In questo stato ripiegato, regioni di DNA lontane possono toccarsi, formando loop di cromatina. Alcuni loop fungono da impalcature che aiutano a organizzare interi quartieri del genoma. Altri sono loop regolatori che connettono promotori genici con enhancer distanti che ne aumentano l’attività. La perturbazione di questi loop regolatori è stata collegata a disordini dello sviluppo e tumori, quindi gli scienziati sono desiderosi di mappare questi contatti nei dettagli.
La sfida di leggere le mappe 3D del genoma
Tecniche come Hi-C e metodi correlati catturano milioni fino a miliardi di contatti DNA–DNA e li riassumono in mappe termiche, dove ogni pixel riflette la frequenza con cui due regioni del genoma si incontrano. Tuttavia, queste mappe sono piene di distorsioni tecniche: alcune regioni sono più facili da leggere a causa della composizione di sequenza, della mappabilità o del modo in cui vengono tagliate nell’esperimento. Per ripulire i dati, i ricercatori usano metodi di normalizzazione come ICE e KR che bilanciano le mappe in modo che ogni regione appaia con pari visibilità. Sebbene questi strumenti rendano più nitide caratteristiche ampie come domini estesi e forti loop strutturali, gli autori mostrano che involontariamente attenuano i loop enhancer–promotori più deboli ma biologicamente cruciali.
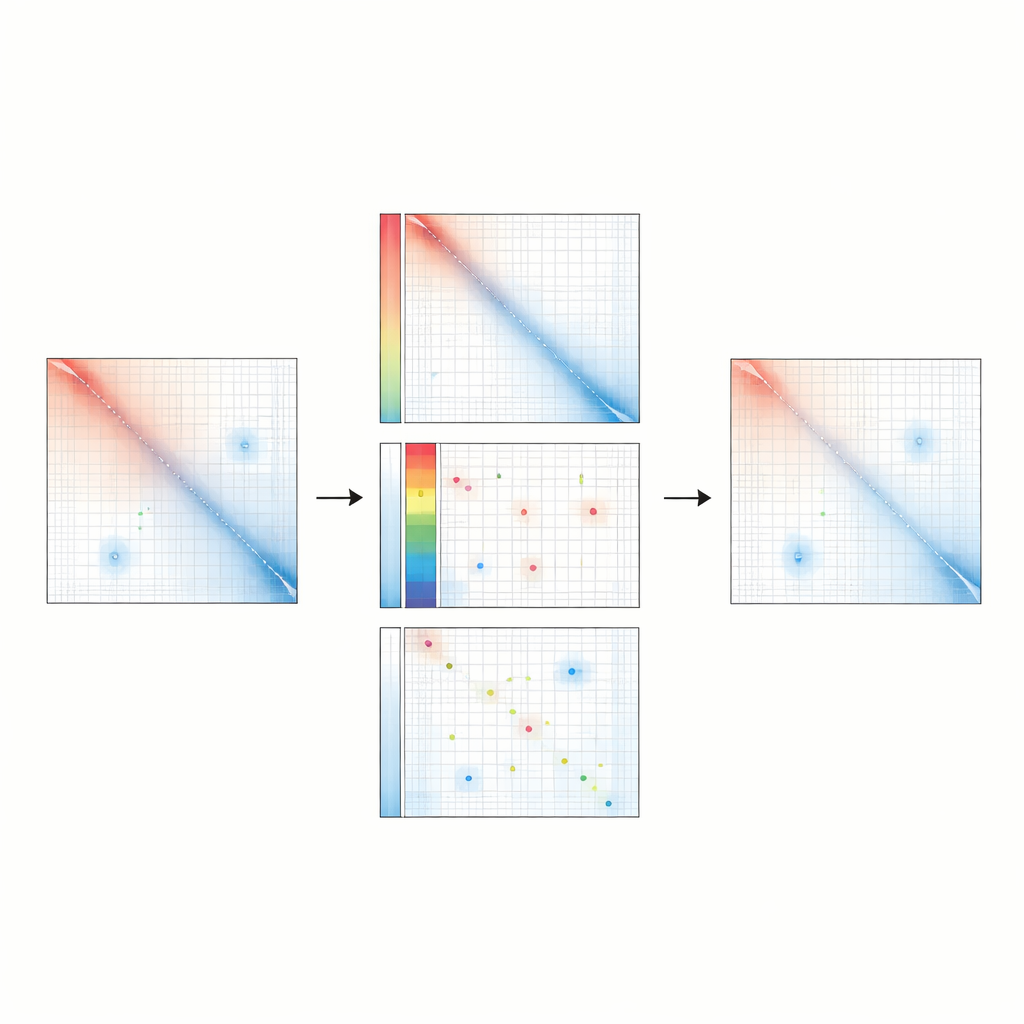
Un nuovo modo per pulire il segnale
Raichu adotta un approccio diverso per pulire i dati di contatto della cromatina. Invece di forzare ogni regione del genoma ad avere la stessa visibilità, modella ogni interazione come somma di tre componenti: un decadimento generale della frequenza di contatto con l’aumentare della distanza lungo il cromosoma, un bias specifico per ogni posizione e un segnale residuo specifico per quel particolare contatto. Utilizzando un algoritmo di ottimizzazione, Raichu stima il pattern di bias che meglio spiega i dati osservati mantenendo fisso il trend globale dipendente dalla distanza. I contatti vengono quindi corretti dividendo per questi valori di bias. Questo preserva il naturale decadimento globale delle interazioni correggendo selettivamente le distorsioni tecniche e lasciando segnali più chiari di contatti specifici reali nel DNA.
Scoprire migliaia di loop regolatori precedentemente mancati
Quando gli autori hanno applicato Raichu a dataset umani e murini con profondità di sequenziamento elevata, ha rivelato quasi il doppio dei loop di cromatina rispetto ai metodi standard, pur recuperando quasi tutti i loop già noti. I loop aggiuntivi individuati da Raichu erano fortemente arricchiti per marcatori biochimici di enhancer e promotori attivi e per il legame di fattori di trascrizione che controllano l’attività genica. Molti di questi loop erano supportati in modo indipendente da altre tecnologie per lo studio del genoma 3D e persino da imaging ad alta risoluzione, confermando che riflettono una reale prossimità fisica nel nucleo. Importante, Raichu ha mantenuto questo vantaggio anche quando i dati venivano ridotti per simulare profondità di sequenziamento inferiori, nello studio di metodi di mappatura specializzati come Micro-C e Micro-C con cattura di regioni, e persino raggruppando piccoli numeri di singole cellule.
Rivelare cambiamenti sottili e pattern evolutivi
Poiché Raichu è particolarmente sensibile ai loop regolatori, è più efficace nel rilevare differenze significative tra condizioni che altrimenti potrebbero apparire simili. In un modello cellulare umano ingegnerizzato portatore di una variante di rischio per leucemia, Raichu ha scoperto nuovi loop che emergevano solo nello stato di rischio, collegando geni chiave ai loro enhancer e corrispondendo a variazioni nell’attività genica. Tra cellule progenitrici neurali di topo e umano, Raichu ha rilevato migliaia di loop enhancer–promotore conservati tra le specie, spesso collegando enhancer distanti a geni coinvolti nello sviluppo cerebrale. Questi risultati suggeriscono che molti contatti regolatori importanti erano nascosti in bella vista, mascherati dagli approcci di normalizzazione precedenti.
Cosa significa per la ricerca genomica futura
Per un lettore non specialista, il messaggio chiave è che il modo in cui processiamo grandi dataset genomici può influenzare profondamente la biologia che osserviamo. Ripensando il passo di pulizia per le mappe 3D del genoma, Raichu ripristina segnali deboli ma importanti che collegano gli interruttori genici ai loro bersagli. Questo rende più semplice tracciare come il ripiegamento del DNA controlla l’attività genica in salute e malattia, dalle singole cellule ai tessuti e tra specie. Con l’adozione crescente di Raichu, i ricercatori possono aspettarsi mappe più ricche della comunicazione enhancer–promotore e un quadro più chiaro di come i cambiamenti nell’architettura del genoma contribuiscono allo sviluppo, al cancro e ad altre condizioni complesse.
Citazione: Wang, X., Shi, D., Xue, F. et al. Boosting the detection of enhancer-promoter loops via normalization methods for chromatin interaction data. Nat Commun 17, 2299 (2026). https://doi.org/10.1038/s41467-026-69082-z
Parole chiave: Organizzazione 3D del genoma, loop enhancer-promotore, analisi dati Hi-C, normalizzazione della cromatina, regolazione genica