Clear Sky Science · it
Motivi Shine-Dalgarno estesi regolano l'inizio della traduzione in Staphylococcus aureus
Come un germe ospedaliero regola finemente le sue fabbriche di proteine
Staphylococcus aureus è un germe comune che può causare di tutto, da lievi infezioni cutanee a malattie potenzialmente letali. Per sopravvivere nell'organismo e resistere ai trattamenti, deve rimettere continuamente a punto quali proteine produce. Questo studio svela come S. aureus controlli il primissimo passo della produzione proteica in modo diverso rispetto ai batteri da manuale come Escherichia coli, e mostra come questo controllo sia collegato alla formazione del biofilm, un fattore chiave nelle infezioni croniche e tolleranti agli antibiotici.
Una “stretta di mano” nascosta tra gene e ribosoma
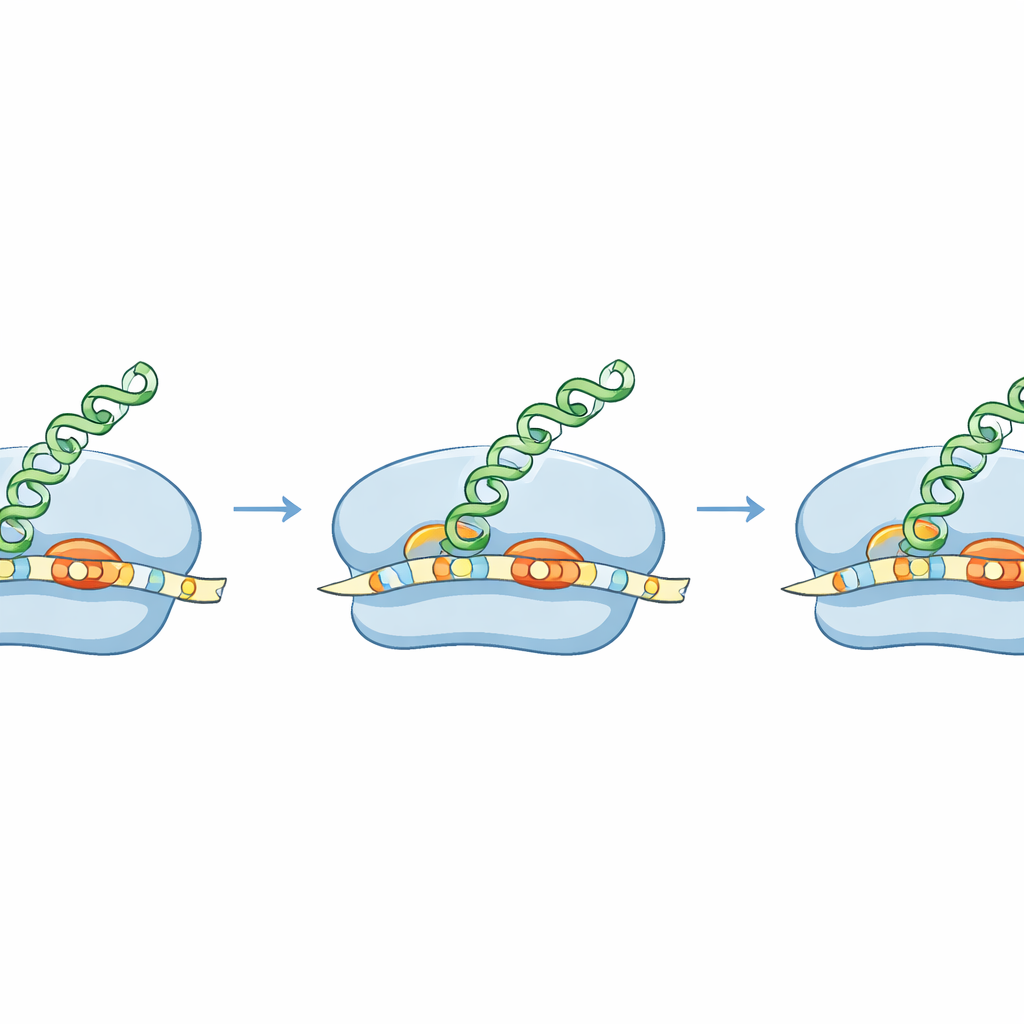
Per trasformare un gene in una proteina, i batteri impiegano i ribosomi, macchine molecolari che scansionano l'mRNA per trovare dove iniziare la lettura. Molti mRNA batterici contengono una breve sequenza, nota da tempo come regione Shine–Dalgarno, che aiuta il ribosoma ad ancorarsi nel punto giusto. Congelando i ribosomi nel momento in cui iniziano la traduzione e sequenziando i frammenti di RNA protetti, gli autori hanno creato una mappa ad alta risoluzione dei siti di inizio in tutto il genoma di S. aureus. Hanno scoperto che spesso S. aureus utilizza una versione insolitamente lunga di questa sequenza di aggancio, posizionata molto vicino al segnale di inizio, formando una «cerniera» estesa tra mRNA e RNA ribosomiale. Questo appaiamento esteso è molto più prominente che in E. coli e sembra essere un segno distintivo di come S. aureus sceglie dove cominciare.
Regole specifiche della specie per l'avvio della sintesi proteica
Il gruppo ha dimostrato che questa elica di aggancio estesa ha conseguenze reali. In diversi geni naturali di S. aureus, le prime lettere possono essere lette in più di un modo, offrendo posti rivali per l'inizio della traduzione. Usando ribosomi purificati, sistemi senza cellule e cellule vive, i ricercatori hanno confrontato come S. aureus ed E. coli gestiscono questi inizi ambigui. I ribosomi di S. aureus sceglievano in modo affidabile lo stesso inizio “corretto” usato nel batterio stesso, guidati dall'elica di aggancio lunga e dallo spaziamento preferito tra questa elica e il sito di inizio. I ribosomi di E. coli, al contrario, favorivano un diverso inizio vicino che produrrebbe una proteina alternativa. Ciò significa che lo stesso mRNA può generare proteine diverse in specie diverse, aprendo la strada a progettare messaggi leggibili soltanto da batteri selezionati.
Nuove proteine minuscole e segnali di inizio deboli
Poiché il loro metodo individua con precisione l'arrivo dei ribosomi nei siti di inizio, gli autori hanno potuto anche scoprire molti geni corti precedentemente sfuggiti. Hanno identificato dozzine di piccoli open reading frame, incluse brevi sequenze “a monte” che precedono immediatamente geni più grandi e noti. Alcune di queste regioni brevi probabilmente codificano piccole proteine con funzioni proprie; altre sembrano agire principalmente come regolatori. Lo studio ha inoltre rivelato che S. aureus talvolta inizia la traduzione da triplette di inizio “non canoniche” che di norma sono considerate segnali deboli. In questi casi, motivi di aggancio forti ed estesi sembrano compensare l'inizio debole, modulando la produzione proteica in modo che alcuni fattori, inclusi regolatori metabolici, siano prodotti solo in piccole quantità o in risposta alle condizioni di crescita.
Un sensore molecolare che collega nutrienti e crescita del biofilm
Un breve elemento a monte, chiamato rbfL, è emerso come un esempio notevole di controllo traslazionale legato alla virulenza. Si trova appena prima di rbf, un gene che codifica un fattore di trascrizione che promuove la formazione del biofilm. La sequenza di rbfL codifica un piccolo peptide «leader» ricco di arginina, compresi codoni per arginina molto rari che sono decodificati da tRNA scarsi. Quando l'arginina è limitata, questi codoni sono tradotti lentamente e i ribosomi si bloccano sulla regione che si sovrappone al sito di aggancio per rbf stesso, bloccando fisicamente l'avvio della traduzione di rbf da parte di nuovi ribosomi. Quando arginina o il suo tRNA corrispondente è abbondante, il blocco si risolve e rbf viene prodotto più efficacemente. Negli esperimenti di crescita, l'aggiunta di arginina extra ha aumentato la formazione del biofilm, collegando questo sensore molecolare direttamente a uno stile di vita comunitario resistente agli antibiotici.
Perché questi risultati sono importanti
Questo lavoro mostra che S. aureus ha evoluto motivi di aggancio estesi e piccoli elementi a monte per regolare con finezza dove e quando inizia la sintesi proteica. Queste caratteristiche non solo lo distinguono da batteri modello come E. coli, ma collegano anche il rilevamento dei nutrienti al controllo dei regolatori del biofilm. Per il lettore non specialista, la conclusione principale è che i «pulsanti di avvio» della produzione proteica del batterio sono più complessi di quanto si pensasse e che questi interruttori specializzati aiutano a determinare quando S. aureus diventa più pericoloso. Capire queste regole di inizio uniche potrebbe guidare la progettazione di antibiotici o strumenti genetici specifici per specie che distruggano selettivamente i batteri dannosi preservando quelli benefici.
Citazione: Kohl, M.P., Bahena-Ceron, R., Chane-Woon-Ming, B. et al. Extended Shine-Dalgarno motifs govern translation initiation in Staphylococcus aureus. Nat Commun 17, 2678 (2026). https://doi.org/10.1038/s41467-026-69079-8
Parole chiave: Staphylococcus aureus, inizio della traduzione, Shine-Dalgarno, piccoli ORF, regolazione del biofilm