Clear Sky Science · it
L’analisi genomica multicountry evidenzia la diffusione regionale del colera in Africa
Perché è importante seguire i germi oltre i confini
Il colera continua a provocare malattie e a uccidere decine di migliaia di persone ogni anno in Africa, eppure permangono questioni fondamentali su come iniziano le epidemie, come si spostano tra paesi e perché si ripresentano. Questo studio mette insieme scienziati e team di sanità pubblica di sette paesi africani per tracciare il batterio che causa il colera leggendo il suo codice genetico. Confrontando centinaia di genomi batterici, i ricercatori mostrano come le ondate recenti di colera abbiano attraversato i confini, quali tipi di ceppi circolano in quali aree e come queste conoscenze possano rendere più efficaci gli sforzi per fermare future epidemie.
Uno sguardo continentale al colera
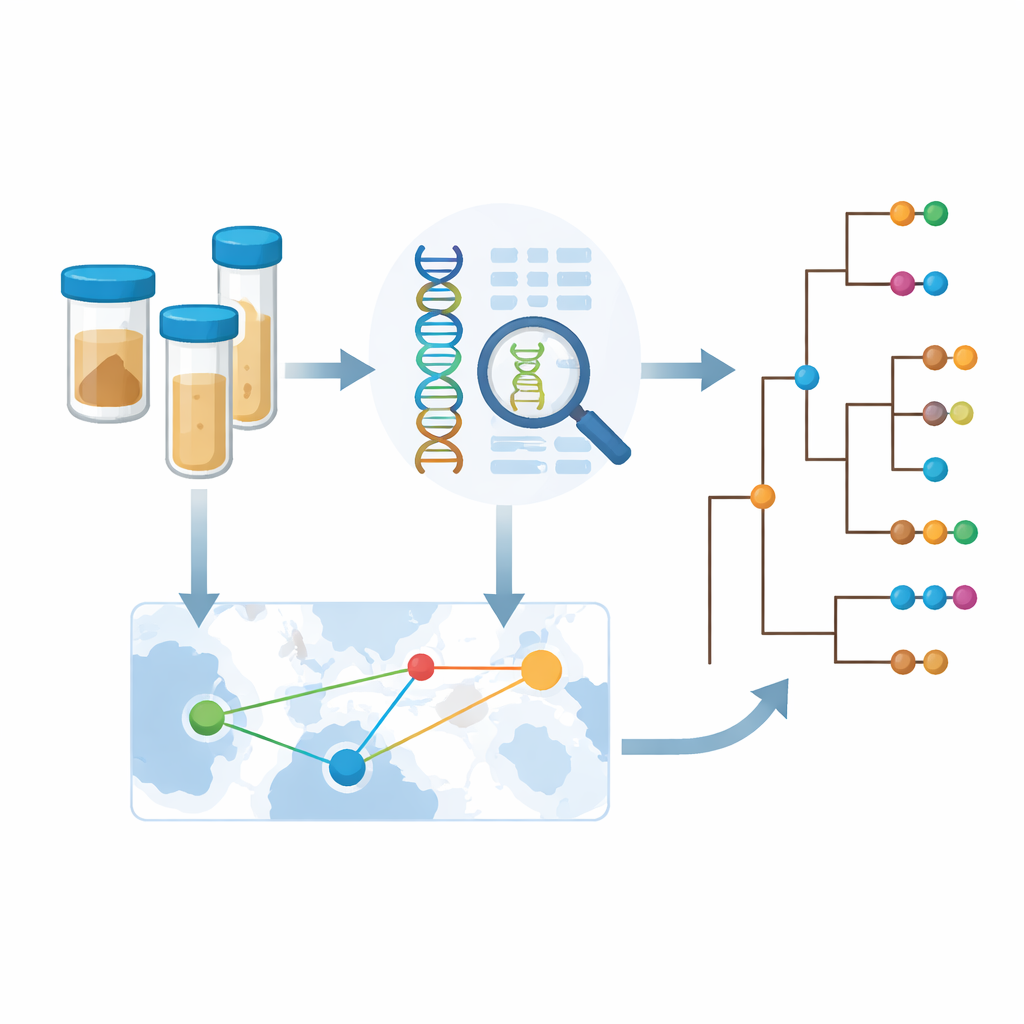
Per andare oltre segnalazioni isolate di casi, i Centri africani per il controllo e la prevenzione delle malattie hanno avviato una collaborazione chiamata Cholera Genomics Consortium in Africa (CholGEN). Laboratori in Camerun, Repubblica Democratica del Congo, Malawi, Mozambico, Nigeria, Uganda e Zambia hanno sequenziato 763 genomi di alta qualità del batterio Vibrio cholerae O1, per lo più raccolti tra il 2019 e il 2024. Questo rappresenta il più ampio insieme di genomi di colera mai generato all’interno dell’Africa. Collocando questi nuovi genomi accanto a quasi 1.800 campioni precedentemente sequenziati provenienti da Africa e Asia, il team ha potuto ricostruire come le recenti epidemie africane si inseriscono nella pandemia globale di colera in corso da tempo.
Ceppi antichi, rotte nuove
L’analisi ha mostrato che i ceppi di colera responsabili delle epidemie attuali in Africa non costituiscono una minaccia del tutto nuova. Tutti i batteri recentemente sequenziati discendono infatti da precedenti introduzioni della linea pandemica della settima ondata, che raggiunse l’Africa dall’Asia nel 1970. Paesi dell’Africa occidentale e centrale come Nigeria, Camerun e Repubblica Democratica del Congo tendono a essere dominati da una o due linee durature che persistono da decenni. I paesi dell’Africa orientale e meridionale, al contrario, ospitano una mescolanza contemporanea di diverse linee. Una in particolare, denominata AFR15, si è diffusa rapidamente negli ultimi anni ed è collegata a epidemie insolitamente grandi in Malawi, Zambia e paesi vicini, oltre che a focolai in alcune aree del Medio Oriente e del Sud Asia.
Quando la dimensione delle epidemie non sta nei geni
Si potrebbe sospettare che la rapida diffusione di AFR15 sia dovuta a importanti cambiamenti genetici che lo rendono più pericoloso o più capace di eludere i trattamenti. Tuttavia, confrontando il tasso e i modelli di mutazione tra diverse linee attive, i ricercatori non hanno trovato differenze marcate. I batteri stavano evolvendo a velocità simili, e i tipi di mutazioni e i geni coinvolti risultavano sostanzialmente analoghi da una linea all’altra. I profili complessivi dei geni di resistenza agli antibiotici sono risultati anch’essi per lo più stabili nel tempo e tra paesi. L’eccezione principale è l’Uganda, dove i batteri hanno acquisito un grande elemento di DNA mobile chiamato plasmide che porta molteplici geni di resistenza, probabilmente importato insieme a ceppi collegati a epidemie in Yemen e Libano. Anche in questo caso, lo studio non ha identificato nuovi geni in grado di spiegare da soli la gravità delle recenti epidemie africane.
Viaggi nascosti svelati da un campionamento migliore
Poiché i genomi batterici conservano traccia dei luoghi in cui si trovavano ceppi strettamente correlati, il team ha potuto inferire con quale frequenza il colera oltrepassa i confini nazionali. Sono stati individuati molti esempi di diffusione internazionale tra paesi vicini, comprese ripetute scambi tra Zambia e Repubblica Democratica del Congo. Tuttavia, analizzando più a fondo, è emerso che i segnali statistici di salti transfrontalieri risultavano più forti negli anni e nei luoghi con un campionamento intensivo. Questo suggerisce che i movimenti reali del colera sono più frequenti di quanto rivelino i dati attuali; molti eventi di trasmissione probabilmente passano inosservati semplicemente perché in quei luoghi o periodi non viene eseguito il sequenziamento dei batteri. Per affrontare questo limite, gli autori hanno sviluppato un quadro metodologico per stimare quante nuove informazioni un paese ottiene sequenziando campioni aggiuntivi, bilanciando diversità genetica, numero di introduzioni e dati esistenti.
Usare la genomica per orientare interventi più intelligenti
Lo studio conclude che, per il colera in Africa oggi, come e dove la malattia si diffonde conta più di qualsiasi cambiamento drammatico nel batterio stesso. I risultati sostengono la necessità di una sorveglianza genomica di routine e coordinata a livello regionale, in modo che i paesi vicini possano individuare tempestivamente focolai condivisi, rintracciarne le fonti e mirare interventi come campagne di vaccinazione, miglioramenti dell’acqua e dei sistemi igienico-sanitari e risposte nelle aree di confine in modo più efficiente. Rafforzando la capacità di sequenziamento nei laboratori di sanità pubblica africani e condividendo i dati oltre i confini, iniziative come CholGEN offrono una tabella di marcia pratica per usare la genetica moderna e avvicinarsi all’ambizioso obiettivo di eliminare il colera come minaccia per la salute pubblica entro il 2030.
Citazione: Mboowa, G., Matteson, N.L., Tanui, C.K. et al. Multicountry genomic analysis underscores regional cholera spread in Africa. Nat Commun 17, 2539 (2026). https://doi.org/10.1038/s41467-026-68642-7
Parole chiave: colera, sorveglianza genomica, Africa, trasmissione transfrontaliera, resistenza antimicrobica