Clear Sky Science · it
Un basecaller contestuale a doppio livello per il sequenziamento diretto dell'RNA con nanopore
Perché è importante decodificare le lettere dell'RNA
Ogni cellula del tuo corpo legge e riscrive continuamente messaggi scritti in RNA, la copia operativa dei nostri geni. I nuovi strumenti a nanopore possono leggere direttamente singole molecole di RNA, promettendo di rivelare come i geni vengono attivati, come gli RNA vengono splicati e come i segni chimici sull'RNA influenzano salute e malattia. C'è però un problema: questi dispositivi misurano in realtà piccole correnti elettriche, che poi devono essere tradotte — «basecalled» — nelle familiari lettere A, C, G e U. Se quella traduzione è sbagliata, la storia biologica che ne deduciamo può risultare gravemente distorta. Questo articolo presenta Coral, un nuovo sistema di intelligenza artificiale che rende questa traduzione molto più accurata.
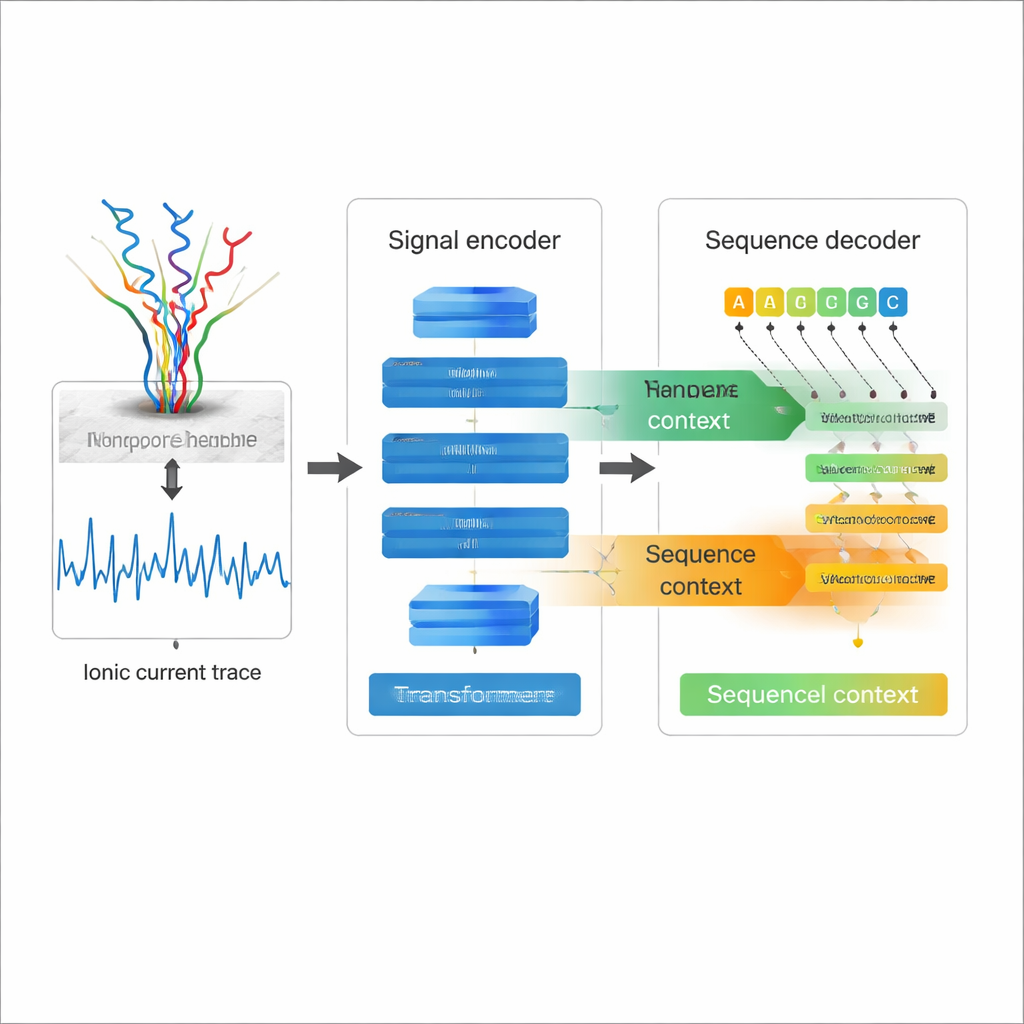
Leggere elettricità invece di lettere
Il sequenziamento diretto dell'RNA con nanopore funziona facendo passare un singolo filamento di RNA attraverso un foro molecolare — un nanopore — mentre si misura come la corrente elettrica cambia quando ogni nucleotide lo attraversa. Quelle irregolari tracce di corrente contengono l'informazione sulla sequenza di RNA e sulle sue modificazioni chimiche. Il sequenziamento tradizionale dell'RNA converte invece l'RNA in DNA e lo amplifica, passaggi che possono introdurre bias ed eliminare molti marchi chimici naturali. Il sequenziamento diretto dell'RNA evita questi problemi, ma il prezzo è stato finora un tasso di errore relativamente alto nel convertire le tracce di corrente in sequenze, specialmente per caratteristiche difficili come basi ripetute e strutture complesse dell'RNA. Un basecalling migliore è essenziale se gli scienziati vogliono fidarsi dei dettagli fini di queste letture lunghe di RNA.
Un traduttore più intelligente che usa due tipi di contesto
La maggior parte dei basecaller per nanopore esistenti tratta il segnale elettrico come la fonte principale di informazione e decodifica ogni posizione quasi indipendentemente, il che limita la capacità di sfruttare la struttura intrinseca della sequenza di RNA. Coral adotta un approccio differente. Usa un'architettura encoder–decoder basata su Transformer, simile nello spirito ai moderni modelli linguistici. Prima, una rete encoder costruita con convoluzioni e strati di self‑attention digerisce il segnale di corrente grezzo in una descrizione compatta di come il segnale cambia nel tempo. Poi un decoder predice ogni nuova base di RNA un passo alla volta, guardando contemporaneamente indietro alle basi già scritte e lateralmente al segnale codificato. Due tipi di attenzione — all'interno della sequenza di RNA in crescita e tra sequenza e segnale — permettono a Coral di ponderare sia il contesto elettrico sia quello della sequenza quando decide quale lettera viene dopo.
Sequenze più nitide e meno molecole perse
Gli autori hanno testato Coral rispetto a diversi basecaller di riferimento, inclusi gli strumenti commerciali di Oxford Nanopore, su RNA umano e di altri organismi e su più chimiche di nanopore. Su sei specie e kit di sequenziamento RNA più vecchi, Coral ha raggiunto una precisione mediana tipica intorno al 97%, nettamente superiore ai metodi concorrenti. Con l'ultimo kit RNA, la sua accuratezza ha superato il 99%. Coral ha prodotto meno mismatch, inserzioni e delezioni, e ha restituito letture più lunghe e meglio allineate con meno sequenze impossibili da mappare. Si è dimostrato particolarmente efficace nel gestire brevi run di basi ripetute — molto comuni nei dati reali — che sono una fonte frequente di errori per altri strumenti. Catturando in modo più affidabile tratti più lunghi di sequenza corretta, Coral ha anche eccelso nel predire brevi patterns di sequenza (k‑mer) e si è mantenuto robusto anche quando passaggi di decodifica precedenti contenevano piccoli errori.
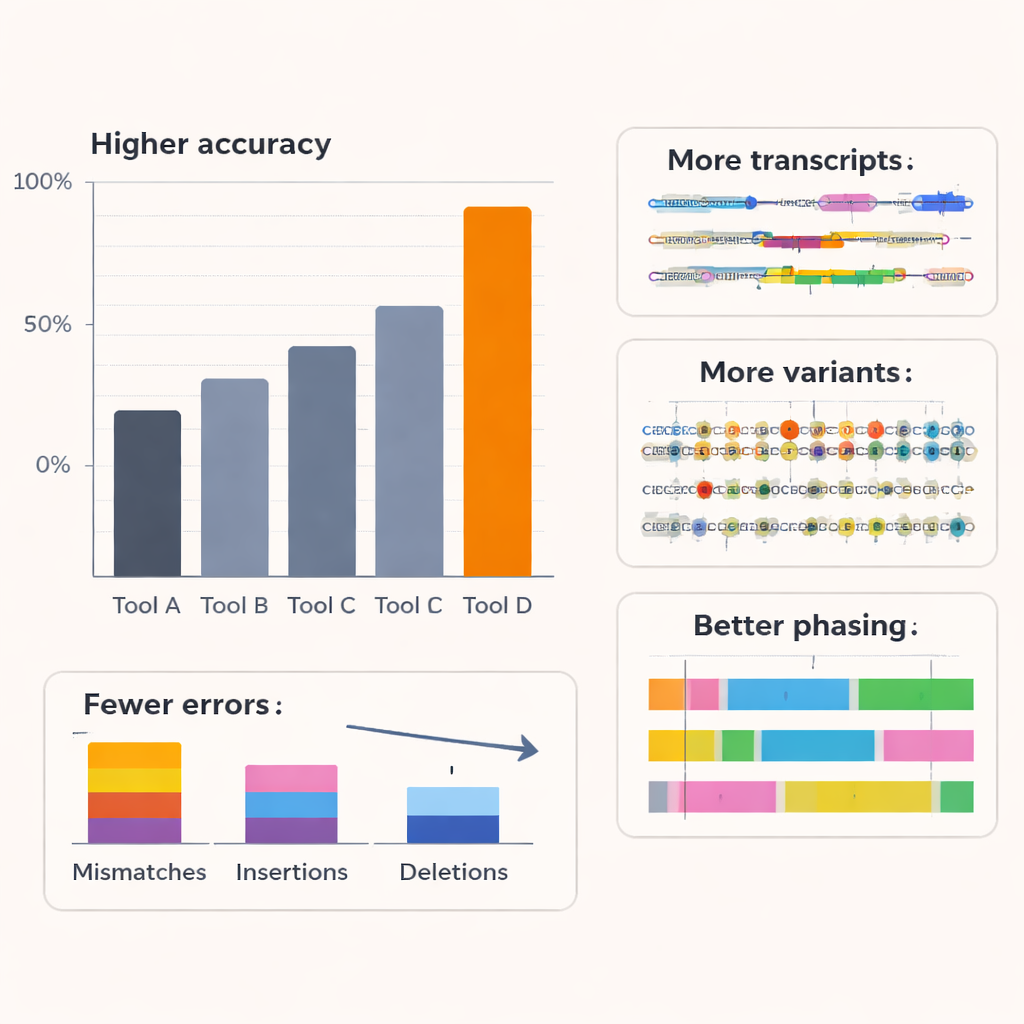
Scoprire più dettagli nascosti del trascrittoma
Un miglior basecalling è utile solo se conduce a una biologia migliore. Per verificare questo, il team ha esaminato come l'output di Coral influenzasse analisi a valle in linee cellulari umane. Usando uno strumento specializzato per ricostruire isoforme complete di RNA — le diverse versioni splice di ciascun gene — hanno trovato che le letture di Coral hanno rivelato più strutture di trascritti conosciute e molte isoforme a bassa abbondanza che altri basecaller avevano mancato. Molti trascritti specifici di Coral erano supportati da dati indipendenti a letture corte, indicando che sono reali piuttosto che artefatti. Coral ha anche rilevato più trascritti di riferimento artificiali con concentrazioni note in un esperimento di spike‑in e ha stimato la loro abbondanza con maggiore accuratezza. Oltre alla scoperta dei trascritti, Coral ha migliorato il rilevamento di eventi di fusione genica in una linea cellulare di carcinoma mammario e ha aumentato il numero e l'affidabilità dei geni con espressione allele‑specifica, in cui una copia parentale di un gene è più attiva dell'altra.
Varianti genetiche più chiare e linee familiari
Poiché le lunghe letture di RNA possono coprire varianti genetiche distanti, sono strumenti potenti per determinare quali varianti viaggiano insieme sulla stessa copia cromosomica — un processo chiamato phasing degli aplotipi. Utilizzando un campione umano ben studiato con una mappa di varianti di riferimento di alta qualità, gli autori hanno dimostrato che le letture di qualità superiore di Coral hanno portato a un rilevamento più accurato delle variazioni a singolo nucleotide e a molti meno errori di phasing: gli switch error e i tassi di mismatch complessivi all'interno dei blocchi phasati sono diminuiti fino a circa tre quarti rispetto ad altri metodi, mentre un numero sostanzialmente maggiore di varianti poteva essere phasato almeno in parte. Studi di simulazione variando l'accuratezza delle letture hanno confermato che una volta che il basecalling si avvicina al 95% di accuratezza, le prestazioni nella scoperta di trascritti, nell'espressione allele‑specifica e nel phasing migliorano nettamente e poi si stabilizzano. Coral si colloca in questa zona di alto beneficio, suggerendo che cattura la maggior parte delle informazioni biologicamente rilevanti presenti nei segnali rumorosi del nanopore.
Cosa significa per la ricerca futura sull'RNA
Per i non specialisti, il messaggio chiave è che Coral funziona come un traduttore molto più affidabile tra il linguaggio elettrico dei sequenziatori a nanopore e il linguaggio genetico dell'RNA. Usando meglio il contesto sia nel segnale sia nella sequenza in crescita, produce letture più pulite che svelano più varianti di trascritti, individuano geni di fusione rari e tracciano con maggiore fiducia quali varianti provengono da quale genitore. Il software è open‑source, così i ricercatori possono adattarlo a nuovi organismi, chimiche, o persino per studiare i marchi chimici sull'RNA stesso. Con il continuo miglioramento della tecnologia nanopore, strumenti come Coral aiuteranno a trasformare le tracce di corrente grezze in mappe dettagliate e affidabili del mondo dell'RNA all'interno delle cellule.
Citazione: Xie, S., Ding, L., Yu, Y. et al. A dual context-aware basecaller for nanopore direct RNA sequencing. Nat Commun 17, 1851 (2026). https://doi.org/10.1038/s41467-026-68566-2
Parole chiave: sequenziamento RNA con nanopore, basecalling, modello Transformer, isoforme di trascritti, fasing di aplotipi