Clear Sky Science · it
Scoperta su scala genomica e fenotipizzazione dei trascritti non codificanti in A. fumigatus rivela lncRNA con un ruolo nella sensibilità agli antifungini
Perché un fungo nelle nostre case conta
La maggior parte di noi pensa alla muffa come a un fastidio sul pane o negli angoli umidi, ma un fungo comune, Aspergillus fumigatus, è responsabile di oltre due milioni di decessi ogni anno—più della malaria e dell’HIV messe insieme. I medici si affidano a un arsenale limitato di farmaci antifungini per tenere sotto controllo questo patogeno, e la resistenza a questi farmaci sta crescendo rapidamente. Questo studio esplora uno strato nascosto del genoma del fungo: gli RNA lunghi non codificanti, o lncRNA, che non producono proteine ma possono comunque influenzare la risposta del fungo al trattamento. Comprendere questi elementi genetici “silenziosi” potrebbe aprire nuove strade per prevedere, monitorare e infine contrastare la resistenza agli antifungini.
Messaggi nascosti nel DNA fungino
Classicamente, i geni sono stati pensati come porzioni di DNA che codificano per proteine, le “operatrici” della cellula. Nell’ultimo decennio, gli scienziati hanno scoperto che vaste regioni del genoma vengono trascritte in molecole di RNA che non diventano proteine. Questi RNA lunghi non codificanti possono comunque influenzare il comportamento cellulare, inclusa la risposta ai farmaci. Mentre gli lncRNA sono stati mappati negli esseri umani e nei lieviti, erano in gran parte sconosciuti nei funghi patogeni come A. fumigatus. Gli autori hanno cercato di colmare questa lacuna costruendo un catalogo genomico di questi trascritti misteriosi e chiedendosi se alcuni di essi possano spostare l’equilibrio tra sensibilità e resistenza ai farmaci.
Ascoltare il fungo sotto attacco farmacologico
Per individuare gli lncRNA, il gruppo ha esposto A. fumigatus a sei diversi composti antifungini, inclusi gli azoli largamente usati che colpiscono la membrana cellulare fungina, e ha quindi sequenziato tutti gli RNA prodotti. Usando una pipeline bioinformatica personalizzata, hanno assemblato decine di migliaia di trascritti e rimosso sistematicamente tutto ciò che corrispondeva a geni noti che codificano proteine o a brevi RNA di manutenzione. Dopo più cicli di filtraggio e una curazione manuale, sono giunti a un set ad alta confidenza di 1.089 nuovi RNA lunghi non codificanti diffusi nel genoma. La maggior parte si trovava o tra geni noti o si sovrapponeva a essi in direzione opposta, e complessivamente hanno ampliato la frazione del genoma fungino nota come attivamente trascritta da circa due terzi a più di quattro quinti.
Risposte coordinate e hotspot conservati
Quando i ricercatori hanno confrontato come questi lncRNA variassero sotto diverse dosi di farmaco, hanno scoperto che il fungo non li impiega a caso. Al contrario, gli lncRNA si raggruppavano in circa 15 schemi di risposta distinti, alcuni condivisi tra più farmaci e altri unici per trattamenti particolari. Per esempio, farmaci che colpiscono vie biochimiche simili tendevano a scatenare firme di lncRNA sovrapposte, mentre un inibitore della sintesi proteica ha prodotto molte risposte uniche. Molti lncRNA erano molto vicini a geni già noti per influenzare la sensibilità agli azoli, come quelli coinvolti nella cattura del ferro o nella biosintesi dell’ergosterolo, componente chiave delle membrane fungine. In diversi casi, un lncRNA vicino e un gene di risposta farmacologica risultavano up‑ o down‑regolati insieme, suggerendo che questi elementi non codificanti possano contribuire a coordinare programmi di sopravvivenza cruciali.
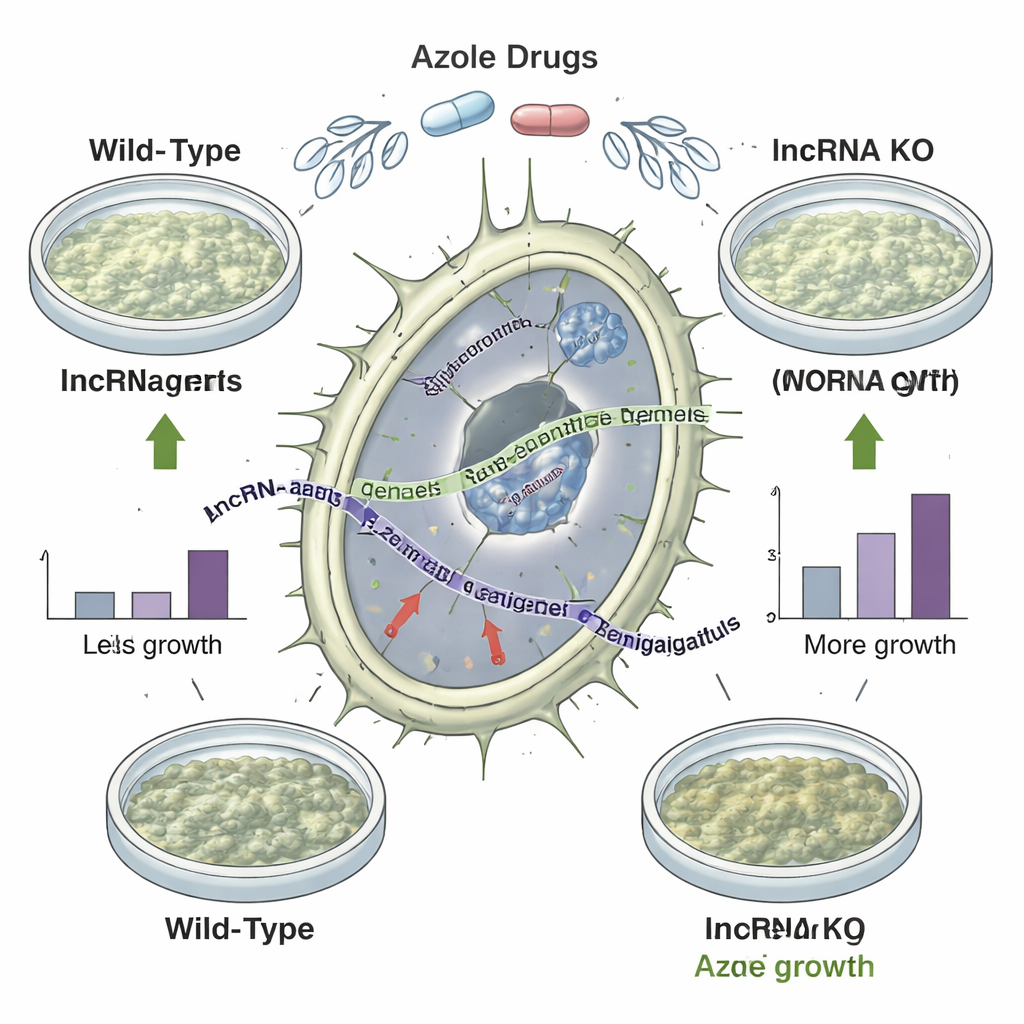
Rimuovere i “geni silenziosi” cambia la sensibilità ai farmaci
Catalogare gli lncRNA è una cosa; dimostrare che contano è un’altra. Il gruppo ha eliminato 92 regioni lncRNA selezionate dal genoma fungino e ha confrontato come i mutanti crescessero sotto una serie di stress, inclusi alta temperatura, carenza di ferro ed esposizione a tre diversi farmaci azolici. Sessanta mutanti hanno mostrato variazioni di fitness specifiche per condizione, e 35 sono effettivamente cresciuti meglio rispetto alla ceppa originale quando sfidati con azoli. Un ceppo delezionato di particolare rilievo mostrava una crescita migliorata con tutti gli azoli testati senza il semplice aumento dell’espressione dei geni proteici vicini, suggerendo fortemente che l’lncRNA assente stava di per sé limitando la tolleranza ai farmaci. Analizzando molti isolati clinici e ambientali con profili di suscettibilità ai farmaci noti, gli autori hanno inoltre trovato che la presenza o l’assenza di certi geni lncRNA si correlava con la facilità con cui ciascuno ceppo veniva inibito dagli azoli.
Cosa significa per la lotta contro le infezioni fungine mortali
Per i non specialisti, il messaggio chiave è che parti del genoma fungino una volta bollate come “spazzatura” stanno attivamente plasmando quanto A. fumigatus possa essere pericoloso e quanto i nostri farmaci siano efficaci contro di esso. Costruendo la prima mappa completa degli RNA lunghi non codificanti in questo importante patogeno e collegando dozzine di essi a cambiamenti misurabili nella risposta ai farmaci, questo lavoro apre una nuova classe di marcatori genetici e potenziali bersagli. A lungo termine, gli lncRNA potrebbero aiutare a spiegare perché alcuni ceppi sono naturalmente più difficili da trattare, orientare la progettazione di diagnostici più efficaci e ispirare terapie che smontino la resistenza non uccidendo il fungo direttamente, ma silenziando i regolatori “silenziosi” che gli permettono di resistere.
Citazione: Weaver, D., Qi, T., Chown, H. et al. Genome-wide discovery and phenotyping of non-coding transcripts in A. fumigatus reveals lncRNAs with a role in antifungal drug sensitivity. Nat Commun 17, 1832 (2026). https://doi.org/10.1038/s41467-026-68543-9
Parole chiave: Aspergillus fumigatus, resistenza agli antifungini, RNA lungo non codificante, farmaci azolici, genomica fungina