Clear Sky Science · it
Predizione robusta e interpretabile di marker genici e tipi cellulari dai dati di trascrittomica spaziale
Trasformare i vetrini di routine in mappe molecolari
Quando viene eseguita una biopsia, i medici vedono di solito solo ciò che il microscopio rivela: le forme e i motivi delle cellule nelle colorazioni rosa e viola. Tuttavia sotto quei colori si nasconde un mondo di geni che si accendono e si spengono, influenzando come un tumore cresce e risponde al trattamento. Questo studio presenta STimage, un nuovo sistema di intelligenza artificiale (IA) che punta a leggere direttamente quel copione molecolare dalle immagini di patologia standard, offrendo potenzialmente informazioni più rapide ed economiche senza esami di laboratorio aggiuntivi.
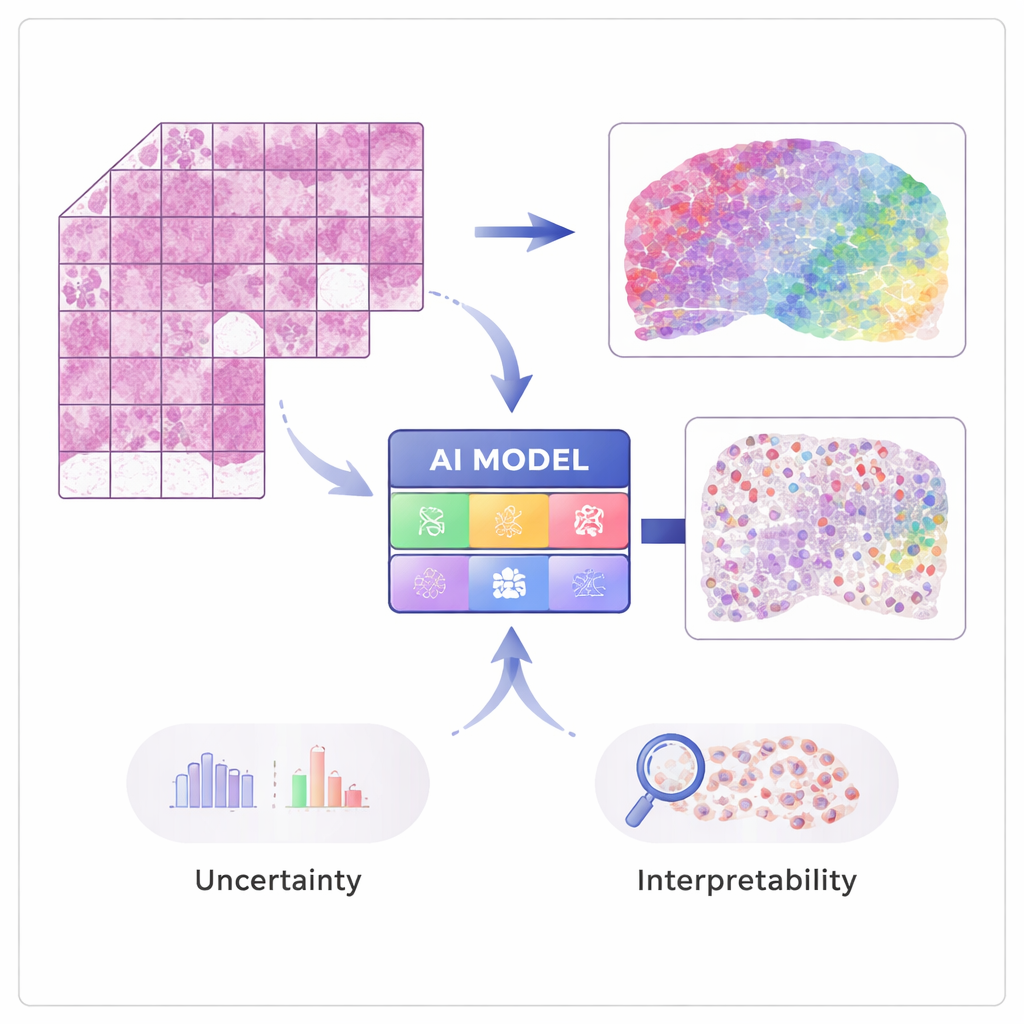
Dalle immagini all’attività genica
Le tecniche moderne di “trascrittomica spaziale” possono misurare l’attività di decine di migliaia di geni preservando la posizione di ciascun segnale nel tessuto. Questi metodi sono potenti ma costosi e non ancora di routine negli ospedali. STimage è addestrato su un numero modesto di tali dataset spaziali, in cui ogni immagine tissutale è accoppiata a misurazioni geniche dettagliate in molti microscopici punti. L’IA impara ad associare pattern visivi locali sul vetrino colorato con ematossilina ed eosina (H&E)—come la densità o l’irregolarità dei nuclei—all’attività genica sottostante, in modo che poi possa prevedere l’espressione genica e i tipi cellulari a partire dalle immagini ordinarie da sole.
Costruire un patologo IA più affidabile
Un obiettivo chiave del lavoro non è solo la precisione, ma l’affidabilità e l’esplicabilità. Piuttosto che restituire un singolo valore per ogni gene, STimage prevede una distribuzione di probabilità completa, descrivendo un intervallo plausibile di attività genica in ciascuna posizione. Separa inoltre due tipi di incertezza: una dovuta a dati rumorosi o variabili e un’altra che riflette la mancanza di conoscenza del modello. Addestrando molte versioni leggermente diverse del modello e mediandole—un approccio a “ensemble”—i ricercatori migliorano sia le prestazioni sia la capacità di capire dove il sistema è sicuro e dove non lo è, cosa cruciale per le decisioni cliniche.
Testare attraverso tumori, tecnologie e ospedali
Il team ha valutato STimage su dataset eterogenei provenienti da tumori della mammella, della pelle e del rene, oltre che da una patologia epatica a componente immunitaria. Ha imparato a prevedere marcatori importanti per il cancro e per la risposta immunitaria, spesso riproducendo i pattern spaziali reali osservati in esperimenti indipendenti. Il modello si è comportato bene anche quando è stato sfidato con dati di laboratori diversi, metodi di preparazione dei campioni e persino tecnologie sottostanti differenti, incluse piattaforme a risoluzione singola cellulare e sistemi più vecchi a risoluzione inferiore. In confronti diretti con diversi strumenti IA esistenti, STimage e le sue varianti ensemble sono generalmente risultati ai vertici, in particolare nel valutare quanto i pattern previsti corrispondessero alla reale distribuzione dell’attività genica nel tessuto.
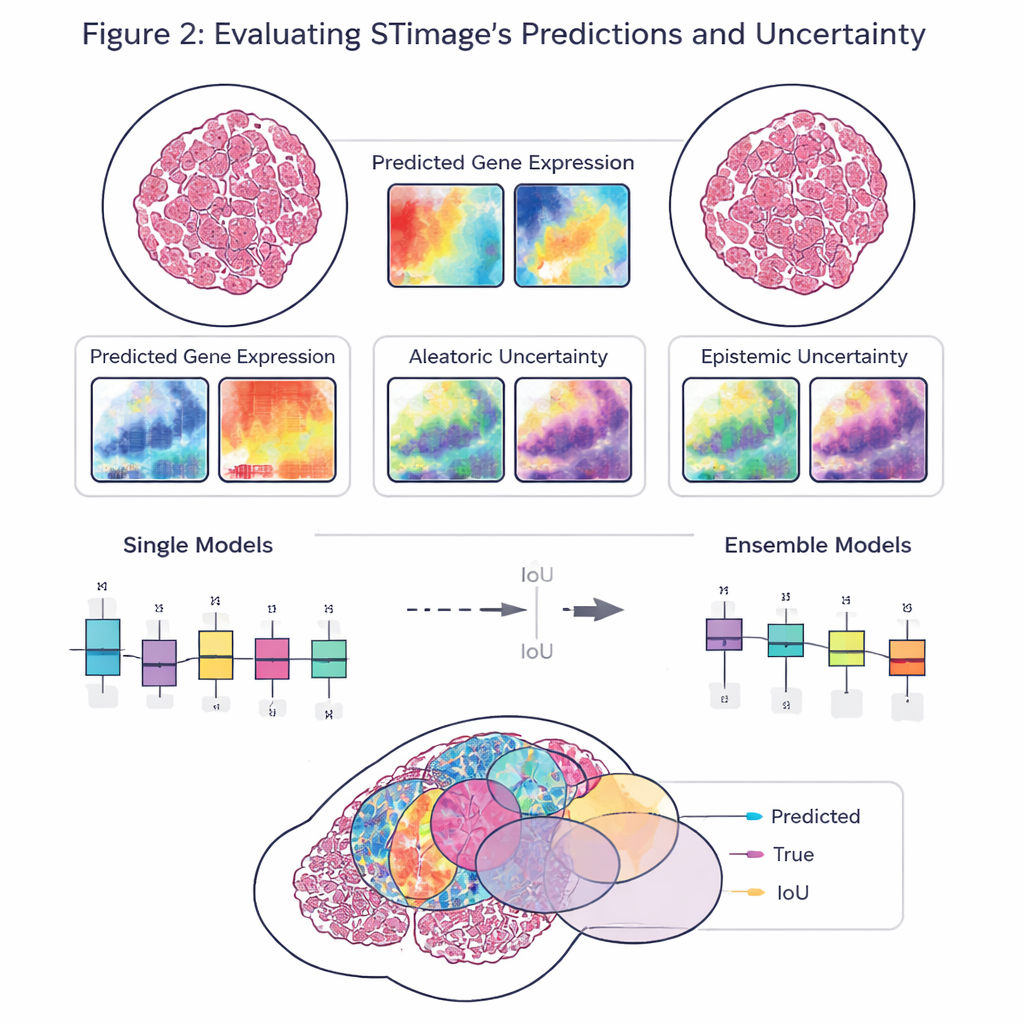
Osservare l’interno dei tumori: cellule, sopravvivenza e risposta ai farmaci
STimage va oltre la previsione genica per inferire quali tipi cellulari occupano ciascuna regione, usando dataset ad alta risoluzione dove l’identità di ogni cellula è nota. Il modello è stato in grado di distinguere cellule tumorali da cellule immunitarie e di supporto e di mappare la loro disposizione su un vetrino. Gli autori hanno poi applicato STimage a grandi raccolte di immagini tumorali di routine provenienti da The Cancer Genome Atlas. Anche senza misurazioni spaziali, i profili genici previsti dall’IA risultavano strettamente allineati con i veri dati di espressione bulk. Queste previsioni erano sufficientemente forti da raggruppare i pazienti in categorie a rischio più alto e più basso e da aiutare a distinguere quelli più propensi a rispondere completamente ad alcune terapie per il cancro al seno.
Perché questo conta per i pazienti del futuro
Per pazienti e clinici, la promessa di STimage è una sorta di “sovrapposizione molecolare” sul vetrino di patologia noto. Invece di ordinare molteplici test costosi, una singola immagine scannerizzata potrebbe un giorno rivelare dove sono attivi programmi genetici aggressivi, come sono distribuite le cellule immunitarie e quali marker indicano esiti migliori o peggiori o diverse risposte ai farmaci. Pur essendo il metodo ancora in fase di perfezionamento e la correlazione con misurazioni reali non perfetta, la sua capacità di catturare pattern spaziali, stimare la propria incertezza e mettere in evidenza quali cellule guidano le previsioni lo rende un passo pratico verso una patologia digitale più informativa e trasparente.
Citazione: Tan, X., Mulay, O., Xie, J. et al. Robust and interpretable prediction of gene markers and cell types from spatial transcriptomics data. Nat Commun 17, 1781 (2026). https://doi.org/10.1038/s41467-026-68487-0
Parole chiave: patologia digitale, trascrittomica spaziale, biomarcatori del cancro, apprendimento profondo, microambiente tumorale