Clear Sky Science · it
L’autoinibizione inter‑monomero di HEXIM1 regola la specificità di legame dell’RNA 7SK e l’inattivazione di P‑TEFb
Perché questo piccolo RNA conta nel controllo genico
Ogni cellula deve decidere quando attivare o spegnere i geni, e lo fa controllando con attenzione un enzima che guida la produzione di RNA. Questo articolo rivela come una piccola proteina chiamata HEXIM1, che lavora insieme a un RNA non codificante denominato 7SK, funzioni come un blocco di sicurezza su quell’enzima. Capire questo sistema molecolare di sicurezza aiuta a spiegare come le nostre cellule prevengano un’attività genica incontrollata e illumina anche i modi in cui virus come l’HIV dirottano la stessa macchina.
Un freno molecolare sull’espressione genica
Nelle cellule umane, un passaggio chiave dell’espressione genica è controllato da un fattore chiamato P‑TEFb, che aiuta l’RNA polimerasi II a passare da uno stato di pausa alla trascrizione a piena velocità. Le proteine HEXIM, in particolare HEXIM1, sono centrali per mantenere P‑TEFb sotto controllo. Lo fanno all’interno di un grande complesso chiamato 7SK RNP, organizzato attorno all’RNA 7SK. Quando HEXIM1 e 7SK collaborano, bloccano P‑TEFb impedendogli di promuovere la trascrizione. Fino ad oggi, il pezzo mancante era come HEXIM1 eviti di legarsi a P‑TEFb troppo presto e come l’RNA 7SK attivi HEXIM1, trasformandolo da inattivo a inibitore al momento giusto.
Una proteina che si abbraccia da sola e viene trattenuta
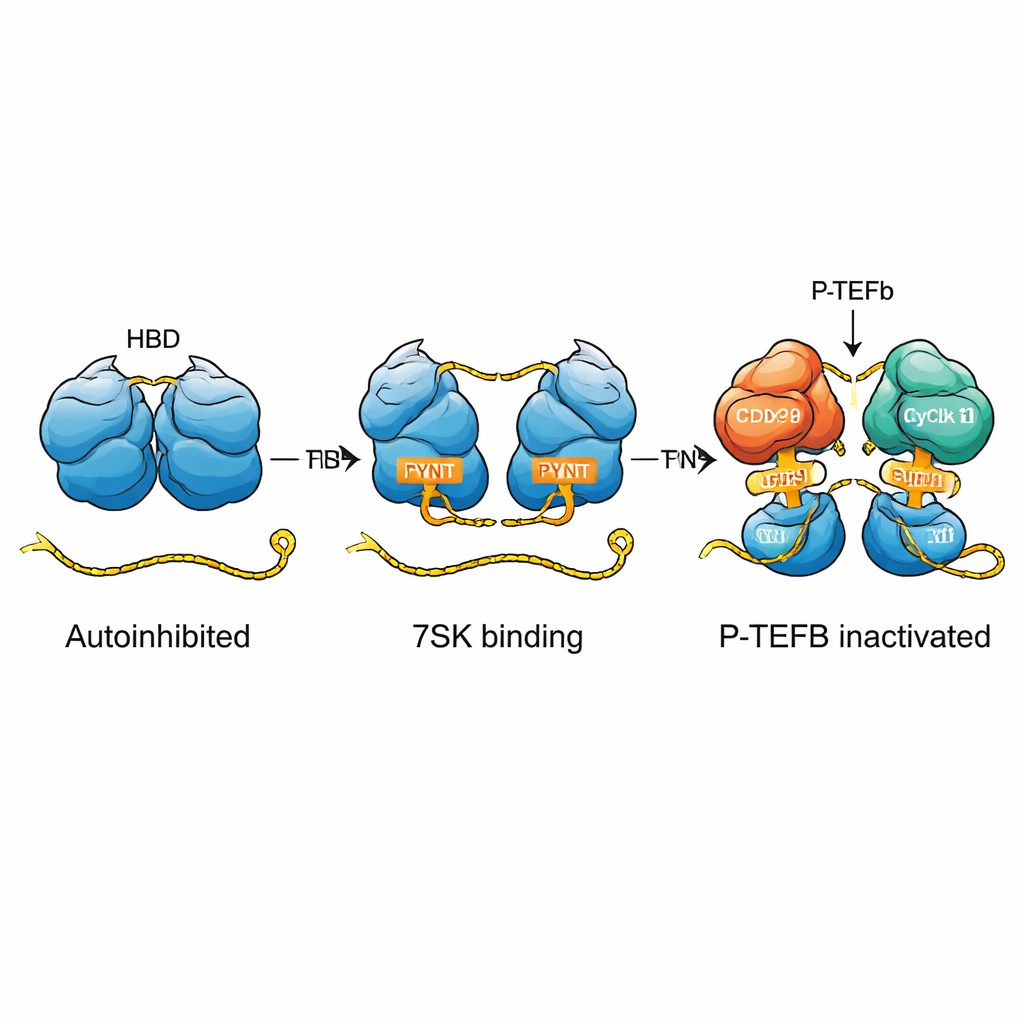
Gli autori mostrano che HEXIM1 forma naturalmente un dimero — due catene proteiche identiche associati — e che le parti centrali flessibili di ciascuna catena si avvolgono l’una attorno all’altra in una disposizione a “auto‑abbraccio”. In questo stato, un segmento breve cruciale chiamato motivo PYNT, che normalmente si lega e spegne la chinasi P‑TEFb, è nascosto all’interfaccia tra le due catene. Utilizzando tecniche NMR sensibili e metodi biofisici, il gruppo ha mappato come regioni basiche (cariche positivamente) e acide (cariche negativamente) dei due monomeri interagiscono per creare questo dimero autoinibito. Questa costrizione intrinseca impedisce a HEXIM1 di aggrapparsi casualmente a P‑TEFb quando l’RNA 7SK non è presente.
Come l’RNA 7SK sblocca HEXIM1
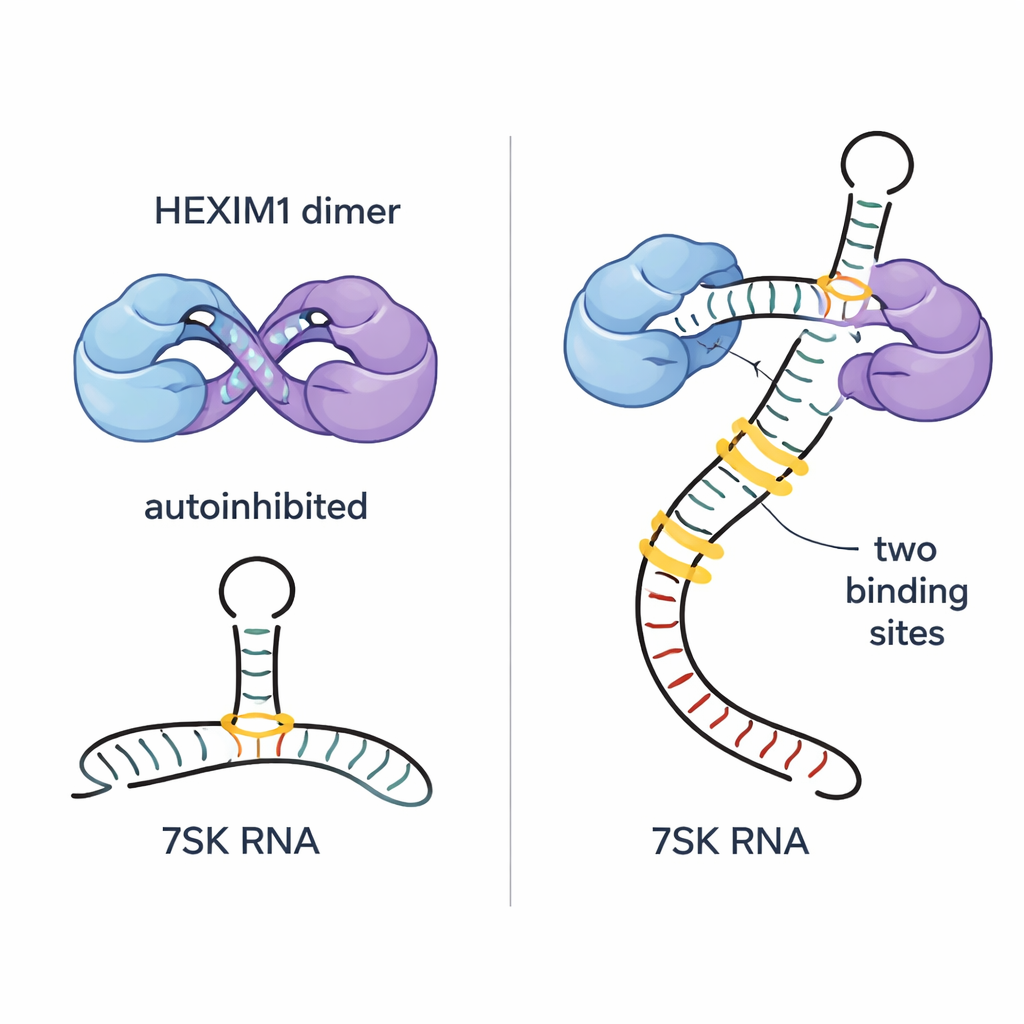
L’RNA 7SK contiene diverse caratteristiche strutturali, inclusa una lunga regione a stelo‑anello chiamata SL1. Dissecando questo RNA in frammenti più piccoli e tracciando sottili cambiamenti nei segnali NMR, i ricercatori hanno individuato cinque possibili siti di legame di HEXIM1 lungo SL1. Due di questi siti risaltano come punti di ancoraggio ad alta affinità; entrambi condividono una sezione ad elica doppia ricca di A–U e una proliferazione vicino ricca di U che può formare interazioni speciali a tre basi. Il gruppo ha scoperto che ciascuna metà del dimero HEXIM1 si lega a uno di questi due siti forti sull’RNA 7SK lineare. Quando entrambi i siti sono occupati, la regione centrale di HEXIM1 si riorganizza, rompendo i contatti dell’auto‑abbraccio ed esponendo i motivi PYNT nascosti, predisponendo così la proteina a catturare P‑TEFb.
Scegliere la forma RNA corretta—e evitare quelle sbagliate
L’RNA 7SK non esiste in un’unica conformazione; può alternarsi tra una forma lineare, che presenta entrambi i siti ad alta affinità, e una forma più circolare con un solo sito adatto. Gli autori mostrano che l’autoinibizione di HEXIM1 lo rende sorprendentemente selettivo: il dimero si lega debolmente a siti singoli isolati, ma molto più strettamente e in modo cooperativo al segmento SL1 lineare completo che offre entrambi i siti forti. Questa necessità di due siti impedisce a HEXIM1 di restare bloccato su RNA casuali presenti nella cellula e rende il suo legame altamente specifico per la conformazione lineare di 7SK che assemblea il complesso repressivo attivo. Dimostrano inoltre che l’aggiunta di cariche negative extra vicino alla regione di legame dell’RNA (imitando la fosforilazione su una serina chiave) indebolisce il legame con l’RNA senza distruggere completamente l’autoinibizione, offrendo un modo potenziale con cui le cellule possono rilasciare P‑TEFb quando necessario.
Da interruttore molecolare all’impatto cellulare
Nel complesso, lo studio rivela HEXIM1 come un interruttore molecolare finemente sintonizzato. Nel suo stato di riposo, a “auto‑abbraccio”, mantiene nascosti i segmenti PYNT che bloccano P‑TEFb. Solo quando incontra l’RNA 7SK lineare con due siti di legame disposti correttamente la proteina scatta in uno stato “on”, esponendo questi segmenti per catturare e inattivare P‑TEFb — spesso due copie contemporaneamente. Questo meccanismo spiega come le cellule usino un piccolo RNA e una proteina flessibile per imporre un controllo preciso sulla trascrizione e fornisce un quadro più chiaro per comprendere come segnali cellulari, modificazioni chimiche o proteine virali come l’HIV Tat possano spostare l’equilibrio tra espressione genica in pausa e attiva.
Citazione: Yang, Y., Murrali, M.G., Galvan, S. et al. HEXIM1 inter-monomer autoinhibition governs 7SK RNA binding specificity and P-TEFb inactivation. Nat Commun 17, 1570 (2026). https://doi.org/10.1038/s41467-026-68285-8
Parole chiave: regolazione della trascrizione, RNA 7SK, HEXIM1, P‑TEFb, HIV Tat