Clear Sky Science · it
Categorizzazione di 34 metodi computazionali per rilevare geni spazialmente variabili dai dati di trascrittomica spazialmente risolta
Perché la posizione è importante per i nostri geni
I nostri corpi sono costruiti da cellule che non solo differiscono per ciò che fanno, ma anche per il luogo in cui si trovano nei tessuti e negli organi. Le nuove tecnologie di "trascrittomica spaziale" possono ora leggere quali geni sono attivi mantenendo traccia dell’indirizzo di ciascuna cellula su una mappa tissutale. Questo articolo di revisione spiega come gli scienziati individuano i geni la cui attività cambia da un luogo all’altro — i cosiddetti geni spazialmente variabili — e perché concordare sul modo di individuarli è fondamentale per comprendere il cancro, il funzionamento del cervello e molte altre malattie.
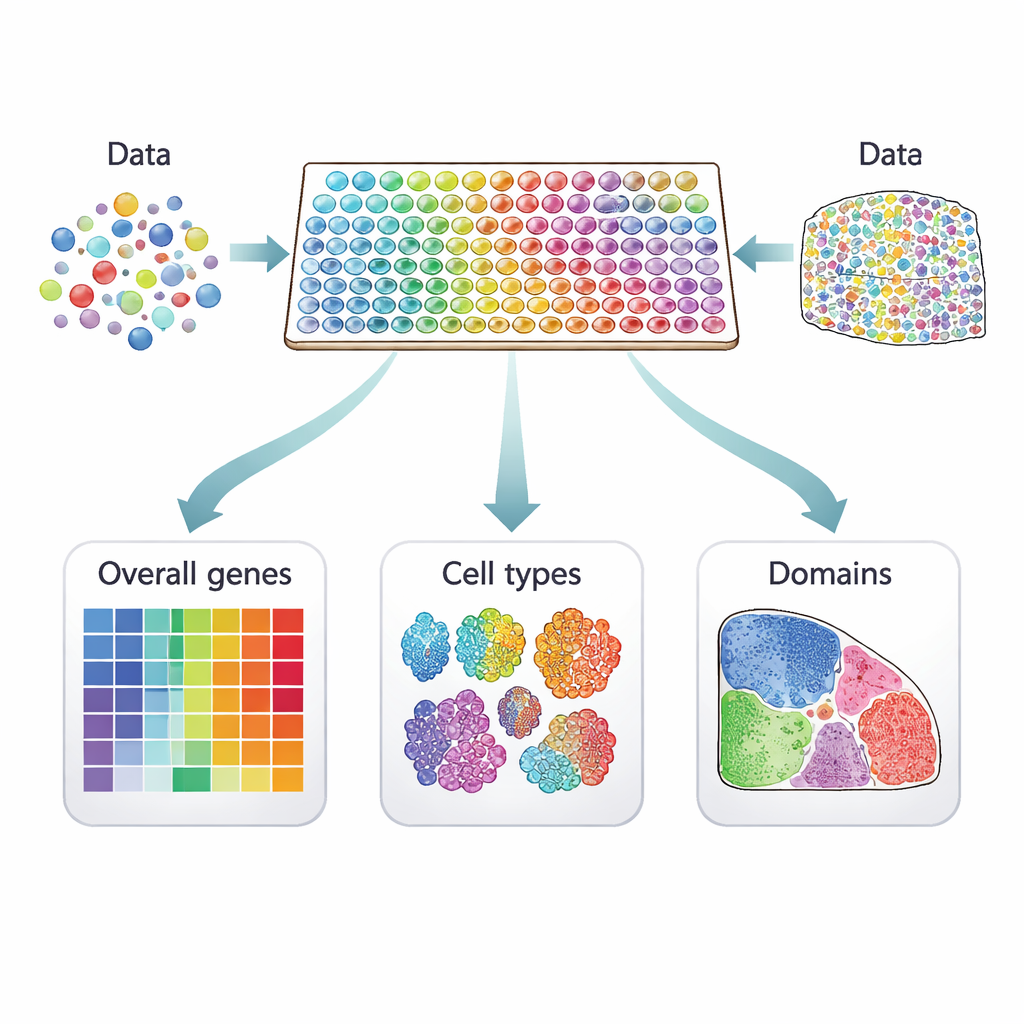
Dalle cellule sparse alle mappe vive
Gli studi tradizionali a singola cellula misurano l’attività genica in migliaia di singole cellule ma perdono l’informazione su dove quelle cellule provengano. La trascrittomica spaziale colma questa lacuna misurando l’attività genica direttamente su sezioni sottili di tessuto. Ogni misura è collegata a una "posizione" sulla sezione, che può contenere una singola cellula o più cellule, a seconda della tecnologia. I metodi basati sull’imaging individuano alcune centinaia di geni selezionati con dettaglio spaziale molto elevato, mentre le piattaforme basate sul sequenziamento catturano quasi tutti i geni a una risoluzione inferiore. Insieme, questi approcci trasformano una sezione di tessuto in una mappa colorata di attività genica che può rivelare strutture nascoste, come i livelli nel cervello o le regioni all’interno di un tumore.
Tre tipi di geni sensibili alla posizione
Sono stati proposti molti metodi computazionali per identificare i geni che mostrano schemi significativi su queste mappe tissutali, ma non tutti cercano la stessa cosa. Gli autori classificano 34 metodi attuali in tre categorie distinte. Il primo gruppo cerca geni spazialmente variabili "globali", la cui attività cambia nel tessuto in qualsiasi modo non casuale — per esempio formando strisce, ammassi o gradienti. Il secondo gruppo si concentra sui geni spaziali "specifici per tipo di cellula" che variano all’interno di un singolo tipo cellulare, aiutando a distinguere, ad esempio, sottotipi di neuroni o diversi stati delle cellule immunitarie. Il terzo gruppo cerca geni "marcatori di dominio" che sono fortemente attivati in particolari regioni o strati, rendendoli utili etichette per quelle zone tissutali.
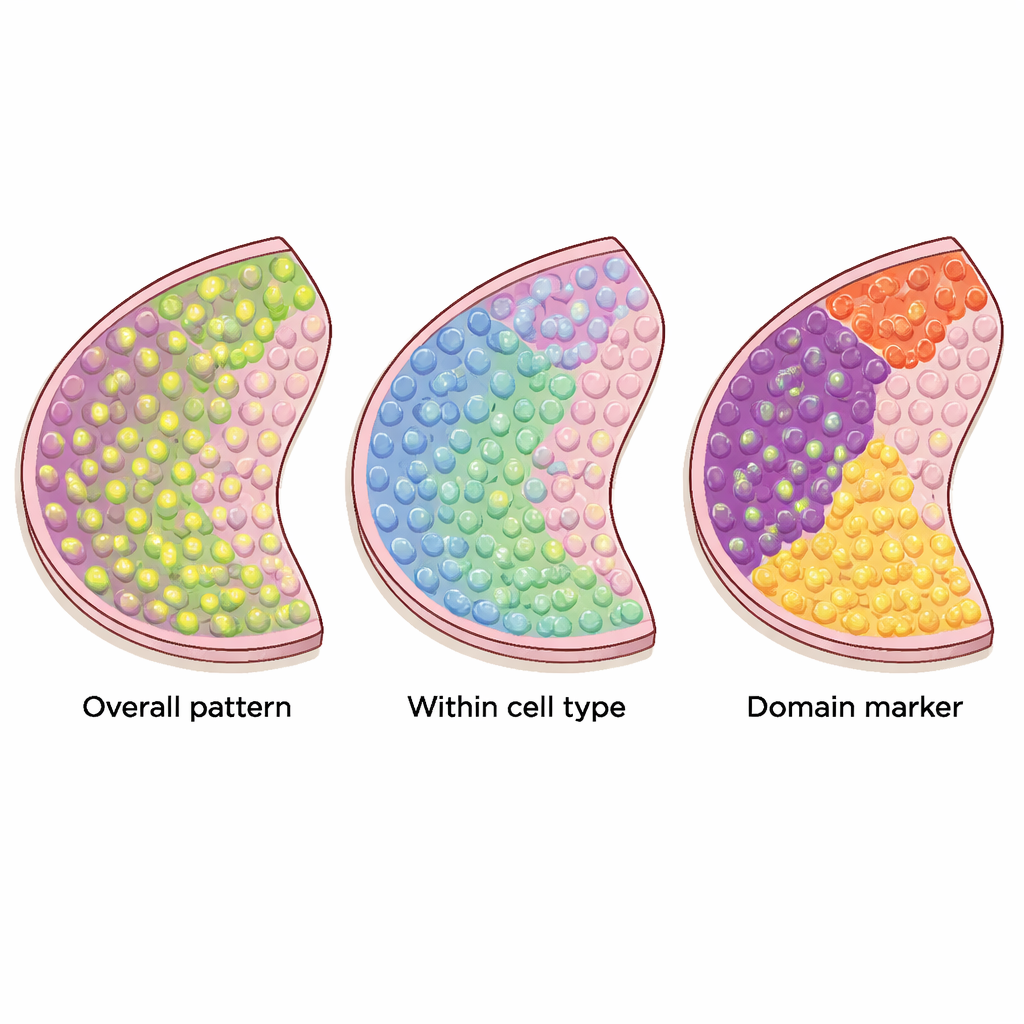
Strumenti diversi per schemi diversi
La revisione spiega come questi metodi funzionano sotto il cofano. Alcuni trattano la sezione di tessuto come punti in uno spazio bidimensionale regolare e usano "kernel" matematici per cercare schemi come macchie o onde. Altri collegano prima le posizioni vicine in una rete, o grafo, e poi verificano se l’alta espressione tende ad aggrapparsi lungo i collegamenti di quel grafo. Certi strumenti si basano su test statistici formali con tassi di errore ben definiti, mentre altri si limitano principalmente a classificare i geni in base a quanto spiccano i loro schemi. I metodi che mirano a schemi molto specifici possono essere potenti quando i dati corrispondono alle loro aspettative, ma possono perdere forme più irregolari o complesse, come quelle osservate in molti tumori. Esiste anche un compromesso tra flessibilità e velocità: alcuni approcci scalano a centinaia di migliaia di posizioni, mentre altri faticano con dataset molto grandi.
Cosa possono rivelare questi geni
Una volta identificati, i geni spazialmente variabili diventano materia prima per scoperte biologiche più profonde. I geni spaziali globali vengono spesso usati come primo filtro per ridurre il numero di geni prima di raggruppare le posizioni in "domini spaziali" — regioni le cui cellule condividono profili di espressione simili. Questi domini possono corrispondere a strutture tissutali note, suggerire nuove sotto-regioni o evidenziare quartieri cellulari distinti come i fronti invasivi nei tumori. I geni marcatore di dominio poi aiutano a spiegare cosa rende unica ciascuna regione e possono essere riutilizzati per etichettare strutture simili in altri campioni. Nel frattempo, i geni spaziali specifici per tipo cellulare promettono una visione più fine di come tipi cellulari particolari cambino attraverso un tessuto, cosa che può chiarire le interazioni tumore–immunità o circuiti specializzati nel cervello.
Sfide e prospettive
Gli autori sottolineano che non esiste un metodo unico migliore per ogni compito, e che confrontare gli strumenti in modo equo richiede una riflessione attenta su che tipo di geni spaziali ciascun metodo è effettivamente progettato per trovare. Chiedono migliori benchmark che utilizzino dataset realistici, standard statistici più chiari per evitare scoperte false e nuovi approcci che rispettino le differenze tra tecnologie e tipi di tessuto. Per i non esperti, il messaggio chiave è che i geni spazialmente variabili trasformano liste piatte di geni in mappe vive, collegando l’attività molecolare alla struttura tissutale. Modi robusti per rilevare e interpretare questi geni saranno centrali per trasformare la trascrittomica spaziale in intuizioni pratiche sullo sviluppo, il funzionamento del cervello e le malattie.
Citazione: Yan, G., Hua, S.H. & Li, J.J. Categorization of 34 computational methods to detect spatially variable genes from spatially resolved transcriptomics data. Nat Commun 16, 1141 (2025). https://doi.org/10.1038/s41467-025-56080-w
Parole chiave: trascrittomica spaziale, geni spazialmente variabili, schemi di espressione genica, microambienti tissutali, genomica computazionale