Clear Sky Science · he
הערכה איכותית של דגמי מבנה תלת־ממדי של RNA באמצעות למידה עמוקה ומפות 2D ביניים
מדוע חשוב לשפוט את צורות ה‑RNA
בתוך כל תא, מולקולות RNA מתעקלות ומתכופפות לצורות תלת־ממדיות מורכבות שעוזרות לשלוט אילו גנים מופעלים, מנחות תגובות כימיות ואפילו מגן מפני וירוסים. כיום תוכניות מחשב חזקות יכולות לנחש רבות מהצורות האלה, אך המדענים עדיין נתקלים בבעיה בסיסית: כשהמחשב מייצר עשרות או מאות צורות מועמדות לאותו RNA, איזו מהן קרובה באמת למציאות? מאמר זה מציג את RNArank, כלי בינה מלאכותית שנועד להתמודד עם השאלה על ידי דירוג דגמי 3D של RNA, בדומה למفتח איכות מבנית, כך שהחוקרים יוכלו להתמקד בתחזיות האמינות ביותר.
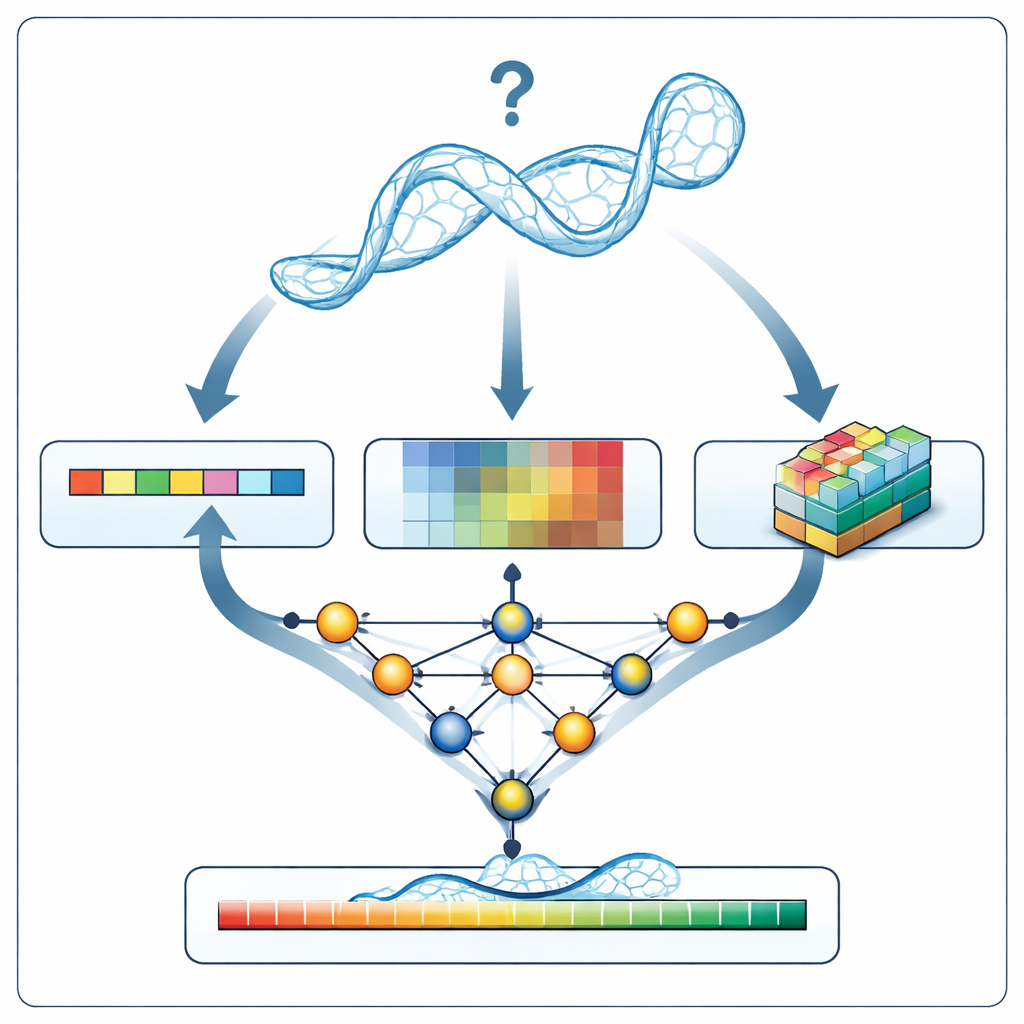
מפקח חדש לדגמי RNA
RNArank נבנה כדי לשפוט את איכות צורת ה‑RNA המוצעת מבלי להזדקק לידיעה כיצד נוצרה הצורה הזו. אם המודל נוצר על ידי מערכת למידה עמוקה, סימולציה מבוססת פיזיקה או מומחה אנושי, RNArank בוחן רק את הקואורדינטות התלת־ממדיות הסופיות. הוא למעשה שואל: "האם המבנה הזה נראה כמו RNA מציאותי?" הערכה בלתי תלויה מסוג זה חיונית מכיוון שלמרות שבעולם החלבונים כלים כמו AlphaFold מספקים לעתים תשובות מהימנות מאוד מבלי הרבה כוונון, עבור RNA הצפייה המדינה נשענת על שילוב שיטות ומומחיות אנושית — ובנוסף על דרך חכמה לדרג את המודלים המתקבלים.
לימוד ה‑AI איך נראה RNA טוב
כדי לאמן את RNArank, המחברים אספו כשני מאה אלף מבני RNA, המכסים ספקטרום רחב מטעויות ברורות ועד מושלמים כמעט. אלו נבנו מתוך מבנים ניסויית ידועים באמצעות מגוון רחב של שיטות, כולל מנבאים מודרניים בלמידה עמוקה, סימולציות דינמיקת מולקולות שמחקות תנועה אטומית ועיויות מכוונות של מבנים מדויקים ליצירת "דקויים". עבור כל מודל, הצוות חישב עד כמה הוא תואם ל‑RNA שנקבע ניסויתית, באמצעות ציון דיוק מעודן המותאם ל‑RNA הנקרא lDDT_RNA. ציון זה מתמקד עד כמה מרחקים בין זוגות נוקלאוטידים משוחזרים, ותופס הן את הקיפול הכללי והן פרטים מקומיים מבלי להיות רגיש מדי לאורך המולקולה.
כיצד RNArank קורא ומדרג RNA
כש‑RNArank בוחן מודל RNA חדש, הוא קודם כל מתרגם את המבנה לשלושה סוגי מידע: תיאור 1D של הרצף והגאומטריה של השלד לאורך השרשרת, תיאורים 2D של האופן שבו כל זוג נוקלאוטידים מתקשר זה עם זה (מרחקיהם, אנרגיות אינטראקציה משוערות והתנגשויות אטומיות אפשריות), ו״ווקסלים״ תלת־ממדיים — רשתות קטנות הלוכדות את ענן האטומים המקומי סביב כל נוקלאוטיד. רשת עצבית מרובת חלקים מארגת רמזים אלו לתמונה מאוחדת ואז חוזה שתי מפות 2D בינוניות: אילו נוקלאוטידים צפויים להיות במגע, ועד כמה כל מרחק במודל צפוי לסטות מהמבנה האמיתי הלא ידוע. מהמפות האלו, RNArank משחזר גם ציון ביטחון לכל נוקלאוטיד וגם ציון כולל לדגם ה‑RNA כולו.
הצבת השיטה במבחן
הצוות בחן את RNArank על שלושה מאגרי נתונים תובעניים: סט של 24 RNAs שנפתרו לאחרונה מבנק מבני החלבון (PDB), ומטרות ה‑RNA משתי תחרויות חיזוי עיוורות בינלאומיות, CASP15 ו‑CASP16, שבהן קבוצות רבות הגישו מודלים מבלי לדעת את התשובות מראש. על פני אלפי מבנים מועמדים, ציוני RNArank עקבו אחרי איכות המודל האמיתית קרוב יותר ממספר שיטות דירוג מבוססות אנרגיה ומגישות למידה עמוקה אחרות. הוא היה חזק במיוחד בזיהוי המודלים הטובים או הקרובים לטובים מתוך המאגורה, ובזיהוי אילו חלקים במבנה סבירים פחות. המחברים הראו גם כי RNArank שמר על ביצועיו אפילו על RNAs שהיו שונים בבירור ברצף מאלה שראה במהלך האימון — עדות להכללה אמיתית ולא לזכירה למדנית.
מגבלות היום והבטחות למחר
RNArank אינו מושלם: הוא עדיין נאבק מול RNAs גמישים במיוחד המקבלים צורות רבות, וכמו מול RNAs שמשנים את צורתם כשהם כבושים על ידי חלבונים בתוך מכונות מולקולריות גדולות. עם זאת, הוא מהיר מספיק כדי לטפל בעשרות או מאות מודלים עבור RNAs של כמה מאות נוקלאוטידים בתוך שניות בלבד, וכבר עוזר לשרתי אוטומציה לבחור תחזיות איכותיות יותר במבחני קהילה. על ידי מתן שופט בלתי תלוי התלוי רק במבנה, RNArank מספק לביולוגים מסננת חדה יותר להפוך פלט מחשב גולמי להשערות מבניות מהימנות, ומקרב את התחום צעד נוסף לעבר חיזוי שגרתי ואמין של צורות RNA ולתובנות עמוקות יותר על אופן פעולתם של מולקולות רב־תכלית אלה.
ציטוט: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
מילות מפתח: מבנה תלת־ממדי של RNA, למידה עמוקה, הערכת איכות מודל, ביואינפורמטיקה מבנית, RNArank