Clear Sky Science · he
עיצוב מונחה-נתונים של חוסמי LNA להסרת זיהומים ביעילות בספריות Ribo-Seq
מדוע ניקוי נתוני ריצוף חשוב
ביולוגיה מודרנית מסתמכת לעתים קרובות על קריאת מיליוני רסיסי RNA זעירים כדי להבין כיצד תאים מייצרים חלבונים. אך מדידות עוצמתיות אלה, ובפרט שיטה הנקראת ribosome profiling (Ribo‑Seq), עלולות להיות מוצפות בחתיכות RNA בלתי רלוונטיות שמבזבזות כוח ריצוף וכסף. המאמר מתאר שיטה פשוטה ומונחת-נתונים לעיצוב "חוסמים" מולקולריים מתמחים שמסירים באופן סלקטיבי את הרסיסים הלא רצויים האלה, וכך כמעט מכפילים את כמות המידע השימושי שמחושב מהניסוי הקיים.
בעיה של תמונת ריבוזומים רעשנית
Ribo‑Seq לוכד תמונה רגעית של אילו מסרים בתא מתורגמים באופן פעיל לחלבונים. לשם כך מדענים מבודדים ריבוזומים יחד עם מקטעי ה-mRNA הקצרים שהם מגינים עליהם. כל השאר מופרק, והמקטעים המוגנים עוברים ריצוף ומיפוי חזרה לגנום. בפועל, עם זאת, רבים מקטעי ה-RNA הקטנים הלא מקודדים מצליחים לעבור את התהליך. מאחר שהרסיסים המזוהמים האלה שכיחים ומשתנים מאוד, הם בולעים חלק גדול מתוך קריאות הריצוף, ומשאירים פחות קריאות לאותות המקודדים לחלבון שהתעניינות החוקרים בהם.
מדוע הטריקים הקיימים לניקוי לא מספיקים
אסטרטגיות סטנדרטיות מנסות להסיר RNA ריבוזומלי ושאר RNA לא מקודדים בשימוש בשרשראות לכידה מתוכננות מראש או באנזימים. שיטות אלה עובדות היטב כשה-RNA היעד שלם וניתן לחיזוי, אך Ribo‑Seq בחירה לחתוך את ה-RNA למגוון מקטעים בגדלים שונים. השיבוש הזה של החתיכה עושה את אזורי המטרה בלתי צפויים עבור ערכות פרובים קבועות, ומקטין את יעילות ההפחתה. בנוסף, התערובת המדויקת של מזהמים תלויה במין הנחקר, בתנאי הגידול ואפילו בסוג הנוקלאז שבו משתמשים. גם זרימות עבודה לניקוי קיימות נוטות לכלול מספר צעדי דגירה וטיהור, שהם גוזלים זמן ועלולים לגרום לאובדן דגימה או להטיה.
חוסמים מותאמים המעוצבים מתוך נתונים אמיתיים
המחברים מציעים גישה מזורזת שמתחילה בריצת ניסוי קטנה ובזולה תחת אותם תנאים שתתבצע בהם הניסוי המלא. הם מספקים סקריפט ב-R שלוקח את הקריאות הממומפות מריצת הפיילוט ומקבץ אוטומטית רסיסי מזהמים דומים על בסיס הרצף. עבור כל קבוצה, הסקריפט מדווח על הרצף המשותף הקצר הקצר ביותר שמופיע בקרב המקטעים. מקטעים קצרים ומשותפים אלה מהווים אתרי מטרה אידיאליים למולקולות מתמחות הנקראות אוליגונוקלאוטידים של locked nucleic acid (LNA). LNAs הם רצועות קצרות עם שינוי כימי שמקנה להן קשירה חזקה מאוד ל-RNA תואם. הסקריפט מייצר גם מפות חום וגרפי סיכום אינטואיטיביים, המסייעים למשתמשים לראות אילו מזהמים דומיננטיים וכמה מטרות LNA יהיו נדרשות לניקוי משמעותי.
ניקוי חד-שלבי במהלך ההגברה
במקום להוציא פיזית את המזהמים מן הדגימה, השיטה משתמשת באוליגונוקלאוטידים LNA כחוסמים במהלך שלב ההגברה של ה-DNA שבונה את ספריית הריצוף. המחברים בחנו הוספת חוסמים אלה либо במהלך השלב הראשוני של הטרנסקריפציה לאחור (reverse transcription) או במהלך ההגברה על ידי PCR בשלב מאוחר יותר. הם מצאו שהוספת LNAs במהלך ההגברה הייתה יעילה יותר ודרשה ריכוזים נמוכים יותר, הפחיתה מזהם ניסיוני ביותר מאלף-פעמיים ופעלה ללא תלות בכיוון גדיל ה-RNA. טיפים פרקטיים לעיצוב כוללים חילוף בין אבני בניין של DNA סטנדרטי ו-LNA, שימוש באורך מינימלי של 14 יחידות עבור הצמח Arabidopsis, ושינוי קצה הזנב כך שהחוסם עצמו לא יוכל להוארך בטעות.
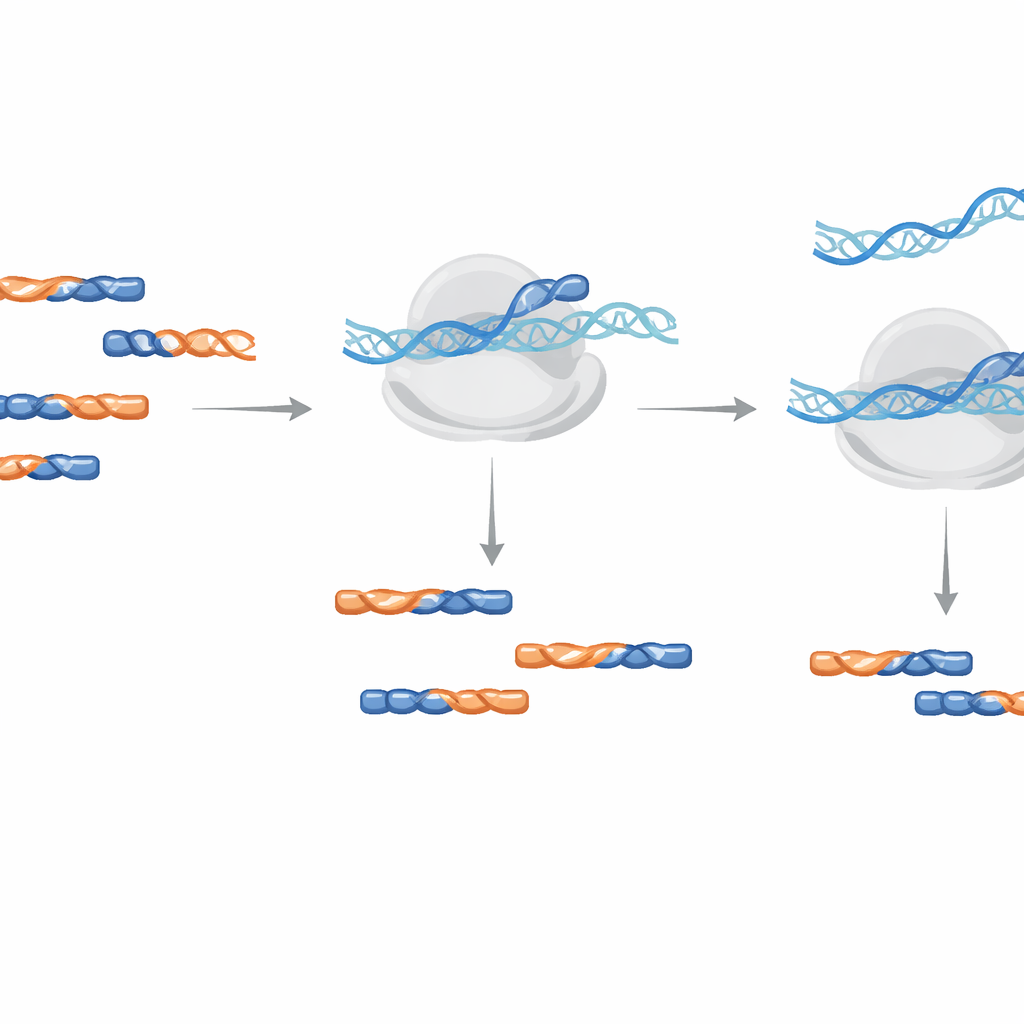
יותר קריאות שימושיות בלי עיוות האות
כדי להדגים ביצועים בעולם האמיתי, הצוות תכנן חמישה חוסמי LNA שפונים לקבוצות המזהמים הנפוצות ביותר שנצפו בתנאי גידול טיפוסיים בצמחי Arabidopsis. כשערבבו תערובת זו במהלך הגברת הספרייה, שיעור המזהים המזוהים ירד ביותר מ-30%, ומספר הקריאות השימושיות המקודדות לחלבון כמעט הכפיל את עצמו. באופן מכריע, כאשר השוו ספירות קריאות ברמת הגן בין ספריות עם ובלי טיפול ב-LNA, הערכים תאם כמעט במדויק, מה שמצביע על כך שהחוסמים הסירו רסיסים מיותרים מבלי לעוות את האות הביולוגי של טביעות הרגל של mRNA אמיתיות.
משמעות הדבר לניסויים עתידיים
עבודה זו מראה שניסוי פיילוט קצר, יחד עם סקריפט ניתוח ידידותי למשתמש וקבוצת חוסמי LNA מותאמת קטנה, יכולים להפוך ספריות Ribo‑Seq מוצפות לסדרות נתונים נקיות ומידעיות הרבה יותר בצעד פיפטינג יחיד. חוקרים מקבלים יותר קריאות בעלות משמעות לכל ריצה, חוסכים בעלויות ומפשטים את תכנון הניסויים, תוך שמירה על מדידות מדויקות של תרגום גנים. המחברים גם מספקים פרופילי מזהמים מעוצבים מראש ותכניות חוסם לתנאי צמיחה שכיחים בצמחים, ומציעים שמשאבים דומים יכולים להיבנות עבור אורגניזמים רבים, מה שיוביל להנגשה של פרופילינג ריבוזומים באיכות גבוהה ברחבי קהילת המחקר.
ציטוט: Ricciardi, D.A., Peter, F.E. & Böhmer, M. Data-driven design of LNA-blockers for efficient contaminant removal in Ribo-Seq libraries. Sci Rep 16, 8565 (2026). https://doi.org/10.1038/s41598-026-43117-3
מילות מפתח: פרופילינג של הריבוזום, מזהמי RNA, נוקלאוטידים ננעלים, ניקוי ספריות לריצוף, ויסות תרגום