Clear Sky Science · he
CiCLoDS: אשכול תאים משותף ובחירת גנים לטרנסקריפטומיקה מרחבית בתא יחיד
מציאת שכונות בעיר התאים
מיקרוסקופים מודרניים יכולים כיום לקרוא אילו גנים פעילים במאות אלפי תאים תוך שמירה על מיקומם המקורי בתוך הרקמה. מהפכת "הטרנסקריפטומיקה המרחבית" הזו דומה להפיכת מפה עירונית מטושטשת לתצוגת רחוב של כל בית. אך יש בעיה: מפות אלה כוללות מדידות לאלפי גנים לכל תא — הרבה יותר ממה שמדענים יכולים לפרש בקלות או להרשות לעצמם למדוד בניסויים המשך. המחקר הזה מציג את CiCLoDS, שיטה חדשה שמוצאת שכונות תאים משמעותיות ובמקביל בוחרת רשימה קטנה וברורה של גנים שמגדירים את אותן שכונות.
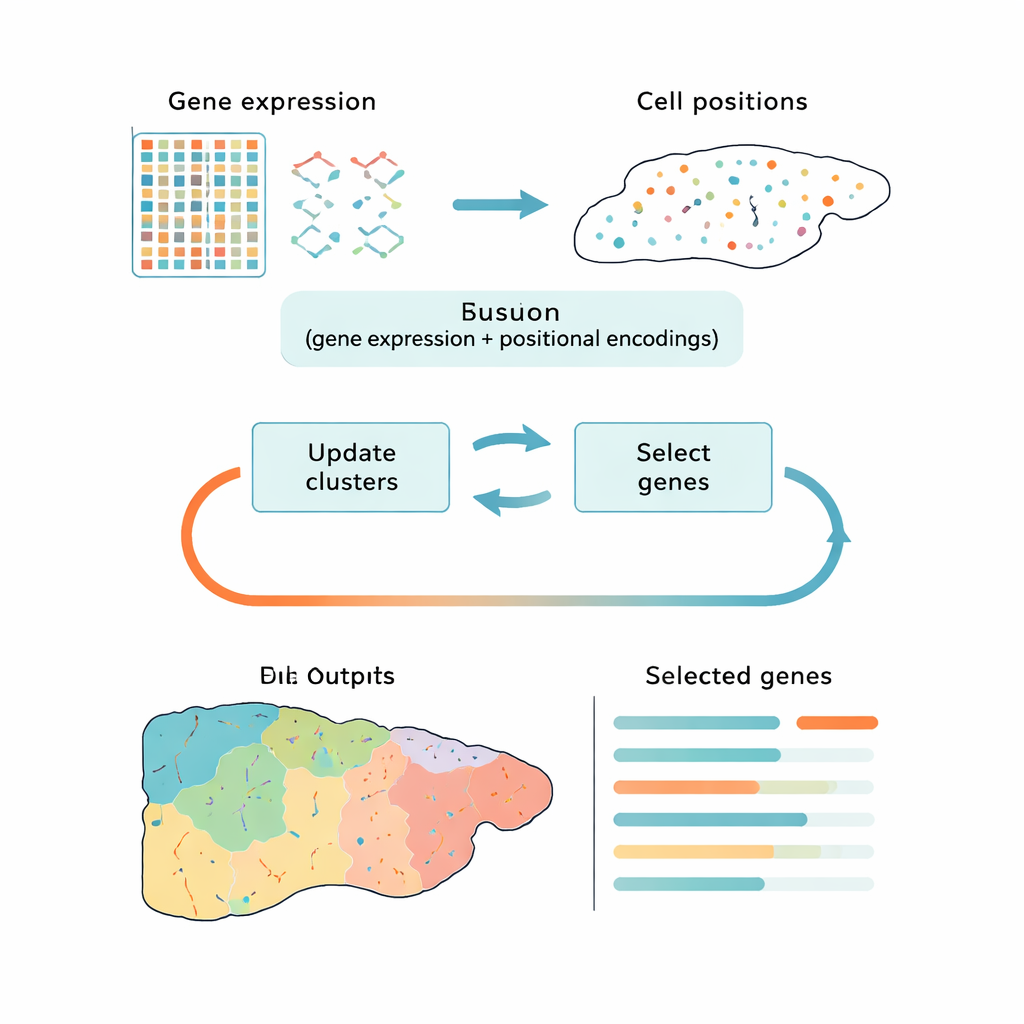
דרך חכמה לצמצם נתונים גדולים
ברוב הכלים הנוכחיים מטפלים באתגר הזה בשתי שלבים מנותקים: קודם מצמצמים את הנתונים לצורה פשוטה יותר, ואז מקבצים את התאים. גישות פופולריות כמו ניתוח רכיבים עיקריים (PCA) שומרות על שונות כללית אך עלולות להתמקד ברעש טכני או באותות כלליים של מחזור התא במקום בהבדלים ביולוגיים מהותיים. שיטות אחרות משתמשות בלמידה עמוקה כדי למצוא דפוסים, אך הן פועלות כשחורות-תיבה ואינן מבהירות אילו גנים חשובים ביותר. CiCLoDS נוקטת בגישה שונה: היא מתייחסת לבחירת גנים ולאשכולות כבעיה משותפת תחת "תקציב" שמוגדר על ידי המשתמש לגבי כמה גנים ניתן לשמר. בפועל היא שואלת: איזו קבוצה מוגבלת של גנים מסבירה הכי טוב איך התאים מתחלקים לקבוצות נבדלות, בהתחשב הן בפעילות הגנים והן, כאשר זמינים, במיקומם הפיזי ברקמה?
ממתמטיקה למפות של רקמות אמיתיות
המחברים מתאימים משפחה של טכניקות שקופות מתמטית הנקראות אשכולות תת-מרחב (subspace clustering) למציאות של טרנסקריפטומיקה מרחבית, שבה מערכי נתונים יכולים להכיל מעל מיליון תאים. CiCLoDS פועלת על טבלת תא-לפי-גן פשוטה, שמקצה תאים לאשכולות תוך דירוג כל גן לפי תרומתו להפרדת האשכולות. היא גם יכולה לשלב מידע מרחבי על ידי הוספת "קידודים" מיקום שמתארים היכן כל תא יושב ברקמה, מבלי לשנות את האופטימיזציה הליבה. על מערכי נתונים גדולים של כבד עכבר וקולון אנושי שנוצרו בפלטפורמות דימות ברזולוציה גבוהה, CiCLoDS רצה במשך דקות במחשבים סטנדרטיים ומייצרת פאנלים קומפקטיים של גנים — בסדר גודל של כמה עשיריות עד כמה מאות גנים — שעדיין לוכדים את המבנה העשיר של הנתונים המקוריים.
גילוי אזורים נסתרים וכלי דם
יישום CiCLoDS על כבד עכבר בדק האם השיטה יכולה לשחזר דפוסי "זורנציה" מוכרים — שינויים הדרגתיים בתפקוד ההפטוציטים מצד אחד של הלובולוס לצד השני. בהשוואה ל-PCA וכלי מוביל לבחירת גנים בשם geneBasis, CiCLoDS יצרה אזורים מרחביים נקיים יותר עם גבולות חדים פחות טעויות בהקצאה, כפי שנמדד במטריקות כמותיות שמודדות הסכמה עם מפה מתייחס. באופן מדהים, כאשר הורשו להשתמש ביותר גנים, CiCLoDS גילתה מחדש קבוצות הפטוציטים בדומה לפרי-פורטלי ופרי-מרכזי שהותאמו בקירוב לאשכולות שהוגדרו על ידי מומחים, אף על פי שלא סופקו לה המיקום המרחבי המפורש או גן הסמן המרכזי AXIN2. כאשר נוספו קידודים מרחביים, CiCLoDS גם למדה פאנלים של גנים שעשירים בתפקודים של פני שטח התא וקשורים לכלי דם, ויכלה להבחין במדויק בין כלי דם אמיתיים לבין ארטיפקטים בדימות — משהו ששיטות פשוטות או נכשלו בו או השיגו רק באמצעות תיקונים אד-הוק רבים יותר.
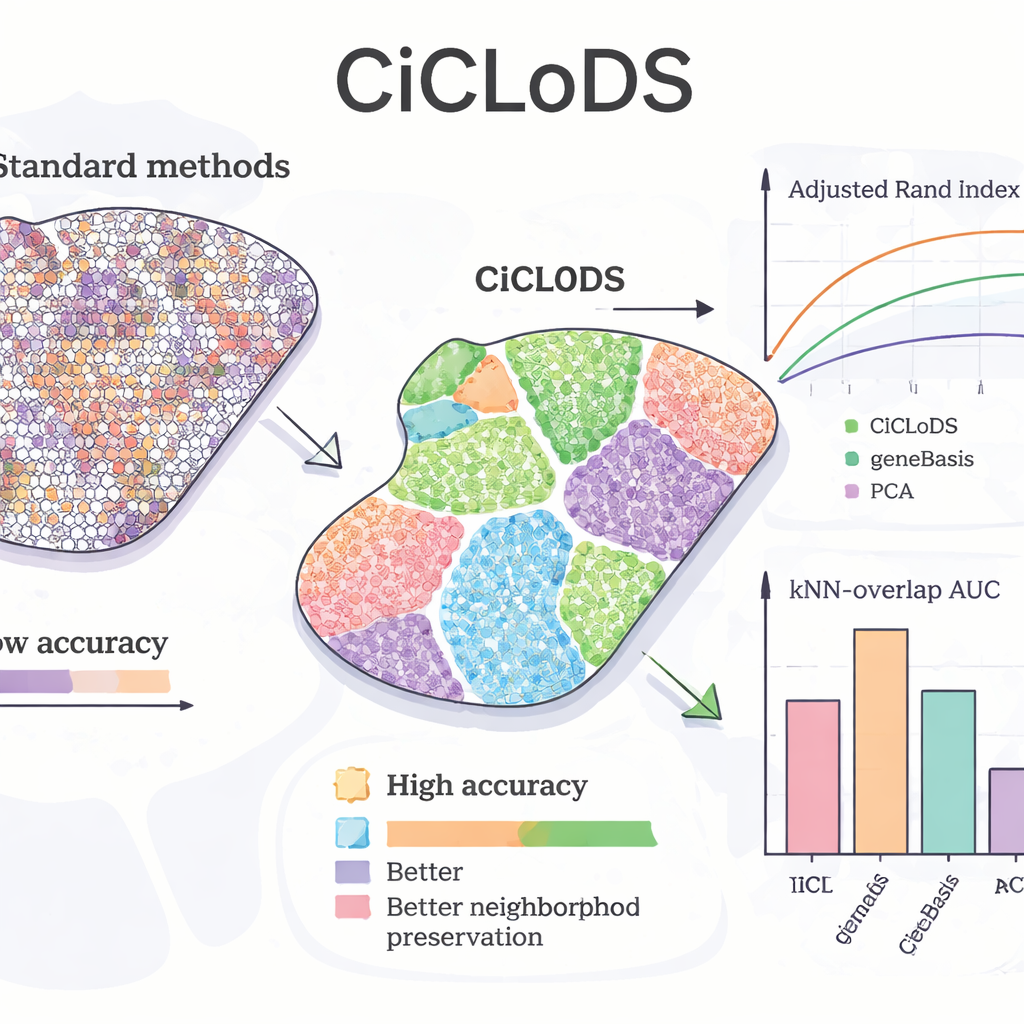
הכללה על מוח והשבחת שיטות אחרות
כדי לבדוק האם CiCLoDS מחזיקה במגוון רקמות ואינדיבידואלים שונים, המחברים ניתחו דגימות של הקורטקס הפרה-פרונטלי הדורסולטרלי האנושי משלושה תורמים. כאן CiCLoDS התפקדה על פי או טוב יותר משיטות מרחביות מיוחדות כגון BayesCafe ו-BayesSpace, במיוחד בדגימה קשה שבה הכלים האחרים התקשו. המחקר גם מדגיש שימוש "היברידי": להריץ תחילה את CiCLoDS לקבלת אשכולות יציבים, ואז להזין אותן ל-BayesSpace. אסטרטגיית ה-warm-start הזו שיפרה את הדיוק הכולל ויצרה דפוסי שכבות מוח שהסכימו בצורה הטובה ביותר עם האנוטציות המומחים, והראתה כי CiCLoDS יכולה לעבוד כשיטה עצמאית ולשפר מודלים הסתברותיים שמריצים לאחר מכן.
מדוע זה חשוב לביולוגיה ולטיפולים רפואיים
ללא-מומחים, המסקנה המרכזית היא ש-CiCLoDS הופכת מפות תאים מוצפות לקיצורים תמציתיים ובעלי משמעות ביולוגית. במקום לעבוד עם אלפי מדידות רועשות, חוקרים מקבלים רשימה ניתנת לניהול של גנים ואשכולות מרחביים ברורים המשקפים ארגון רקמתי אמיתי — אזורי מטבוליזם בכבד, כלי דם והנישות שלהם, ומבנים שכבתיים במוח. משום שתקציב הגנים נשלט על ידי המשתמש והחישובים קלים יחסית, CiCLoDS יכולה לסייע בעיצוב פאנלי גנים ממוקדים לניסויים עתידיים, לכוון את הפרשנות של מערכי נתונים מרחביים מורכבים ולהניח נקודות פתיחה יציבות למודלים מפורטים יותר. בעידן שבו צוואר הבקבוק אינו איסוף הנתונים אלא ההבנה שלהם, כלים כמו CiCLoDS מבטיחים להפוך מפות רקמה רב-ממדיות לפרקטיות ותובנתיות.
ציטוט: Wang, N., He, Y., Ray, E. et al. CiCLoDS: Joint cell clustering and gene selection for single-cell spatial transcriptomics. Sci Rep 16, 5356 (2026). https://doi.org/10.1038/s41598-026-39168-1
מילות מפתח: טרנסקריפטומיקה מרחבית, אשכולת תאים, בחירת פאנל גנים, ארכיטקטורת רקמה, ניתוח בתא יחיד